Clear Sky Science · fr
HRCHY-CytoCommunity identifie l’organisation tissulaire hiérarchique dans les cartes spatiales de types cellulaires
Comment les cellules construisent des voisinages au sein de nos tissus
Nos organes ne sont pas de simples sacs de cellules ; ce sont des cités soigneusement organisées où différents « voisins » cellulaires s’associent pour nous maintenir en vie et, en cas de maladie, parfois contre nous. Les nouveaux outils d’imagerie et de séquençage peuvent désormais enregistrer la position de chaque cellule dans une coupe de tissu, ainsi que son activité. Mais interpréter ce foisonnement d’informations spatiales est difficile. Cette étude présente HRCHY‑CytoCommunity, une méthode computationnelle qui reconstruit automatiquement comment les cellules se groupent en voisinages et en districts plus larges dans les organes sains et les tumeurs, et relie ces motifs aux résultats cliniques des patients.
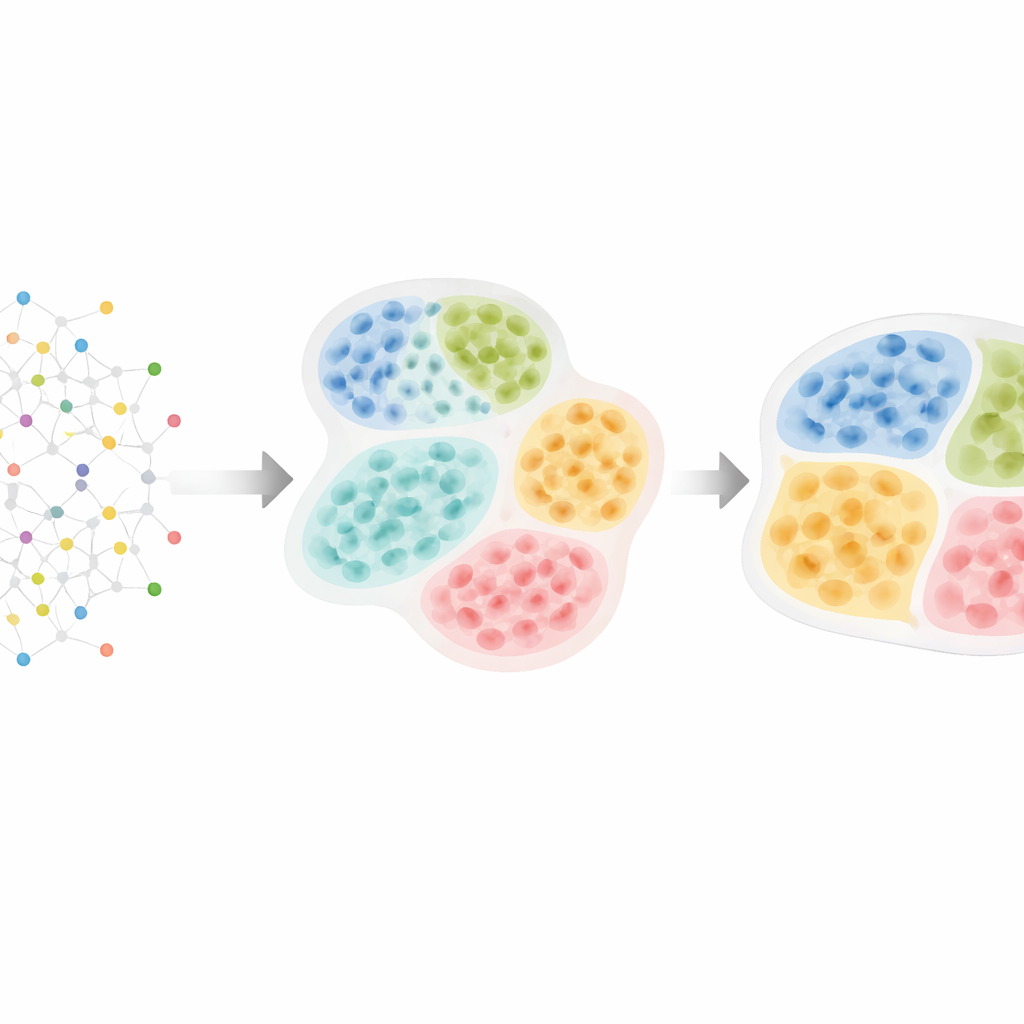
Des cartes cellulaires à la structure tissulaire cachée
Les technologies « omiques » spatiales modernes peuvent mesurer des milliers de molécules dans des dizaines à des centaines de milliers de cellules tout en préservant leur localisation exacte dans le tissu. Les chercheurs savent que les cellules s’organisent en couches, zones et compartiments — par exemple, régions immunitaires versus tumorales dans les tumeurs, ou noyaux distincts dans le cerveau. Ces motifs importent : les tumeurs où les cellules immunitaires sont séparées des cellules cancéreuses se comportent souvent différemment de celles où elles sont mélangées, et des agrégats immunitaires particuliers appelés structures lymphoïdes tertiaires peuvent prédire une meilleure survie dans plusieurs cancers. Cependant, la plupart des outils informatiques existants ignorent cette hiérarchie naturelle ou ne détectent des structures qu’à un seul niveau, ce qui rend difficile de comprendre comment de petits voisinages cellulaires s’insèrent dans des districts tissulaires plus larges.
Une nouvelle manière de lire les voisinages cellulaires
HRCHY‑CytoCommunity relève ce défi en traitant le tissu comme un réseau de cellules. Chaque cellule est un nœud dans un graphe, connecté à ses voisins spatiaux les plus proches. Plutôt que de s’appuyer directement sur les mesures brutes de gènes ou de protéines, la méthode utilise le type de chaque cellule (par exemple cellule cancéreuse, cellule T, fibroblaste) comme entrée principale. Un réseau neuronal sur graphe apprend alors les motifs d’organisation de ces types cellulaires. En une étape il regroupe les cellules voisines en « voisinages cellulaires » fins. En une seconde étape il regroupe ces voisinages en « compartiments tissulaires » plus grossiers, en veillant à ce que chaque cellule appartienne exactement à un voisinage et que chaque voisinage soit contenu proprement dans un unique compartiment. Des astuces d’entraînement — comme l’élagage des connexions faibles, l’ajout de bruit aléatoire et l’encouragement de clusters stables et équilibrés — aident la méthode à éviter des groupements fragiles ou triviaux.
Identifier des structures à travers organes, technologies et maladies
Les auteurs ont testé HRCHY‑CytoCommunity sur un large éventail de jeux de données spatiales de souris et d’humains, couvrant à la fois des cartes protéiques basées sur l’imagerie et des cartes ARN basées sur le séquençage, et englobant la rate, le cerveau, l’intestin et les tumeurs. Dans la rate de souris, la méthode a retrouvé des structures classiques telles que la pulpe rouge et les régions lymphoïdes, même lorsque ces régions étaient fragmentées en plaques déconnectées. Dans les tissus de cancer colorectal, elle a séparé nettement les zones tumorales des zones normales et mis en évidence des voisinages distincts aux bords et au cœur des tumeurs. Dans des régions cérébrales de souris, elle a tracé avec précision des noyaux connus, souvent minuscules, et des couches corticales que de nombreuses autres méthodes fusionnaient, et elle a traité des jeux de données très larges contenant des centaines de milliers de points en seulement quelques minutes. Le cadre fonctionne aussi lorsque chaque point mesuré contient un mélange de types cellulaires : en estimant d’abord quelles cellules sont présentes dans chaque point, il peut toujours reconstruire des couches et sous‑régions anatomiquement significatives.
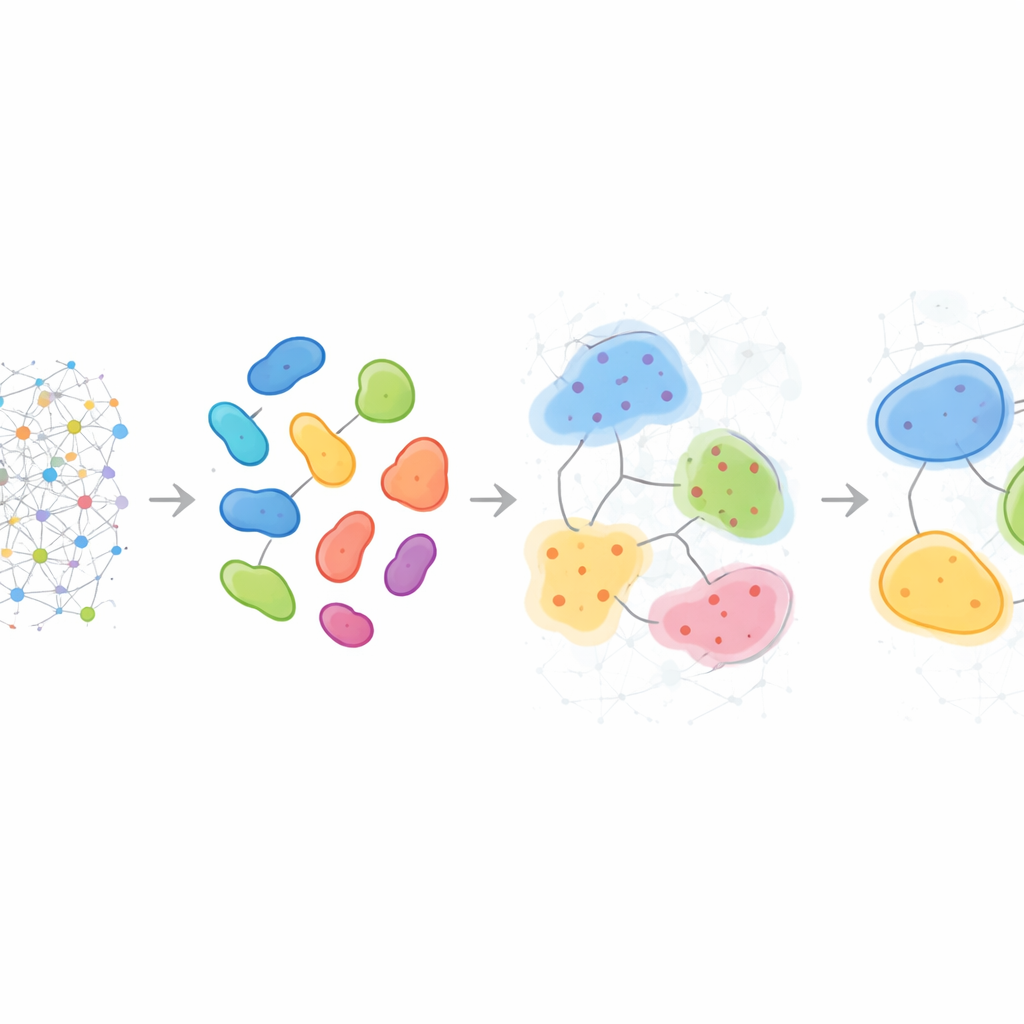
Des motifs qui varient d’un patient à l’autre
Au‑delà de la description d’échantillons isolés, HRCHY‑CytoCommunity peut aligner voisinages et compartiments à travers de nombreux patients pour définir un « vocabulaire » partagé de structures multicellulaires. Dans le cancer du sein triple négatif, la méthode a systématiquement identifié des compartiments riches en cellules immunitaires et d’autres riches en cellules tumorales, mais les voisinages plus fins à l’intérieur de ces compartiments différaient d’un individu à l’autre. Certaines tumeurs contenaient des combinaisons uniques de macrophages, de cellules T et de vaisseaux sanguins, ou des poches mélangeant cellules cancéreuses et neutrophiles, révélant des micro‑écologies individualisées invisibles aux simples comptes de types cellulaires. Appliquées à une large cohorte de cancers du sein, ces structures multi‑échelles ont aidé à stratifier les patients selon la survie : un compartiment enrichi en un phénotype particulier de cellules cancéreuses désignait des patients avec de meilleurs résultats, tandis que certains voisinages riches en fibroblastes ou en mélanges spécifiques de cellules T et de macrophages identifiaient des groupes avec un pronostic significativement plus mauvais, reflétant probablement des barrières physiques ou fonctionnelles à une immunité antitumorale efficace.
Ce que cela signifie pour la compréhension et le traitement des maladies
En transformant des cartes spatiales complexes de types cellulaires en une hiérarchie claire de voisinages et de districts, HRCHY‑CytoCommunity offre un puissant prisme pour comprendre comment les tissus se construisent et comment ils se dégradent en maladie. La capacité de la méthode à fonctionner sur différentes plates‑formes expérimentales, à gérer des jeux de données massifs et à fournir une couverture complète et imbriquée des cellules en fait un outil pratique pour la biologie fondamentale comme pour la recherche clinique. Dans les cancers, elle peut révéler des micro‑architectures liées à la survie des patients et à la réponse aux traitements ; dans les organes sains, elle peut cartographier la coopération entre régions spécialisées. À terme, des approches comme celle‑ci pourraient aider les médecins à lire l’organisation tissulaire aussi couramment qu’ils lisent aujourd’hui des tests de laboratoire, guidant des diagnostics et des traitements plus précis.
Citation: Xie, R., Wang, Z., Liu, J. et al. HRCHY-CytoCommunity identifies hierarchical tissue organization in cell-type spatial maps. Nat Commun 17, 3312 (2026). https://doi.org/10.1038/s41467-026-70069-z
Mots-clés: omiques spatiales, architecture tissulaire, réseaux neuronaux graphiques, microenvironnement tumoral, voisinages cellulaires