Clear Sky Science · pt
Inferência baseada em simulação no limite teórico para MRI microestrutural rápida e robusta com dados de difusão mínimos
Por que exames cerebrais mais rápidos importam
A ressonância magnética (RM) pode revelar detalhes finos do tecido cerebral, mas os exames mais informativos costumam ser lentos e ruidosos. Tempos longos de exame são desconfortáveis para os pacientes, difíceis de agendar em hospitais movimentados e quase impossíveis para crianças ou pessoas gravemente enfermas. Este estudo faz uma pergunta simples com grandes consequências: podemos usar simulações computacionais inteligentes e inteligência artificial para extrair a mesma riqueza de informação de exames de RM de difusão muito mais curtos e imperfeitos, sem sacrificar a confiabilidade?
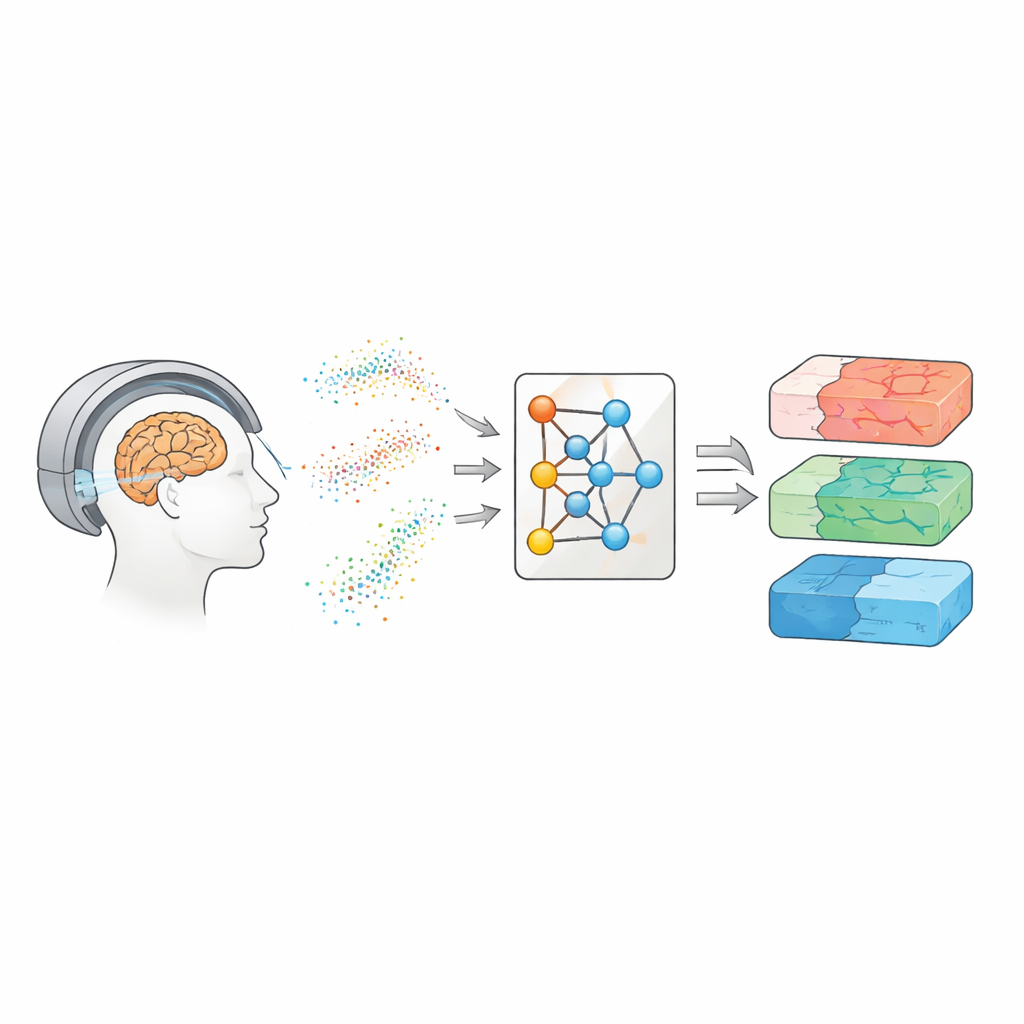
Olhando para dentro do cérebro com água em movimento
A RM de difusão acompanha como moléculas de água se movimentam e se dispersam pelo tecido cerebral. Como a água se move de maneira diferente ao longo de fibras nervosas, através de corpos celulares ou em torno de áreas danificadas, esses padrões podem funcionar como uma impressão digital da microestrutura cerebral. Ao longo dos anos, pesquisadores construíram várias famílias de modelos para traduzir sinais de difusão em mapas das propriedades do tecido. Abordagens mais simples, como a imagem por tensor de difusão, resumem quão facilmente a água se move e quão direcional é esse movimento. Métodos mais avançados, como a imagem de curtose de difusão e modelos biofísicos como CHARMED e AxCaliber, procuram capturar detalhes como a densidade de fibras e até diâmetros típicos de axônios. Esses mapas poderiam servir como “biópsias virtuais”, oferecendo pistas sobre doenças sem cirurgia — mas geralmente exigem muitas medidas repetidas e exames longos.
O gargalo do ajuste tradicional
Transformar medições brutas de difusão em mapas significativos é um problema matemático de ajuste: os parâmetros do modelo são ajustados até que o sinal previsto corresponda ao observado pelo aparelho. As ferramentas mais comuns hoje, como mínimos quadrados não lineares, fazem isso minimizando a diferença ao quadrado entre modelo e dados. Embora simples e amplamente disponíveis, esses métodos funcionam melhor quando há muito mais medições do que o estritamente necessário — o equivalente, em tempo de exame, a tirar dez vezes mais fotos só para garantir. Eles também têm dificuldade quando o ruído é alto ou quando as estimativas iniciais são ruins, situação comum em dados clínicos reais. Abordagens estatísticas mais novas podem ajudar, mas costumam ser lentas, sensíveis a suposições sobre o ruído e raramente usadas fora de centros de pesquisa.
Aprender com simulações em vez de pacientes
Os autores seguem um caminho diferente: em vez de aprender diretamente com exames de pacientes, eles treinam uma rede neural usando apenas dados simulados. Eles amostram muitas combinações possíveis de parâmetros do modelo, usam a física conhecida da difusão para gerar sinais sintéticos, adicionam ruído realista e então treinam um chamado estimador posterior neural. Essa rede aprende a produzir uma distribuição de probabilidade completa sobre os parâmetros que poderiam ter gerado um determinado sinal, fornecendo naturalmente tanto um palpite principal quanto uma estimativa de incerteza. Para tornar o método flexível a diferentes configurações de aparelho, a equipe não alimenta medidas brutas. Em vez disso, comprimem cada sinal em recursos compactos informados pela física que resumem como ele varia com a intensidade do gradiente, direção e tempo de difusão. Esses recursos capturam a essência do sinal mantendo-se amplamente independentes do esquema de aquisição exato.
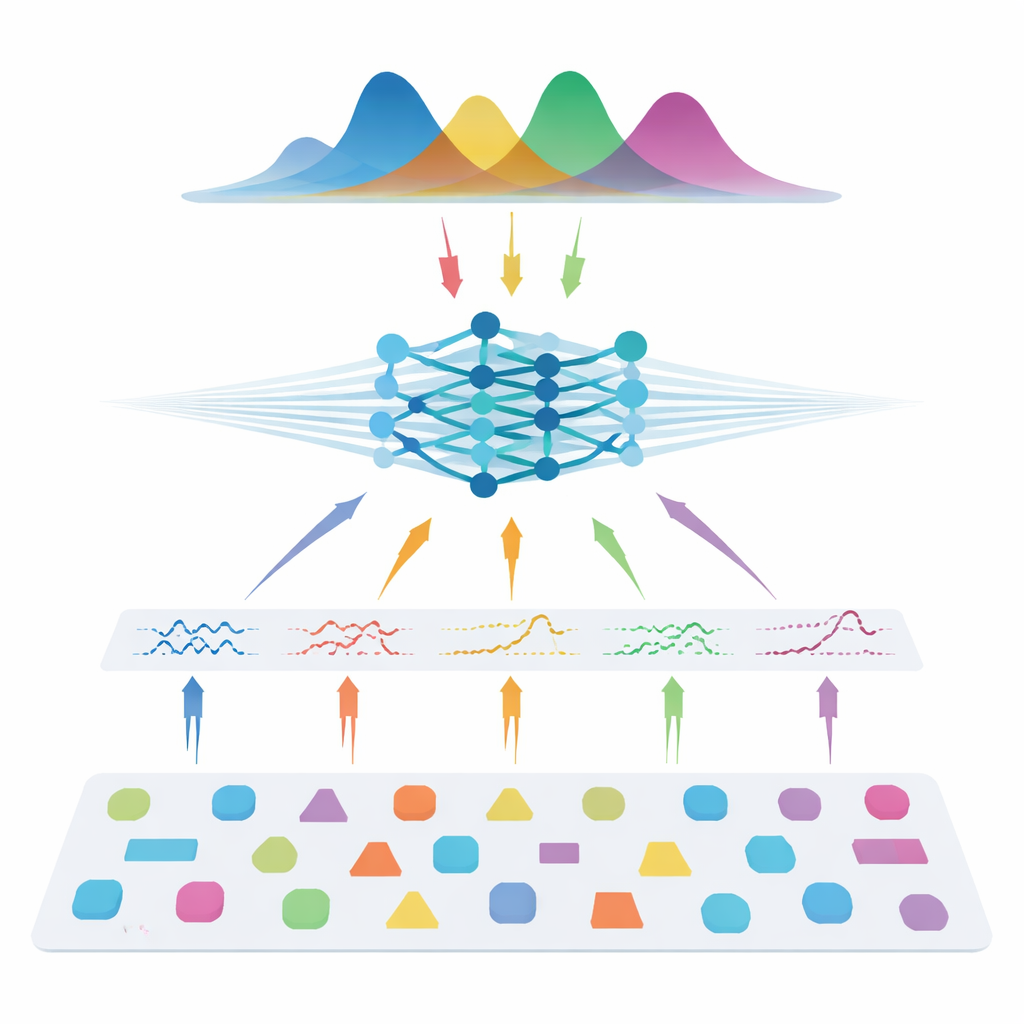
Igualando o melhor com uma fração dos dados
Uma vez treinado, o sistema é testado tanto em dados sintéticos com “verdade de base” conhecida quanto em vários conjuntos de dados humanos, incluindo voluntários saudáveis e pessoas com esclerose múltipla. Em todas as três famílias de modelos — imagem por tensor de difusão, imagem de curtose de difusão e AxCaliber — a abordagem baseada em simulação recupera métricas microestruturais-chave com precisão mesmo usando apenas 7–22 medições em vez de protocolos completos com 69–271 medições. Isso pode significar até 90% menos exames. Em condições ruidosas ou quando o número de medições é severamente reduzido, o novo método supera consistentemente o ajuste padrão, produzindo mapas mais limpos que preservam estruturas importantes. Também detecta mudanças esperadas dentro de lesões de esclerose múltipla e recupera padrões conhecidos de tamanhos de axônios através do corpo caloso, sugerindo que generaliza bem para tecido saudável e doente.
O que isso significa para pacientes e clínicas
Para não especialistas, a conclusão é que os autores mostram como obter quase a mesma visão microscópica do tecido cerebral a partir de exames de RM de difusão muito mais curtos e potencialmente de qualidade inferior, apoiando-se fortemente em simulações e inferência avançada. Em vez de pedir ao aparelho por mais dados, eles pedem aos computadores que façam melhor uso de menos dados. Isso pode reduzir o tempo dos exames, ampliar o acesso a imagens avançadas em hospitais de rotina e até resgatar estudos mais antigos adquiridos com configurações subótimas. Como o método é treinado inteiramente em sinais simulados, também é favorável à privacidade e mais fácil de compartilhar e escalar. Se amplamente adotada, essa forma de inferência baseada em simulação pode ajudar a reduzir a distância entre protocolos de pesquisa de ponta e a RM clínica do dia a dia, aproximando as biópsias virtuais do atendimento padrão.
Citação: Eggl, M.F., De Santis, S. Simulation-based inference at the theoretical limit for fast, robust microstructural MRI with minimal diffusion data. Commun Med 6, 275 (2026). https://doi.org/10.1038/s43856-026-01614-6
Palavras-chave: RM de difusão, microestrutura cerebral, inferência baseada em simulação, redes neurais, redução do tempo de exame