Clear Sky Science · es
Inferencia basada en simulaciones en el límite teórico para una RM microestructural rápida y robusta con datos de difusión mínimos
Por qué importan las exploraciones cerebrales más rápidas
La resonancia magnética (RM) puede revelar detalles finos del tejido cerebral, pero las exploraciones más informativas suelen ser lentas y ruidosas. Los tiempos de exploración prolongados resultan incómodos para los pacientes, difíciles de coordinar en hospitales concurridos y casi imposibles para niños o personas muy enfermas. Este estudio plantea una pregunta sencilla con grandes consecuencias: ¿podemos usar simulaciones informáticas inteligentes e inteligencia artificial para extraer la misma información rica de exploraciones de RM de difusión mucho más cortas y menos perfectas, sin sacrificar la fiabilidad?
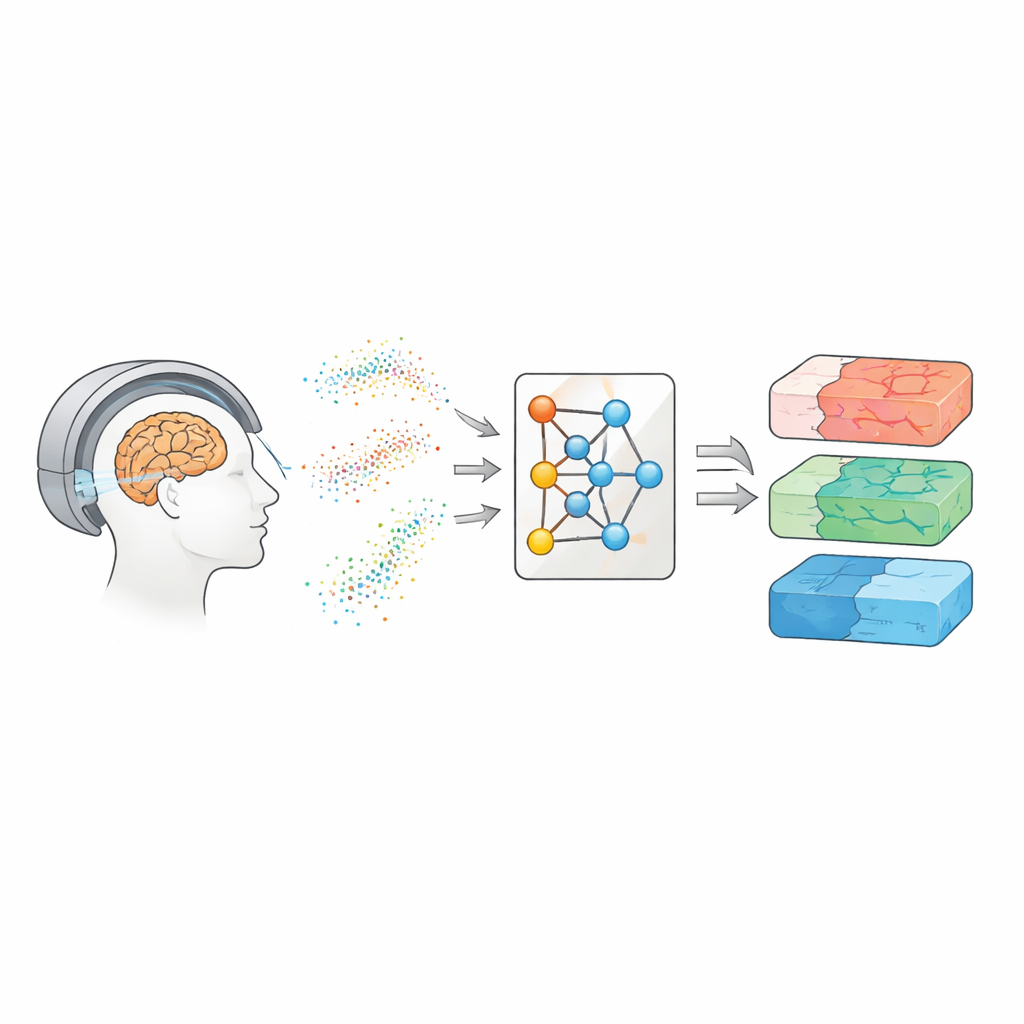
Mirar dentro del cerebro con agua en movimiento
La RM de difusión rastrea cómo las moléculas de agua se desplazan y difunden a través del tejido cerebral. Dado que el agua se mueve de forma distinta a lo largo de las fibras nerviosas, a través de los cuerpos celulares o alrededor de zonas dañadas, estos patrones pueden comportarse como la huella dactilar de la microestructura cerebral. A lo largo de los años, los científicos han desarrollado varias familias de modelos para traducir las señales de difusión en mapas de propiedades tisulares. Enfoques más simples, como la imagen de tensores de difusión, resumen cuán fácilmente se mueve el agua y cuán direccional es ese movimiento. Métodos más avanzados, como la imagen de curtosis de difusión y modelos biofísicos como CHARMED y AxCaliber, intentan capturar detalles como la densidad de fibras e incluso los diámetros típicos de los axones. Estos mapas podrían servir como “biopsias virtuales”, ofreciendo pistas sobre enfermedades sin cirugía, pero por lo general exigen muchas mediciones repetidas y exploraciones largas.
El cuello de botella del ajuste tradicional
Convertir las mediciones crudas de difusión en mapas significativos es un problema de ajuste matemático: los parámetros del modelo se modifican hasta que la señal predicha coincide con lo que registró el escáner. Las herramientas más comunes hoy en día, como los mínimos cuadrados no lineales, lo hacen minimizando la diferencia al cuadrado entre el modelo y los datos. Aunque son sencillas y ampliamente disponibles, estos métodos funcionan mejor cuando hay muchas más mediciones de las estrictamente necesarias—el equivalente en tiempo de exploración a tomar diez veces más fotos por si acaso. También tienen dificultades cuando el ruido es alto o cuando las conjeturas iniciales son pobres, algo común en datos clínicos reales. Enfoques estadísticos más nuevos pueden ayudar, pero a menudo son lentos, sensibles a supuestos sobre el ruido y rara vez se usan fuera de centros de investigación.
Aprender de simulaciones en lugar de pacientes
Los autores adoptan una ruta distinta: en vez de aprender directamente de exploraciones de pacientes, entrenan una red neuronal usando únicamente datos simulados. Muestran muchas combinaciones posibles de parámetros del modelo, usan la física conocida de la difusión para generar señales sintéticas, añaden ruido realista y luego entrenan un llamado estimador de posterior neural. Esta red aprende a devolver una distribución de probabilidad completa sobre los parámetros que podrían haber generado una señal dada, proporcionando de forma natural tanto la mejor estimación como una medida de incertidumbre. Para que el método sea flexible ante diferentes configuraciones de escáner, el equipo no alimenta mediciones crudas. En su lugar, comprime cada señal en características compactas e informadas por la física que resumen cómo varía con la intensidad del gradiente, la dirección y el tiempo de difusión. Estas características capturan la esencia de la señal y, al mismo tiempo, son en gran medida independientes del esquema de adquisición exacto.
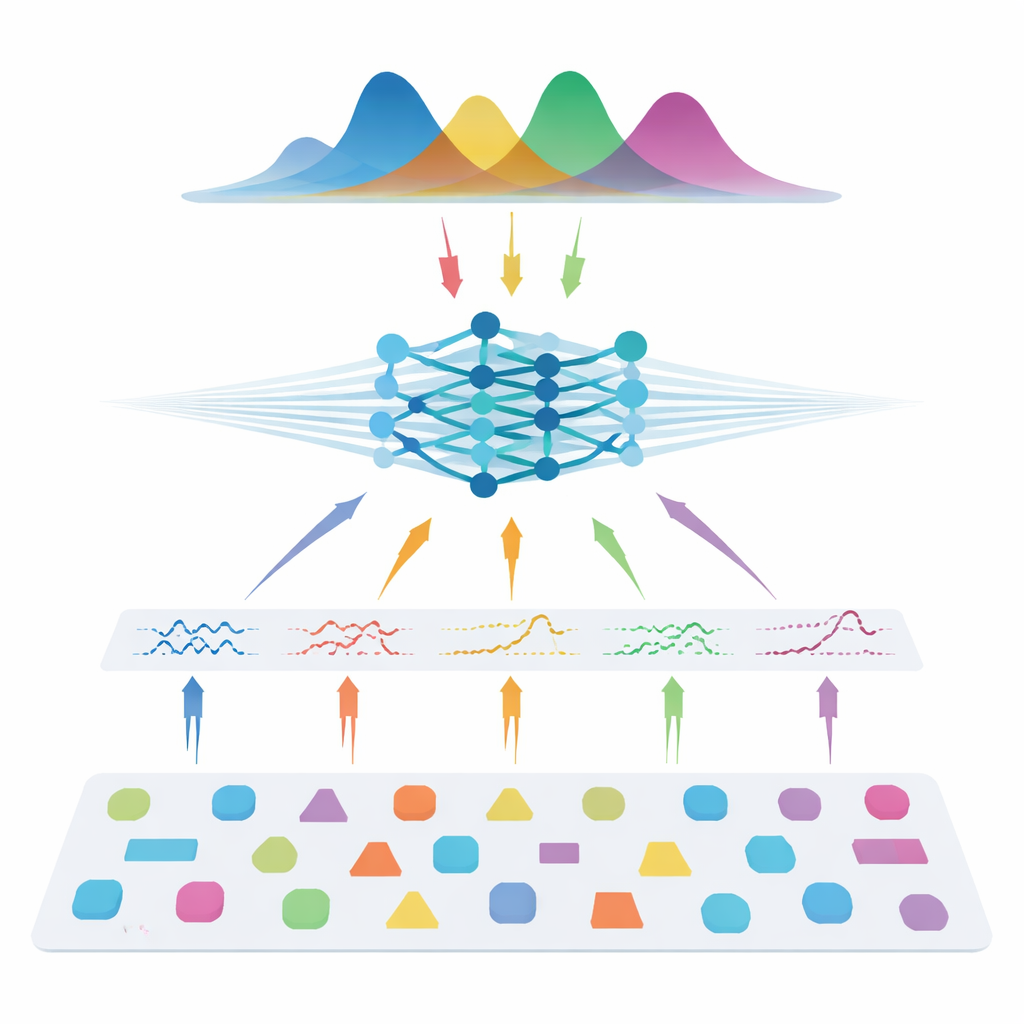
Igualando a los mejores con una fracción de los datos
Una vez entrenado, el sistema se prueba tanto en datos sintéticos con “verdad” conocida como en varios conjuntos de datos humanos, incluidos voluntarios sanos y personas con esclerosis múltiple. En las tres familias de modelos—imagen de tensores de difusión, imagen de curtosis de difusión y AxCaliber—el enfoque basado en simulaciones recupera métricas microestructurales clave con precisión, incluso cuando usa tan solo 7–22 mediciones en lugar de protocolos completos con 69–271 mediciones. Eso puede significar hasta un 90% menos de exploraciones. En condiciones ruidosas o cuando el número de mediciones se reduce severamente, el nuevo método supera de forma consistente al ajuste estándar, produciendo mapas más limpios que preservan estructuras importantes. También detecta cambios esperados dentro de lesiones por esclerosis múltiple y recupera patrones conocidos de tamaños axonales a lo largo del cuerpo calloso, lo que sugiere que se generaliza bien tanto a tejido sano como enfermo.
Qué significa esto para pacientes y clínicas
Para no especialistas, la conclusión es que los autores muestran cómo obtener casi la misma visión microscópica del tejido cerebral a partir de exploraciones de RM de difusión mucho más cortas y potencialmente de menor calidad, apoyándose intensamente en simulaciones e inferencia avanzada. En lugar de pedirle al escáner más datos, piden a los ordenadores que hagan mejor uso de menos datos. Esto podría acortar los tiempos de examen, ampliar el acceso a técnicas avanzadas en hospitales de rutina e incluso recuperar estudios antiguos adquiridos con configuraciones subóptimas. Dado que el método se entrena completamente con señales simuladas, también es respetuoso con la privacidad y más fácil de compartir y escalar. Si se adopta de forma generalizada, este estilo de inferencia basada en simulaciones podría ayudar a cerrar la brecha entre protocolos de investigación de vanguardia y la RM clínica cotidiana, acercando las biopsias tisulares virtuales a la atención estándar.
Cita: Eggl, M.F., De Santis, S. Simulation-based inference at the theoretical limit for fast, robust microstructural MRI with minimal diffusion data. Commun Med 6, 275 (2026). https://doi.org/10.1038/s43856-026-01614-6
Palabras clave: RM de difusión, microestructura cerebral, inferencia basada en simulaciones, redes neuronales, reducción del tiempo de exploración