Clear Sky Science · nl
Simulatiegebaseerde inferentie aan de theoretische limiet voor snelle, robuuste microstructurele MRI met minimale diffusiegegevens
Waarom snellere hersenscans belangrijk zijn
Magnetische resonantiebeeldvorming (MRI) kan fijne details van hersenweefsel onthullen, maar de meest informatieve scans zijn vaak traag en ruisig. Lange scantijden zijn ongemakkelijk voor patiënten, lastig in te plannen in drukke ziekenhuizen en vrijwel onmogelijk voor kinderen of ernstig zieken. Deze studie stelt een eenvoudige vraag met grote gevolgen: kunnen we met slimme computersimulaties en kunstmatige intelligentie dezelfde rijke informatie uit veel kortere, rommeligere diffusie-MRI-scans persen, zonder betrouwbaarheid in te leveren?
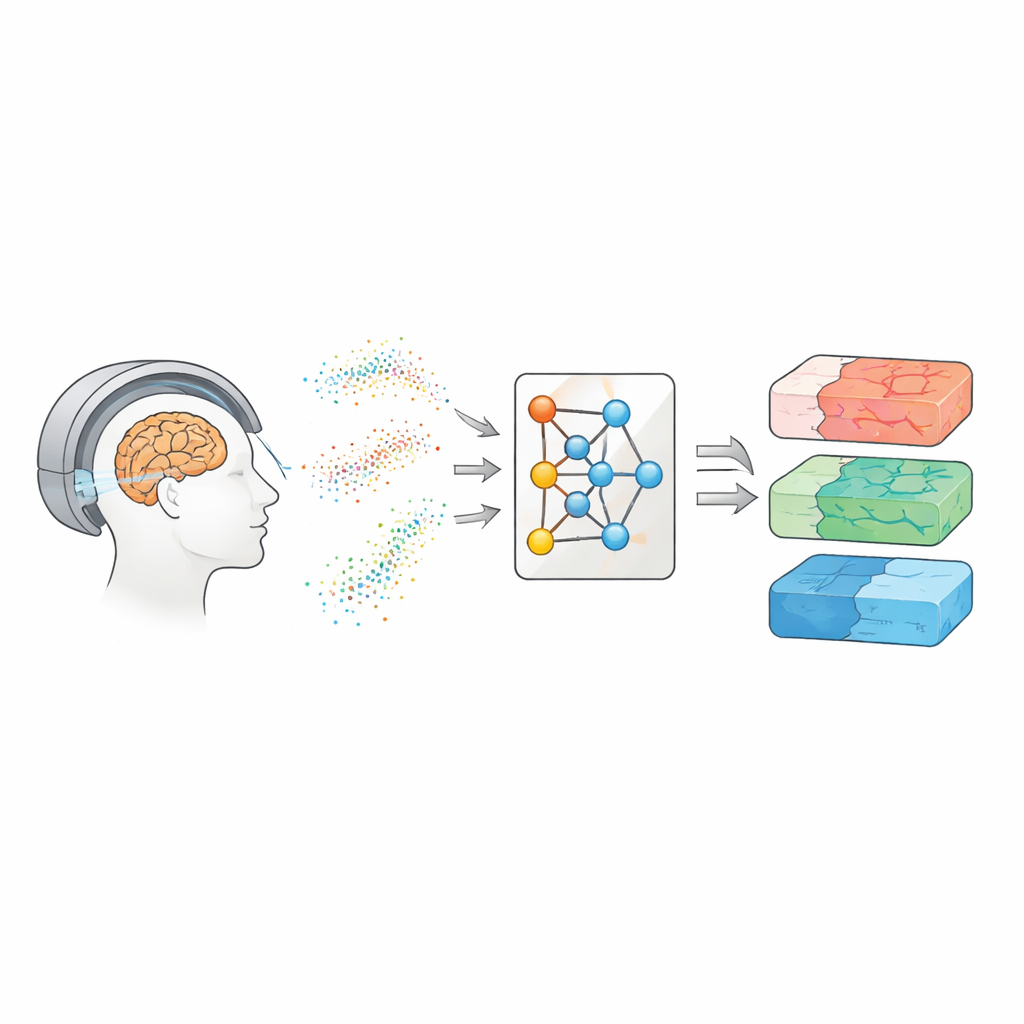
In de hersenen kijken met bewegend water
Diffusie-MRI volgt hoe watermoleculen schudden en dwalen door hersenweefsel. Omdat water zich anders gedraagt langs zenuwvezels, door cellichamen of rond beschadigde gebieden, kunnen deze patronen fungeren als een vingerafdruk van de microscopische structuur van de hersenen. In de loop der jaren hebben onderzoekers verschillende modelgroepen ontwikkeld om diffusiesignalen te vertalen naar kaarten van weefselkenmerken. Simpelere benaderingen, zoals diffusietensorbeeldvorming, vatten samen hoe gemakkelijk water beweegt en hoe richtinggebonden die beweging is. Geavanceerdere methoden, zoals diffusiekurtosisbeeldvorming en biofysische modellen zoals CHARMED en AxCaliber, proberen details vast te leggen zoals de dichtheid van vezels en zelfs typische axondiameters. Deze kaarten zouden kunnen dienen als “virtuele biopsieën” die aanwijzingen over ziekte geven zonder operatie — maar ze vergen meestal veel herhaalde metingen en lange scans.
De knelpunt van traditionele fitting
Het omzetten van ruwe diffusiegegevens in betekenisvolle kaarten is een wiskundig fitted-probleem: de parameters van het model worden aangepast totdat het voorspelde signaal overeenkomt met wat de scanner registreerde. De meest gebruikte instrumenten vandaag, zoals niet-lineaire kleinste kwadraten, doen dit door het kwadraat van het verschil tussen model en data te minimaliseren. Hoewel eenvoudig en breed beschikbaar, werken deze methoden het beste wanneer er veel meer metingen zijn dan strikt noodzakelijk — het scantijd-equivalent van tien keer zoveel foto’s nemen om zeker te zijn. Ze hebben ook moeite wanneer de ruis hoog is of wanneer begingissingen slecht zijn, wat vaak voorkomt in klinische data. Nieuwere statistische benaderingen kunnen helpen, maar zijn vaak traag, gevoelig voor aannames over ruis en worden zelden buiten onderzoekscentra toegepast.
Leren van simulaties in plaats van patiënten
De auteurs kiezen een andere route: in plaats van direct van patiëntscans te leren, trainen ze een neuraal netwerk uitsluitend met gesimuleerde data. Ze trekken vele mogelijke combinaties van modelparameters, gebruiken de bekende fysica van diffusie om synthetische signalen te genereren, voegen realistische ruis toe en trainen vervolgens een zogenoemde neurale posterior-estimator. Dit netwerk leert een volledige kansverdeling over de parameters te geven die een bepaald signaal mogelijk gemaakt zouden hebben, en levert daarmee zowel een beste schatting als een onzekerheidsinschatting. Om de methode flexibel te houden voor verschillende scannersettings, voeren ze geen ruwe metingen in. In plaats daarvan comprimeren ze elk signaal tot compacte, fysica-geïnformeerde kenmerken die samenvatten hoe het varieert met gradientsterkte, richting en diffusietijd. Deze kenmerken vangen de essentie van het signaal terwijl ze grotendeels onafhankelijk blijven van het exacte acquisitieschema.
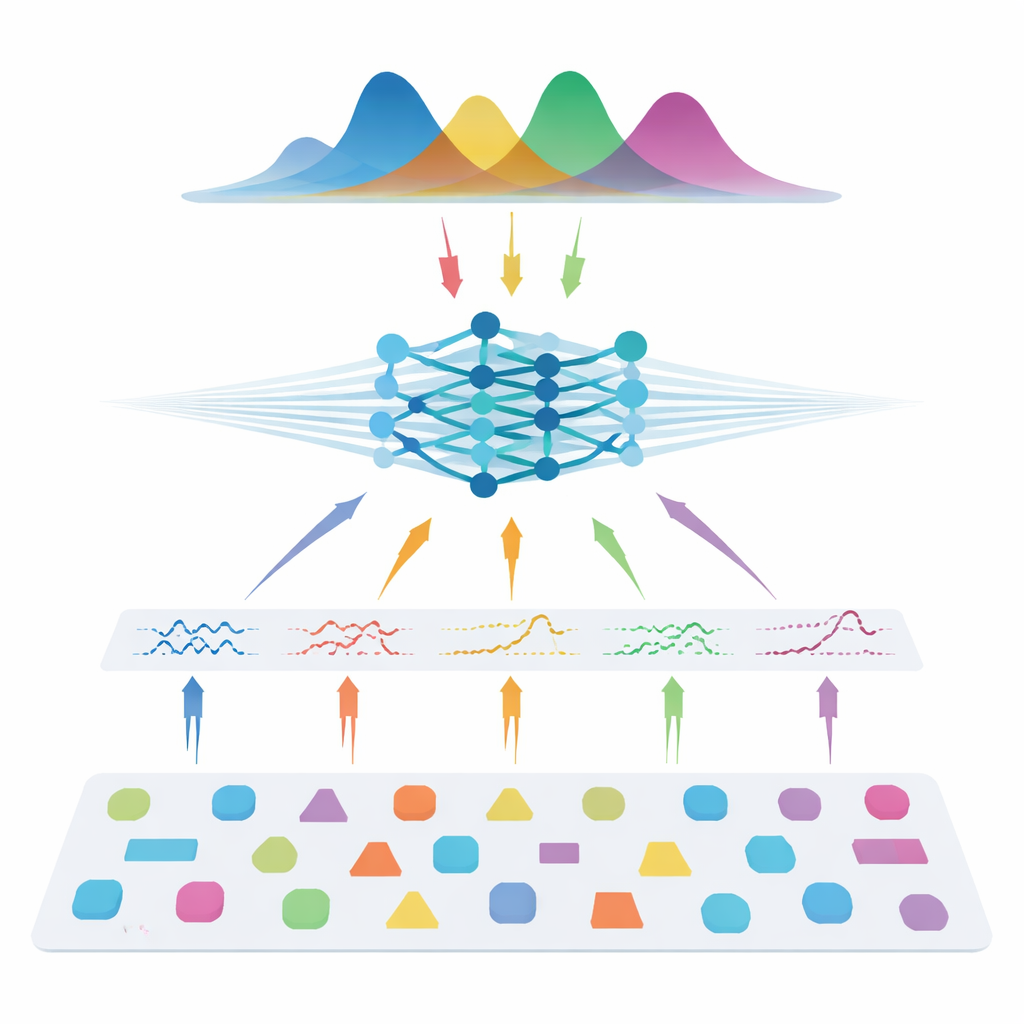
Het beste halen met een fractie van de data
Eens getraind, wordt het systeem getest op zowel synthetische data met bekende “grondwaarheid” als op meerdere menselijke datasets, waaronder gezonde vrijwilligers en mensen met multiple sclerose. Over alle drie modelgroepen — diffusietensorbeeldvorming, diffusiekurtosisbeeldvorming en AxCaliber — herstelt de simulatiegebaseerde benadering belangrijke microstructurele maten nauwkeurig, zelfs wanneer ze slechts 7–22 metingen gebruiken in plaats van volledige protocollen met 69–271 metingen. Dat kan tot 90% minder scans betekenen. Onder ruizige omstandigheden of wanneer het aantal metingen sterk is verminderd, presteert de nieuwe methode consequent beter dan standaard fitting en produceert schonere kaarten die belangrijke structuren behouden. Ze detecteert ook verwachte veranderingen binnen multiple-sclerose-laesies en herstelt bekende patronen van axongroottes in het corpus callosum, wat suggereert dat de methode goed generaliseert naar zowel gezond als ziek weefsel.
Wat dit betekent voor patiënten en klinieken
Voor niet-specialisten is de kernboodschap dat de auteurs aantonen hoe je bijna hetzelfde microscopische beeld van hersenweefsel kunt krijgen uit veel kortere en potentieel lagere kwaliteit diffusie-MRI-scans door sterk te leunen op simulaties en geavanceerde inferentie. In plaats van de scanner om meer data te vragen, vragen ze computers om beter gebruik te maken van minder data. Dit kan onderzoekstijden verkorten, de toegang tot geavanceerde beeldvorming in reguliere ziekenhuizen vergroten en zelfs oudere studies redden die met suboptimale instellingen zijn verworven. Omdat de methode volledig op gesimuleerde signalen is getraind, is ze ook privacyvriendelijker en makkelijker te delen en op te schalen. Bij brede adoptie zou deze vorm van simulatiegebaseerde inferentie kunnen helpen de kloof te dichten tussen state-of-the-art onderzoeksprotocollen en alledaagse klinische MRI, waardoor virtuele weefselbiopsieën dichter bij standaardzorg komen.
Bronvermelding: Eggl, M.F., De Santis, S. Simulation-based inference at the theoretical limit for fast, robust microstructural MRI with minimal diffusion data. Commun Med 6, 275 (2026). https://doi.org/10.1038/s43856-026-01614-6
Trefwoorden: diffusie-MRI, hersenmicrostructuur, simulatiegebaseerde inferentie, neurale netwerken, verkorting scantijd