Clear Sky Science · de
Simulationsbasierte Inferenz am theoretischen Limit für schnelle, robuste mikrostrukturelle MRT mit minimalen Diffusionsdaten
Warum schnellere Hirnscans wichtig sind
Die Magnetresonanztomographie (MRT) kann feine Details des Hirngewebes offenlegen, doch die informativsten Aufnahmen sind oft langsam und verrauscht. Lange Untersuchungszeiten sind für Patientinnen und Patienten unangenehm, schwer in überfüllten Kliniken einzuplanen und für Kinder oder schwer kranke Menschen oftmals kaum durchführbar. Diese Studie stellt eine einfache Frage mit großen Konsequenzen: Lassen sich mithilfe intelligenter Computersimulationen und künstlicher Intelligenz die gleichen reichhaltigen Informationen aus deutlich kürzeren, unordentlicheren Diffusions‑MRT‑Scans gewinnen, ohne die Zuverlässigkeit zu opfern?
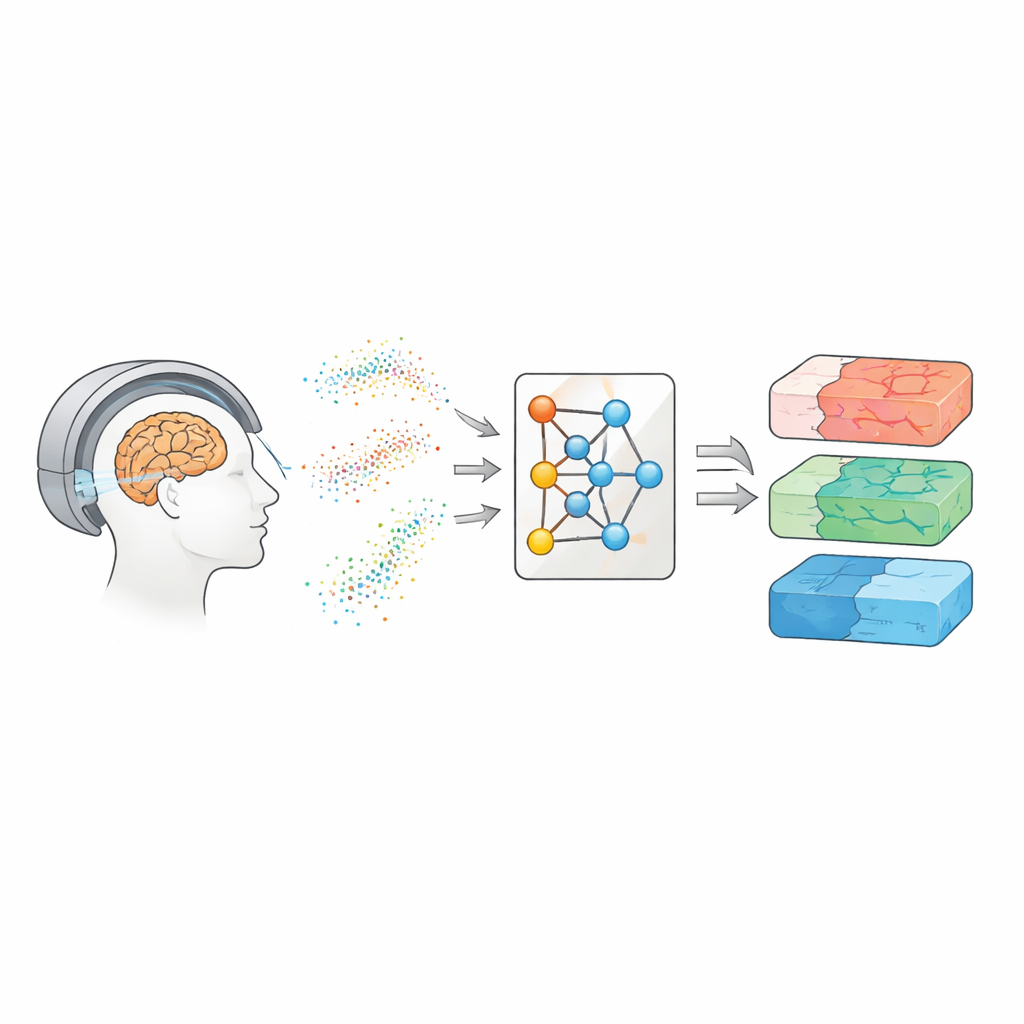
Mit bewegtem Wasser ins Gehirn blicken
Die Diffusions‑MRT verfolgt, wie sich Wassermoleküle im Hirngewebe stochastisch bewegen und umherschweifen. Weil Wasser entlang von Nervenfasern, durch Zellkörper oder um geschädigte Regionen herum unterschiedlich diffundiert, können diese Muster wie ein Fingerabdruck der mikroskopischen Geometrie wirken. Im Lauf der Jahre haben Forschende verschiedene Modellfamilien entwickelt, um Diffusionssignale in Karten von Gewebeigenschaften zu übersetzen. Einfachere Ansätze wie die Diffusionstensorbildgebung fassen zusammen, wie leicht Wasser bewegt werden kann und wie gerichtet diese Bewegung ist. Fortgeschrittenere Methoden, etwa die Diffusionskurtosisbildgebung und biophysikalische Modelle wie CHARMED und AxCaliber, zielen darauf ab, Details wie die Faserdichte oder typische Axondurchmesser zu erfassen. Solche Karten könnten als „virtuelle Biopsien“ dienen und Hinweise auf Erkrankungen ohne Operation liefern – sie erfordern jedoch meist viele Wiederholungsmessungen und lange Messzeiten.
Das Nadelöhr traditioneller Anpassungsverfahren
Rohmessungen der Diffusion in aussagekräftige Karten zu überführen ist ein mathematisches Anpassungsproblem: Die Modellparameter werden so verändert, dass das vorhergesagte Signal dem vom Scanner gemessenen entspricht. Die heute gängigen Werkzeuge, etwa nichtlineare Kleinste-Quadrate‑Methoden, minimieren die quadrierte Differenz zwischen Modell und Daten. Diese Verfahren sind zwar einfach und weit verbreitet, funktionieren aber am besten, wenn es deutlich mehr Messungen gibt als unbedingt nötig – das messzeitliche Äquivalent dazu, aus Sicherheitsgründen zehnmal so viele Fotos zu machen. Sie geraten außerdem ins Straucheln, wenn das Rauschen hoch ist oder Anfangsschätzungen schlecht sind, wie es in klinischen Daten häufig der Fall ist. Neuere statistische Ansätze können helfen, sind aber oft langsam, empfindlich gegenüber Annahmen über das Rauschen und außerhalb von Forschungseinrichtungen selten im Einsatz.
Vom Lernen an Simulationen statt an Patienten
Die Autoren gehen einen anderen Weg: Statt direkt aus Patientenmessungen zu lernen, trainieren sie ein neuronales Netz ausschließlich mit simulierten Daten. Sie ziehen viele mögliche Kombinationen von Modellparametern, verwenden die bekannte Physik der Diffusion, um synthetische Signale zu erzeugen, fügen realistisches Rauschen hinzu und trainieren dann einen sogenannten neuronalen Posterior‑Schätzer. Dieses Netzwerk lernt, eine vollständige Wahrscheinlichkeitsverteilung über die Parameter auszugeben, die ein gegebenes Signal erzeugt haben könnten, und liefert damit sowohl eine beste Schätzung als auch eine Unsicherheitsabschätzung. Um die Methode über verschiedene Scanner‑Einstellungen hinweg flexibel zu machen, speisen die Forschenden nicht die rohen Messungen ein. Stattdessen komprimieren sie jedes Signal in kompakte, physik‑informierte Merkmale, die zusammenfassen, wie sich das Signal mit Gradientstärke, Richtung und Diffusionszeit verändert. Diese Merkmale fangen das Wesentliche des Signals ein und sind weitgehend unabhängig vom genauen Akquisitionsschema.
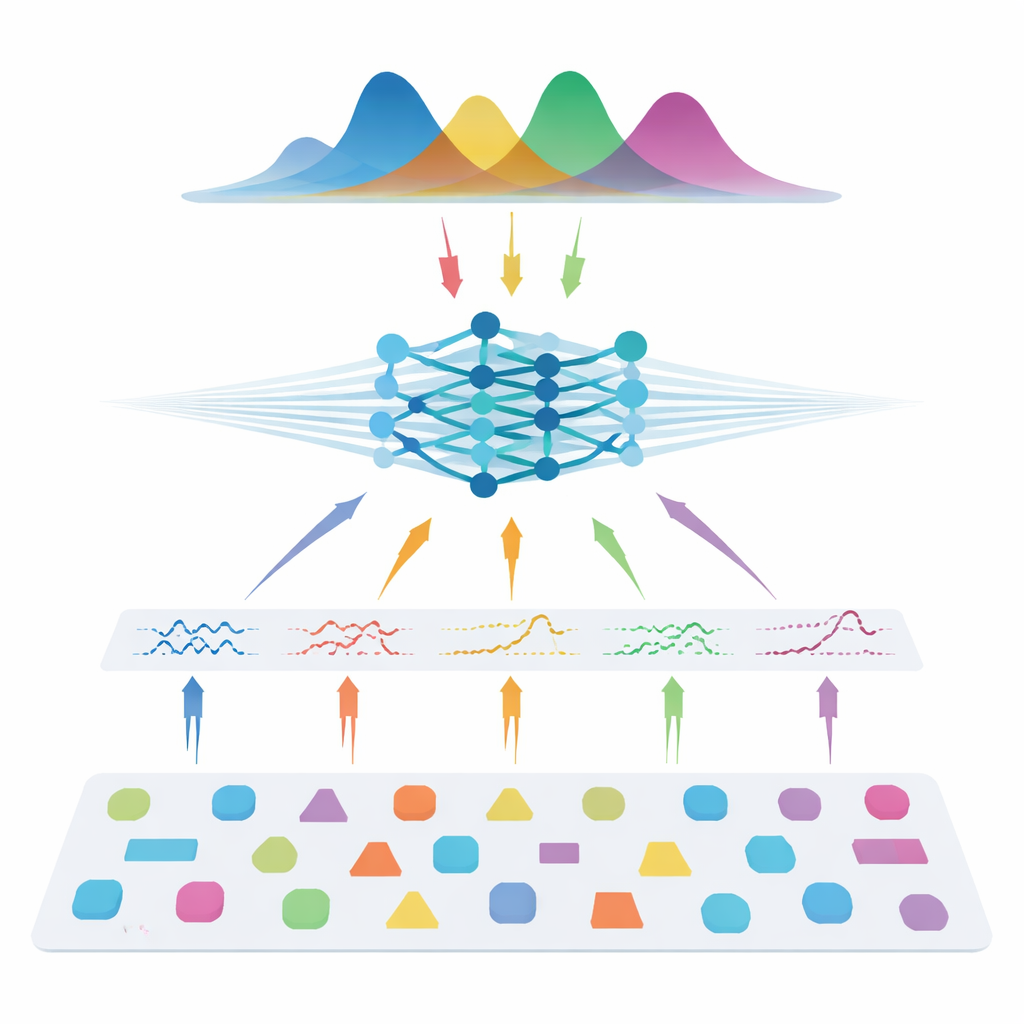
Mit einem Bruchteil der Daten die Besten erreichen
Nach dem Training wird das System sowohl an synthetischen Daten mit bekannter „Ground Truth“ als auch an mehreren menschlichen Datensätzen getestet, darunter gesunde Versuchspersonen und Menschen mit Multipler Sklerose. Über alle drei Modellfamilien hinweg – Diffusionstensorbildgebung, Diffusionskurtosisbildgebung und AxCaliber – rekonstruiert der simulationsbasierte Ansatz wichtige mikrostrukturelle Metriken genau, selbst wenn nur 7–22 Messungen anstelle vollständiger Protokolle mit 69–271 Messungen verwendet werden. Das kann bis zu 90 % weniger Messzeit bedeuten. Unter verrauschten Bedingungen oder bei starker Reduktion der Messanzahl übertrifft die neue Methode konstant die Standardanpassung und produziert sauberere Karten, die wichtige Strukturen erhalten. Sie detektiert außerdem erwartete Veränderungen in Multipler‑Sklerose‑Läsionen und rekonstruiert bekannte Muster der Axondurchmesser im Corpus callosum, was darauf hindeutet, dass sie sowohl auf gesundes als auch auf erkranktes Gewebe gut generalisiert.
Was das für Patienten und Kliniken bedeutet
Für Nichtfachleute lautet die Botschaft: Die Autoren zeigen, wie sich ein nahezu gleiches mikroskopisches Bild des Hirngewebes aus deutlich kürzeren und potenziell qualitativ schlechteren Diffusions‑MRT‑Scans gewinnen lässt, indem sie stark auf Simulationen und fortgeschrittene Inferenzmethoden setzen. Statt vom Scanner mehr Daten zu verlangen, fordern sie von Computern, mit weniger Daten besser zu arbeiten. Das könnte Untersuchungszeiten verkürzen, den Zugang zu fortgeschrittener Bildgebung in Regelkliniken erweitern und sogar ältere Studien retten, die mit suboptimalen Einstellungen akquiriert wurden. Da die Methode vollständig mit simulierten Signalen trainiert wird, ist sie zudem datenschutzfreundlich und leichter zu teilen und zu skalieren. Bei breiter Anwendung könnte diese Form der simulationsbasierten Inferenz dazu beitragen, die Lücke zwischen Spitzenforschungsprotokollen und der alltäglichen klinischen MRT zu schließen und virtuelle Gewebebiopsien näher an die Standardversorgung zu bringen.
Zitation: Eggl, M.F., De Santis, S. Simulation-based inference at the theoretical limit for fast, robust microstructural MRI with minimal diffusion data. Commun Med 6, 275 (2026). https://doi.org/10.1038/s43856-026-01614-6
Schlüsselwörter: Diffusions‑MRT, Hirnmikrostruktur, simulationsbasierte Inferenz, neuronale Netze, Reduktion der Untersuchungszeit