Clear Sky Science · fr
Inférence basée sur la simulation à la limite théorique pour une IRM microstructurale rapide et robuste avec des données de diffusion minimales
Pourquoi des examens cérébraux plus rapides comptent
L’imagerie par résonance magnétique (IRM) peut révéler des détails fins du tissu cérébral, mais les examens les plus informatifs sont souvent longs et bruités. Des temps d’acquisition prolongés sont inconfortables pour les patients, difficiles à planifier dans des hôpitaux chargés et presque impossibles pour les enfants ou les personnes très malades. Cette étude pose une question simple aux conséquences importantes : peut-on utiliser des simulations informatiques intelligentes et l’intelligence artificielle pour extraire la même richesse d’information à partir d’examens d’IRM de diffusion beaucoup plus courts et plus brouillons, sans sacrifier la fiabilité ?
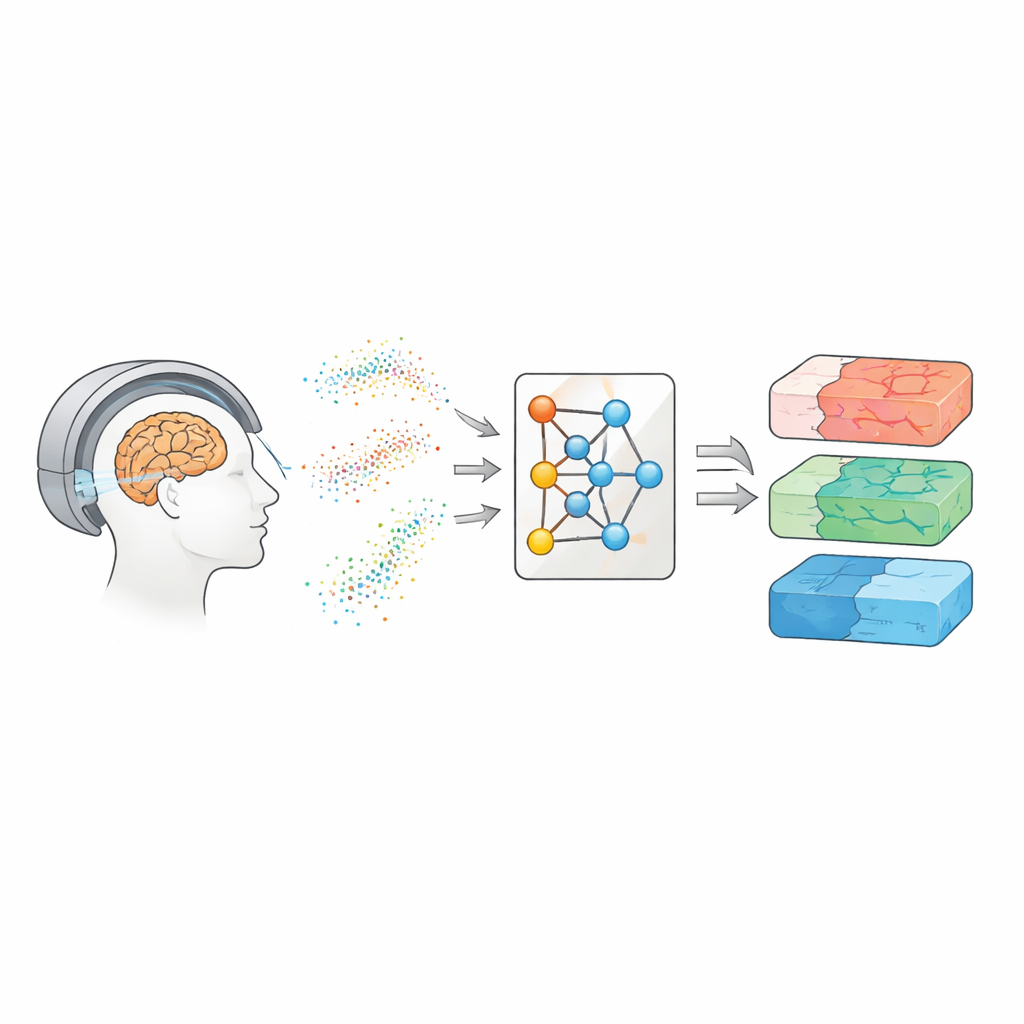
Regarder à l’intérieur du cerveau grâce à l’eau en mouvement
L’IRM de diffusion suit la manière dont les molécules d’eau se bousculent et se déplacent à travers le tissu cérébral. Comme l’eau se déplace différemment le long des fibres nerveuses, à travers les corps cellulaires ou autour des régions endommagées, ces motifs peuvent faire office d’empreinte de la microstructure cérébrale. Au fil des années, les chercheurs ont développé plusieurs familles de modèles pour traduire les signaux de diffusion en cartes des propriétés tissulaires. Les approches plus simples, comme l’imagerie par tenseur de diffusion, résument la facilité de déplacement de l’eau et la directionnalité de ce mouvement. Des méthodes plus avancées, comme l’imagerie du kurtosis de diffusion et des modèles biophysiques tels que CHARMED et AxCaliber, visent à capturer des détails comme la densité des fibres et même les diamètres typiques des axones. Ces cartes pourraient servir de « biopsies virtuelles », offrant des indices sur la maladie sans chirurgie — mais elles exigent généralement de nombreuses mesures répétées et des temps de scan longs.
Le goulot d’étranglement de l’ajustement traditionnel
Transformer des mesures de diffusion brutes en cartes signifiantes est un problème d’ajustement mathématique : les paramètres du modèle sont ajustés jusqu’à ce que le signal prédit corresponde à ce que le scanner a mesuré. Les outils les plus courants aujourd’hui, comme les moindres carrés non linéaires, procèdent en minimisant la différence au carré entre modèle et données. Bien que simples et largement disponibles, ces méthodes fonctionnent mieux lorsqu’il y a beaucoup plus de mesures que strictement nécessaire — l’équivalent en temps de scan de prendre dix fois plus de photos pour être sûr. Elles peinent aussi quand le bruit est élevé ou quand les estimations initiales sont mauvaises, ce qui est fréquent dans les données cliniques réelles. Des approches statistiques plus récentes peuvent aider, mais elles sont souvent lentes, sensibles aux hypothèses sur le bruit et rarement utilisées en dehors des centres de recherche.
Apprendre à partir de simulations plutôt que de patients
Les auteurs empruntent une voie différente : au lieu d’apprendre directement à partir des scans de patients, ils entraînent un réseau de neurones en utilisant uniquement des données simulées. Ils échantillonnent de nombreuses combinaisons possibles de paramètres de modèle, utilisent la physique connue de la diffusion pour générer des signaux synthétiques, ajoutent un bruit réaliste, puis entraînent ce qu’on appelle un estimateur de postérieure neuronale. Ce réseau apprend à produire une distribution de probabilité complète sur les paramètres susceptibles d’avoir généré un signal donné, fournissant naturellement à la fois une estimation centrale et une mesure d’incertitude. Pour rendre la méthode adaptable à différents réglages de scanner, l’équipe n’utilise pas les mesures brutes. À la place, ils compressent chaque signal en caractéristiques compactes informées par la physique qui résument la manière dont il varie avec l’intensité du gradient, la direction et le temps de diffusion. Ces caractéristiques captent l’essentiel du signal tout en restant largement indépendantes du schéma d’acquisition exact.
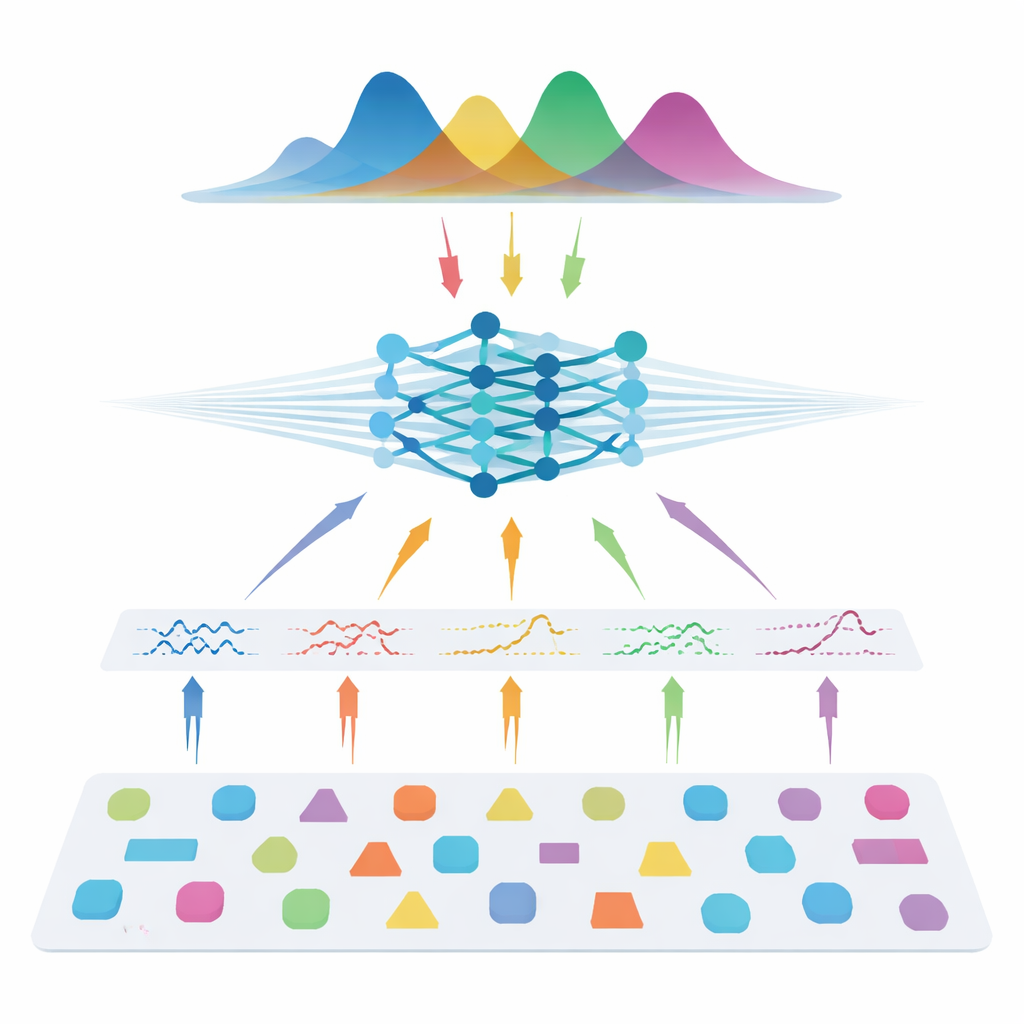
Égaler les meilleurs avec une fraction des données
Une fois entraîné, le système est testé sur des données synthétiques de « vérité terrain » connue et sur plusieurs jeux de données humains, incluant des volontaires sains et des personnes atteintes de sclérose en plaques. Pour les trois familles de modèles — imagerie par tenseur de diffusion, imagerie du kurtosis de diffusion et AxCaliber — l’approche basée sur la simulation récupère des métriques microstructurales clés avec précision, même en n’utilisant que 7 à 22 mesures au lieu de protocoles complets de 69 à 271 mesures. Cela peut représenter jusqu’à 90 % de scans en moins. Dans des conditions bruitées ou lorsque le nombre de mesures est fortement réduit, la nouvelle méthode surpasse systématiquement l’ajustement standard, produisant des cartes plus propres qui préservent la structure importante. Elle détecte également les changements attendus au sein des lésions de la sclérose en plaques et retrouve des motifs connus de tailles d’axones à travers le corps calleux, ce qui suggère une bonne généralisation aux tissus sains comme malades.
Ce que cela signifie pour les patients et les cliniques
Pour les non-spécialistes, l’essentiel est que les auteurs montrent comment obtenir presque la même vue microscopique du tissu cérébral à partir d’examens d’IRM de diffusion beaucoup plus courts et potentiellement de moindre qualité en s’appuyant fortement sur des simulations et une inférence avancée. Plutôt que de demander au scanner plus de données, ils demandent aux ordinateurs de mieux utiliser moins de données. Cela pourrait raccourcir les temps d’examen, élargir l’accès à l’imagerie avancée dans les hôpitaux de routine et même sauver d’anciennes études acquises avec des réglages sous-optimaux. Parce que la méthode est entièrement entraînée sur des signaux simulés, elle est aussi respectueuse de la vie privée et plus facile à partager et à déployer. Si elle est largement adoptée, ce type d’inférence basée sur la simulation pourrait aider à réduire l’écart entre les protocoles de recherche de pointe et l’IRM clinique quotidienne, rapprochant les biopsies tissulaires virtuelles des soins standard.
Citation: Eggl, M.F., De Santis, S. Simulation-based inference at the theoretical limit for fast, robust microstructural MRI with minimal diffusion data. Commun Med 6, 275 (2026). https://doi.org/10.1038/s43856-026-01614-6
Mots-clés: IRM de diffusion, microstructure cérébrale, inférence basée sur la simulation, réseaux de neurones, réduction du temps de scan