Clear Sky Science · pl
CSWin-MDKDNet: sieć z oknem w kształcie krzyża z wielowymiarową fuzją i destylacją wiedzy do segmentacji obrazów medycznych
Bardziej wyraźne spojrzenie we wnętrze ciała
Współczesna medycyna w dużej mierze polega na obrazach — tomografia komputerowa, rezonans magnetyczny i zdjęcia skóry — do wykrywania narządów, guzów i innych struktur. Zanim jednak lekarze lub systemy komputerowe będą mogli mierzyć lub śledzić chorobę, często trzeba precyzyjnie „wypełnić” każdy narząd lub zmianę, zadanie zwane segmentacją. W artykule przedstawiono nowy system sztucznej inteligencji, CSWin-MDKDNet, który sprawia, że ten etap obrysowywania jest dokładniejszy i wydajniejszy dla różnych typów obrazów medycznych, co może poprawić diagnostykę, planowanie leczenia i opiekę kontrolną u wielu pacjentów.
Dlaczego rysowanie granic ma znaczenie
Gdy radiolodzy planują zabieg chirurgiczny, mierzą wydolność skurczową serca lub szacują rozmiar zmiany skórnej, polegają na wyraźnych granicach na obrazach. Tradycyjnie eksperci rysują te obrysy ręcznie, co jest powolne, męczące i może się różnić między osobami. Wcześniejsze metody komputerowe oparte na konwolucyjnych sieciach neuronowych nauczyły się rozpoznawać lokalne wzorce, takie jak krawędzie i tekstury, i zrewolucjonizowały analizę obrazów medycznych. Jednak te systemy wciąż miały problemy z uchwyceniem „szerszego kontekstu” — jak odległe części obrazu się ze sobą wiążą — przy jednoczesnym zachowaniu drobnych detali na krawędziach narządów. Ten kompromis między globalnym kontekstem a lokalną precyzją ograniczał niezawodność narzędzi automatycznych w wymagających warunkach klinicznych.
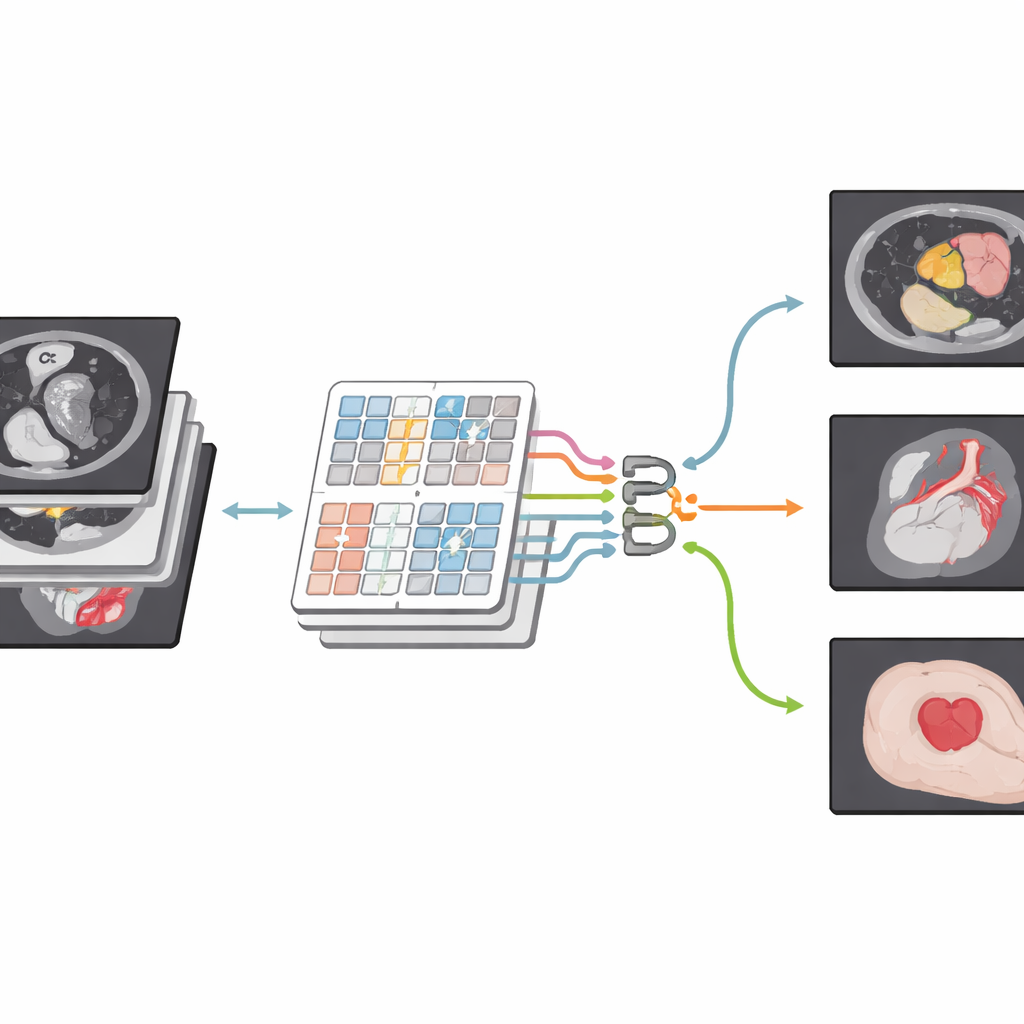
Nowy sposób patrzenia na obrazy medyczne
Autorzy budują na nowszej rodzinie modeli znanych jako Transformery, pierwotnie opracowanych do języka, a dziś szeroko stosowanych w wizji komputerowej. Ich sieć, CSWin-MDKDNet, zaczyna od podziału obrazu medycznego na fragmenty i przepuszcza je przez moduł Transformera, który ogląda obraz w paskach ułożonych krzyżowo — poziomo i pionowo. Takie rozwiązanie pozwala systemowi powiązać odległe regiony — na przykład górę i dół wątroby — bez eksplozji kosztów obliczeniowych. Wokół tego rdzenia model przyjmuje układ enkoder–dekoder w kształcie litery U, który stał się standardem w obrazowaniu medycznym: jedna ścieżka stopniowo zmniejsza rozdzielczość, aby uchwycić strukturę wysokiego poziomu, podczas gdy druga ścieżka przywraca obraz do pełnego rozmiaru, tworząc szczegółową mapę segmentacji zgodną z oryginalnym skanem.
Mieszanie detali z wielu kierunków
Proste dodanie kolejnych warstw i bloków uwagi może uczynić model potężnym, ale też rozrośniętym i nieukierunkowanym. Aby to rozwiązać, autorzy wprowadzają moduł Multi-dimensional Selective Fusion, który działa jak inteligentny mikser cech obrazu. Analizuje informacje jednocześnie w trzech aspektach: różne „kanały” kodujące rozmaite wskazówki wizualne, rozmieszczenie przestrzenne uchwytujące, gdzie występują krawędzie i tekstury, oraz kilka skal od drobnych detali po szeroki kontekst. Dzięki zastosowaniu ukierunkowanego ważenia zamiast traktowania wszystkich cech równo, moduł wzmacnia informacje naprawdę pomocne w rozróżnianiu jednego narządu od drugiego — na przykład subtelnego, nieregularnego obrysu trzustki — jednocześnie tłumiąc zakłócenia pochodzące z szumu i tkanek tła.
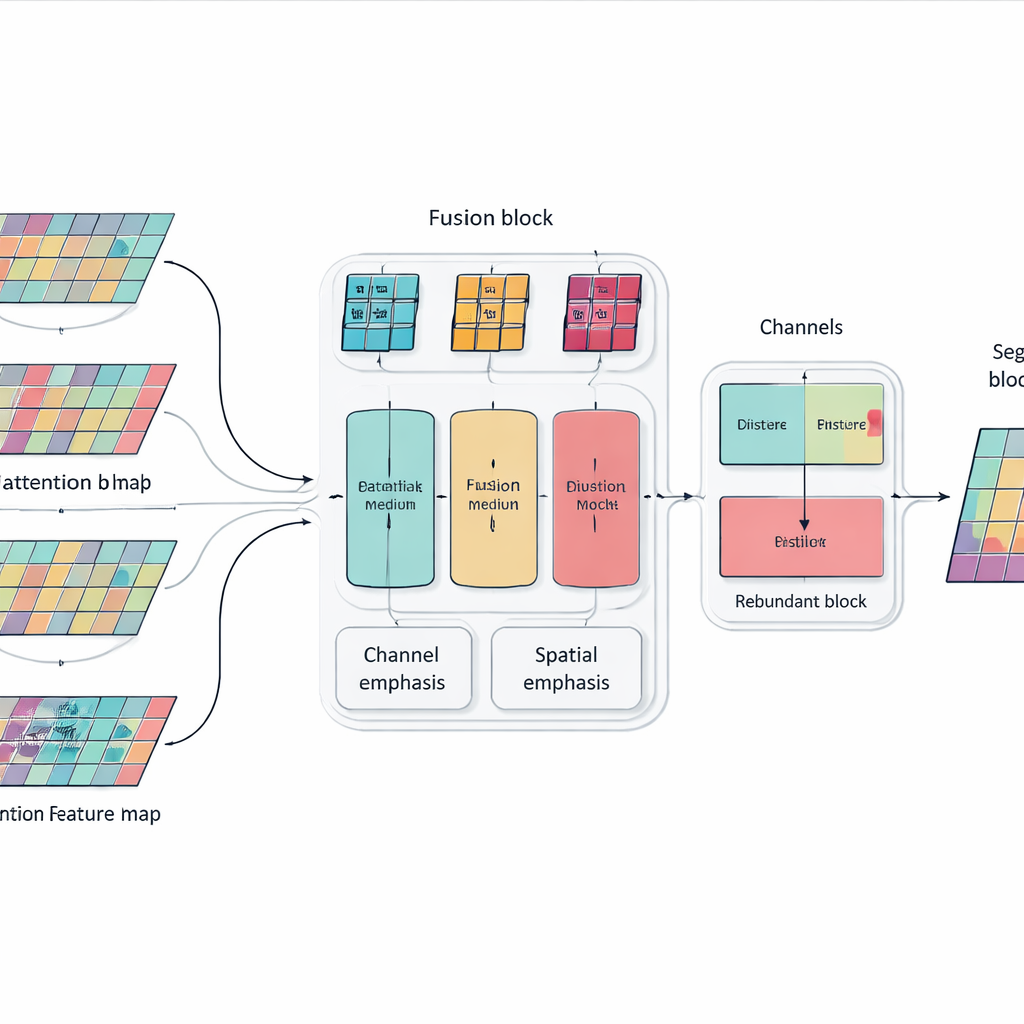
Nauczanie sieci, by się nie powtarzała
Innym problemem bardzo głębokich sieci jest redundancja: późniejsze warstwy mogą powtarzać wzorce już nauczone wcześniej, marnując pojemność i czasem myląc proces decyzyjny. Zamiast dodawać dodatkowe moduły przycinające, badacze wprowadzają prostą regułę treningową inspirowaną destylacją wiedzy. W każdym bloku sieci zachęcają głębsze kanały do przejmowania najbardziej użytecznych informacji od płytszych, jednocześnie unikając niepotrzebnego duplikowania. Ta wewnętrzna relacja „nauczyciel–uczeń” skłania model do tworzenia kompaktowych, spójnych reprezentacji, co pomaga mu lepiej uogólniać na nowych pacjentach i różnych skanerach bez zwiększania kosztów działania systemu.
Udowodnione korzyści w różnych narządach i modalnościach
Aby przetestować swoje podejście, zespół ocenił CSWin-MDKDNet na trzech wymagających benchmarkach. W przypadku wielonarządowych skanów brzucha z CT system osiągnął najwyższe średnie pokrycie między przewidywaniami a etykietami ekspertów, szczególnie poprawiając wyniki dla trudno obrysowalnych narządów, takich jak trzustka. W rezonansie magnetycznym serca dostarczał dokładniejszych konturów jam serca i mięśnia, co jest kluczowe przy pomiarze funkcji serca. W dużym zbiorze zdjęć zmian skórnych generował czystsze granice niż kilka silnych konkurencyjnych modeli. Co istotne, te usprawnienia wystąpiły przy mniejszej liczbie parametrów i niższym koszcie obliczeniowym niż w klasycznych konstrukcjach opartych na Transformerach, co oznacza, że metoda jest lepiej dostosowana do praktycznego wdrożenia w klinikach i szpitalach.
Bardziej czytelne obrysy dla lepszej opieki
Mówiąc prościej, praca ta pokazuje, jak inteligentniejsze oprogramowanie może dokładniej odrysowywać kształty narządów i zmian na obrazach medycznych, przy jednoczesnym bardziej efektywnym wykorzystaniu zasobów komputerowych. Łącząc szerokie spojrzenie na obraz z precyzyjnie dostrojonym skupieniem na istotnych detalach oraz ograniczając marnotrawne powtórzenia wewnątrz sieci, CSWin-MDKDNet dostarcza bardziej niezawodnych cyfrowych obrysów, na które lekarze mogą polegać. Takie ulepszenia mogą nie być bezpośrednio widoczne dla pacjentów, ale mogą wspierać dokładniejsze planowanie zabiegów, bardziej konsekwentne śledzenie przebiegu choroby w czasie i ostatecznie pewniejsze decyzje przy łóżku pacjenta.
Cytowanie: Cui, G., Lin, H., Sun, L. et al. CSWin-MDKDNet: cross-shaped window network with multi-dimensional fusion and knowledge distillation for medical image segmentation. Sci Rep 16, 11532 (2026). https://doi.org/10.1038/s41598-026-40690-5
Słowa kluczowe: segmentacja obrazów medycznych, uczenie głębokie, sieci Transformer, analiza narządów i zmian chorobowych, wspomaganie diagnostyki komputerowej