Clear Sky Science · it
Apprendimento automatico completo identifica firme di anoikis che prevedono la resistenza terapeutica e la sopravvivenza nel tumore gastrico
Perché questa ricerca conta per i pazienti
Il cancro allo stomaco rimane uno dei tumori più letali al mondo, in gran parte perché molti tumori smettono di rispondere alla chemioterapia e alle nuove immunoterapie. Questo studio pone una domanda semplice ma cruciale: possiamo leggere i “trucchetti di sopravvivenza” molecolari delle cellule tumorali e del loro microambiente per prevedere quali pazienti resisteranno ai trattamenti e quali ne trarranno beneficio? Analizzando migliaia di geni con tecniche moderne di machine learning, i ricercatori hanno costruito un punteggio potente che potrebbe aiutare i medici a scegliere terapie più efficaci e personalizzate per le persone con cancro gastrico.
Come le cellule tumorali sfuggono ai loro freni naturali
Le cellule normali sono programmate per autodistruggersi quando perdono la loro corretta posizione nei tessuti, un processo chiamato morte cellulare indotta dal distacco. Le cellule cancerose spesso imparano a eludere questo destino, permettendo loro di diffondersi e dare origine a nuovi tumori. Gli autori si sono concentrati sui geni collegati a questa risposta al distacco e su come questi si relazionano con la reattività ai farmaci. Usando 10 grandi banche dati pubbliche sul cancro gastrico, hanno incrociato set genici associati alla morte cellulare, alla sensibilità o resistenza alla chemioterapia e alla risposta all’immunoterapia. Da questo complesso sovrapporsi hanno estratto 125 geni chiave che riflettono sia la facilità con cui le cellule evitano la morte per distacco sia il loro comportamento sotto trattamento; li hanno chiamati geni di anoikis naturalizzati dai farmaci, o DNAGs.
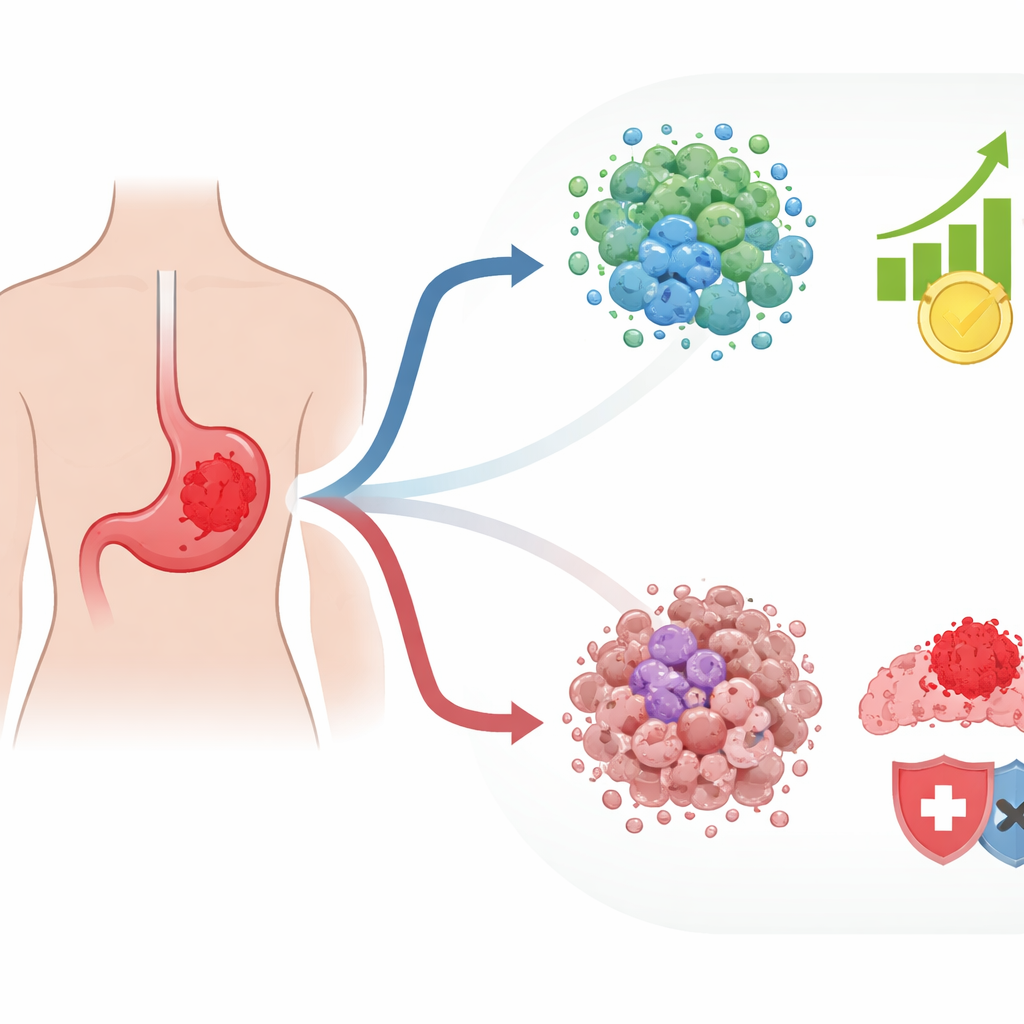
Due tipi nascosti di tumori gastrici
Quando il team ha raggruppato oltre 800 tumori gastrici in base all’attività dei DNAG, sono emersi due pattern principali. Un gruppo di tumori presentava numerose mutazioni genetiche e alterazioni strutturali dei cromosomi, il che può sembrare preoccupante ma può effettivamente rendere il cancro più visibile al sistema immunitario. Questi tumori avevano più segni di attacco immunitario attivo e includevano cellule immunitarie in grado di riconoscere e combattere il cancro. Il secondo gruppo appariva molto diverso: si riscontrava più spesso in pazienti più giovani e in un particolare sottotipo molecolare noto per la sua aggressività. Questi tumori erano inseriti in un ambiente fortemente soppresso dominato da cellule di supporto strutturale e altri componenti che tendono a proteggere il cancro dall’attacco immunitario. I pazienti con questo secondo pattern avevano prognosi complessivamente peggiori.
Il punteggio terapeutico che legge il comportamento del tumore
Partendo da questi pattern, i ricercatori hanno utilizzato combinazioni di 101 approcci di machine learning per ridurre un insieme più ampio a un set di 11 geni definito “firma prognostica orientata al trattamento”, o TOPS. Questo punteggio divide i pazienti in gruppi a rischio alto e basso. In diverse coorti indipendenti, i pazienti con punteggi TOPS elevati avevano costantemente sopravvivenza più breve, malattia più avanzata e tipi tumorali noti per un comportamento invasivo. Contemporaneamente, i tumori con TOPS elevato erano meno propensi a rispondere sia alla chemioterapia sia ai farmaci anti‑checkpoint immunitari, mentre i tumori con TOPS basso mostravano risposte migliori e sopravvivenza prolungata dopo immunoterapia. Il punteggio ha superato le caratteristiche cliniche tradizionali come età, sesso e stadio nella predizione dell’esito.
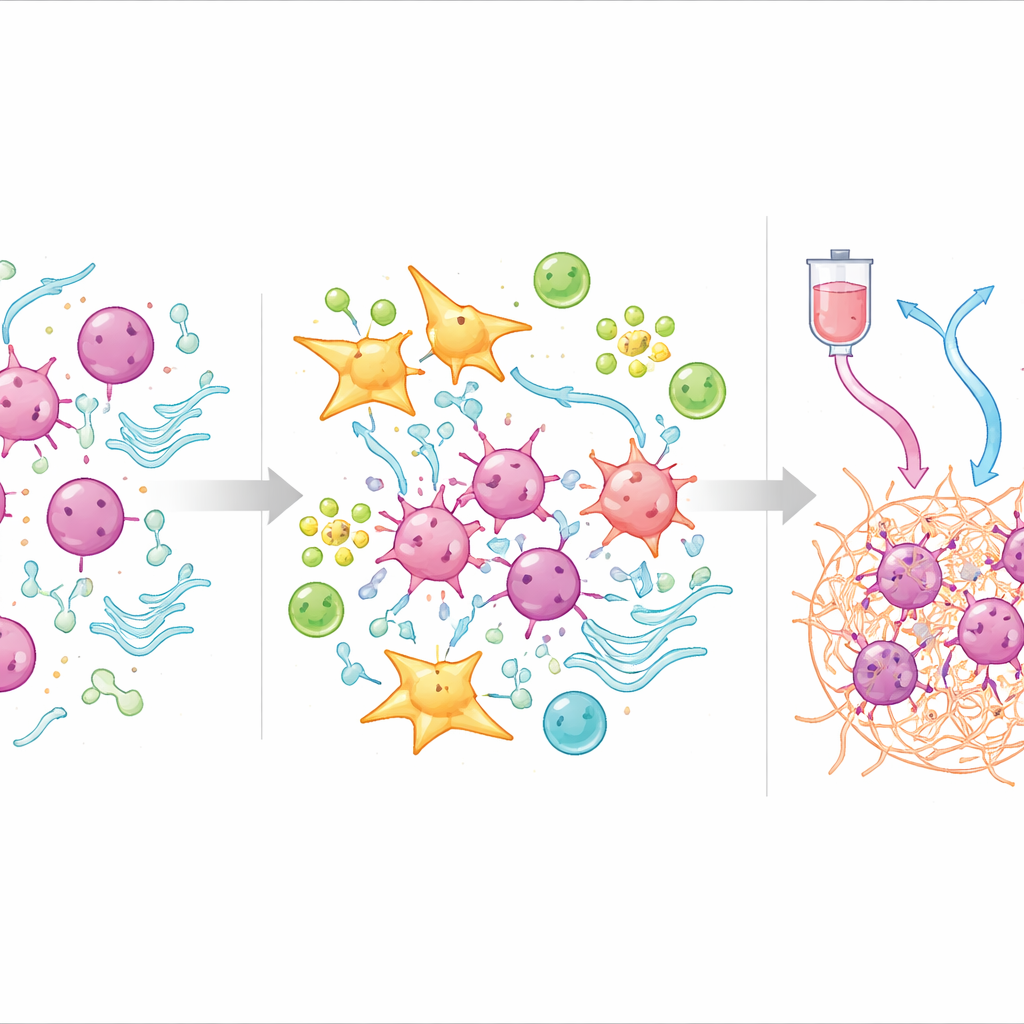
Cosa rivela l’ecosistema tumorale sulla resistenza
Per capire perché il punteggio funziona, il team ha analizzato dati di sequenziamento a singola cellula, che esaminano le singole cellule all’interno dei tumori. Hanno scoperto che i tumori con TOPS elevato erano ricchi di fibroblasti—cellule che contribuiscono a costruire l’impalcatura tissutale—e di alcune cellule dei vasi sanguigni, formando un guscio denso e protettivo attorno alle cellule tumorali. All’interno di questo guscio, i fibroblasti seguivano un percorso di differenziazione verso un sottotipo che comunica intensamente con le cellule tumorali e attiva vie associate alla neoangiogenesi, al metabolismo alterato e alla soppressione immunitaria. Al contrario, i tumori con TOPS basso contenevano più cellule T, cellule B e plasmacellule in grado di montare un attacco immunitario efficace e mostravano modelli di espressione genica favorevoli al metabolismo normale e al mantenimento tissutale piuttosto che all’invasione.
Cosa potrebbe significare per i trattamenti futuri
Per i pazienti, il messaggio principale dello studio è che non tutti i tumori gastrici sono uguali, anche quando appaiono simili al microscopio. Leggendo una firma di 11 geni relativa al modo in cui le cellule gestiscono il distacco e al comportamento del tessuto circostante, un giorno i medici potrebbero prevedere meglio chi trarrà beneficio dalla chemioterapia o dall’immunoterapia standard e chi potrebbe necessitare di strategie alternative o combinate che prendano di mira anche le cellule di supporto e i segnali nel microambiente tumorale. Sebbene il modello debba ancora essere testato in studi clinici prospettici, offre una promettente roadmap per rendere il trattamento del cancro gastrico più davvero personalizzato e migliorare le prospettive per i pazienti colpiti da questa malattia difficile.
Citazione: Liu, F., Zhou, Y., Xie, Y. et al. Comprehensive machine learning identifies anoikis signatures predicting therapeutic resistance and survival in gastric cancer. Sci Rep 16, 11571 (2026). https://doi.org/10.1038/s41598-026-38996-5
Parole chiave: cancro gastrico, resistenza ai trattamenti, microambiente tumorale, risposta all’immunoterapia, biomarcatori di machine learning