Clear Sky Science · de
Umfassendes maschinelles Lernen identifiziert Anoikis-Signaturen zur Vorhersage von Therapie‑Resistenz und Überleben bei Magenkrebs
Warum diese Forschung für Patientinnen und Patienten wichtig ist
Magenkrebs gehört weiterhin zu den tödlichsten Krebsarten weltweit, vor allem weil viele Tumoren irgendwann nicht mehr auf Chemotherapie und neuere Immuntherapien ansprechen. Diese Studie stellt eine einfache, aber entscheidende Frage: Lassen sich die molekularen „Überlebenstricks“ von Tumorzellen und ihrem Umfeld so auslesen, dass man vorhersagen kann, welche Patienten gegen Therapien resistent sind und welche davon profitieren? Durch das Durchsuchen von Tausenden Genen mit modernen Methoden des maschinellen Lernens entwickeln die Forschenden einen leistungsfähigen Score, der Ärztinnen und Ärzten helfen könnte, wirksamere, personalisierte Therapien für Menschen mit Magenkrebs auszuwählen.
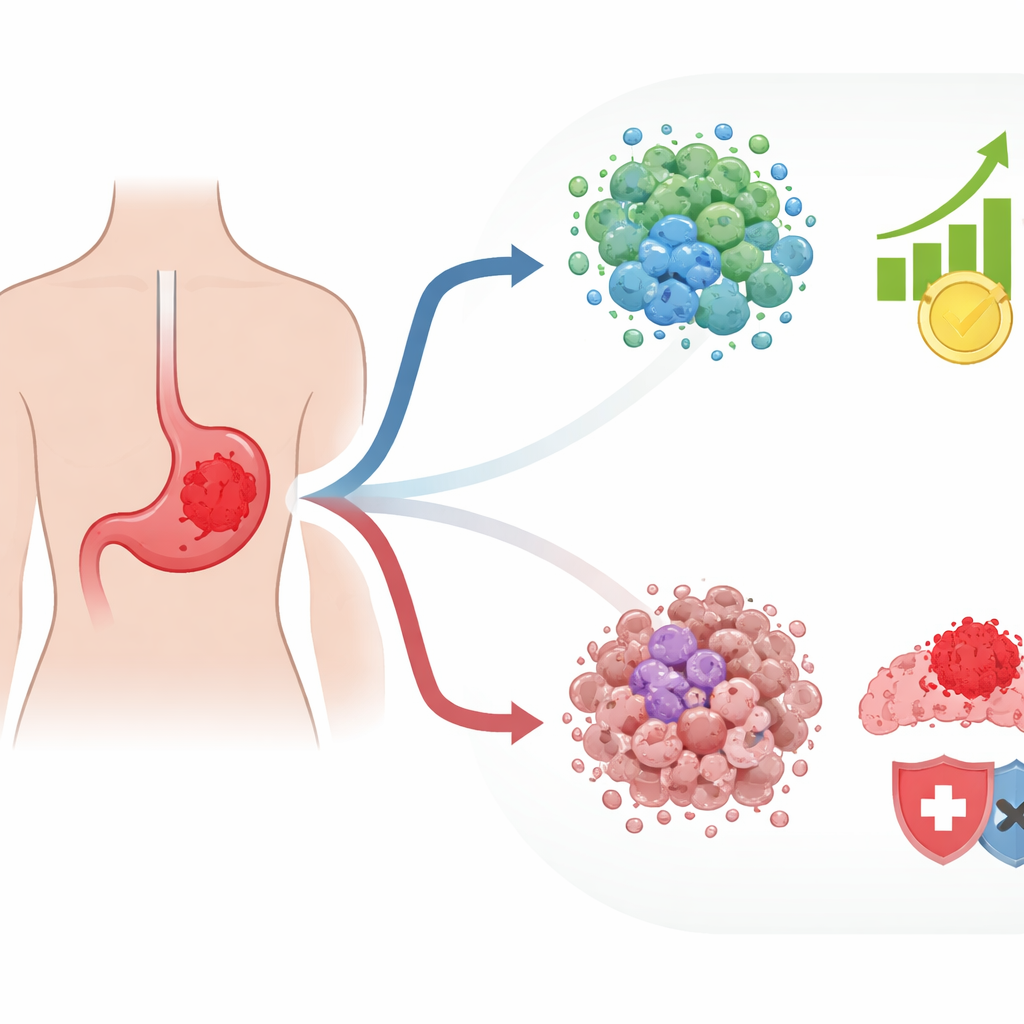
Wie Tumorzellen ihren natürlichen Selbstschutz umgehen
Normale Zellen verfügen über ein Selbstzerstörungsprogramm, das aktiviert wird, wenn sie ihren normalen Aufenthaltsort im Gewebe verlieren – ein Prozess, der als detachment‑induziertes Absterben bezeichnet wird. Krebszellen lernen häufig, diesem Schicksal zu entgehen, was ihnen Ausbreitung und Besiedelung neuer Herde ermöglicht. Die Autorinnen und Autoren konzentrierten sich auf Gene, die mit dieser Reaktion auf Zell‑Detachment verknüpft sind, sowie darauf, wie diese Gene mit der Wirkungsweise von Medikamenten zusammenhängen. Unter Verwendung von zehn großen öffentlichen Datenbanken zu Magenkrebs kreuzverglichen sie Genmengen, die mit Zelltod, Chemotherapie‑Sensitivität oder ‑Resistenz sowie dem Ansprechen auf Immuntherapie assoziiert sind. Aus dieser komplexen Überlappung extrahierten sie 125 Schlüsselgene, die sowohl widerspiegeln, wie leicht Zellen dem detachment‑induzierten Tod entkommen, als auch wie sie sich unter Behandlung verhalten; sie bezeichnen diese als drug‑naturalized anoikis genes (DNAGs).
Zwei verborgene Typen von Magen‑Tumoren
Als das Team mehr als 800 Magenkarzinome anhand ihrer DNAG‑Aktivität gruppierte, traten zwei Hauptmuster hervor. Eine Gruppe wies viele genetische Mutationen und chromosomale Veränderungen auf, was bedrohlich klingen mag, aber tatsächlich das Krebsgewebe für das Immunsystem sichtbarer machen kann. Diese Tumoren zeigten mehr Hinweise auf aktive Immunangriffe und enthielten Immunzellen, die Krebs erkennen und bekämpfen können. Die zweite Gruppe unterschied sich deutlich: Sie trat häufiger bei jüngeren Patientinnen und Patienten sowie in einer bestimmten, als aggressiv bekannten molekularen Untergruppe auf. Diese Tumoren befanden sich in einer stark unterdrückten Umgebung, dominiert von stützenden Zellen und weiteren Komponenten, die den Krebs vor Immunangriffen abschirmen. Patienten mit diesem zweiten Muster hatten insgesamt eine schlechtere Prognose.
Der Therapiescore, der Tumorverhalten abbildet
Aufbauend auf diesen Mustern nutzten die Forschenden Kombinationen aus 101 Verfahren des maschinellen Lernens, um aus einer kleineren Menge von 11 Genen eine „therapieorientierte prognostische Signatur“ (TOPS) zu destillieren. Dieser Score teilt Patientinnen und Patienten in Hoch‑ und Niedrigrisikogruppen ein. In mehreren unabhängigen Patientenkollektiven hatten Personen mit hohen TOPS‑Werten durchgängig kürzere Überlebenszeiten, weiter fortgeschrittene Erkrankungen und Tumortypen, die für invasives Verhalten bekannt sind. Gleichzeitig sprachen Tumoren mit hohem TOPS seltener auf Chemotherapie und Checkpoint‑Inhibitoren an, während Niedrig‑TOPS‑Tumoren bessere Ansprechraten und längeres Überleben nach Immuntherapie zeigten. Der Score übertraf traditionelle klinische Merkmale wie Alter, Geschlecht und Stadieneinteilung bei der Vorhersage des Ergebnisses.
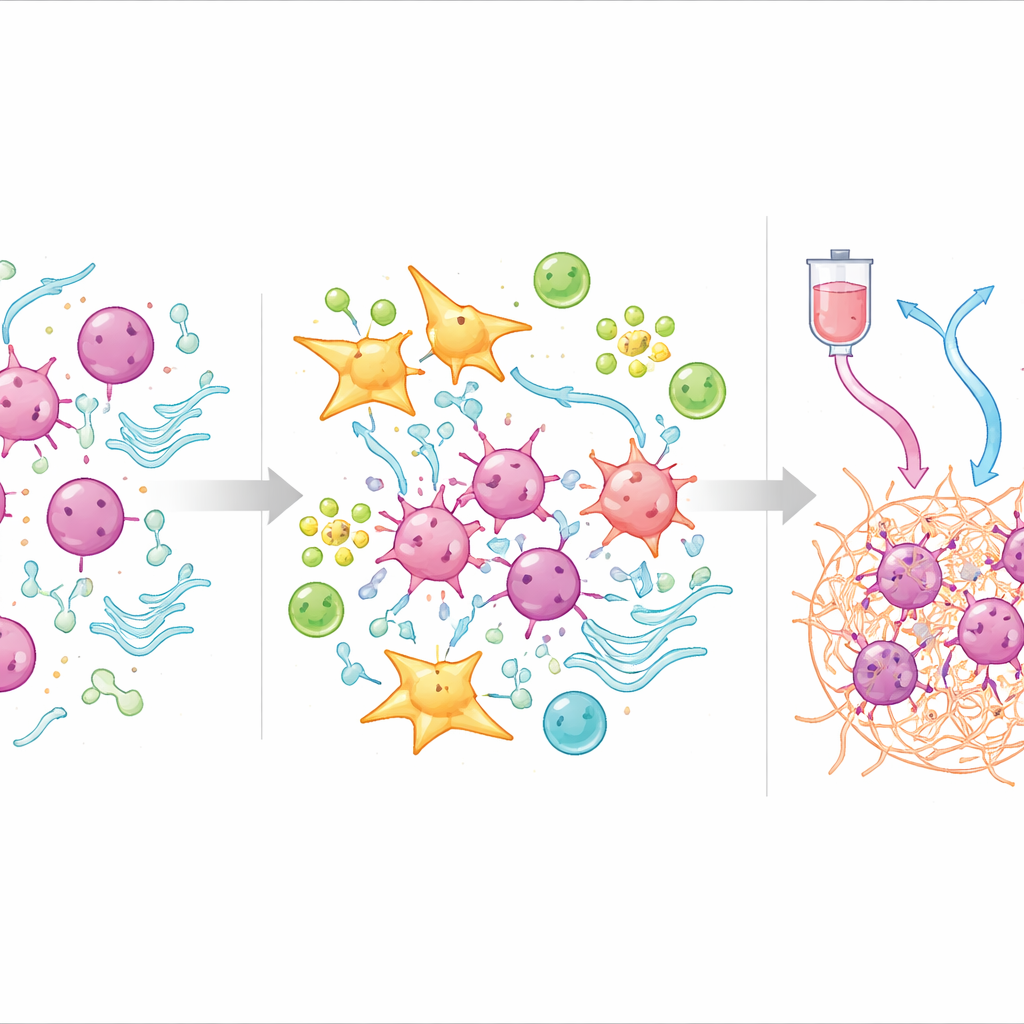
Was das Tumorökosystem über Resistenz verrät
Um zu erklären, warum der Score funktioniert, nutzte das Team Einzelzellsequenzierung, die einzelne Zellen innerhalb der Tumoren untersucht. Sie fanden heraus, dass Hoch‑TOPS‑Tumoren reich an Fibroblasten waren – Zellen, die zum Aufbau des Gewebegerüsts beitragen – sowie an bestimmten Gefäßzellen, die eine dichte, schützende Hülle um die Krebszellen bildeten. Innerhalb dieser Hülle durchliefen Fibroblasten einen Entwicklungsweg hin zu einem Subtyp, der stark mit Tumorzellen kommuniziert und Signalwege aktiviert, die mit Neubildung von Blutgefäßen, verändertem Stoffwechsel und Immunsuppression verbunden sind. Im Gegensatz dazu enthielten Niedrig‑TOPS‑Tumoren mehr T‑Zellen, B‑Zellen und Plasmazellen, die effektive Immunantworten auslösen können, und zeigten Genaktivitätsmuster, die für normalen Stoffwechsel und Gewebeerhalt statt für Invasion sprechen.
Welche Bedeutung das für zukünftige Behandlungen haben könnte
Für Patientinnen und Patienten lautet die zentrale Botschaft der Studie: Nicht alle Magenkrebse sind gleich, selbst wenn sie unter dem Mikroskop ähnlich aussehen. Indem man eine 11‑Gen‑Signatur liest, die mit dem Umgang von Zellen mit Detachment und mit dem Verhalten des umgebenden Gewebes zusammenhängt, können Ärztinnen und Ärzte künftig möglicherweise besser vorhersagen, wer von Standardchemotherapie oder Immuntherapie profitiert und wer alternative oder kombinierte Strategien braucht, die auch die stützenden Zellen und Signale im Tumornachbarschaft ansprechen. Obwohl das Modell noch prospektiv in klinischen Studien geprüft werden muss, bietet es eine vielversprechende Roadmap, um die Behandlung von Magenkrebs wirklich personalisierter zu gestalten und die Chancen für Betroffene zu verbessern.
Zitation: Liu, F., Zhou, Y., Xie, Y. et al. Comprehensive machine learning identifies anoikis signatures predicting therapeutic resistance and survival in gastric cancer. Sci Rep 16, 11571 (2026). https://doi.org/10.1038/s41598-026-38996-5
Schlüsselwörter: Magenkrebs, Therapie‑Resistenz, Tumormikroumgebung, Ansprechen auf Immuntherapie, Biomarker aus maschinellem Lernen