Clear Sky Science · es
El aprendizaje automático integral identifica firmas de anoikis que predicen la resistencia terapéutica y la supervivencia en el cáncer gástrico
Por qué esta investigación importa para los pacientes
El cáncer de estómago sigue siendo uno de los cánceres más mortales del mundo, en gran parte porque muchos tumores dejan de responder a la quimioterapia y a las nuevas inmunoterapias. Este estudio plantea una pregunta sencilla pero crucial: ¿podemos leer los “trucos” moleculares de supervivencia de las células tumorales y su entorno para predecir qué pacientes resistirán el tratamiento y quiénes se beneficiarán? Mediante el análisis de miles de genes con técnicas modernas de aprendizaje automático, los investigadores construyen una puntuación potente que podría ayudar a los médicos a elegir terapias más eficaces y personalizadas para personas con cáncer gástrico.
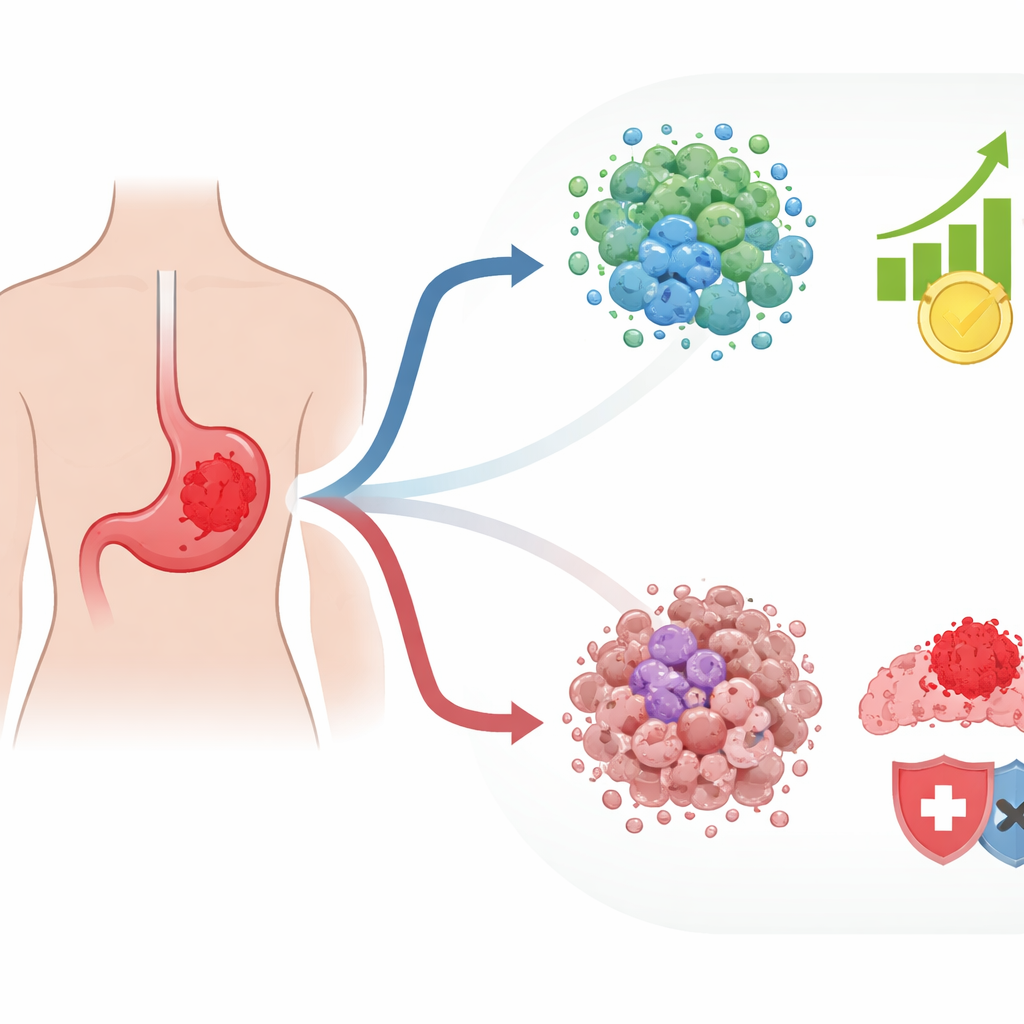
Cómo las células tumorales eluden sus controles de seguridad naturales
Las células normales están programadas para autodestruirse cuando pierden su anclaje adecuado en el tejido, un proceso llamado muerte celular inducida por desprendimiento. Las células cancerosas suelen aprender a evitar este destino, lo que les permite diseminarse y sembrar nuevos tumores. Los autores se centraron en genes relacionados con esta respuesta al desprendimiento y en cómo se vinculan con las formas en que los tumores responden a los fármacos. Usando 10 grandes bases de datos públicas de cáncer gástrico, cruzaron conjuntos de genes asociados con la muerte celular, la sensibilidad o resistencia a la quimioterapia y la respuesta a la inmunoterapia. A partir de esta superposición compleja, destilaron 125 genes clave que reflejan tanto la facilidad con la que las células evaden la muerte por desprendimiento como su comportamiento bajo tratamiento; los denominaron genes de anoikis naturalizados por fármacos, o DNAGs.
Dos tipos ocultos de tumores gástricos
Cuando el equipo agrupó más de 800 tumores gástricos según la actividad de los DNAGs, emergieron dos patrones principales. Un grupo de tumores presentaba muchas mutaciones genéticas y alteraciones en la estructura cromosómica, lo que podría sonar ominoso pero en realidad puede hacer que el cáncer sea más visible para el sistema inmune. Estos tumores mostraban más señales de ataque inmune activo e incluían células inmunitarias capaces de reconocer y combatir el cáncer. El segundo grupo se veía muy diferente: apareció con mayor frecuencia en pacientes más jóvenes y en un subtipo molecular conocido por su agresividad. Estos tumores se encontraban en un entorno fuertemente suprimido dominado por células de soporte estructural y otros componentes que tienden a proteger al cáncer del ataque inmune. Los pacientes con este segundo patrón tuvieron un peor pronóstico en general.
La puntuación de tratamiento que interpreta el comportamiento tumoral
Partiendo de estos patrones, los investigadores emplearon combinaciones de 101 enfoques de aprendizaje automático para destilar un conjunto más pequeño de 11 genes en una “firma pronóstica orientada al tratamiento”, o TOPS. Esta puntuación divide a los pacientes en grupos de alto y bajo riesgo. En varias cohortes de pacientes independientes, aquellos con puntuaciones TOPS altas consistentemente tuvieron una supervivencia más corta, enfermedad más avanzada y tipos tumorales asociados a un comportamiento invasivo. Al mismo tiempo, los tumores con TOPS alto eran menos propensos a responder tanto a la quimioterapia como a los inhibidores de puntos de control inmunitario, mientras que los tumores con TOPS bajo mostraron mejores respuestas y mayor supervivencia tras la inmunoterapia. La puntuación superó a características clínicas tradicionales como edad, sexo y estadio al predecir el resultado.
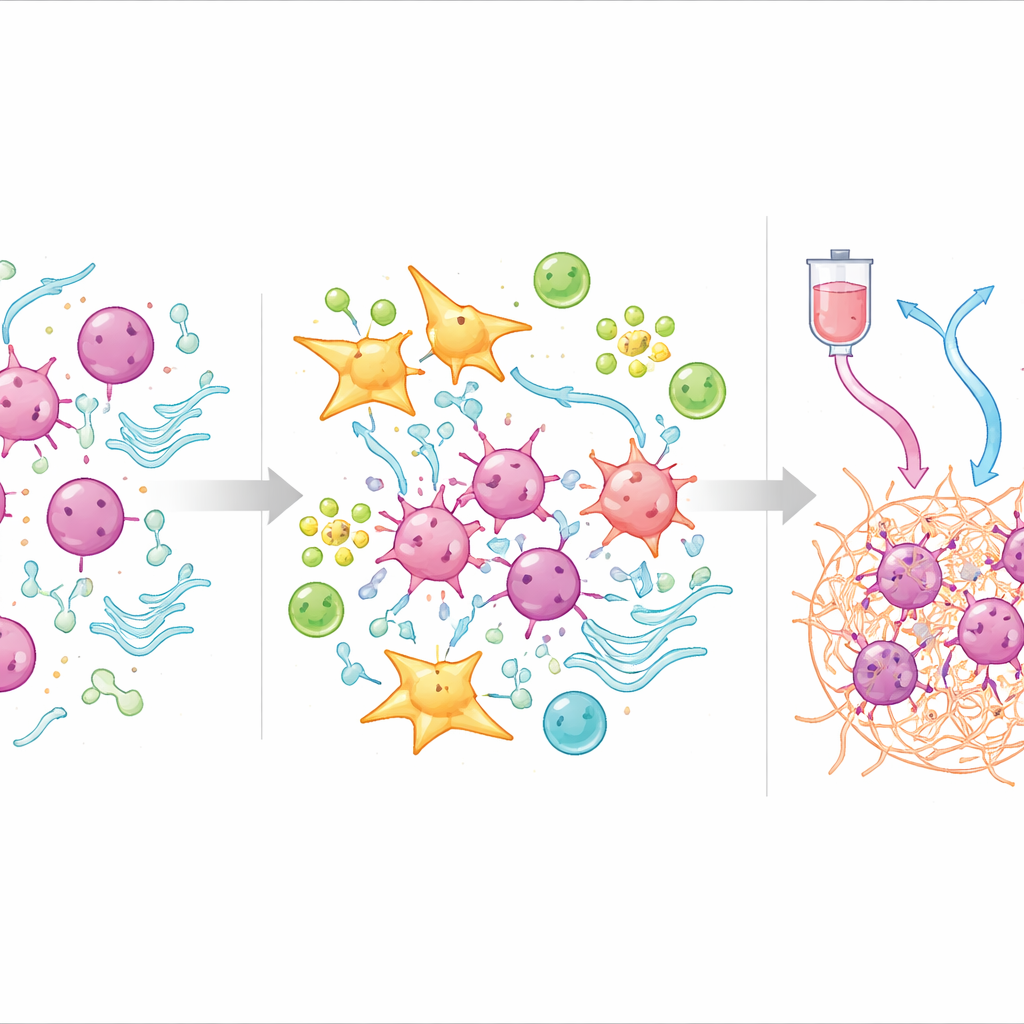
Lo que revela el ecosistema tumoral sobre la resistencia
Para comprender por qué funciona la puntuación, el equipo recurrió a la secuenciación unicelular, que examina células individuales dentro de los tumores. Encontraron que los tumores con TOPS alto estaban repletos de fibroblastos —células que ayudan a construir el armazón del tejido— y ciertos tipos de células vasculares, formando una coraza densa y protectora alrededor de las células cancerosas. Dentro de esta coraza, los fibroblastos seguían una trayectoria de desarrollo hacia un subtipo que comunica intensamente con las células tumorales y activa vías relacionadas con la formación de nuevos vasos sanguíneos, el metabolismo alterado y la supresión inmune. En contraste, los tumores con TOPS bajo contenían más células T, células B y células plasmáticas capaces de montar un ataque inmune eficaz y mostraron patrones de actividad génica que favorecían el metabolismo normal y el mantenimiento tisular en lugar de la invasión.
Qué podría significar esto para tratamientos futuros
Para los pacientes, el mensaje principal del estudio es que no todos los cánceres de estómago son iguales, incluso cuando se parecen bajo el microscopio. Al leer una firma de 11 genes relacionada con cómo las células manejan el desprendimiento y cómo se comporta el tejido circundante, los médicos podrían en el futuro predecir mejor quién se beneficiará de la quimioterapia estándar o de la inmunoterapia, y quién puede necesitar estrategias alternativas o combinadas que también apunten a las células de soporte y a las señales del vecindario tumoral. Aunque el modelo aún necesita evaluarse en ensayos clínicos prospectivos, ofrece una hoja de ruta prometedora para que el tratamiento del cáncer gástrico sea realmente más personalizado y mejore las probabilidades para los pacientes que enfrentan esta enfermedad difícil.
Cita: Liu, F., Zhou, Y., Xie, Y. et al. Comprehensive machine learning identifies anoikis signatures predicting therapeutic resistance and survival in gastric cancer. Sci Rep 16, 11571 (2026). https://doi.org/10.1038/s41598-026-38996-5
Palabras clave: cáncer gástrico, resistencia al tratamiento, microambiente tumoral, respuesta a la inmunoterapia, biomarcadores mediante aprendizaje automático