Clear Sky Science · fr
Prédiction explicable des effets indésirables des médicaments sur le système nerveux central via un réseau de neurones graphiques informé biologiquement
Pourquoi les risques cachés des médicaments comptent
Beaucoup de médicaments qui aident notre cerveau peuvent aussi lui nuire discrètement. Vertiges, confusion, convulsions ou dépression peuvent n’apparaître qu’après une large utilisation d’un médicament. Les tests de laboratoire et cliniques traditionnels sont trop lents et coûteux pour détecter tous les problèmes possibles avant autorisation, en particulier pour le système nerveux central, où les effets indésirables peuvent être subtils mais modifier la vie. Cette étude présente un nouveau modèle informatique qui exploite d’immenses jeux de données biologiques pour signaler précocement les effets probables liés au cerveau et pour montrer la chaîne d’événements moléculaires qui pourrait les causer.
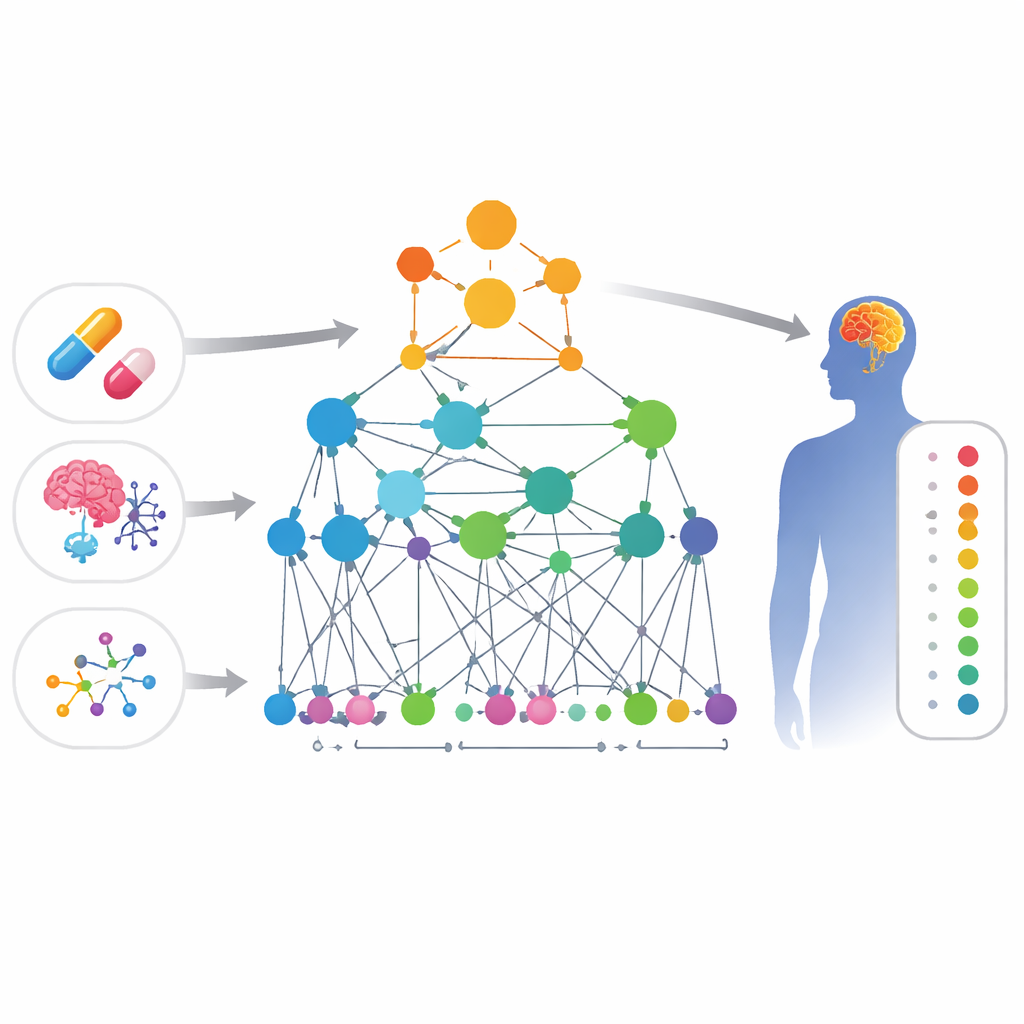
Relier les points entre médicaments et symptômes
Les chercheurs ont construit une grande « carte » de connaissances biologiques reliant quatre types d’éléments : médicaments, effets indésirables, gènes et fonctions géniques. Dans cette carte, chaque élément est un point et les lignes entre points représentent des preuves de leur relation — par exemple, deux gènes qui interagissent physiquement, deux médicaments aux structures chimiques similaires, ou un médicament connu pour provoquer un certain effet indésirable. Parce que les plaintes liées au système nerveux central sont à la fois fréquentes et souvent négligées, l’équipe a axé cette carte sur des problèmes cérébraux tels que les changements d’humeur, les troubles du mouvement et d’autres symptômes neurologiques.
Un réseau intelligent qui apprend la biologie
Par-dessus cette carte, les auteurs ont conçu une forme spécialisée d’intelligence artificielle appelée réseau de neurones graphiques. Contrairement à un modèle classique qui considère chaque médicament isolément, cette approche examine le réseau de connexions entourant chaque médicament et chaque effet indésirable. Le modèle, nommé HHAN-DSI, est « informé biologiquement » : il n’est autorisé à transmettre l’information que le long de chemins ayant un sens biologique — par exemple, d’un gène à un autre avec lequel il interagit directement, d’un gène à un médicament qui le cible, puis de ce médicament à des effets observés avec des médicaments similaires. En donnant plus de poids aux chemins les plus informatifs, le système apprend des empreintes mathématiques compactes pour chaque médicament et chaque effet indésirable, puis attribue une probabilité qu’un couple donné soit lié.
Mettre le modèle à l’épreuve
Pour vérifier si ces prédictions correspondaient à la réalité, l’équipe a entraîné le modèle sur une base de données curatée d’effets indésirables rapportés dans les informations officielles des produits, puis l’a testé à la fois sur cette source et sur un ensemble séparé de rapports de sécurité post-commercialisation. Ces rapports externes capturent des problèmes apparus seulement après la large utilisation des médicaments. Le modèle n’a pas seulement distingué les paires médicament–effet indésirable vraies des fausses, mais, plus important, a classé en tête les effets les plus préoccupants. Il a surpassé plusieurs méthodes d’apprentissage automatique existantes sur cette tâche de classement, surtout lorsque les données étaient peu abondantes, comme c’est typique pour les nouveaux médicaments. Dans de nombreux cas où le modèle semblait « se tromper » parce qu’un effet prédit manquait dans la base curatée, le même lien médicament–symptôme apparaissait dans les rapports de sécurité du monde réel, suggérant que le modèle avait identifié des risques négligés.
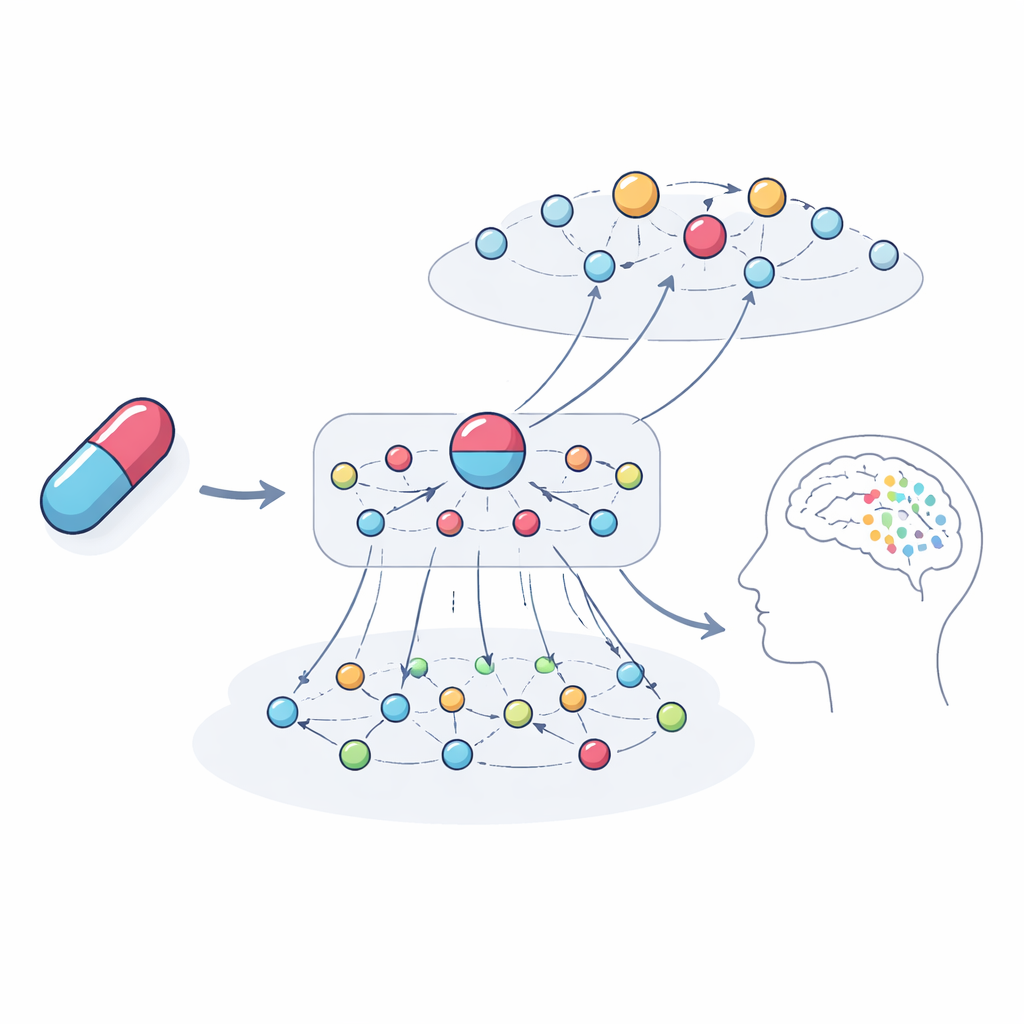
Regarder à l’intérieur de la boîte noire
Un objectif clé n’était pas seulement de prédire des problèmes mais de les expliquer. Les auteurs ont retracé les chaînes de connexions les plus influentes que le modèle utilisait pour des exemples spécifiques. Pour l’anesthésique et antidépresseur kétamine, le système a mis en évidence des réseaux de gènes et de médicaments associés pointant vers des hallucinations et la dépression comme issues potentielles. Ces chemins impliquaient des familles de gènes liées à la signalisation de la dopamine et de la sérotonine, des voies immunitaires et hormonales, et des médicaments aux cibles similaires qui ont des rapports de cas décrivant des problèmes analogues. Lorsque l’équipe a analysé les gènes mis en avant par le modèle, ils ont constaté une forte enrichissement pour des processus déjà connus pour façonner la fonction cérébrale et les symptômes psychiatriques, renforçant l’idée que les explications sont biologiquement significatives plutôt qu’arbitraires.
Ce que cela signifie pour les patients et les futurs médicaments
Concrètement, ce travail montre qu’il est possible d’utiliser des données biologiques et de sécurité existantes pour construire un système d’alerte précoce des effets indésirables liés au cerveau — et d’en comprendre les raisons. HHAN-DSI n’a pas vocation à remplacer les médecins ou les essais cliniques, mais à aider les chercheurs et les experts en sécurité à prioriser les effets indésirables potentiels à investiguer et à surveiller, en particulier pour les nouveaux médicaments peu documentés. En éclairant les voies moléculaires qui relient les médicaments aux symptômes indésirables, l’approche pourrait guider une conception de médicaments plus sûre, une surveillance plus ciblée et, finalement, une meilleure protection des patients qui dépendent de traitements agissant sur le cerveau.
Citation: Huang, T., Lin, KH., Machado-Vieira, R. et al. Explainable drug side effect prediction in central neural system via biologically informed graph neural network. Transl Psychiatry 16, 205 (2026). https://doi.org/10.1038/s41398-026-03971-1
Mots-clés: effets indésirables des médicaments, système nerveux central, réseaux de neurones graphiques, pharmacovigilance, IA explicable