Clear Sky Science · es
Predicción explicable de efectos adversos medicamentosos en el sistema nervioso central mediante una red neuronal de grafos informada biológicamente
Por qué importan los riesgos ocultos de los fármacos
Muchos medicamentos que benefician al cerebro también pueden dañarlo de forma silenciosa. Mareos, confusión, convulsiones o depresión pueden aparecer solo después de que un fármaco se use ampliamente. Las pruebas de laboratorio y clínicas tradicionales son demasiado lentas y costosas para detectar todos los problemas posibles antes de la aprobación, especialmente en el sistema nervioso central, donde los efectos secundarios pueden ser sutiles pero cambiar la vida. Este estudio presenta un nuevo modelo informático que recorre enormes conjuntos de datos biológicos para señalar pronto los efectos adversos relacionados con el cerebro y mostrar la cadena de eventos moleculares que podría causarlos.
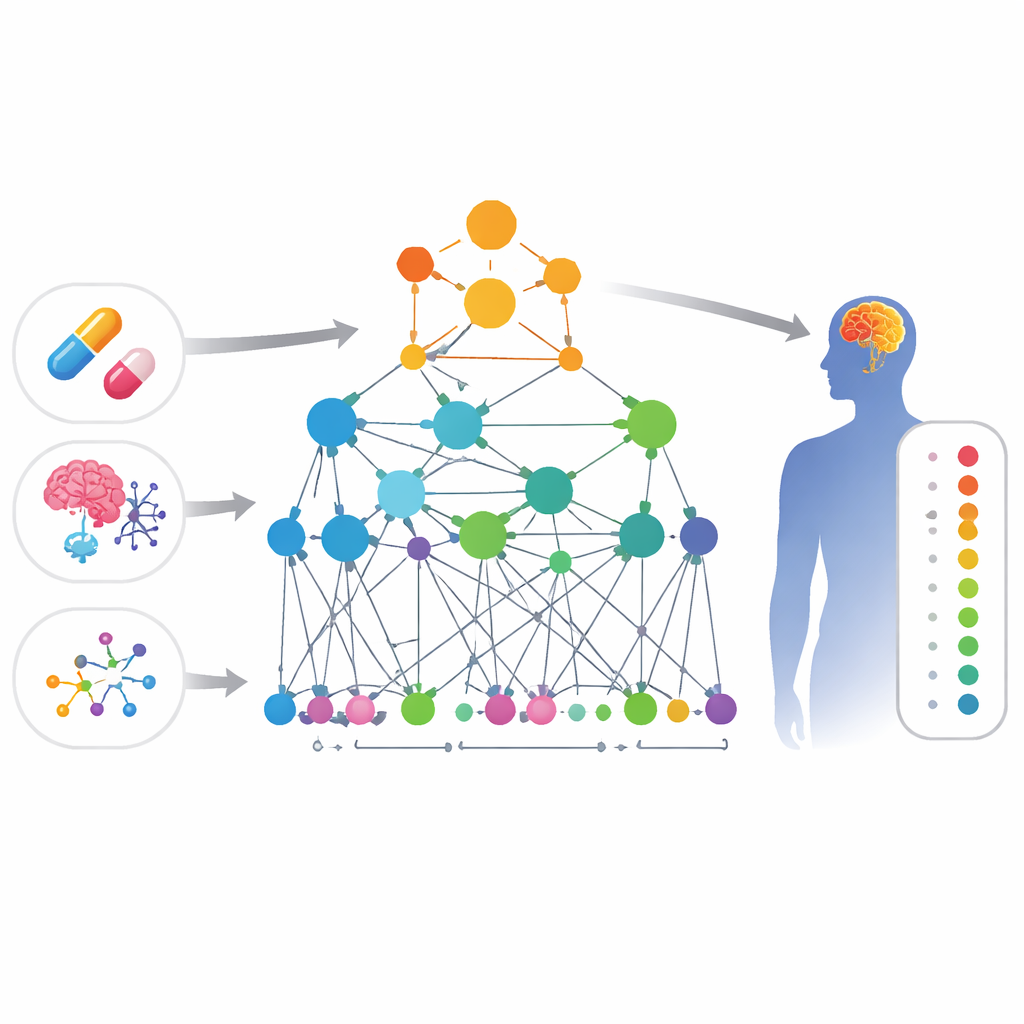
Conectando puntos entre fármacos y síntomas
Los investigadores construyeron un gran “mapa” de conocimiento biológico que enlaza cuatro tipos de entidades: fármacos, efectos adversos, genes y funciones génicas. En este mapa, cada elemento es un punto y las líneas entre puntos representan evidencias de relación —por ejemplo, dos genes que interactúan físicamente, dos fármacos con estructuras químicas similares o un fármaco conocido por causar cierto efecto adverso. Dado que las quejas relacionadas con el sistema nervioso central son a la vez frecuentes y a menudo pasadas por alto, el equipo centró este mapa en problemas cerebrales como cambios de ánimo, alteraciones del movimiento y otros síntomas neurológicos.
Una red inteligente que aprende biología
Sobre este mapa, los autores diseñaron una forma especializada de inteligencia artificial llamada red neuronal de grafos. A diferencia de un modelo estándar que ve cada fármaco de forma aislada, este enfoque analiza la red de conexiones alrededor de cada fármaco y efecto adverso. El modelo, llamado HHAN-DSI, está “informado biológicamente”: solo se le permite transmitir información a lo largo de rutas que tienen sentido biológico —por ejemplo, de un gen a otro con el que interactúa directamente, de un gen a un fármaco que lo apunta, y luego de ese fármaco a efectos adversos observados con fármacos similares. Al dar más peso a las rutas más informativas, el sistema aprende huellas matemáticas compactas para cada fármaco y cada efecto adverso, y luego puntúa la probabilidad de que cualquier par dado esté vinculado.
Poniendo el modelo a prueba
Para comprobar si estas predicciones se corresponden con la realidad, el equipo entrenó el modelo con una base de datos curada de efectos adversos reportados en la información oficial del producto y después lo probó tanto contra esa fuente como contra un conjunto separado de informes de seguridad poscomercialización. Estos informes externos capturan problemas que surgieron solo después de que los fármacos se usaran ampliamente. El modelo no solo distinguió pares fármaco‑efecto adverso verdaderos de falsos, sino que, más importante, situó los efectos más preocupantes en la parte alta de sus listas. Superó a varios métodos de aprendizaje automático existentes en esta tarea de clasificación, especialmente cuando los datos eran escasos, como suele ocurrir con medicamentos nuevos. En muchos casos en los que el modelo parecía “equivocado” porque un efecto previsto faltaba en la base de datos curada, el mismo vínculo fármaco‑síntoma apareció en los informes de seguridad del mundo real, lo que sugiere que el modelo había detectado riesgos pasados por alto.
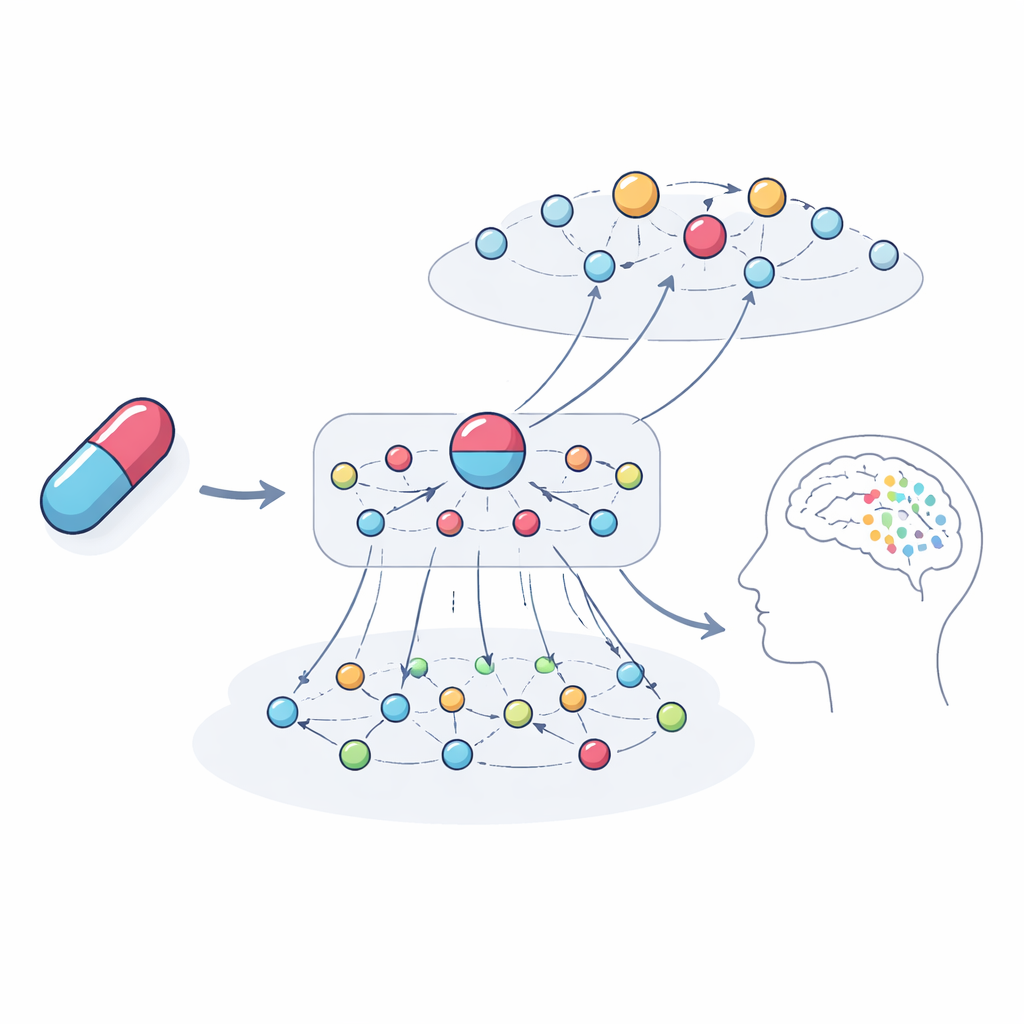
Asomarse dentro de la caja negra
Un objetivo clave no fue solo predecir problemas, sino explicarlos. Los autores trazaron las cadenas de conexiones más influyentes que el modelo utilizó en ejemplos concretos. Para el anestésico y antidepresivo ketamina, el sistema destacó redes de genes y fármacos relacionados que apuntan a alucinaciones y depresión como posibles resultados. Estas rutas implicaron familias génicas vinculadas a la señalización de dopamina y serotonina, vías inmunitarias y hormonales, y fármacos con objetivos similares que cuentan con informes de casos de problemas parecidos. Cuando el equipo analizó los genes enfatizados por el modelo, encontró que estaban fuertemente enriquecidos en procesos ya conocidos por moldear la función cerebral y los síntomas psiquiátricos, lo que refuerza que las explicaciones son biológicamente significativas y no arbitrarias.
Qué significa esto para los pacientes y los fármacos futuros
En términos sencillos, este trabajo demuestra que es posible usar datos biológicos y de seguridad existentes para construir un sistema de alerta temprana de efectos adversos relacionados con el cerebro —y para entender por qué surgen esas alertas. HHAN-DSI no pretende reemplazar a los médicos ni a los ensayos clínicos, sino ayudar a investigadores y expertos en seguridad a priorizar qué efectos adversos potenciales investigar y vigilar, especialmente para fármacos nuevos con poca experiencia directa. Al arrojar luz sobre las vías moleculares que vinculan los medicamentos con síntomas no deseados, el enfoque podría orientar un diseño de fármacos más seguro, una vigilancia más dirigida y, en última instancia, una mejor protección para los pacientes que dependen de tratamientos que actúan en el cerebro.
Cita: Huang, T., Lin, KH., Machado-Vieira, R. et al. Explainable drug side effect prediction in central neural system via biologically informed graph neural network. Transl Psychiatry 16, 205 (2026). https://doi.org/10.1038/s41398-026-03971-1
Palabras clave: efectos adversos de medicamentos, sistema nervioso central, redes neuronales de grafos, farmacovigilancia, IA explicable