Clear Sky Science · de
Erklärbare Vorhersage von Arzneimittelnebenwirkungen im zentralen Nervensystem mittels biologisch informierter Graph-Neural-Networks
Warum versteckte Arzneimittelrisiken wichtig sind
Viele Medikamente, die unserem Gehirn helfen, können ihm zugleich unbemerkt schaden. Schwindel, Verwirrung, Krampfanfälle oder Depressionen treten mitunter erst auf, nachdem ein Medikament breit eingesetzt wurde. Traditionelle Labor- und klinische Tests sind zu langsam und zu teuer, um jedes mögliche Problem vor der Zulassung zu erkennen — besonders für das zentrale Nervensystem, wo Nebenwirkungen subtil, aber lebensverändernd sein können. Diese Studie stellt ein neues Computermodell vor, das große biologische Datensätze durchforstet, um frühzeitig wahrscheinliche gehirnbezogene Nebenwirkungen zu identifizieren und die Kette molekularer Ereignisse zu zeigen, die sie verursachen könnten.
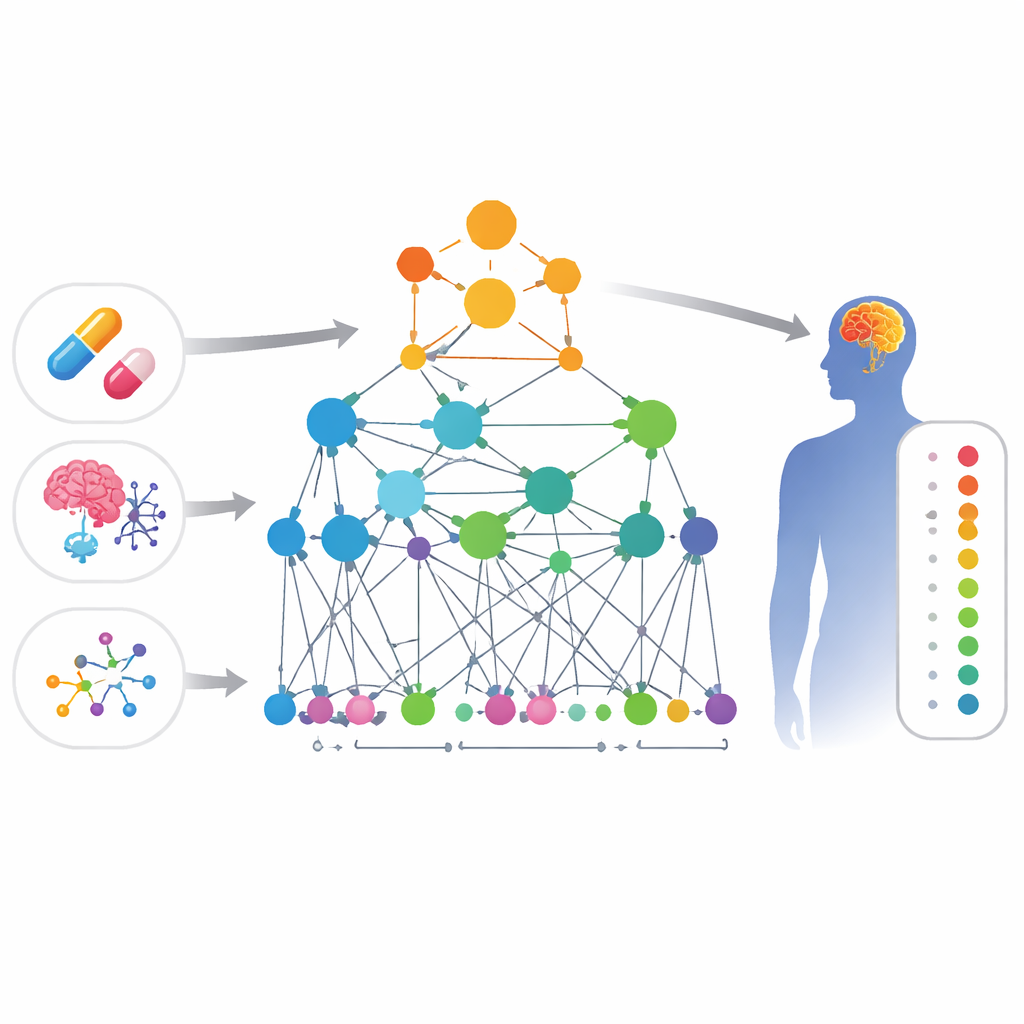
Verbindungen zwischen Medikamenten und Symptomen herstellen
Die Forschenden bauten eine umfangreiche „Karte“ biologischen Wissens, die vier Arten von Objekten verknüpft: Medikamente, Nebenwirkungen, Gene und Genfunktionen. In dieser Karte ist jedes Element ein Knoten, und Kanten zwischen Knoten stehen für Belege, dass sie zusammenhängen — etwa zwei Gene, die physisch interagieren, zwei Medikamente mit ähnlicher chemischer Struktur oder ein Medikament, das bekanntermaßen eine bestimmte Nebenwirkung verursacht. Da Beschwerden des zentralen Nervensystems sowohl häufig als auch oft übersehen werden, richtete das Team die Karte gezielt auf gehirnbezogene Probleme wie Stimmungsschwankungen, Bewegungsstörungen und andere neurologische Symptome aus.
Ein intelligentes Netzwerk, das Biologie lernt
Auf dieser Karte bauten die Autorinnen und Autoren eine spezialisierte Form künstlicher Intelligenz auf, ein Graph-Neural-Network. Im Unterschied zu einem Standardmodell, das jedes Medikament isoliert betrachtet, berücksichtigt dieser Ansatz das Netzwerk von Verbindungen um jedes Medikament und jede Nebenwirkung. Das Modell, HHAN-DSI genannt, ist „biologisch informiert“: Es darf Informationen nur entlang biologisch sinnvoller Pfade weitergeben — etwa von einem Gen zu einem direkt interagierenden Gen, von einem Gen zu einem Medikament, das es anvisiert, und weiter von diesem Medikament zu Nebenwirkungen, die bei ähnlichen Medikamenten beobachtet wurden. Indem es den informativsten Pfaden mehr Gewicht gibt, lernt das System kompakte mathematische Fingerabdrücke für jedes Medikament und jede Nebenwirkung und bewertet dann, wie wahrscheinlich eine Verbindung zwischen einem bestimmten Paar ist.
Das Modell auf die Probe stellen
Um zu prüfen, ob diese Vorhersagen mit der Realität übereinstimmen, trainierte das Team das Modell auf einer kuratierten Datenbank mit in offiziellen Produkthinweisen berichteten Nebenwirkungen und testete es anschließend sowohl gegen diese Quelle als auch gegen eine separate Sammlung von Sicherheitsberichten aus der Post‑Marketing‑Phase. Diese externen Berichte erfassen Probleme, die erst nach breiter Anwendung der Medikamente auftraten. Das Modell unterschied nicht nur echte Arzneimittel–Nebenwirkungs‑Paare von falschen, sondern sortierte vor allem die besorgniserregendsten Effekte weit oben in seinen Listen ein. Es schlug mehrere bestehende Methoden des maschinellen Lernens bei dieser Rangfolge, insbesondere wenn die Daten dünn sind, wie es bei neuen Medikamenten typisch ist. In vielen Fällen, in denen das Modell „falsch“ schien, weil eine vorhergesagte Nebenwirkung in der kuratierten Datenbank fehlte, fand sich derselbe Medikament–Symptom‑Zusammenhang in den realen Sicherheitsberichten, was darauf hindeutet, dass das Modell übersehene Risiken aufgespürt hatte.
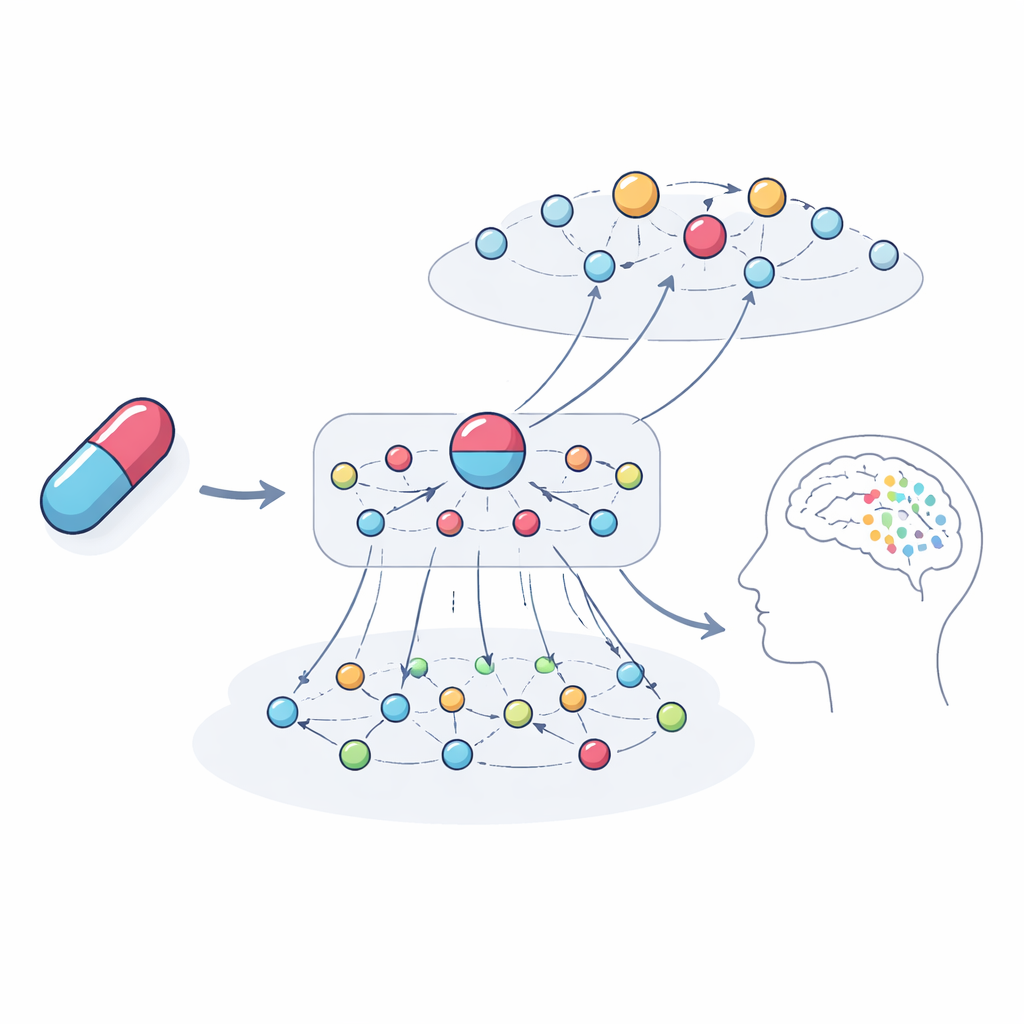
Ins Innere der Black Box schauen
Ein zentrales Ziel war nicht nur, Probleme vorherzusagen, sondern sie zu erklären. Die Autorinnen und Autoren verfolgten die einflussreichsten Verbindungswege, die das Modell für konkrete Beispiele nutzte. Beim Anästhetikum und Antidepressivum Ketamin hob das System Netzwerke von Genen und verwandten Medikamenten hervor, die auf Halluzinationen und Depressionen als mögliche Folgen hinweisen. Diese Pfade betrafen Genfamilien, die mit Dopamin- und Serotonin‑Signalübertragung, Immun- und Hormonwegen verknüpft sind, sowie Medikamente mit ähnlichen Zielstrukturen, zu denen Fallberichte über vergleichbare Probleme vorliegen. Bei der Analyse der vom Modell betonten Gene zeigte sich eine starke Anreicherung für Prozesse, die bereits als prägend für Gehirnfunktion und psychiatrische Symptome bekannt sind, was die biologische Plausibilität der Erklärungen untermauert statt sie willkürlich erscheinen zu lassen.
Was das für Patientinnen, Patienten und zukünftige Medikamente bedeutet
Einfach gesagt zeigt diese Arbeit, dass sich vorhandene biologische und Sicherheitsdaten nutzen lassen, um ein Frühwarnsystem für gehirnbezogene Nebenwirkungen zu bauen — und zu verstehen, warum solche Warnungen entstehen. HHAN-DSI soll nicht Ärztinnen, Ärzte oder klinische Studien ersetzen, sondern Forschende und Sicherheitsexperten dabei unterstützen, welche potenziellen Nebenwirkungen sie priorisieren und überwachen sollten, besonders bei neuen Medikamenten mit wenig direkter Erfahrung. Indem die Methode die molekularen Pfade beleuchtet, die Medikamente mit unerwünschten Symptomen verknüpfen, kann sie sicherere Wirkstoffentwicklung, gezieltere Überwachung und letztlich besseren Schutz für Patientinnen und Patienten fördern, die auf Behandlungen angewiesen sind, die im Gehirn wirken.
Zitation: Huang, T., Lin, KH., Machado-Vieira, R. et al. Explainable drug side effect prediction in central neural system via biologically informed graph neural network. Transl Psychiatry 16, 205 (2026). https://doi.org/10.1038/s41398-026-03971-1
Schlüsselwörter: Arzneimittelnebenwirkungen, zentrales Nervensystem, Graph-Neural-Networks, Pharmakovigilanz, erklärbare KI