Clear Sky Science · es
Vigilancia genómica a escala continental del paludismo por Plasmodium falciparum en el África subsahariana mediante secuenciación rápida por nanoporo
Por qué los genes del paludismo importan en la vida cotidiana
El paludismo todavía mata a cientos de miles de personas cada año en el África subsahariana, y el parásito está aprendiendo nuevas estrategias para eludir nuestras pruebas y medicinas. Este estudio muestra cómo científicos y equipos locales de salud pueden leer rápidamente el código genético del parásito en laboratorios africanos ordinarios, de modo que los países puedan ver casi en tiempo real dónde el paludismo se vuelve más difícil de diagnosticar y tratar.
Problemas crecientes para las pruebas y los tratamientos
El parásito más letal, Plasmodium falciparum, está mostrando resistencia contra dos de nuestras herramientas principales. Algunas cepas han perdido genes llamados hrp2 y hrp3, lo que hace que las pruebas rápidas estándar puedan no detectar infecciones. Otras portan cambios en un gen conocido como kelch13, asociados a una eliminación más lenta del parásito tras el tratamiento con los fármacos de primera línea actuales. Estas variantes preocupantes se han ido propagando por el este, centro y sur de África. Las agencias de salud están considerando cambiar el tipo de pruebas o rotar combinaciones de fármacos, pero necesitan información detallada y oportuna sobre qué cepas del parásito circulan en cada lugar.
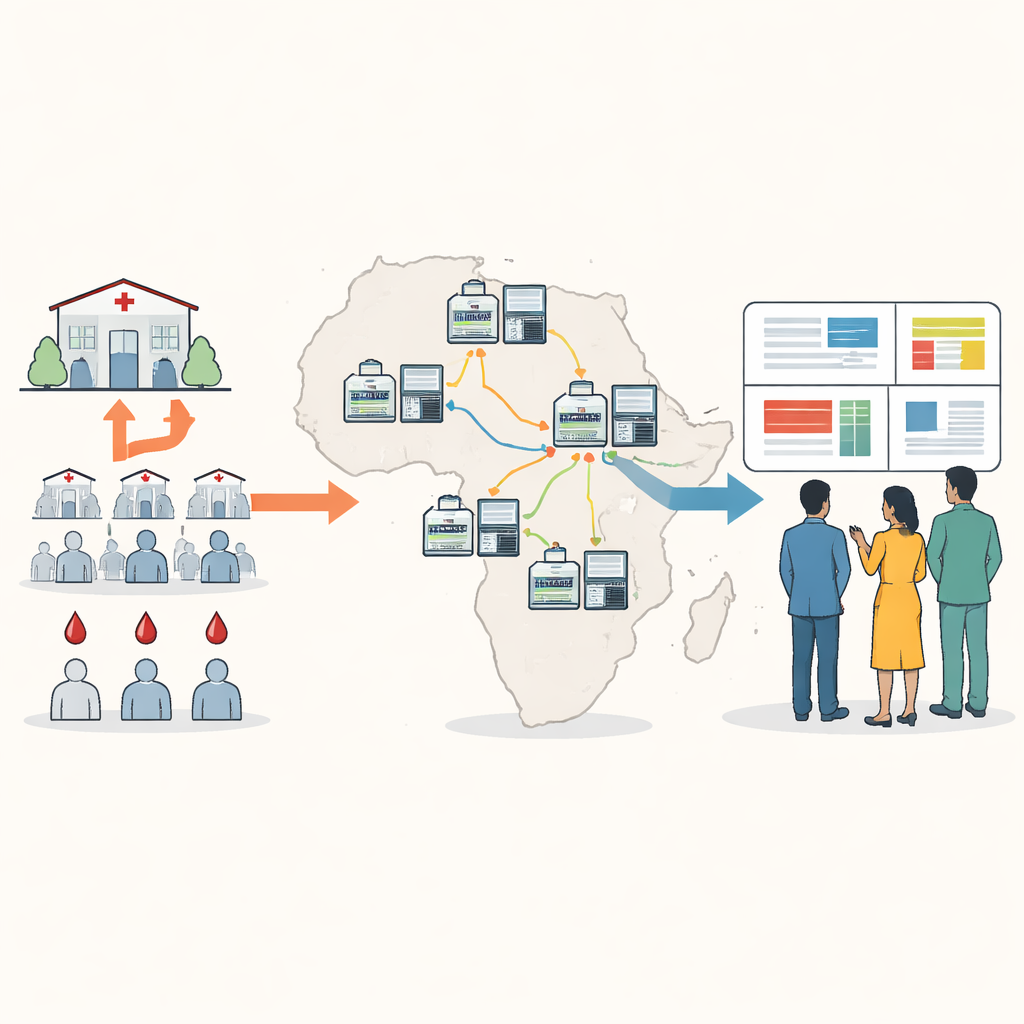
Acercar el seguimiento genético a los pacientes
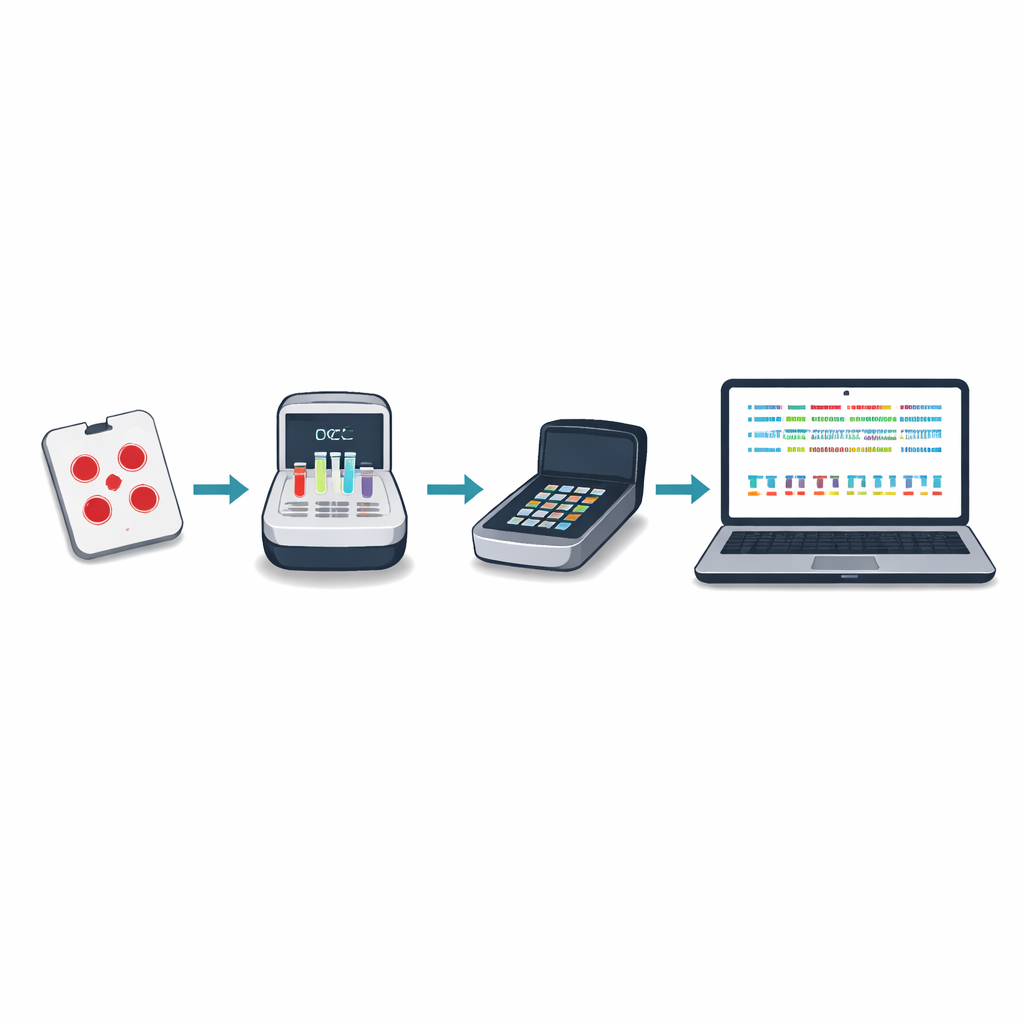
La secuenciación tradicional de ADN para el paludismo a menudo requiere enviar muestras de sangre al extranjero o a unos pocos centros regionales grandes, lo que puede ser lento, costoso y estar desconectado de la toma de decisiones local. Los autores diseñaron un enfoque nuevo alrededor de un pequeño dispositivo portátil conocido como secuenciador de nanoporo. Usando puntos de sangre seca tomados en las pruebas rutinarias de paludismo, el personal local puede amplificar y secuenciar genes clave del parásito en unas cinco horas, a un coste inferior a veinticinco dólares por muestra. El nuevo “panel mínimo viable” se centra en diez regiones genéticas que revelan resistencia a fármacos, la presencia o ausencia de hrp2 y hrp3, cambios relevantes para vacunas y cuántas cepas diferentes del parásito están presentes en una sola infección.
Software sencillo en un portátil corriente
Para que el método sea usable en lugares con internet y potencia informática limitados, el equipo creó un paquete de software llamado Nomadic. Se ejecuta en el mismo portátil que controla el secuenciador y funciona totalmente sin conexión. A medida que avanza la secuenciación, el programa asigna cada lectura al genoma del parásito, verifica la calidad y marca mutaciones importantes, todo mientras muestra gráficos intuitivos en un panel local. El software también genera archivos resumen compactos que son fáciles de compartir por correo electrónico o conexiones lentas, permitiendo a los socios combinar resultados de muchos sitios sin mover grandes archivos de datos crudos.
Prueba del sistema en todo África
Entre 2024 y 2025, laboratorios en seis países africanos usaron el protocolo para secuenciar y analizar más de mil muestras de paludismo, la mayoría procesadas localmente por 13 científicos con distintos niveles de experiencia previa. El método produjo una cobertura sólida y coherente de los genes objetivo a lo largo de una amplia gama de niveles de parásitos en sangre. Una nueva herramienta de llamada de variantes, llamada Delve, pudo detectar de forma fiable cambios genéticos presentes en cepas menores del parásito que constituían tan solo el cinco a diez por ciento de una infección, un nivel que las herramientas estándar a menudo no detectan. Las mismas corridas de secuenciación también identificaron correctamente casi todas las deleciones en los genes hrp2 y hrp3 al compararlas con métodos de laboratorio convencionales, y en algunas infecciones mixtas detectaron deleciones que las pruebas estándar pasaron por alto.
Qué significa esto para la lucha contra el paludismo
Este trabajo demuestra que la vigilancia genética de alta calidad del paludismo no tiene por qué limitarse a centros de alta tecnología distantes. Al emparejar un protocolo de laboratorio asequible y simplificado con análisis en portátiles, los laboratorios de salud pública ordinarios pueden rastrear marcadores de resistencia a fármacos y parásitos que evaden los diagnósticos casi en tiempo real. Aunque otros métodos siguen siendo más adecuados para algunas tareas especializadas, este enfoque está bien adaptado a la necesidad urgente de información práctica y rápida para guiar la elección de pruebas y las políticas de tratamiento en el África subsahariana.
Cita: Mwenda, M., Mosler, K., Bohmeier, B. et al. Continental-scale genomic surveillance of Plasmodium falciparum malaria across sub-Saharan Africa with rapid nanopore sequencing. Nat Commun 17, 4218 (2026). https://doi.org/10.1038/s41467-026-72358-z
Palabras clave: paludismo, vigilancia genómica, resistencia a fármacos, secuenciación por nanoporo, África subsahariana