Clear Sky Science · es
La quinasa dependiente de Dbf4 ajusta finamente la función de Ino80 en los orígenes de replicación cromosómica
Por qué esto importa para nuestro ADN
Cada vez que una célula se divide, debe copiar todo su ADN sin errores importantes. Fallos en este paso de copiado pueden desestabilizar el genoma y están estrechamente vinculados al cáncer. Este estudio revela cómo una enzima clave del ciclo celular no solo activa la maquinaria de replicación del ADN, sino que también ordena el empaquetamiento local del ADN para que la replicación pueda iniciarse sin tropiezos y reanudarse bajo estrés. 
Un semáforo para arrancar la copia del ADN
Las células dependen de «orígenes» especializados a lo largo de los cromosomas donde comienza la replicación del ADN. Un par de enzimas bien conocido, la quinasa dependiente de Dbf4 (DDK), ayuda a arrancar este proceso modificando la máquina central que desenrolla el ADN, la helicasa. Hasta ahora solo se conocían unos pocos blancos directos de DDK, lo que dejaba gran parte de su papel enigmático. Los autores se propusieron cartografiar, a escala global, qué proteínas nucleares dependen de DDK para su fosforilación—una marca química que a menudo actúa como interruptor de encendido/apagado para la función proteica.
Escaneando el núcleo en busca de los socios ocultos de DDK
Para ello, los investigadores usaron la levadura por gemación como modelo y combinaron dos estrategias complementarias para reducir la actividad de DDK en células vivas: un mutante termossensible de su subunidad catalítica y un estrés de replicación inducido por fármaco que bloquea indirectamente la acción de DDK. A continuación aislaron núcleos y emplearon espectrometría de masas para catalogar miles de fragmentos proteicos fosforilados, comparando muestras con DDK activo frente a inhibido. Al centrarse en los sitios que disminuyeron en ambos contextos de inhibición, construyeron una lista de alta confianza de alrededor de 400 blancos dependientes de DDK. Muchas de estas proteínas están unidas a la cromatina, el material ADN–proteína que organiza el genoma, lo que sugiere que DDK tiene un papel más amplio en modelar el paisaje físico donde ocurre la replicación.
Una máquina de remodelación afinada por una pequeña cola proteica
Entre los hallazgos más fuertes estuvo Arp8, parte de una gran máquina remodeladora de cromatina llamada complejo INO80. Se sabe que INO80 reposiciona nucleosomas—estructuras en forma de cuentas de ADN enrollado alrededor de proteínas histonas—y que los organiza en arreglos regulares alrededor de los orígenes de replicación. El equipo demostró bioquímicamente que DDK fosforila directamente dos serinas específicas en una cola no estructurada de Arp8. Cuando reemplazaron esas serinas por alaninas, que no pueden fosforilarse, la composición global de INO80 se mantuvo intacta, pero su arquitectura interna cambió: experimentos de entrecruzamiento revelaron contactos debilitados entre módulos clave del complejo. En términos funcionales, el INO80 mutante consumía ATP mucho más despacio y era notablemente peor deslizando nucleosomas a nuevas posiciones, aunque aún podía unirse al ADN y a los nucleosomas, a veces incluso con mayor afinidad que lo normal.
De la separación local al éxito global de la replicación
Para conectar estos defectos moleculares con el comportamiento cromosómico, los autores reconstruyeron la cromatina in vitro sobre una biblioteca de fragmentos de ADN de levadura que contenía cientos de orígenes de replicación. Con INO80 normal y el complejo de reconocimiento de orígenes presentes, observaron arreglos de nucleosomas ordenadamente espaciados flanqueando una brecha libre de nucleosomas en cada origen. En contraste, el mutante de Arp8 produjo arreglos menos precisos con distancias de enlace entre nucleosomas alteradas. Usando un sistema de replicación totalmente reconstituido, encontraron que la cromatina ensamblada con INO80 mutante soportaba una iniciación más débil en los orígenes, aunque el crecimiento de las trazas de replicación individuales que sí se iniciaron era similar. En levaduras vivas que llevaban las mismas mutaciones en Arp8, la entrada en la síntesis de ADN tras un arresto del ciclo celular se retardó, aumentaron los eventos de recombinación espontánea y las células fueron especialmente sensibles a la hidroxiurea, un fármaco que agota los bloques de construcción del ADN y detiene la replicación. Sin embargo, la expresión génica global, incluida la de genes del ciclo celular y de replicación, permaneció en gran medida sin cambios, lo que indica que el problema principal radica en la arquitectura de la cromatina en los orígenes más que en la cantidad de factores de replicación que se producen. 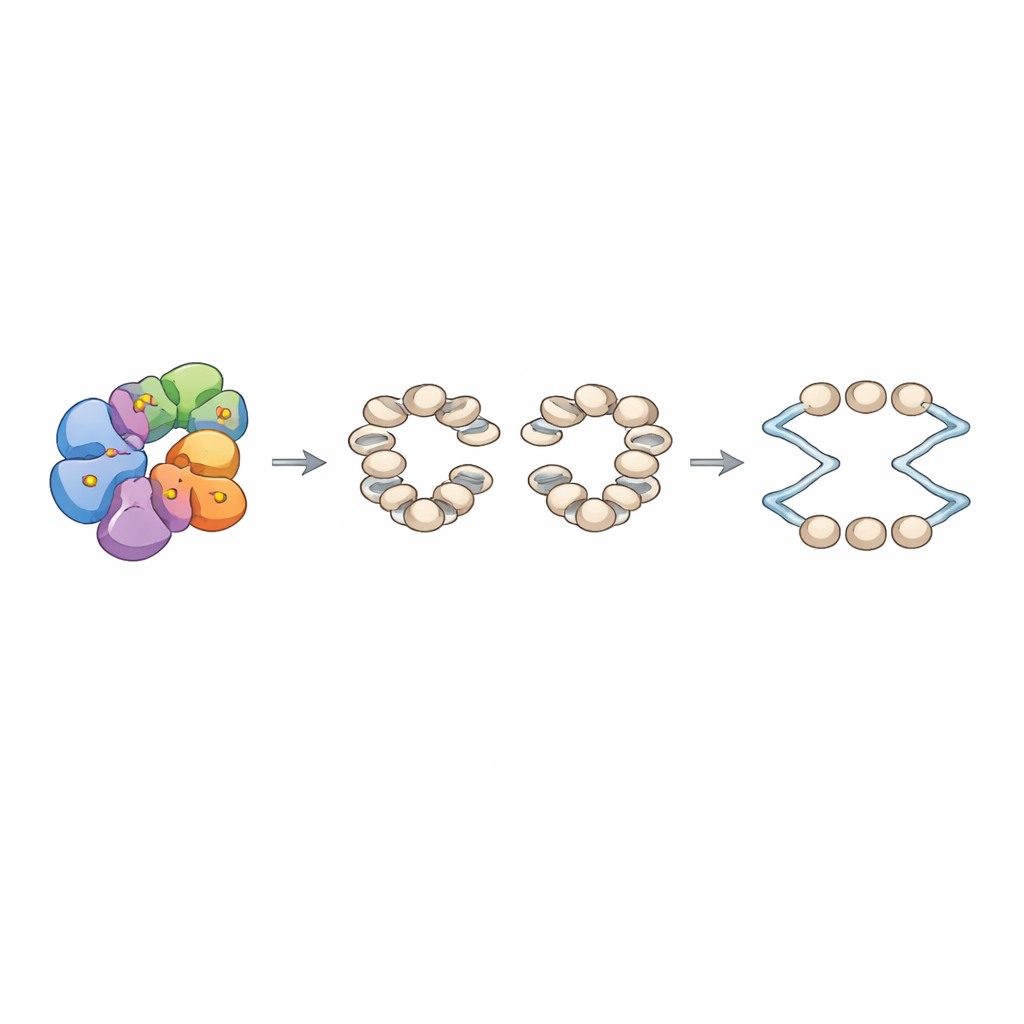
Cómo el empaquetamiento cuidadoso del ADN protege nuestros genomas
En conjunto, el trabajo revela que DDK hace más que accionar la maquinaria central de replicación. Al fosforilar Arp8, ajusta finamente el remodelador INO80 para que los nucleosomas alrededor de los orígenes de replicación estén espaciados de forma adecuada. Este empaquetamiento ordenado parece ser una puerta de control para un inicio eficiente de los orígenes y para la reanudación segura de las horquillas de replicación detenidas bajo estrés. En términos prácticos, el estudio muestra que la forma en que el ADN está envuelto y dispuesto no es solo un obstáculo que la replicación debe superar: es una característica activa y regulada que ayuda a determinar cuándo y dónde empieza la replicación, con implicaciones directas para el mantenimiento de la estabilidad genómica.
Cita: Bansal, P., Lahiri, S., Kumar, C.N. et al. Dbf4-dependent kinase finetunes Ino80 function at chromosome replication origins. Nat Commun 17, 3029 (2026). https://doi.org/10.1038/s41467-026-70698-4
Palabras clave: Replicación del ADN, remodelación de la cromatina, quinasa del ciclo celular, estabilidad genómica, modelo de levadura