Clear Sky Science · es
Identificación de eventos de intercambio de isoformas vinculados con la supervivencia de pacientes con adenocarcinoma esofágico informa sobre nuevos objetivos pronósticos y terapéuticos
Por qué importa esta investigación
El adenocarcinoma esofágico es un tipo de cáncer del conducto alimentario cuya incidencia está aumentando y que, pese a ello, mantiene una tasa de supervivencia muy baja. Las pruebas de cribado actuales con frecuencia no detectan a las personas en riesgo, y los tratamientos estándar como la quimioterapia y la cirugía solo benefician a una fracción de los pacientes. Este estudio plantea una pregunta novedosa: en lugar de fijarse únicamente en qué genes están activados o desactivados en los tumores, ¿y si miramos con más detalle qué versiones de esos genes se están utilizando? Al centrarse en estas versiones «cambiadas», los investigadores descubren nuevas señales de mal pronóstico y señalan estrategias terapéuticas potenciales que podrían ahorrar daño a las células sanas.
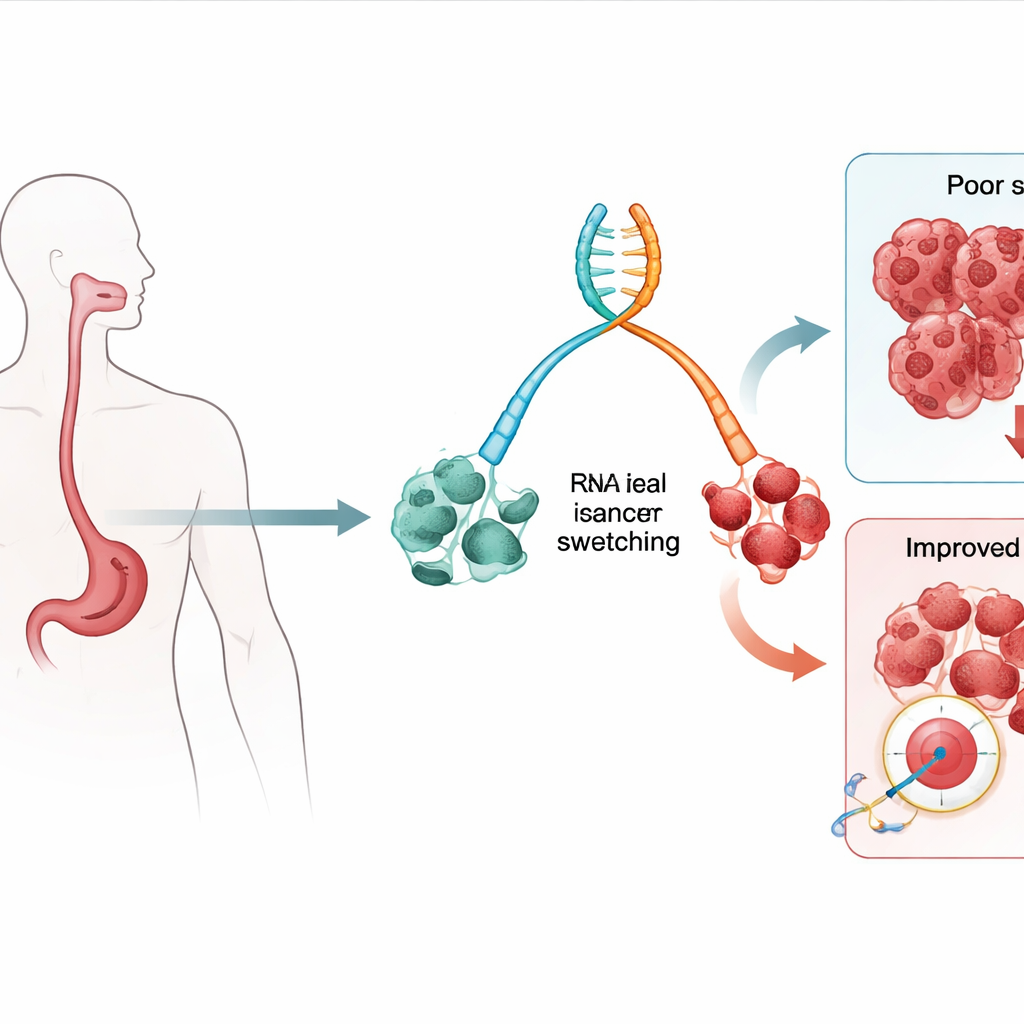
Desplazamientos en los mensajes génicos como señales de alerta temprana
Nuestros genes pueden producir múltiples mensajes ligeramente distintos, conocidos como isoformas, a partir de la misma secuencia de ADN. El equipo analizó el ARN, la molécula que porta esos mensajes, en muestras de tejido tomadas de personas con esófago de Barrett (una lesión precancerosa conocida) y de quienes ya habían desarrollado adenocarcinoma esofágico. Buscaron «cambios de isoforma», donde una versión de un gen se vuelve más común y otra menos común a medida que el tejido progresa de Barrett de bajo riesgo a enfermedad de alto riesgo y cáncer. Utilizando modelos estadísticos que relacionan esos cambios con los resultados de los pacientes, identificaron docenas de isoformas cuya presencia o ausencia se asociaba con mayores probabilidades de muerte por todas las causas y por cáncer específicamente.
Dos versiones génicas que presagian problemas
Entre las muchas isoformas detectadas, dos destacaron: versiones particulares de los genes denominados TTLL12 y HM13. Estas versiones específicas eran más frecuentes en lesiones precancerosas de alto grado y en cánceres que en el tejido de Barrett de bajo grado, y los pacientes cuyos tumores dependían en gran medida de estas isoformas tendían a presentar peor supervivencia. Es importante: los niveles totales de los genes TTLL12 y HM13 no contaban toda la historia; fue el cambio hacia estas isoformas concretas lo que transmitió la señal de advertencia. Los investigadores confirmaron estos patrones no solo en muestras de pacientes, sino también en un modelo de rata de cáncer esofágico impulsado por reflujo y en un conjunto de datos humanos independiente, lo que sugiere que los hallazgos son robustos y biológicamente relevantes.
Convertir las isoformas perjudiciales contra el cáncer
Para comprobar si estas isoformas son meros marcadores o verdaderos impulsores de la enfermedad, los científicos utilizaron pequeñas herramientas de ARN para silenciar selectivamente las versiones de riesgo de TTLL12 y HM13 en dos líneas celulares de cáncer esofágico cultivadas en el laboratorio. Bloquear cualquiera de las isoformas redujo drásticamente el crecimiento de las células cancerosas y ralentizó su capacidad de migrar —un paso clave en la diseminación— mientras que tuvo solo efectos menores sobre las células esofágicas normales. Aún más llamativo, cuando las isoformas fueron silenciadas, los fármacos de quimioterapia estándar (paclitaxel y carboplatino) se volvieron más eficaces, actuando de forma sinérgica con la inhibición para matar a muchas más células cancerosas que cada enfoque por separado.
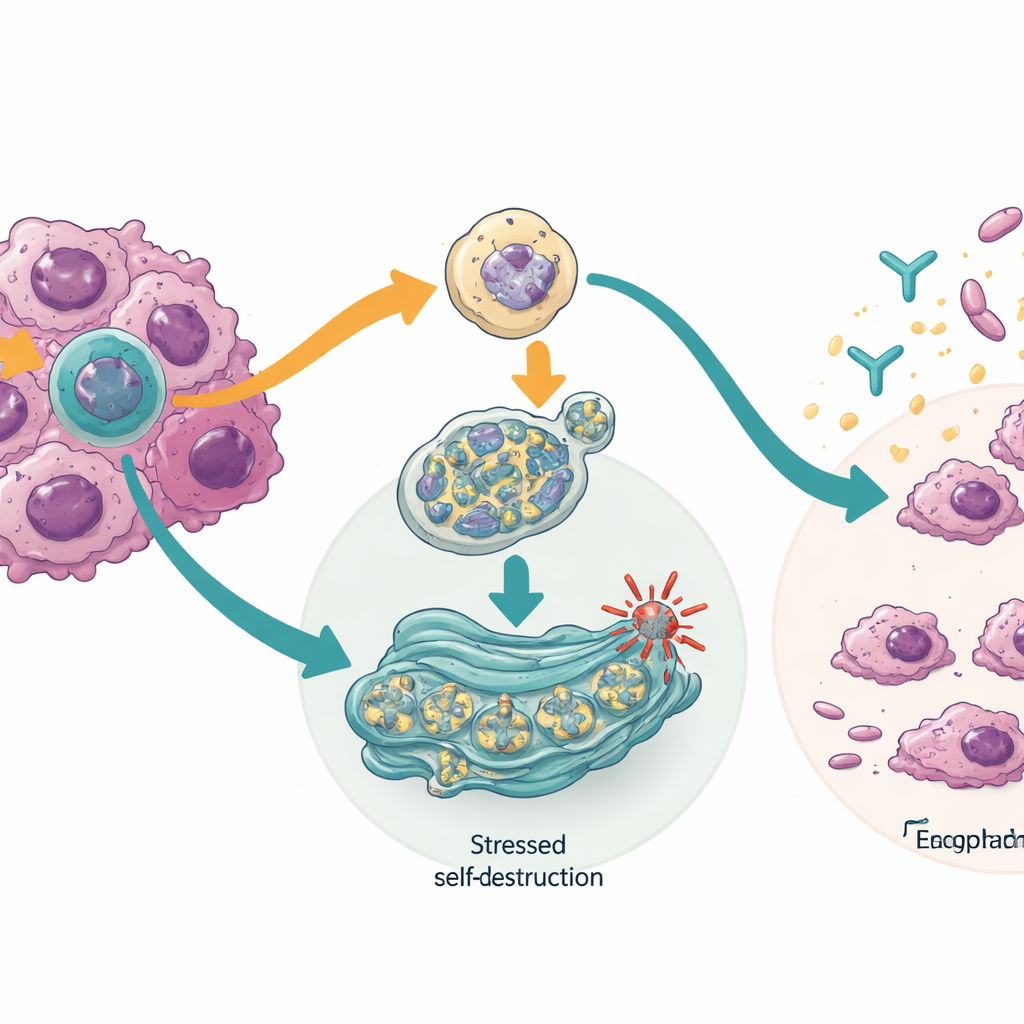
Cómo se empuja a las células cancerosas hacia la autodestrucción
Al investigar el mecanismo, el equipo encontró que bloquear la isoforma de TTLL12 activó un sistema de control de calidad dentro de las células llamado autofagia mediada por chaperonas. Este sistema ayuda a descomponer proteínas dañadas o peligrosas. En las células cancerosas, su activación redujo los niveles de proteínas que ayudan a los tumores a sobrevivir al daño del ADN, incluidos CHK1 y formas mutantes del conocido gen guardián TP53. Bloquear la isoforma de HM13, en cambio, estresó la fábrica de plegado de proteínas de la célula, el retículo endoplásmico, activando una vía de respuesta que puede detener la producción de proteínas, activar el reciclado de componentes celulares defectuosos y, en última instancia, llevar a la célula a la muerte programada. En algunas células cancerosas, este mismo cambio también las hizo más vulnerables a un fármaco inmunoterapéutico dirigido a PD-L1, lo que sugiere que el intercambio de isoformas puede ayudar a los tumores a ocultarse del sistema inmunitario.
Qué podría significar esto para los pacientes
En conjunto, estos hallazgos sugieren que prestar atención a qué isoformas utiliza un tumor podría mejorar la forma en que los médicos predicen quién tiene mayor riesgo y quién podría responder mejor a ciertos tratamientos. Las versiones específicas de TTLL12 y HM13 destacadas aquí hacen más que señalar peligro; parecen ayudar a las células cancerosas a sobrevivir, moverse y resistir la terapia, pero pueden ser atacadas sin apenas dañar las células esofágicas normales en el laboratorio. Aunque este trabajo aún está en una fase experimental temprana y se necesitan estudios más amplios en pacientes, abre la puerta a futuras pruebas que rastreen patrones de isoformas y al desarrollo de nuevos fármacos o terapias basadas en ARN diseñadas para apagar selectivamente las versiones génicas más dañinas en el cáncer esofágico.
Cita: Zhang, Y., Ntsiful, D.A., Israel, R. et al. Identification of isoform switching events linked with esophageal adenocarcinoma patient survival informs novel prognostic and therapeutic targets. Cell Death Dis 17, 305 (2026). https://doi.org/10.1038/s41419-026-08542-2
Palabras clave: cáncer de esófago, esófago de Barrett, isoformas de ARN, terapia dirigida, autofagia