Clear Sky Science · zh
MechFind:一种用于从头预测酶催化机制的计算框架
理解酶为什么重要
每个生物细胞都依赖称为酶的小型分子机器运转。这些蛋白质加速驱动我们身体、促进作物生长并制造药物的化学反应。尽管我们对数以万计的酶促反应的总体“前后”化学已知,但关于它们如何从起始物到最终产物逐步运作的确切步骤我们却很少知道。本文介绍了 MechFind —— 一个能够仅凭基本化学信息自动提出详细酶反应步骤的计算框架,帮助科学家为医学、工业和可持续化学设计更好的酶。
从缺失步骤到数字侦探
大多数生物化学数据库列出酶促反应的输入和输出,但并不记录中间的断键与成键序列。文献中带有完整机制注释的反应不到一千个,留下了巨大的“机制缺口”。先前的计算工具试图填补这一空白,但通常需要酶的详细三维结构或提前知道蛋白中哪些氨基酸参与化学反应,从而大大限制了其适用范围。MechFind 以不同的方式解决该问题:它忽略完整的三维蛋白结构,而专注于小的化学片段如何重排,使其能够应用于任何已知输入和输出分子的反应。
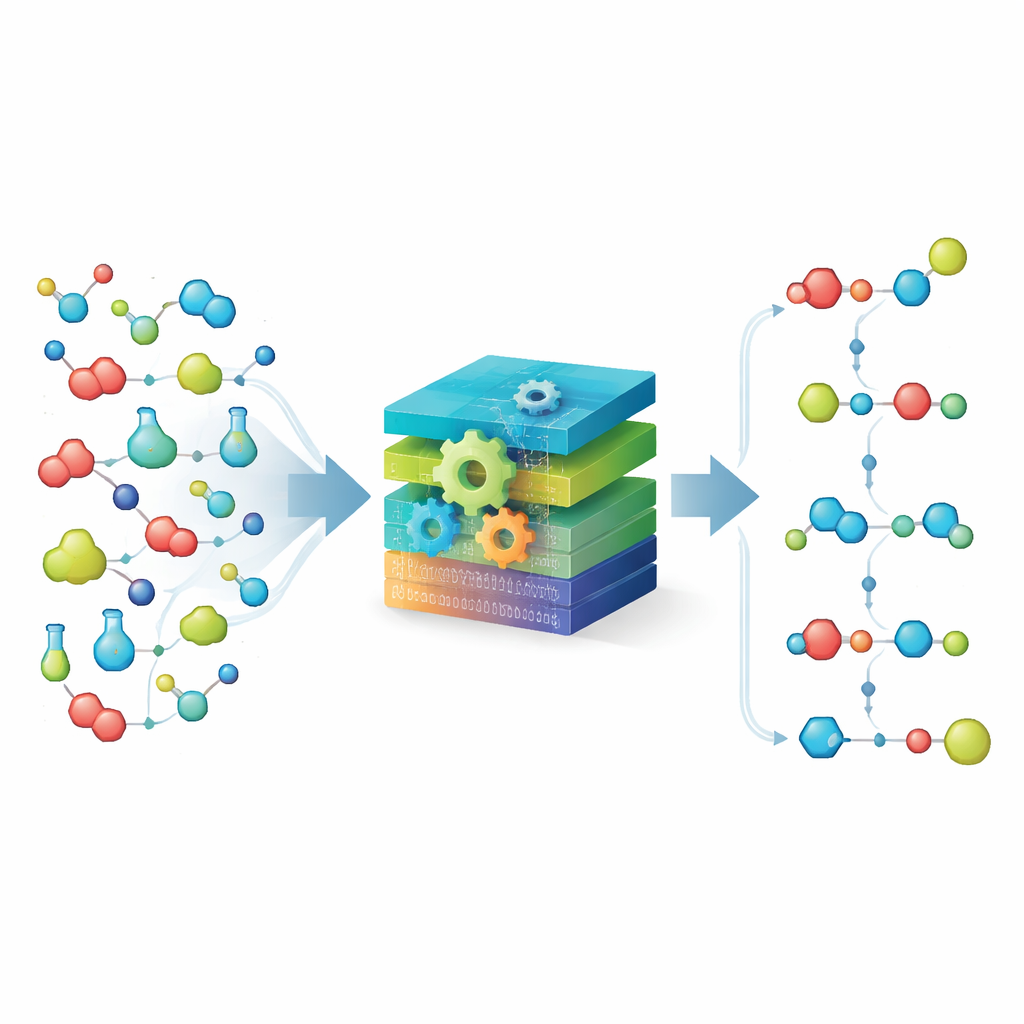
将化学分解为简单构件
MechFind 的核心是基于“官能基片段”(moiety)的化学视角。该方法并不跟踪完整分子,而是根据每个原子的直接邻居将分子分解为带标签的微小片段,然后将任意反应表示为这些片段的获得与丧失。利用大量经过整理的已知酶学步骤,MechFind 组装出能整体重现该反应的小片段变化链。它偏好最简单的解释,搜索尽可能少步骤的机制,并强制保持原子与电荷的严格守恒,确保过程中没有物质或电荷非法出现或消失。
检验准确性并发现新路径
为了判断预测是否合理,作者首先在数百个已在可信数据库中记录有机制的反应上测试了 MechFind。仅使用起始与结束分子作为输入,MechFind 在近三分之二的案例中将公认机制排在首位,并在85%的案例中将其列入前十名。随后,团队用六个最近发表且系统未见过的酶机制对该系统发起挑战。MechFind 仍在其主要候选中识别出正确的步骤序列,常常通过重用来自不相关物种的化学模式实现,例如用最初从酵母或植物酶学习到的步骤构建人类酶的机制。
扩展到数万条反应
在验证其准确性之后,作者将 MechFind 应用于两大生化反应集合,涵盖近 38,000 个不同反应。在每个数据库中超过一半的反应,工具至少生成了一个合理的多步机制,常常提出多达十条替代路径。这一工作产生了超过18,000条新的机制性假设,使得带有详细步骤建议的反应数量增长了十倍以上。与此同时,大规模测试也指出了该方法目前的局限性——要么在分配的计算时间内优化变得过于复杂,要么所需的片段类型在训练数据中从未出现过。
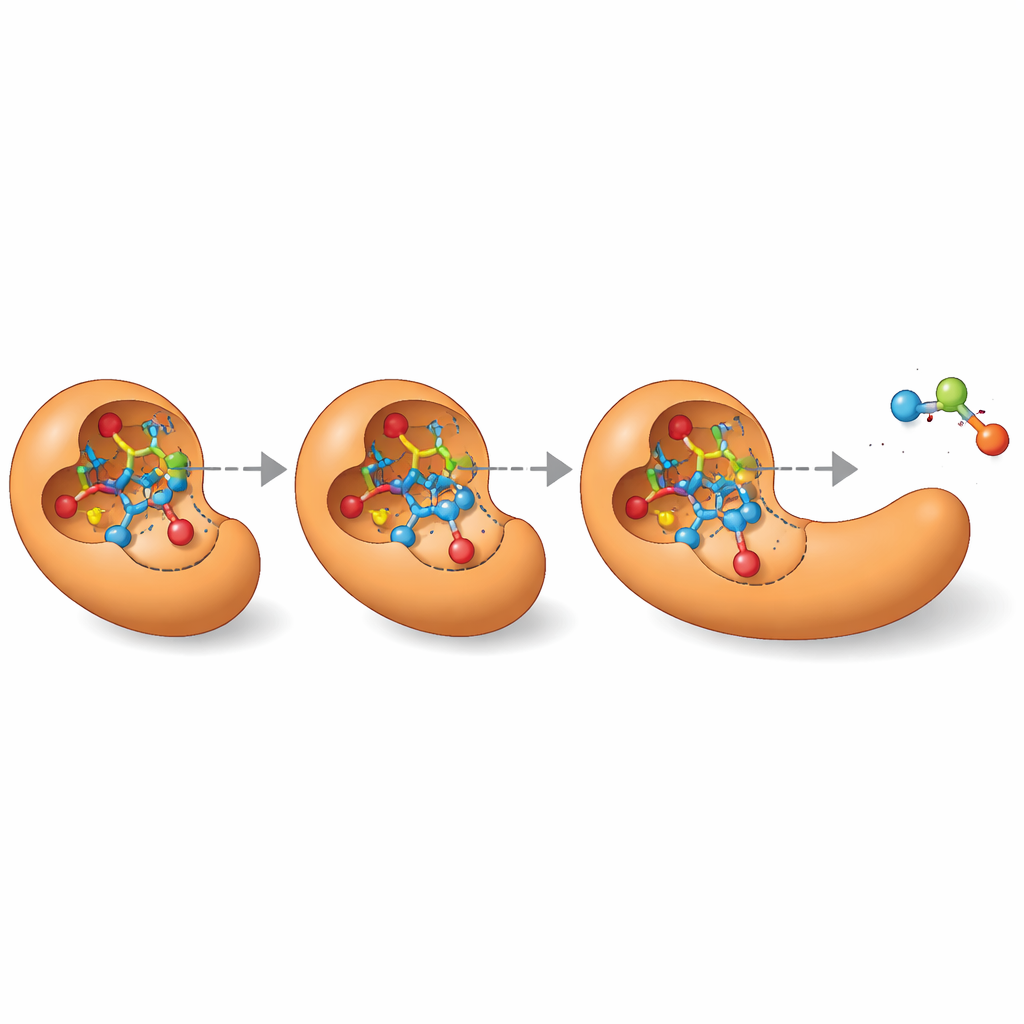
为酶设计打开新门
除了列出单一的“最佳猜测”外,MechFind 还能绘制出酶在给定反应中可能采用的不同可行路线的完整网络。这种备选路线的景观对从头设计新酶尤其有价值。现代蛋白质设计工具需要关于反应通过的短暂过渡态的精确三维图像。通过阐明逐步机制,MechFind 直接指向那些关键中间体和过渡态,将诸如“构建一种酯酶”之类的模糊设计目标转化为诸如“稳定这个特定的高能构象”之类的具体靶标。尽管其预测仍需专家审查以及后续计算或实验验证,MechFind 实质性地扩展了我们关于可能酶化学的目录,并为更系统、基于数据的酶工程绘出了一条可行路径。
引用: Hartley, A.D., Upadhyay, V., Boorla, V.S. et al. MechFind: a computational framework for de novo prediction of enzyme mechanisms. Nat Commun 17, 3903 (2026). https://doi.org/10.1038/s41467-026-71957-0
关键词: 酶的作用机制, 计算生物化学, 酶设计, 代谢反应, 反应预测