Clear Sky Science · fr
MechFind : un cadre computationnel pour la prédiction de novo des mécanismes enzymatiques
Pourquoi comprendre les enzymes est important
Chaque cellule vivante fonctionne grâce à de petites machines moléculaires appelées enzymes. Ces protéines accélèrent les réactions chimiques qui alimentent nos organismes, font pousser les cultures et permettent la fabrication de médicaments. Si nous connaissons la chimie globale « avant et après » de dizaines de milliers de réactions enzymatiques, nous ignorons souvent les mouvements exacts étape par étape qu'elles utilisent pour passer des réactifs aux produits finaux. Cet article présente MechFind, un cadre informatique capable de proposer automatiquement des étapes détaillées de réactions enzymatiques en n'utilisant que des informations chimiques de base, aidant ainsi les scientifiques à concevoir de meilleurs enzymes pour la médecine, l'industrie et la chimie durable.
Du manque d'étapes à un détective numérique
La plupart des bases de données biochimiques listent ce qui entre et ce qui sort d'une réaction catalysée par une enzyme, mais pas la séquence des ruptures et formations de liaisons qui se produisent entre les deux. Moins d'un millier de réactions dans la littérature sont annotées avec des mécanismes complets, laissant un vaste « trou de mécanisme ». Des outils computationnels antérieurs ont tenté de combler ce vide mais nécessitaient souvent des structures 3D détaillées des enzymes ou une connaissance préalable des acides aminés responsables de la chimie, ce qui limitait fortement leur portée. MechFind aborde le problème différemment : il ignore la protéine en 3D et se concentre plutôt sur la façon dont de petits morceaux chimiques sont réarrangés, ce qui lui permet de travailler sur toute réaction dont les molécules d'entrée et de sortie sont connues.
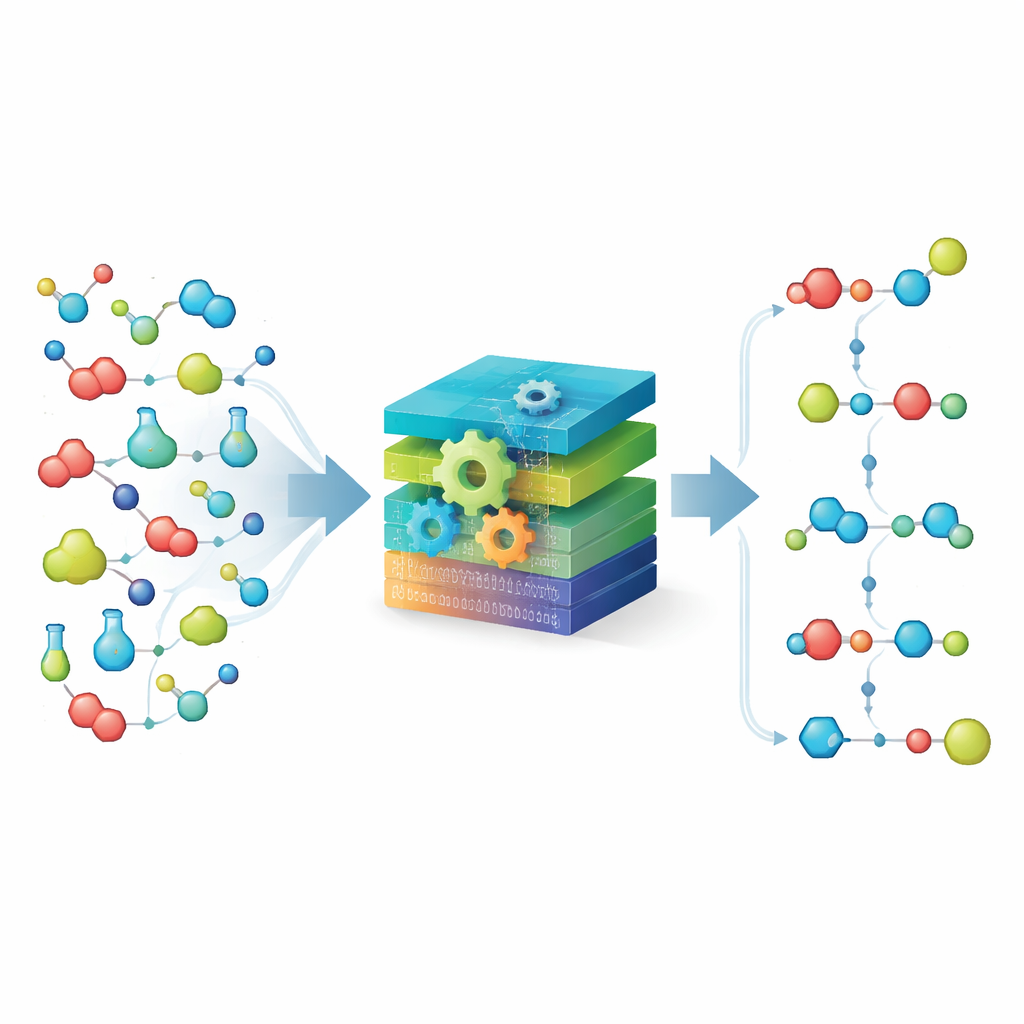
Décomposer la chimie en briques élémentaires
Au cœur de MechFind se trouve une vision « basée sur les groupements » de la chimie. Plutôt que de suivre des molécules entières, la méthode les décompose en petits fragments étiquetés en fonction des voisins immédiats de chaque atome. Elle représente ensuite toute réaction comme des gains et des pertes de ces fragments. En utilisant une grande collection soigneusement curatée d'étapes enzymatiques connues, MechFind assemble des chaînes de petits changements de fragments qui reproduisent collectivement la réaction globale. Il privilégie les explications les plus simples, recherchant des mécanismes avec le moins d'étapes possible et appliquant une stricte conservation des atomes et de la charge afin que rien n'apparaisse ni ne disparaisse illégalement en cours de route.
Vérifier la précision et découvrir de nouveaux chemins
Pour évaluer la pertinence de ses prédictions, les auteurs ont d'abord testé MechFind sur des centaines de réactions dont les mécanismes étaient déjà documentés dans une base de données de référence. En n'utilisant que les molécules de départ et d'arrivée comme entrées, MechFind a retrouvé le mécanisme accepté en première position dans près des deux tiers des cas et l'a placé dans le top dix dans 85 % d'entre eux. L'équipe a ensuite mis le système au défi avec six mécanismes enzymatiques récemment publiés qu'il n'avait jamais vus auparavant. MechFind a néanmoins identifié la séquence d'étapes correcte parmi ses principaux candidats, souvent en réutilisant des motifs chimiques dérivés d'espèces non apparentées, comme construire le mécanisme d'une enzyme humaine à partir d'étapes apprises initialement sur des enzymes de levure ou de plantes.
Passer à l'échelle : des dizaines de milliers de réactions
Après avoir validé sa précision, les auteurs ont lancé MechFind sur deux grandes collections de réactions biochimiques, couvrant près de 38 000 réactions distinctes. Pour plus de la moitié des réactions de chaque base, l'outil a produit au moins un mécanisme multistep plausible, proposant souvent jusqu'à dix chemins alternatifs. Cet effort a généré plus de 18 000 nouvelles hypothèses mécanistiques, soit une multiplication par plus de dix du nombre de réactions avec des étapes détaillées proposées. En parallèle, le test à grande échelle a mis en évidence les limites actuelles de la méthode — soit parce que l'optimisation devient trop complexe dans le temps de calcul imparti, soit parce que les types de fragments nécessaires n'étaient jamais apparus dans les données d'entraînement.
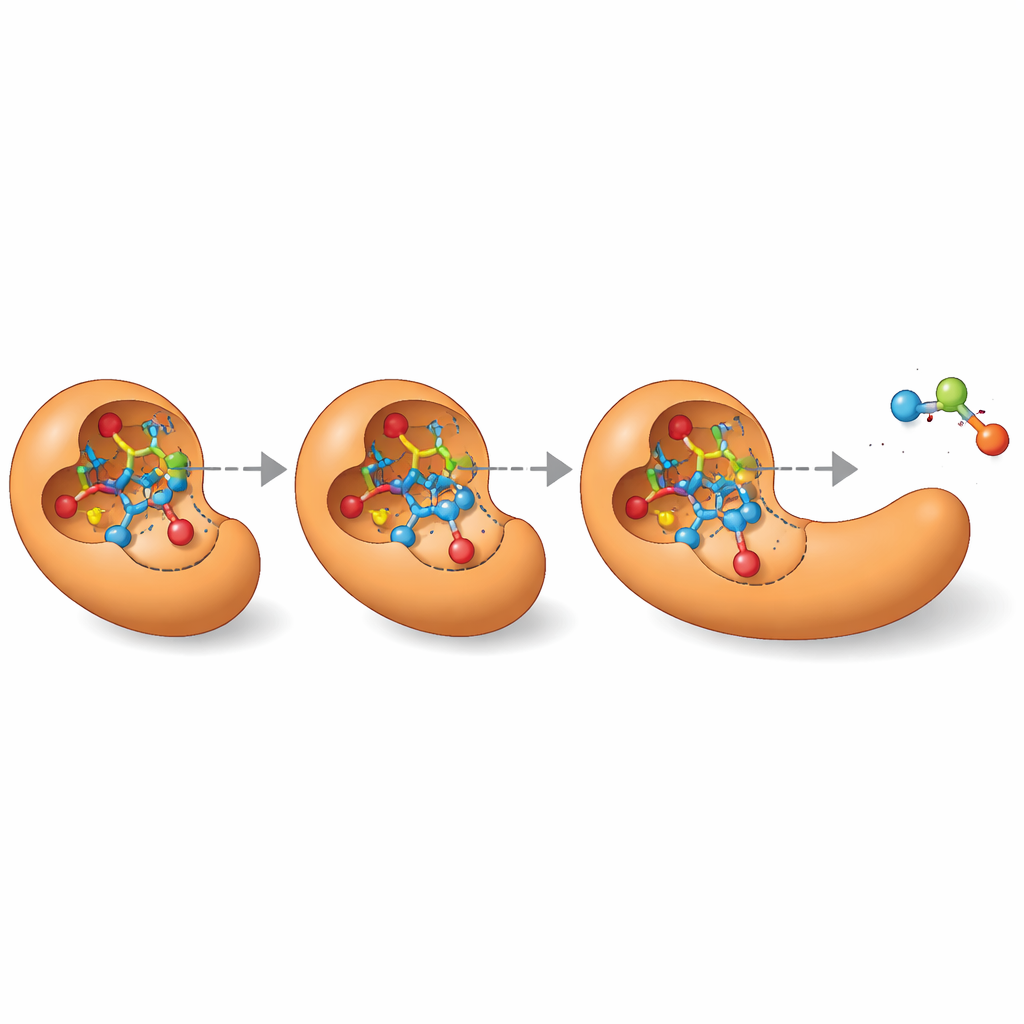
Ouvrir des perspectives pour la conception d'enzymes
Au-delà d'une simple « meilleure estimation », MechFind peut cartographier des réseaux entiers de routes plausibles qu'une enzyme pourrait emprunter pour une réaction donnée. Ce paysage d'alternatives est particulièrement précieux pour la conception d'enzymes de novo. Les outils modernes de conception de protéines nécessitent une image tridimensionnelle précise des états de transition éphémères par lesquels passent les réactions. En détaillant des mécanismes étape par étape, MechFind indique directement ces intermédiaires et états de transition clés, transformant des objectifs de conception vagues comme « construire une estérase » en cibles concrètes telles que « stabiliser cette structure particulière à haute énergie ». Bien que ses prédictions exigent toujours une expertise pour être vérifiées et des calculs ou expériences de suivi, MechFind élargit considérablement notre catalogue de chimies enzymatiques possibles et trace une voie pratique vers une ingénierie d'enzymes plus systématique et guidée par les données.
Citation: Hartley, A.D., Upadhyay, V., Boorla, V.S. et al. MechFind: a computational framework for de novo prediction of enzyme mechanisms. Nat Commun 17, 3903 (2026). https://doi.org/10.1038/s41467-026-71957-0
Mots-clés: mécanismes enzymatiques, biochimie computationnelle, conception d'enzymes, réactions métaboliques, prédiction de réactions