Clear Sky Science · de
MechFind: ein rechnerisches Framework zur de‑novo‑Vorhersage von Enzymmechanismen
Warum das Verständnis von Enzymen wichtig ist
Jede lebende Zelle arbeitet mit winzigen molekularen Maschinen, den Enzymen. Diese Proteine beschleunigen chemische Reaktionen, die unseren Körper antreiben, Ernten wachsen lassen und Medikamente herstellen. Zwar kennen wir für Zehntausende von Enzymreaktionen die übergeordnete „Vorher‑Nachher“‑Chemie, doch wissen wir selten die exakten Schritt‑für‑Schritt‑Abläufe, mit denen sie von Ausgangsstoffen zu Endprodukten gelangen. Dieser Artikel stellt MechFind vor, ein Computerframework, das automatisch detaillierte Enzymreaktionsschritte vorschlagen kann – allein auf Basis einfacher chemischer Informationen – und so Forschern hilft, bessere Enzyme für Medizin, Industrie und nachhaltige Chemie zu entwerfen.
Vom Fehlen der Schritte zum digitalen Detektiv
Die meisten biochemischen Datenbanken listen, was in eine enzymgetriebene Reaktion eingeht und was herauskommt, aber nicht die Reihe von Bindungsbrüchen und -bildungen dazwischen. Weniger als tausend Reaktionen in der Literatur sind mit vollständigen Mechanismen annotiert, was eine große „Mechanismuslücke“ hinterlässt. Frühere rechnerische Werkzeuge versuchten, diese Lücke zu schließen, benötigten dafür jedoch oft detaillierte 3‑D‑Strukturen der Enzyme oder Vorwissen darüber, welche Aminosäuren der Protein aktive Chemie leisten — was ihre Anwendbarkeit stark einschränkte. MechFind geht das Problem anders an: Es ignoriert das vollständige 3‑D‑Protein und konzentriert sich stattdessen darauf, wie kleine chemische Bausteine umgeordnet werden, sodass es für jede Reaktion funktionieren kann, bei der Ein‑ und Ausgangsmoleküle bekannt sind.
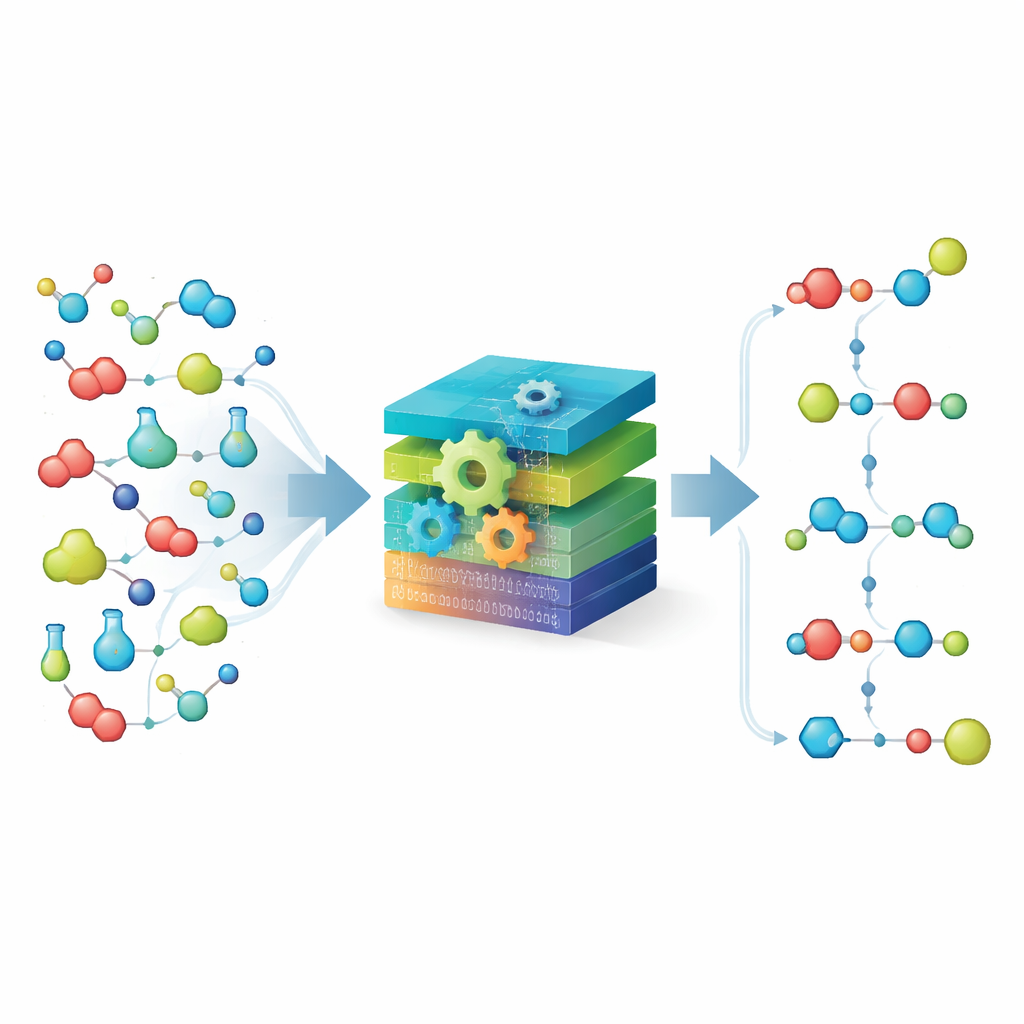
Chemie in einfache Bausteine aufspalten
Kernstück von MechFind ist eine „moietätsbasierte“ Sicht auf die Chemie. Anstatt ganze Moleküle zu verfolgen, zerlegt die Methode sie in winzige, gelabelte Fragmente, die auf den unmittelbaren Nachbarn jedes Atoms beruhen. Jede Reaktion wird dann als Gewinn und Verlust dieser Fragmente dargestellt. Unter Verwendung einer großen, kuratierten Sammlung bekannter enzymatischer Schritte setzt MechFind Ketten kleiner Fragmentänderungen zusammen, die zusammen die Gesamtreaktion reproduzieren. Es bevorzugt die einfachsten Erklärungen, sucht nach Mechanismen mit möglichst wenigen Schritten und erzwingt eine strikte Erhaltung von Atomen und Ladung, sodass nichts unrechtmäßig verschwindet oder entsteht.
Genauigkeitsprüfung und Entdeckung neuer Wege
Um zu prüfen, ob seine Vorhersagen sinnvoll sind, testeten die Autoren MechFind zunächst an Hunderten von Reaktionen, deren Mechanismen bereits in einer vertrauenswürdigen Datenbank dokumentiert waren. Mit nur den Start‑ und Zielmolekülen als Eingabe stellte MechFind den akzeptierten Mechanismus in fast zwei Dritteln der Fälle als erste Wahl wieder her und führte ihn in 85 % der Fälle unter die Top Ten. Das Team forderte das System anschließend mit sechs kürzlich veröffentlichten Enzymmechanismen heraus, die es zuvor nie gesehen hatte. MechFind identifizierte die korrekte Schrittabfolge dennoch unter seinen führenden Kandidaten, häufig indem es chemische Muster wiederverwendete, die aus bislang unverwandten Arten stammten — etwa indem ein menschlicher Enzymmechanismus aus Schritten konstruiert wurde, die ursprünglich aus Hefen oder Pflanzen gelernt wurden.
Skalierung auf Zehntausende von Reaktionen
Nach der Validierung seiner Genauigkeit setzte das Team MechFind auf zwei große biochemische Reaktionssammlungen an, die fast 38.000 verschiedene Reaktionen abdecken. Für mehr als die Hälfte der Reaktionen in jeder Datenbank erzeugte das Tool mindestens einen plausiblen mehrstufigen Mechanismus und schlug häufig bis zu zehn alternative Wege vor. Dieser Einsatz generierte über 18.000 neue mechanistische Hypothesen — ein mehr als zehnfacher Anstieg der Anzahl von Reaktionen mit vorgeschlagenen detaillierten Schritten. Gleichzeitig machte der groß angelegte Test deutlich, wo die Methode derzeit scheitert — entweder weil die Optimierung innerhalb der verfügbaren Rechenzeit zu komplex wird oder weil die erforderlichen Fragmenttypen nie in den Trainingsdaten vorkamen.
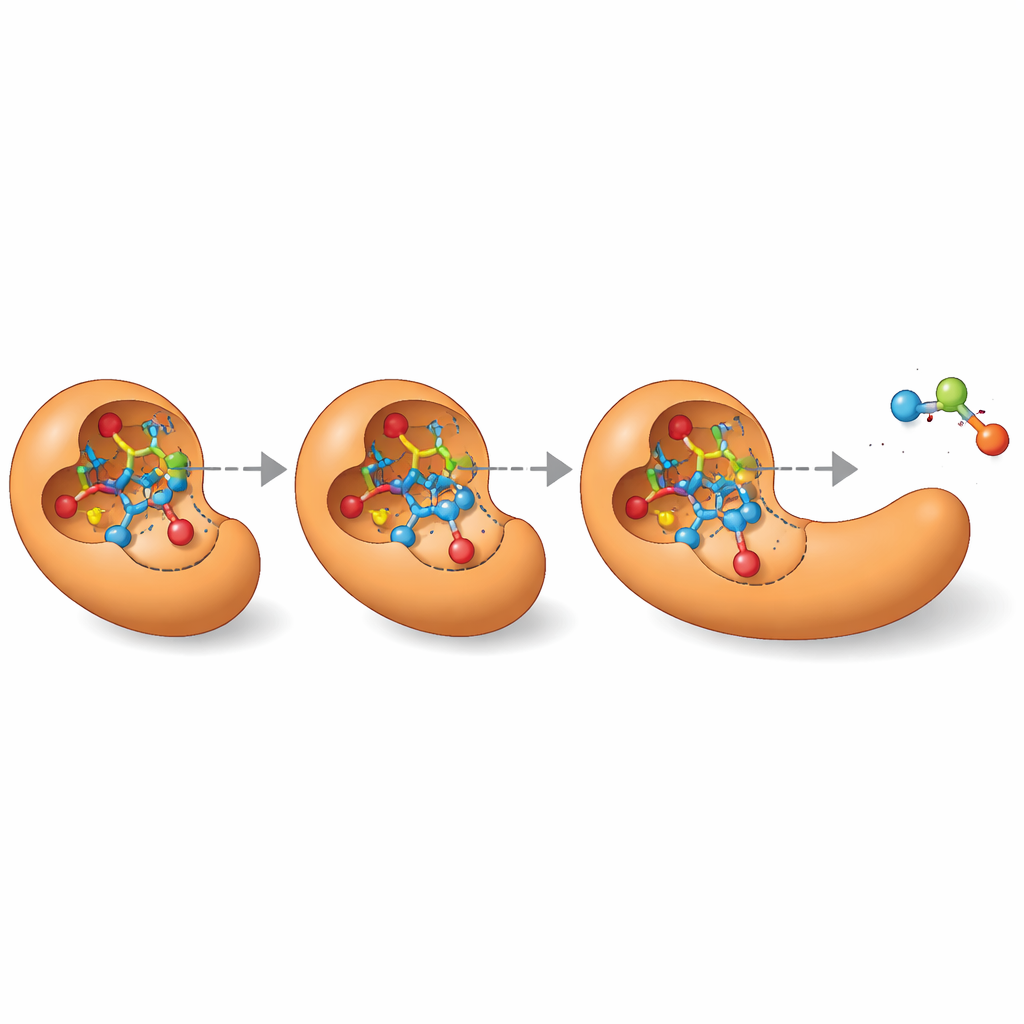
Türen öffnen für Enzymdesign
Über die Auflistung einer einzigen „besten Vermutung“ hinaus kann MechFind ganze Netzwerke unterschiedlicher plausibler Routen abbilden, die ein Enzym für eine gegebene Reaktion nutzen könnte. Diese Landschaft von Alternativen ist besonders wertvoll für das Design neuer Enzyme von Grund auf. Moderne Protein‑Design‑Werkzeuge benötigen ein präzises dreidimensionales Bild der flüchtigen Übergangszustände, die Reaktionen durchlaufen. Indem MechFind schrittweise Mechanismen aufzeigt, verweist es direkt auf jene Schlüsselzwischenstufen und Übergangszustände und verwandelt vage Designziele wie „baue eine Esterase“ in konkrete Ziele wie „stabilisiere diese spezielle hochenergetische Struktur“. Zwar erfordern die Vorhersagen weiterhin fachliche Prüfung und weiterführende Berechnungen oder Experimente, doch erweitert MechFind unseren Katalog möglicher Enzymchemien deutlich und zeichnet einen praktischen Pfad hin zu systematischerem, datengetriebenem Enzymengineering.
Zitation: Hartley, A.D., Upadhyay, V., Boorla, V.S. et al. MechFind: a computational framework for de novo prediction of enzyme mechanisms. Nat Commun 17, 3903 (2026). https://doi.org/10.1038/s41467-026-71957-0
Schlüsselwörter: Enzymmechanismen, computationale Biochemie, Enzymdesign, metabolische Reaktionen, Reaktionsvorhersage