Clear Sky Science · pl
MechFind: komputerowe ramy do de novo przewidywania mechanizmów enzymatycznych
Dlaczego zrozumienie enzymów ma znaczenie
Każda żywa komórka działa dzięki mikroskopijnym maszynom molekularnym zwanym enzymami. Te białka przyspieszają reakcje chemiczne, które napędzają nasze ciała, pozwalają uprawiać rośliny i wytwarzać leki. Choć znamy ogólną chemię „przed i po” dla dziesiątek tysięcy reakcji enzymatycznych, rzadko znamy dokładne, krok po kroku, ruchy prowadzące od substratów do produktów. W artykule wprowadzono MechFind — komputerowe ramy, które potrafią automatycznie proponować szczegółowe kroki reakcji enzymatycznych, korzystając wyłącznie z podstawowych informacji chemicznych, co pomaga naukowcom projektować lepsze enzymy dla medycyny, przemysłu i chemii zrównoważonej.
Od brakujących kroków do cyfrowego detektywa
Większość baz biochemicznych podaje, co wchodzi w reakcję napędzaną przez enzym i co z niej wychodzi, ale nie sekwencję pęknięć i tworzeń wiązań pośrednio. Mniej niż tysiąc reakcji w literaturze jest opisanych pełnymi mechanizmami, pozostawiając dużą „luki mechanistyczną”. Poprzednie narzędzia obliczeniowe próbowały wypełnić tę lukę, ale często wymagały szczegółowych struktur 3D enzymów lub wcześniejszej wiedzy o tym, które aminokwasy w białku prowadzą reakcję, co wyraźnie ograniczało ich zastosowanie. MechFind podchodzi do problemu inaczej: pomija pełne 3D białka i zamiast tego skupia się na tym, jak małe fragmenty chemiczne są przearanżowywane, co pozwala mu działać dla dowolnej reakcji, gdy znane są molekuły wejściowe i wyjściowe.
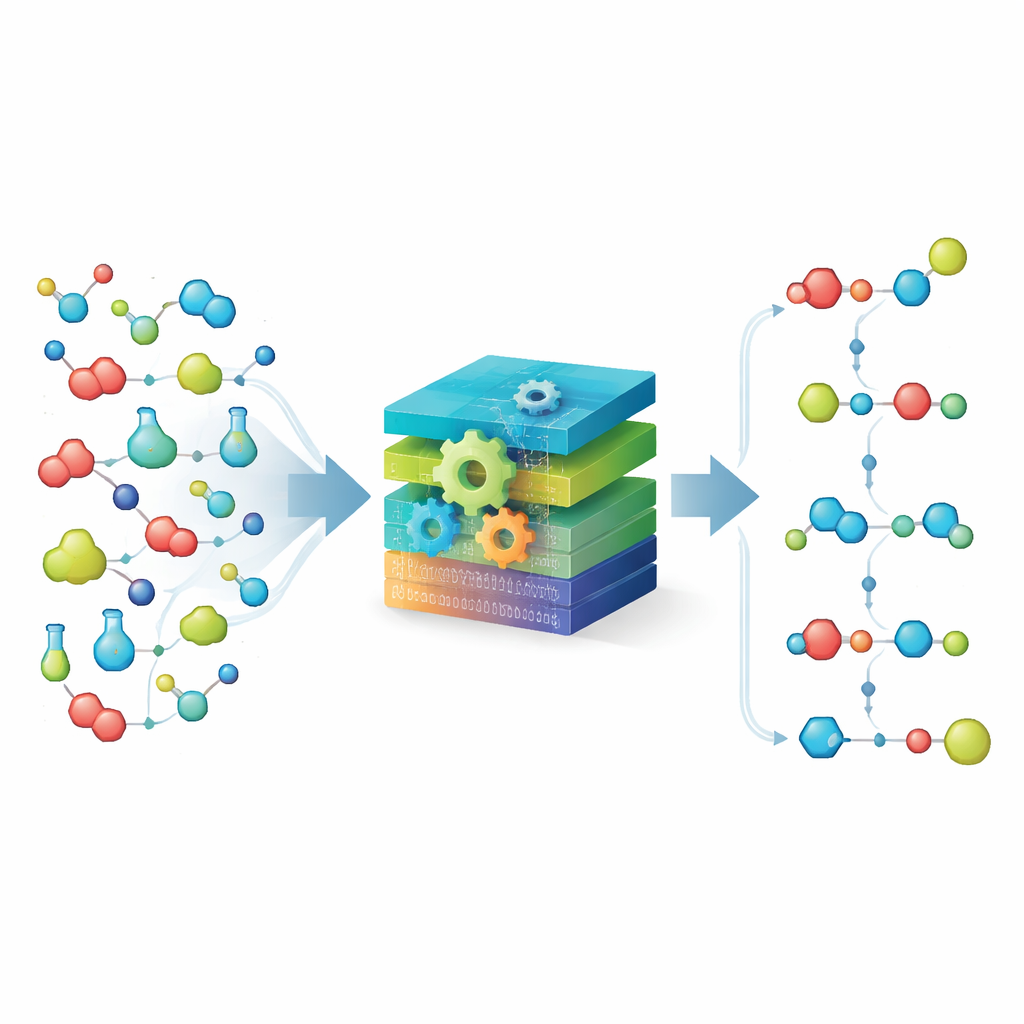
Rozbijanie chemii na proste bloki konstrukcyjne
W sercu MechFind leży podejście oparte na „moiety” (fragmentach). Zamiast śledzić całe cząsteczki, metoda rozbija je na drobne, oznakowane fragmenty oparte na bezpośrednich sąsiadach każdego atomu. Następnie reprezentuje dowolną reakcję jako zyski i straty tych fragmentów. Korzystając z dużej, skrupulatnie przygotowanej kolekcji znanych kroków enzymatycznych, MechFind składa łańcuchy małych zmian fragmentów, które łącznie odtwarzają całą reakcję. Preferuje najprostsze wyjaśnienia — szuka mechanizmów z jak najmniejszą liczbą kroków i egzekwuje ścisłą konserwację atomów oraz ładunku, tak aby nic nie pojawiało się ani nie znikało wbrew zasadom.
Sprawdzanie trafności i odkrywanie nowych ścieżek
Aby sprawdzić, czy jego przewidywania mają sens, autorzy najpierw przetestowali MechFind na setkach reakcji, których mechanizmy były już udokumentowane w zaufanej bazie danych. Korzystając tylko z molekuł początkowych i końcowych jako danych wejściowych, MechFind odzyskał akceptowany mechanizm jako swój najlepszy wybór w niemal dwóch trzecich przypadków i umieścił go w pierwszej dziesiątce w 85% przypadków. Zespół następnie rzucił systemowi wyzwanie, prezentując sześć niedawno opublikowanych mechanizmów enzymatycznych, których wcześniej nie widział. MechFind nadal identyfikował prawidłową sekwencję kroków wśród swoich czołowych kandydatów, często ponownie wykorzystując wzorce chemiczne wyuczone z niepowiązanych gatunków, na przykład budując mechanizm enzymu ludzkiego z kroków pierwotnie nauczonych na enzymach drożdży lub roślin.
Skalowanie do dziesiątek tysięcy reakcji
Po zwalidowaniu swojej trafności autorzy uruchomili MechFind na dwóch głównych zbiorach reakcji biochemicznych, obejmujących niemal 38 000 odrębnych reakcji. Dla ponad połowy reakcji w każdej bazie narzędzie wygenerowało przynajmniej jeden prawdopodobny mechanizm wielokrokowy, często proponując do dziesięciu alternatywnych ścieżek. Wysiłek ten wygenerował ponad 18 000 nowych hipotez mechanistycznych, co stanowi ponad dziesięciokrotny wzrost liczby reakcji z proponowanymi szczegółowymi krokami. Jednocześnie test na dużą skalę uwypuklił obszary, w których metoda obecnie zawodzi — albo dlatego, że optymalizacja staje się zbyt złożona w ramach przydzielonego czasu obliczeniowego, albo dlatego, że potrzebne typy fragmentów nigdy nie pojawiły się w danych treningowych.
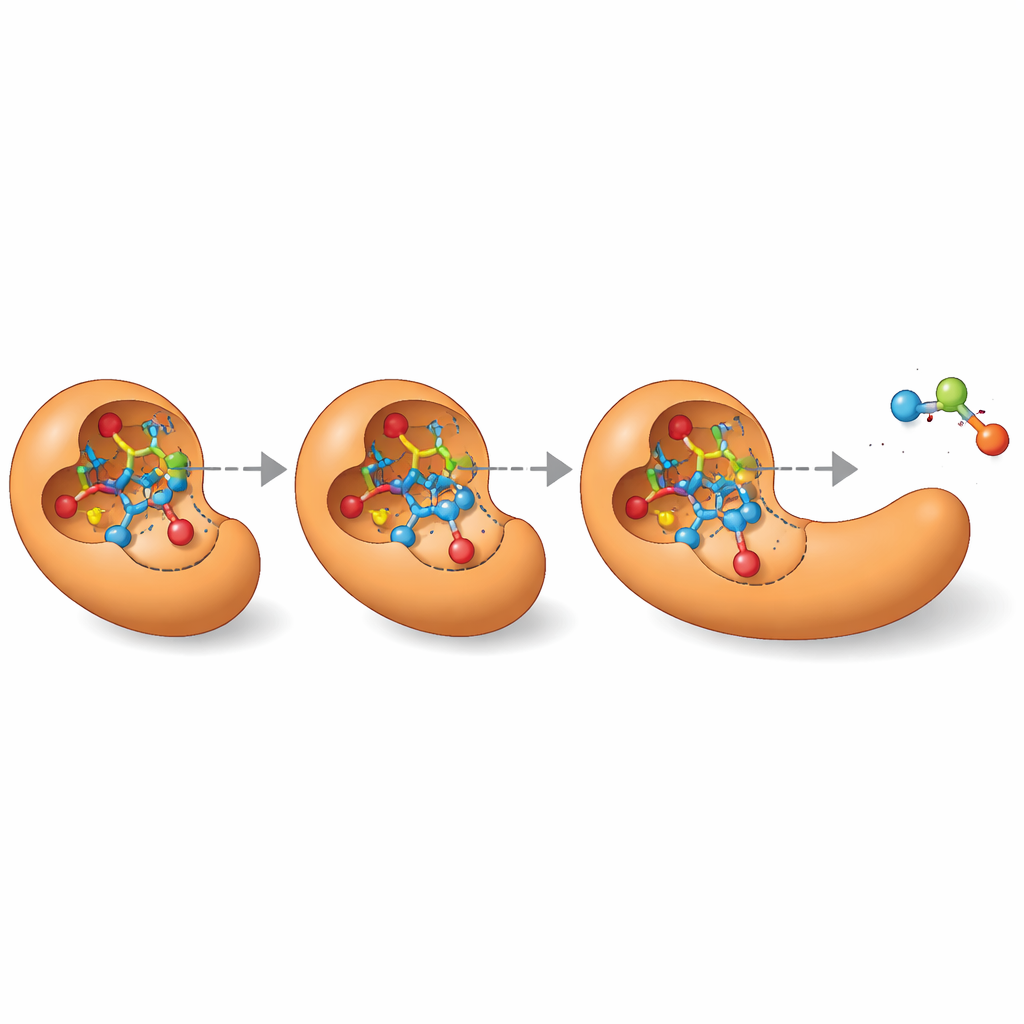
Otwierając drzwi do projektowania enzymów
Ponad przedstawieniem jednego „najlepszego przypuszczenia”, MechFind może odwzorować całe sieci różnych prawdopodobnych dróg, które enzym może wykorzystać dla danej reakcji. Ten pejzaż alternatyw jest szczególnie cenny przy projektowaniu nowych enzymów od podstaw. Nowoczesne narzędzia projektowania białek potrzebują precyzyjnego obrazu trójwymiarowego ulotnych stanów przejściowych, przez które przechodzą reakcje. Prezentując mechanizmy krok po kroku, MechFind wskazuje bezpośrednio na kluczowe intermediata i stany przejściowe, przekształcając niejasne cele projektowe, takie jak „zbuduj esterazę”, w konkretne cele, np. „stabilizuj tę konkretną strukturę o wysokiej energii”. Chociaż jego przewidywania nadal wymagają przeglądu eksperckiego oraz dalszych obliczeń lub eksperymentów, MechFind znacząco rozszerza katalog możliwych chemii enzymatycznych i wytycza praktyczną ścieżkę ku bardziej systematycznemu, opartego na danych inżynierowania enzymów.
Cytowanie: Hartley, A.D., Upadhyay, V., Boorla, V.S. et al. MechFind: a computational framework for de novo prediction of enzyme mechanisms. Nat Commun 17, 3903 (2026). https://doi.org/10.1038/s41467-026-71957-0
Słowa kluczowe: mechanizmy enzymów, biochemia obliczeniowa, projektowanie enzymów, reakcje metaboliczne, przewidywanie reakcji