Clear Sky Science · zh
在密歇根地区传播期间通过基因组推断blaNDM肺炎克雷伯菌传播地点
为何这一隐蔽的医院威胁重要
耐抗生素的病原体可以随着患者在医院、养老院和康复中心之间转运而悄然流动。当公共卫生人员发现一种危险的菌株时,迫切需要知道它在何处传播以及哪些机构在不自知中助长了传播。本研究表明,将细菌的DNA序列与常规的患者流动记录结合起来,可以揭示整个区域内那些隐藏的传播热点。
追踪密歇根州的危险病原体
研究人员聚焦于一种尤其令人担忧的细菌——肺炎克雷伯菌(Klebsiella pneumoniae),它携带称为blaNDM-1的基因,从而对强效碳青霉烯类抗生素产生耐药性。在2019年底至2022年期间,密歇根卫生当局从47家不同的医疗机构的72名患者处采集了样本。起初看似单一医院的问题,随着更多病例在其他地方出现,演变为区域性问题。通过比较细菌的全基因组序列,研究团队发现几乎所有病例都可追溯到一次近期引入的单一菌株的扩散与传播,而非多次无关的输入。
把DNA当作接触者追踪工具
为了解该菌株如何移动,团队并不只是计算样本间有多少DNA变异差异。他们采用了一种“最大共享变异”方法,简单地问:对于每个新病例,哪些早期样本是其最接近的遗传邻居。因为该方法不依赖于严格的遗传距离阈值,它既能捕捉到非常紧密的关联,也能识别那些略远但仍可能共享近期来源的联系。科学家随后将患者先前的医疗暴露时间地点叠加到DNA谱系图上,查找遗传上接近的患者在哪些时间和地点有重叠。

定位最可能的传播场所
对于每位患者,团队模拟了一次实时调查,假设他们仅知道直到该时间点报告的病例。他们查找新病例与其最近遗传匹配之间在医疗机构暴露上的重叠。当超过一半的这些关联指向同一医疗机构时,该机构就被标记为患者最可能获得耐药菌株的地点。按照这一规则,他们能够为70名可分析患者中的66名指定单一的最可能来源机构。大约一半的病例最好由诊断地机构内的传播解释,其余病例则似乎是在其他机构获得感染并随患者带入的。
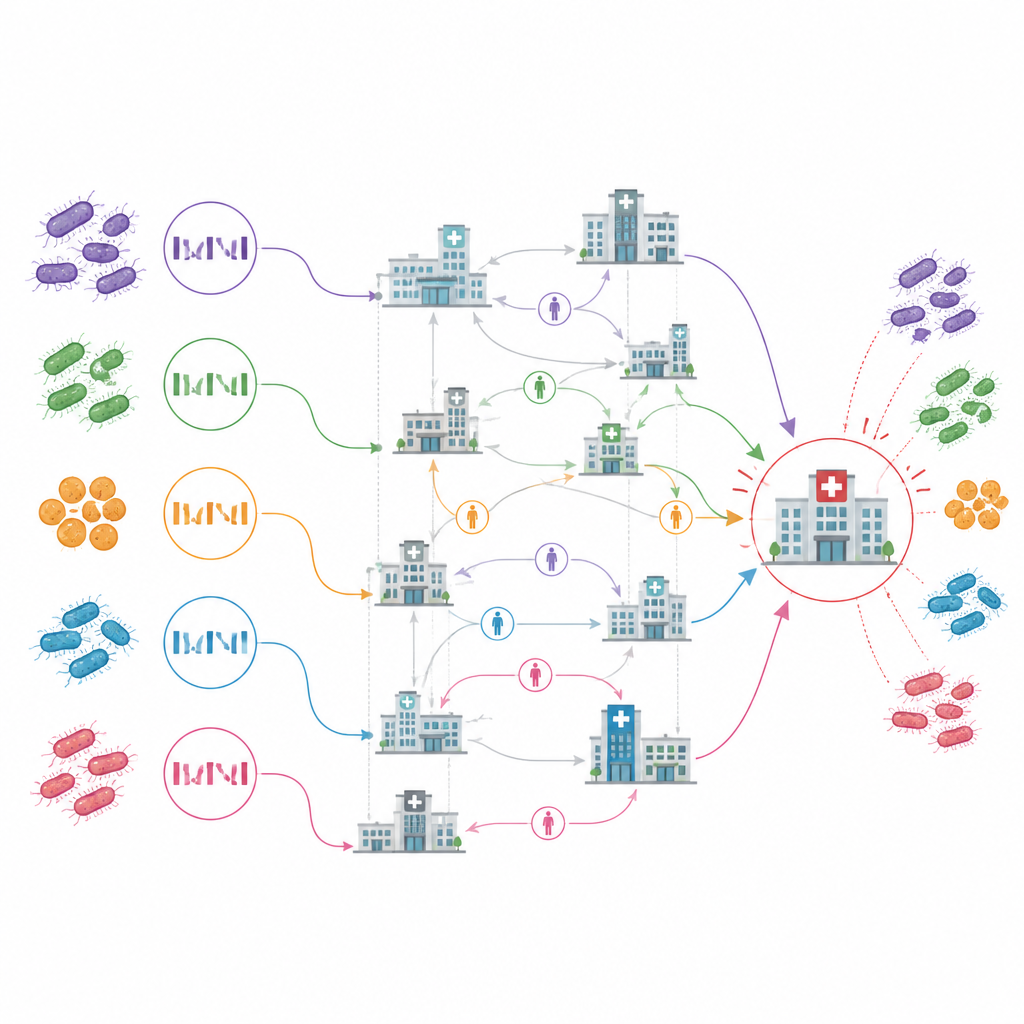
揭示关键枢纽与隐匿储存库
由此得到的医疗机构间传播图凸显出一所综合急症医院(在研究中标为ACH10)作为一个中心枢纽。它是最早出现病例的地点,显示出院内持续传播,并且似乎是超过四分之一跨机构传播事件的来源。大多数其它机构间的联系看起来只是一次性引入,随后仅有限传播。值得注意的是,分析还指出若干在首次报告病例前就可能是感染来源的机构,甚至标记出一些从未报告过病例但却位于密切相关感染常见暴露路径上的机构。
这对感染控制意味着什么
通过将细菌基因组与关于患者去向的常规信息结合,本研究表明卫生机构可以用他们已经收集的样本重建耐药菌株如何在整个医院与护理中心网络中移动。这种方法有助于识别哪些机构在推动区域传播、哪些机构主要是接收输入病例,以及哪些地方可能存在尚未被发现的隐性储存库。有了这种基因组信息支持的实时监测,公共卫生团队可以更快地把清洁、筛查和隔离等干预针对到正确的地点,从而减缓危险抗生素耐药细菌在区域内的扩散。
引用: Wan, T., McNamara, S., Brennan, B. et al. Genomic inference of sites of transmission during regional spread of blaNDM Klebsiella pneumoniae in Michigan. Nat Commun 17, 4154 (2026). https://doi.org/10.1038/s41467-026-70839-9
关键词: 抗生素耐药性, 医院感染, 基因组监测, 肺炎克雷伯菌, 患者转运