Clear Sky Science · pt
Inferência genômica dos locais de transmissão durante a disseminação regional de Klebsiella pneumoniae blaNDM em Michigan
Por que essa ameaça oculta em hospitais importa
Germes resistentes a antibióticos podem se deslocar silenciosamente com pacientes enquanto estes são transferidos entre hospitais, asilos e centros de reabilitação. Quando autoridades de saúde detectam uma linhagem perigosa, precisam com urgência saber onde ela está se espalhando e quais instituições a estão transmitindo sem perceber. Este estudo mostra como a leitura do DNA das bactérias, combinada com registros rotineiros de movimentação de pacientes, pode revelar esses pontos quentes de transmissão ocultos em toda uma região.
Rastreando um germe perigoso por Michigan
Os pesquisadores se concentraram em uma bactéria particularmente preocupante chamada Klebsiella pneumoniae, que adquiriu resistência aos carbapenêmicos por meio de um gene conhecido como blaNDM-1. Entre o final de 2019 e 2022, autoridades de saúde de Michigan coletaram amostras de 72 pacientes atendidos em 47 diferentes unidades de saúde. O que inicialmente parecia um problema em um único hospital tornou‑se uma questão regional à medida que casos surgiram em muitos outros locais. Ao comparar as sequências completas do DNA das bactérias, a equipe descobriu que quase todos esses casos se originaram de uma única introdução recente de uma mesma linhagem que se expandiu e se disseminou, em vez de várias importações não relacionadas.
Usando o DNA como ferramenta de rastreamento de contato
Para entender como a linhagem se moveu, a equipe não se limitou a contar quantas mudanças genéticas separavam uma amostra da outra. Em vez disso, usaram uma abordagem de “variantes máximas compartilhadas” que simplesmente pergunta: para cada novo caso, quais amostras anteriores são seus vizinhos genéticos mais próximos. Como esse método não depende de um corte rígido na distância genética, ele pode captar tanto ligações muito próximas quanto conexões um pouco mais distantes que ainda provavelmente compartilham uma fonte recente. Os cientistas então sobrepuseram os históricos de internação dos pacientes à árvore genealógica do DNA, verificando onde pacientes geneticamente próximos coincidiram em tempo e local.

Identificando locais prováveis de disseminação
Para cada paciente, a equipe simulou uma investigação em tempo real, supondo que só sabia dos casos relatados até aquele momento. Procuraram sobreposições na exposição a unidades de saúde entre um novo caso e seus pares genéticos mais próximos. Quando mais da metade dessas ligações apontava para a mesma instituição, esse local era marcado como o lugar mais provável onde o paciente adquiriu a linhagem resistente. Usando essa regra, eles conseguiram atribuir uma única instituição fonte provável para 66 dos 70 pacientes analisáveis. Cerca de metade dos casos foi melhor explicada por transmissão dentro da própria instituição onde foram diagnosticados, enquanto o restante pareceu refletir infecções adquiridas em outras instituições e trazidas por pacientes transferidos.
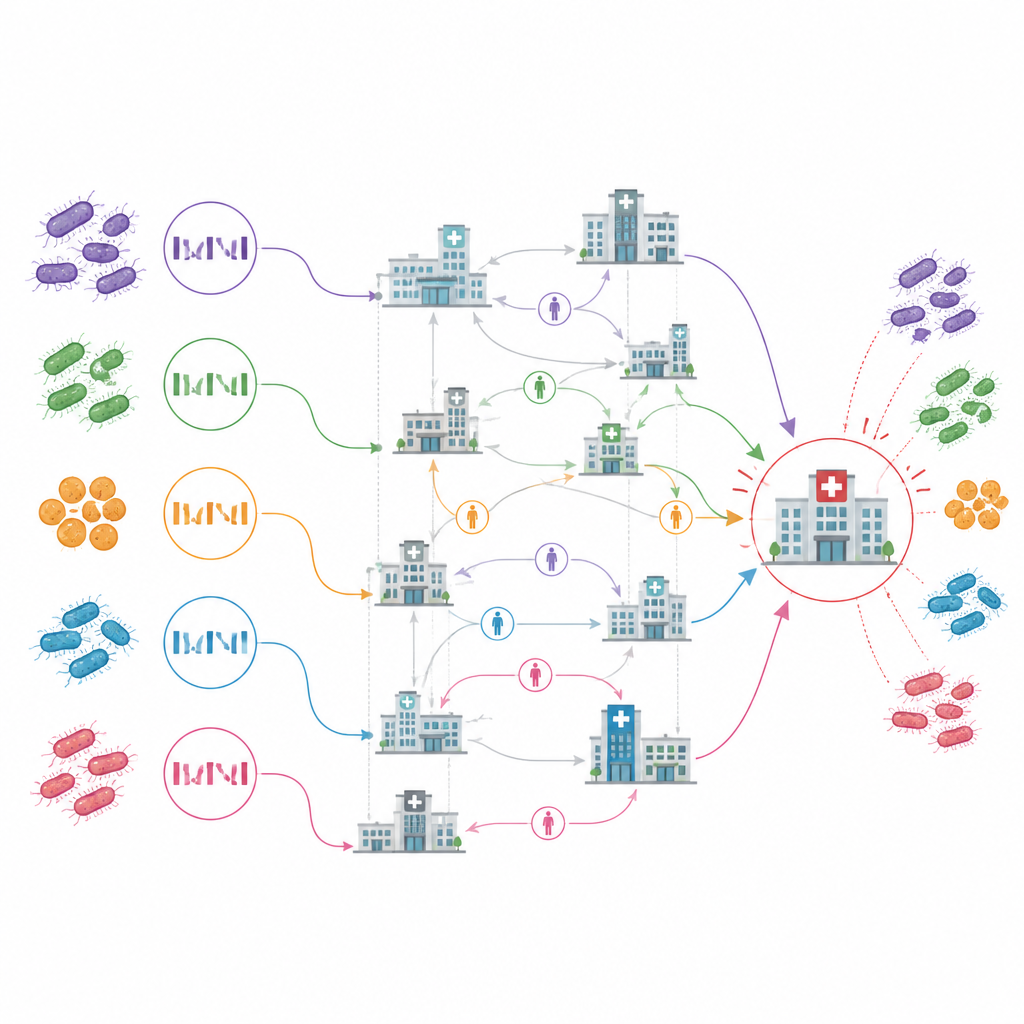
Revelando hubs chave e reservatórios ocultos
O mapa resultante das transmissões entre instituições destacou um hospital de cuidados agudos, rotulado ACH10 no estudo, como um hub central. Foi o local com os primeiros casos, mostrou disseminação contínua internamente e apareceu como a fonte de mais de um quarto dos eventos de transmissão entre instituições. A maioria das outras ligações entre unidades pareceu ser introduções pontuais com pouco espalhamento subsequente. De forma marcante, a análise também implicou várias instituições como fontes prováveis de infecção antes mesmo de terem relatado um caso, e até identificou algumas que nunca reportaram casos, mas estavam em caminhos comuns de exposição para infecções intimamente relacionadas.
O que isso significa para o controle de infecções
Ao combinar DNA bacteriano com informações rotineiras sobre onde os pacientes estiveram, este estudo mostra que agências de saúde podem reconstruir como uma linhagem resistente circula por toda uma rede de hospitais e centros de cuidado usando amostras que já coletam. A abordagem ajuda a identificar quais instituições impulsionam a disseminação regional, quais são principalmente receptoras de casos importados e onde reservatórios ocultos podem estar se formando antes que alguém perceba. Com esse tipo de vigilância em tempo real informada pelo genoma, equipes de saúde pública poderiam direcionar mais rapidamente limpeza, triagem e medidas de isolamento aos locais certos, freando a propagação de bactérias resistentes a antibióticos em toda uma região.
Citação: Wan, T., McNamara, S., Brennan, B. et al. Genomic inference of sites of transmission during regional spread of blaNDM Klebsiella pneumoniae in Michigan. Nat Commun 17, 4154 (2026). https://doi.org/10.1038/s41467-026-70839-9
Palavras-chave: resistência a antibióticos, infecções hospitalares, vigilância genômica, Klebsiella pneumoniae, transferências de pacientes