Clear Sky Science · tr
Biyomedikal varlık ilişkileri için ontoloji odaklı birliktelik kuralı madenciliği: hiyerarşik bilgiyi bütünleştirerek gen–hastalık keşfini iyileştirme
Gizli gen–hastalık bağlantıları neden önemli
Modern tıp giderek daha fazla hangi genlerin hangi hastalıklarla bağlantılı olduğunu bulmaya dayanıyor. Bu bağlantılar hastalıkların neden ortaya çıktığını açıklayabilir, yeni ilaç hedeflerini önerebilir ve daha yüksek risk taşıyan kişileri işaret edebilir. Ancak çoğu bilgisayar aracı yalnızca aynı cümlede veya makalede birlikte geçen genleri ve hastalıkları arar; bu da birçok ince ama önemli bağı kaçırır. Bu çalışma, hem iyi bilinen hem de gözden kaçmış gen–hastalık ilişkilerini daha güvenilir biçimde ortaya çıkarmayı amaçlayarak uzmanlar tarafından oluşturulmuş bilgi hiyerarşilerinden yaranan yeni bir biyomedikal literatür madenciliği yöntemi tanıtıyor.
Ham metinden aday bağlantılara
Yazarlar önce PubMed’den geniş bir bilimsel makale koleksiyonu toplayıp her makaleyi cümlelere ayırıyor. Her cümle bir veya daha fazla gen adı ile bir veya daha fazla hastalık adı içerebilecek küçük bir “sepet” olarak ele alınıyor. Yerleşik veri madenciliği algoritmaları (Apriori, FP-Growth ve Eclat) kullanılarak milyonlarca bu sepet taranıyor ve tesadüften daha sık birlikte görülen gen–hastalık çiftleri bulunuyor. Varlık-özgü birliktelik olarak adlandırılan bu ilk adım, mevcut araçların dayandığı doğrudan birliktelikleri yakalıyor. Bu aşama zaten binlerce potansiyel bağlantı ortaya koyuyor, ancak literatürde baskın olan iyi çalışılmış genler ve yaygın hastalıkları tercih etme eğiliminde kalıyor.
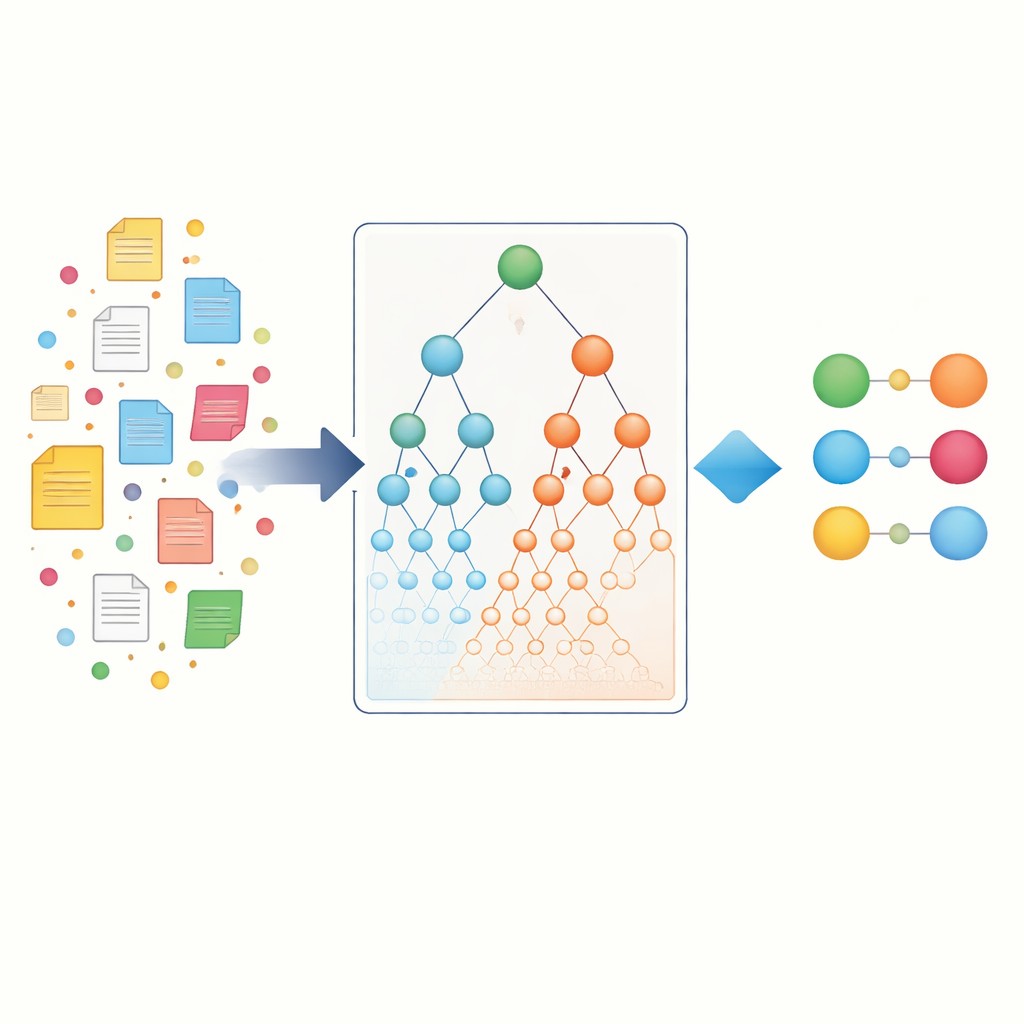
Biyolojik hiyerarşileri harita olarak kullanmak
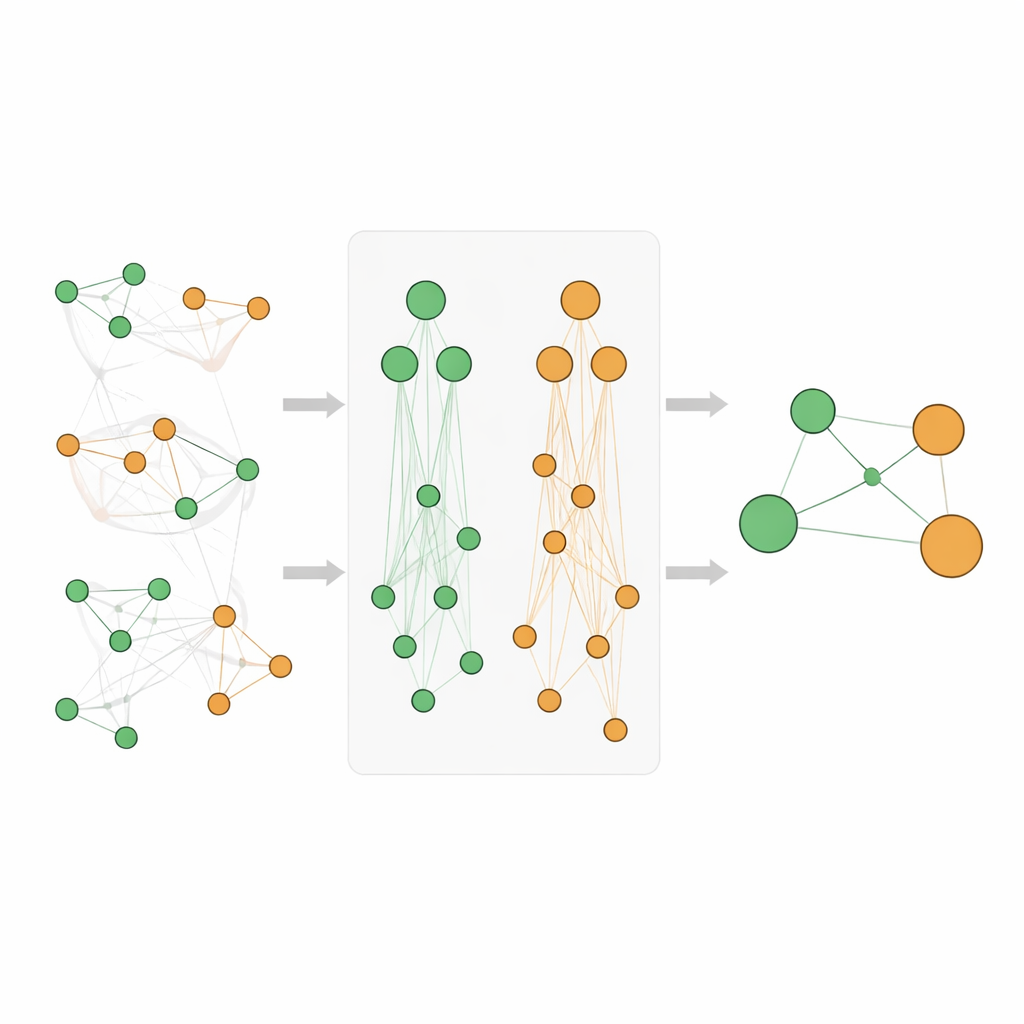
Basit kelime sayımının ötesine geçmek için araştırmacılar ontolojiler olarak bilinen biyolojik “haritalara” başvuruyor. Gen Ontolojisi genlerin ne yaptığını ve hücrede nerede işlev gördüğünü açıklarken, Hastalık Ontolojisi hastalıkları aileler ve alt tipler halinde düzenliyor. Bu hiyerarşilerde nadir bir epilepsi gibi spesifik terimler, “nörolojik hastalık” gibi daha geniş üst kavramların altında yer alır. Temel fikir şudur: belirli bir gen çok spesifik bir hastalıkla güçlü biçimde ilişkiliyse ve o hastalık daha büyük bir aileye aitse, genin muhtemelen o bütün aile ile de bir ilişkisi vardır. Yazarlar bunu, hem gen hem de hastalık tarafında kanıtı üst terimlere doğru yayarak ve ortak bir üst terimi paylaşan “kardeş” terimleri dolaylı olarak yakalayarak hiyerarşik ontoloji birliktelikleri oluşturarak biçimlendiriyor.
Doğrudan kanıtı miras alınan sinyallerle harmanlama
Hiyerarşinin birçok seviyesinden gelen sayıları basitçe toplamak puanları çarpıtabilir; özellikle “kanser” gibi çok genel terimler son derece sık görünür. Bu nedenle ekip dikkatli bir puanlama sistemi tasarlıyor. Bir gen ile hastalığın tesadüften daha güçlü şekilde bağlantılı olup olmadığını ölçmek için veri madenciliğinde standart bir ölçü olan lift kullanılıyor ve ardından bu puanlar çarpıklığı azaltmak ve karşılaştırılabilir hale getirmek için dönüştürülüyor. Yeni Athar Semantic-Enriched Association (ASEA) puanı üç bileşeni harmanlıyor: doğrudan gen–hastalık bağlantısı, gen ile daha geniş hastalık aileleri arasındaki bağlantılar ve daha geniş gen işlevleri ile hastalık aileleri arasındaki bağlantılar. Ayrıca puanların ontolojilerin farklı derinliklerinde benzer davranmasını sağlayacak ve adil karşılaştırma ve sıralamaya izin verecek sıra-temelli normalizasyon uygulanıyor.
Yöntemi güvenilir veri tabanlarına karşı test etme
ASEA’nın biyolojik açıdan anlamlı sonuçlar üretip üretmediğini değerlendirmek için yazarlar en yüksek sıralı birlikteliklerini Comparative Toxicogenomics Database ve DisGeNET gibi uzman küratörlüğündeki kaynaklardaki girişlerle karşılaştırıyor. ASEA’nın klasik algoritmaların tek başına elde ettiğinden daha fazla yüksek dereceli bilinen ilişkiyi geri kazandığını ve aynı zamanda zengin bir ek aday bağlantı seti ürettiğini buluyorlar. Toplamda ASEA 185 dikkate değer gen–hastalık çifti belirliyor. Bunlar sonra dört kategoriye ayrılıyor: büyük veri tabanlarında zaten yer alan iyi kurulmuş bağlantılar; yakın zamanda yapılan çalışmalarla güçlü şekilde desteklenen ancak henüz küratörlüğü yapılmamış bağlantılar; sadece zayıf veya dağınık veri tabanı desteğine sahip bağlantılar; ve şu anda hiçbir desteği olmayan tamamen spekülatif ilişkiler — bunlar gelecekteki laboratuvar veya klinik çalışmalar için hipotez olarak öneriliyor.
Geleceğin tıbbı için anlamı
Uzman olmayanlar için en önemli mesaj, bu çerçevenin biyomedikal literatürü ölçekli olarak okumanın daha akıllı bir yolunu sunduğudur. Bir gen ve hastalığın yan yana açıkça anılmalarını saymak yerine, genlerin ve hastalıkların nasıl ailelere ayrıldıkları konusundaki uzman bilgisinden yararlanarak nadir ama umut verici sinyalleri güçlendirir. Ortaya çıkan ASEA skoru bir genin bir hastalığa neden olduğunu kanıtlamaz; ancak araştırmacıların ve klinisyenlerin incelemesi için şeffaf, istatistiksel temelli bir aday kısa liste sunar. Uzun vadede, ontoloji farkındalıklı böyle bir madencilik biyobelirteç keşfini hızlandırabilir, kişiselleştirilmiş tedaviyi bilgilendirebilir ve artan biyomedikal metin selini uygulanabilir tıbbi içgörülere dönüştürmeye yardımcı olabilir.
Atıf: Naqash, M.A., Amin, M., Uddin, J. et al. Ontology-driven association rule mining for biomedical entity relationships: integrating hierarchical knowledge to improve gene-disease discovery. Sci Rep 16, 13072 (2026). https://doi.org/10.1038/s41598-026-42584-y
Anahtar kelimeler: gen–hastalık ilişkileri, biyomedikal metin madenciliği, ontolojiler, kişiselleştirilmiş tıp, hesaplamalı biyoloji