Clear Sky Science · pt
Mineração de regras de associação guiada por ontologias para relacionamentos entre entidades biomédicas: integrando conhecimento hierárquico para melhorar a descoberta gene-doença
Por que links ocultos entre genes e doenças importam
A medicina moderna depende cada vez mais de identificar quais genes estão ligados a quais doenças. Esses vínculos podem revelar por que doenças surgem, sugerir novos alvos farmacológicos e apontar pessoas com risco aumentado. No entanto, a maioria das ferramentas computacionais procura apenas genes e doenças que aparecem juntos na mesma frase ou no mesmo artigo, deixando passar muitas conexões sutis, porém importantes. Este estudo apresenta uma nova forma de minerar a literatura biomédica que aproveita hierarquias de conhecimento construídas por especialistas, com o objetivo de descobrir relações gene–doença tanto bem conhecidas quanto negligenciadas, de maneira mais confiável.
Do texto bruto a links candidatos
Os autores começam reunindo uma grande coleção de artigos científicos do PubMed e dividindo cada artigo em sentenças. Cada sentença é tratada como uma pequena “cesta” de itens que pode conter um ou mais nomes de genes e uma ou mais denominações de doenças. Usando algoritmos estabelecidos de mineração de dados (Apriori, FP-Growth e Eclat), eles varrem milhões dessas cestas para encontrar pares gene–doença que tendem a aparecer juntos com mais frequência do que o esperado ao acaso. Esse primeiro passo, chamado associação específica de entidades, captura as coocorrências diretas nas quais a maioria das ferramentas existentes se apoia. Já revela milhares de potenciais conexões, mas ainda favorece genes bem estudados e doenças comuns que dominam a literatura.
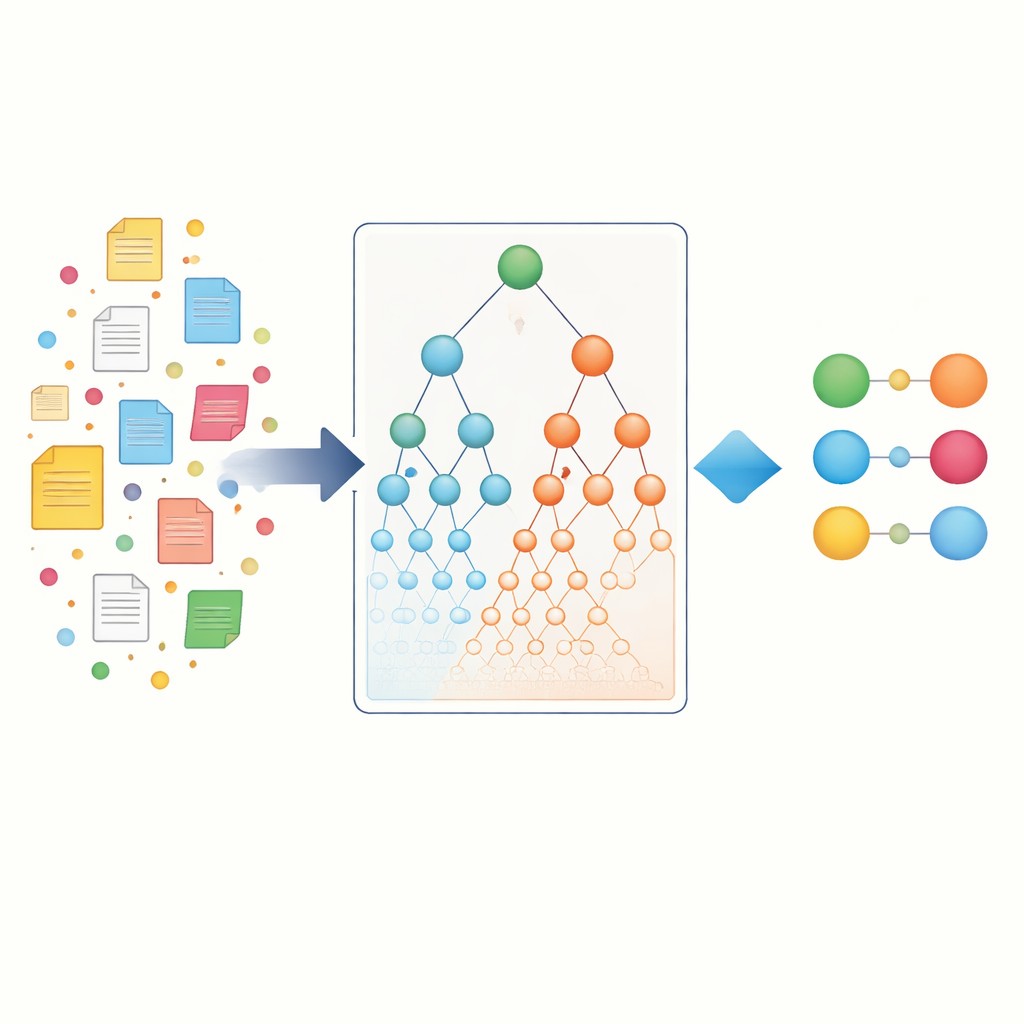
Usando hierarquias biológicas como mapa
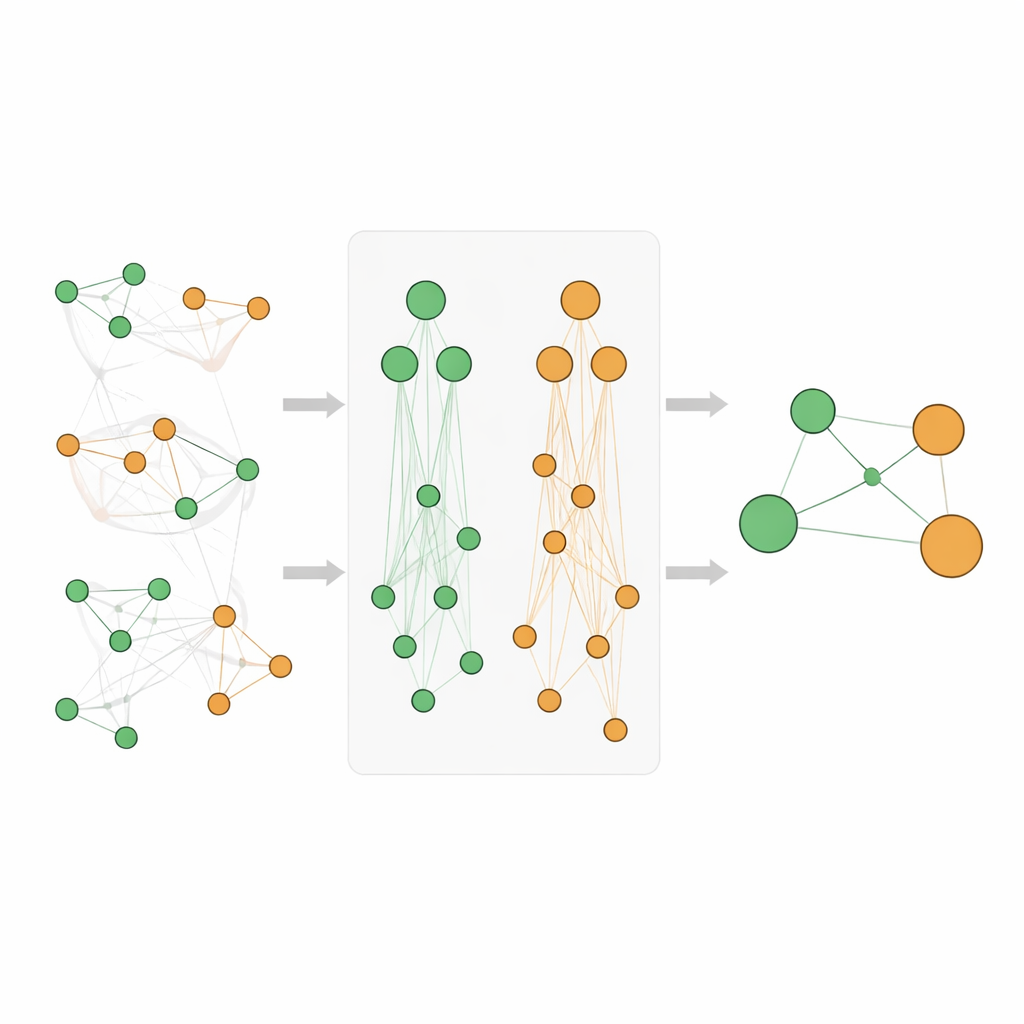
Para ir além da simples contagem de palavras, os pesquisadores recorrem a “mapas” biológicos conhecidos como ontologias. a Gene Ontology descreve o que os genes fazem e onde atuam na célula, enquanto a Disease Ontology organiza as doenças em famílias e subtipos. Nessas hierarquias, termos específicos, como uma epilepsia rara, estão sob pais mais amplos, como “doença neurológica”. A ideia central é que, se um gene particular está fortemente ligado a uma doença muito específica, e essa doença pertence a uma família maior, então o gene provavelmente tem alguma relação com toda essa família também. Os autores formalizam isso criando associações hierárquicas de ontologias, que propagam evidências para cima através dos termos-pai em ambos os lados — gene e doença — e também capturam indiretamente “irmãos” que compartilham um mesmo pai.
Misturando evidência direta com sinais herdados
Simplesmente somar contagens de muitos níveis da hierarquia pode distorcer as pontuações, especialmente porque termos muito gerais como “câncer” aparecem com extrema frequência. A equipe, portanto, desenha um sistema de pontuação cuidadoso. Eles usam uma medida padrão da mineração de dados, chamada lift, para avaliar o quão fortemente um gene e uma doença estão ligados além do acaso e então transformam essas pontuações para reduzir a assimetria e torná-las comparáveis. Sua nova pontuação Athar Semantic-Enriched Association (ASEA) mistura três ingredientes: o vínculo direto gene–doença, vínculos entre o gene e famílias de doenças mais amplas, e vínculos entre funções gênicas mais amplas e famílias de doenças. Também aplicam normalização baseada em postos para que as pontuações se comportem de forma semelhante em diferentes profundidades das ontologias, permitindo comparação e ranqueamento justos.
Testando o método contra bases de dados confiáveis
Para avaliar se a ASEA produz resultados biologicamente significativos, os autores comparam suas associações mais bem ranqueadas com entradas em recursos curados por especialistas, como o Comparative Toxicogenomics Database e o DisGeNET. Eles constatam que a ASEA recupera mais associações conhecidas de alta qualidade do que qualquer um dos algoritmos clássicos isoladamente, ao mesmo tempo em que gera um conjunto rico de links candidatos adicionais. No total, a ASEA identifica 185 pares gene–doença notáveis. Estes são então agrupados em quatro categorias: conexões bem estabelecidas já presentes em grandes bases de dados; conexões fortemente sustentadas por estudos recentes, mas ainda não curadas; vínculos com apenas suporte fraco ou disperso em bases de dados; e associações puramente especulativas sem suporte atual, propostas como hipóteses para trabalhos laboratoriais ou clínicos futuros.
O que isso significa para a medicina do futuro
Para não especialistas, a mensagem crucial é que essa estrutura oferece uma maneira mais inteligente de ler a literatura biomédica em grande escala. Em vez de contar apenas menções óbvias de um gene e uma doença lado a lado, ela aproveita o conhecimento especialista sobre como genes e doenças são organizados em famílias para fortalecer sinais promissores, porém raros. A pontuação ASEA resultante não prova que um gene causa uma doença, mas fornece uma lista curta transparente e estatisticamente fundamentada de candidatos para cientistas e clínicos investigarem. A longo prazo, essa mineração consciente de ontologias pode acelerar a descoberta de biomarcadores, informar a medicina de precisão e ajudar a transformar o crescente volume de texto biomédico em insights médicos acionáveis.
Citação: Naqash, M.A., Amin, M., Uddin, J. et al. Ontology-driven association rule mining for biomedical entity relationships: integrating hierarchical knowledge to improve gene-disease discovery. Sci Rep 16, 13072 (2026). https://doi.org/10.1038/s41598-026-42584-y
Palavras-chave: associações gene–doença, mineração de textos biomédicos, ontologias, medicina de precisão, biologia computacional