Clear Sky Science · ru
Извлечение ассоциативных правил на основе онтологий для взаимосвязей биомедицинских сущностей: интеграция иерархических знаний для улучшения обнаружения ген—болезнь
Почему скрытые связи между генами и заболеваниями важны
Современная медицина всё больше полагается на установление связей между генами и заболеваниями. Эти связи помогают понять причины болезней, указывают новые мишени для лекарств и выявляют людей с повышенным риском. Тем не менее большинство компьютерных инструментов ищут только те гены и заболевания, которые встречаются вместе в одном предложении или статье, упуская многие тонкие, но важные связи. В этом исследовании представлен новый подход к анализу биомедицинской литературы, который использует экспертно созданные иерархии знаний и направлен на более надёжное обнаружение как известных, так и ранее незамеченных отношений «ген—болезнь».
От сырого текста к кандидатам-связям
Авторы начинают со сбора большой коллекции статей из PubMed и разбивают каждую статью на предложения. Каждое предложение рассматривается как небольшая «корзина» элементов, которая может содержать одно или несколько названий генов и одно или несколько названий заболеваний. С помощью проверенных алгоритмов добычи данных (Apriori, FP-Growth и Eclat) они просматривают миллионы таких корзин в поисках пар «ген—болезнь», которые встречаются вместе чаще, чем ожидается случайно. Этот первый этап, называемый ассоциацией, специфичной для сущностей, фиксирует прямые со-встречаемости, на которых полагаются большинство существующих инструментов. Он уже выявляет тысячи потенциальных связей, но по-прежнему отдаёт предпочтение хорошо изученным генам и распространённым заболеваниям, доминирующим в литературе.
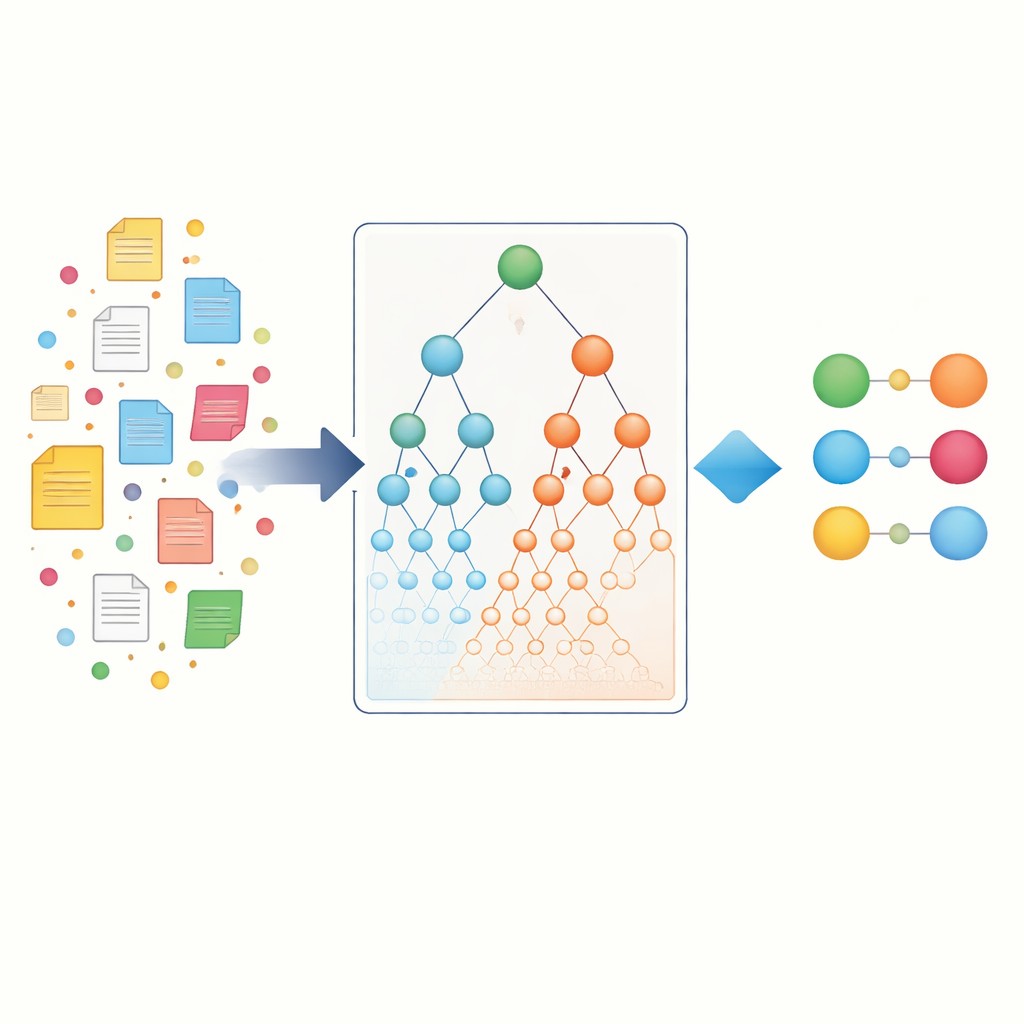
Использование биологических иерархий как карты
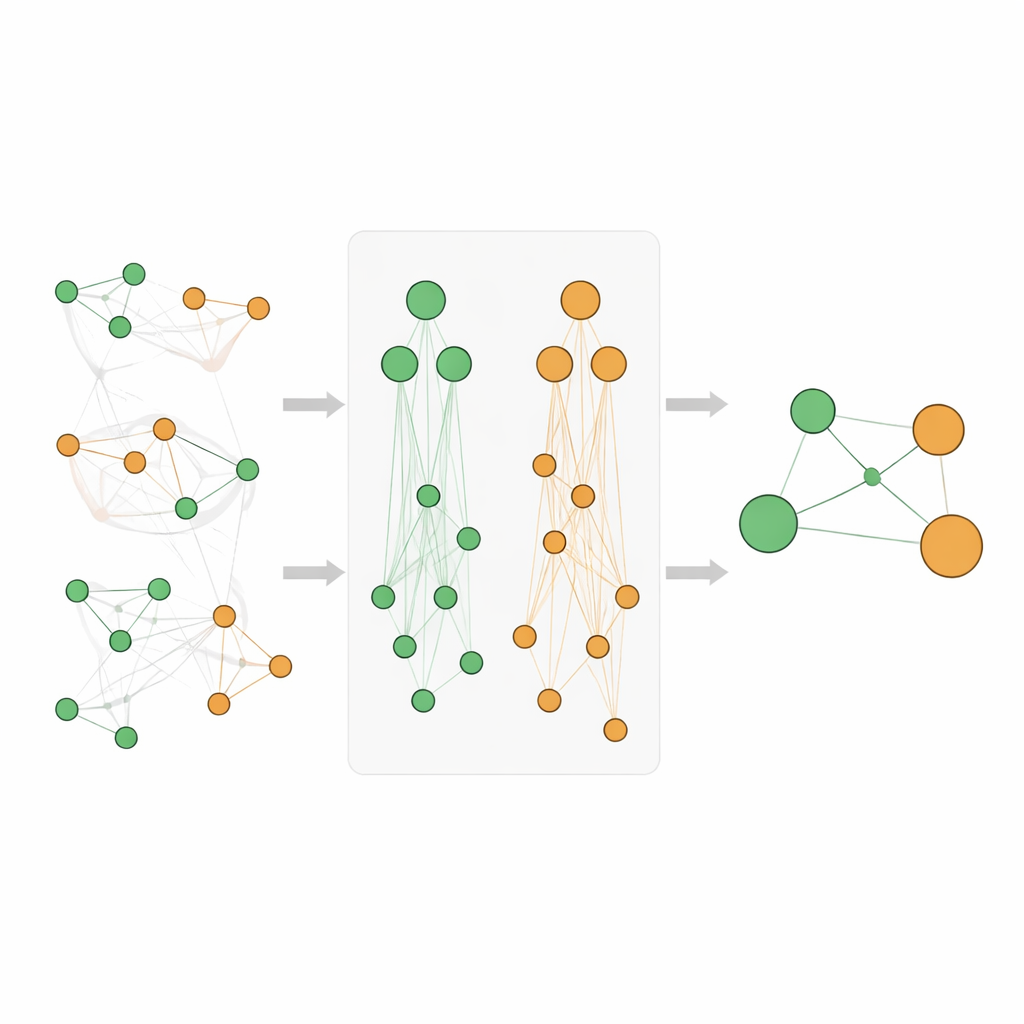
Чтобы выйти за рамки простого подсчёта слов, исследователи обращаются к биологическим «картам», известным как онтологии. Онтология генов (Gene Ontology) описывает функции генов и где они действуют в клетке, тогда как Онтология заболеваний (Disease Ontology) организует болезни в семьи и подтипы. В этих иерархиях конкретные термины, например редкая эпилепсия, находятся под более общими родительскими понятиями, такими как «неврологическое заболевание». Ключевая идея состоит в том, что если определённый ген тесно связан с очень конкретным заболеванием, а это заболевание принадлежит более широкой группе, то ген, вероятно, имеет некоторое отношение и к этой всей группе. Авторы формализуют это, создавая иерархические онтологические ассоциации, которые распространяют доказательства вверх по родительским терминам как со стороны генов, так и со стороны заболеваний, а также косвенно фиксируют «сиблингов», у которых общий родитель.
Смешение прямых доказательств с унаследованными сигналами
Простое суммирование счётов с разных уровней иерархии может искажать оценки, особенно потому, что очень общие термины, такие как «рак», встречаются чрезвычайно часто. Поэтому команда разработала аккуратную систему оценки. Они используют стандартную метрику из майнинга данных — lift, чтобы измерить, насколько сильно связаны ген и заболевание сверх случайного совпадения, а затем преобразуют эти значения, чтобы уменьшить скошенность и сделать их сопоставимыми. Их новый рейтинг Athar Semantic-Enriched Association (ASEA) объединяет три составляющих: прямую связь «ген—болезнь», связи между геном и более широкими семействами заболеваний и связи между более общими функциями генов и семействами заболеваний. Также применяется ранжировочная нормализация, чтобы оценки вели себя сопоставимо на разных глубинах онтологий, что позволяет честно сравнивать и ранжировать результаты.
Тестирование метода на сверенных базах данных
Чтобы оценить, дают ли результаты ASEA биологически значимые результаты, авторы сравнивают свои топовые ассоциации с записями в экспертно курируемых ресурсах, таких как Comparative Toxicogenomics Database и DisGeNET. Они обнаруживают, что ASEA воспроизводит больше высококачественных известных ассоциаций, чем любой из классических алгоритмов по отдельности, при этом генерируя богатый набор дополнительных кандидатур. В сумме ASEA идентифицирует 185 заметных пар «ген—болезнь». Эти пары затем группируются в четыре категории: устоявшиеся связи, уже представленные в крупных базах; связи, сильно поддержанные недавними исследованиями, но ещё не курируемые; связи с лишь слабой или разрозненной поддержкой в базах данных; и чисто спекулятивные ассоциации без текущей поддержки, предложенные как гипотезы для будущих лабораторных или клинических исследований.
Что это означает для медицины будущего
Для неспециалистов ключевой вывод в том, что эта система предлагает более разумный способ чтения биомедицинской литературы в масштабах. Вместо того чтобы учитывать только явные упоминания гена и заболевания рядом друг с другом, она использует экспертные знания о том, как гены и заболевания организованы в семейства, чтобы усиливать многообещающие, но редкие сигналы. Получаемый балл ASEA не доказывает, что ген вызывает заболевание, но предоставляет прозрачный, статистически обоснованный краткий список кандидатов для дальнейшего изучения учёными и клиницистами. В долгосрочной перспективе такой майнинг с учётом онтологий может ускорить обнаружение биомаркеров, информировать персонализированную медицину и помочь превратить растущий поток биомедицинских текстов в практически применимые медицинские выводы.
Цитирование: Naqash, M.A., Amin, M., Uddin, J. et al. Ontology-driven association rule mining for biomedical entity relationships: integrating hierarchical knowledge to improve gene-disease discovery. Sci Rep 16, 13072 (2026). https://doi.org/10.1038/s41598-026-42584-y
Ключевые слова: ассоциации ген—болезнь, биомедицинский текстовой майнинг, онтологии, персонализированная медицина, вычислительная биология