Clear Sky Science · pl
Wydobywanie reguł asocjacyjnych sterowane ontologią dla relacji między jednostkami biomedycznymi: integracja wiedzy hierarchicznej w celu poprawy odkrywania związków gen–choroba
Dlaczego ukryte powiązania gen–choroba mają znaczenie
Nowoczesna medycyna coraz bardziej zależy od ustalania, które geny są związane z określonymi chorobami. Te powiązania mogą wyjaśniać, dlaczego pojawiają się choroby, wskazywać nowe cele terapeutyczne i identyfikować osoby o wyższym ryzyku. Większość narzędzi komputerowych skupia się jednak na poszukiwaniu genów i chorób występujących razem w tym samym zdaniu lub artykule, przez co pomija wiele subtelnych, lecz istotnych związków. W pracy tej przedstawiono nową metodę eksploracji literatury biomedycznej, która wykorzystuje hierarchie wiedzy tworzone przez ekspertów, aby bardziej wiarygodnie odkrywać zarówno dobrze znane, jak i przeoczone relacje gen–choroba.
Od surowego tekstu do kandydatów na powiązania
Autorzy zaczynają od zgromadzenia dużego zbioru artykułów naukowych z PubMed i podziału każdego artykułu na zdania. Każde zdanie traktowane jest jak mały „koszyk” elementów, który może zawierać jedną lub więcej nazw genów oraz jedną lub więcej nazw chorób. Korzystając z ustalonych algorytmów eksploracji danych (Apriori, FP-Growth i Eclat), przeszukują miliony takich koszyków w poszukiwaniu par gen–choroba, które pojawiają się razem częściej niż można by oczekiwać przypadkowo. Ten pierwszy etap, nazwany asocjacją specyficzną dla encji, wychwytuje bezpośrednie współwystępowania, na których opiera się większość istniejących narzędzi. Już na tym etapie ujawnia się tysiące potencjalnych powiązań, choć preferowane są geny dobrze zbadane i powszechne choroby dominujące w literaturze.
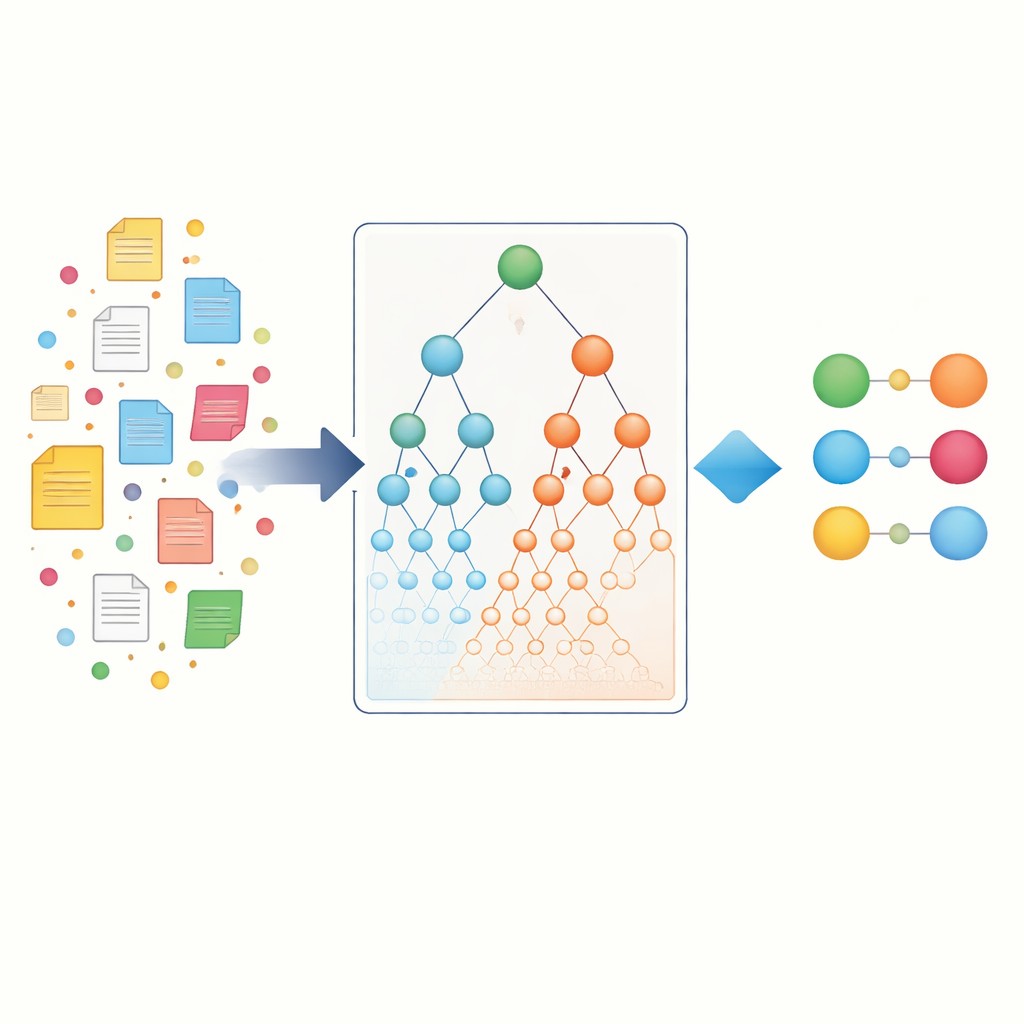
Wykorzystanie biologicznych hierarchii jako mapy
Aby wyjść poza proste zliczanie słów, badacze sięgają po biologiczne „mapy” zwane ontologiami. Ontologia genów (Gene Ontology) opisuje, co geny robią i gdzie działają w komórce, natomiast Ontologia chorób porządkuje choroby w rodziny i podtypy. W tych hierarchiach specyficzne terminy, na przykład rzadka padaczka, leżą pod szerszymi rodzicami jak „choroba neurologiczna”. Kluczowa idea polega na tym, że jeśli dany gen jest silnie powiązany z bardzo konkretną chorobą, a ta choroba należy do większej rodziny, to gen prawdopodobnie ma pewien związek także z tą całą rodziną. Autorzy sformalizowali to, tworząc hierarchiczne asocjacje ontologiczne, które propagują dowody w górę przez terminy rodzicielskie zarówno po stronie genu, jak i choroby, a także pośrednio wychwytują „rodzeństwo” dzielące wspólnego rodzica.
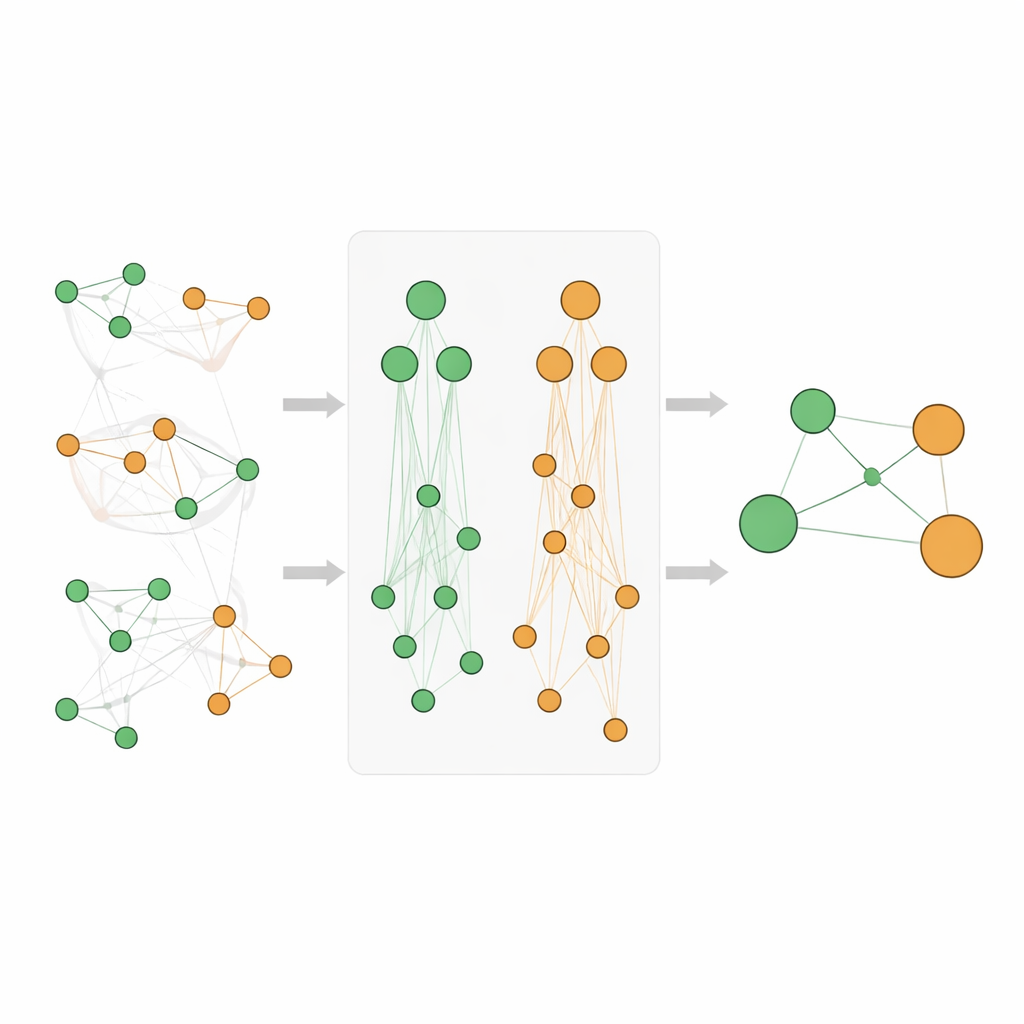
Mieszanie dowodów bezpośrednich z odziedziczonymi sygnałami
Proste sumowanie zliczeń z wielu poziomów hierarchii może zniekształcać wyniki, zwłaszcza że bardzo ogólne terminy, takie jak „rak”, pojawiają się niezwykle często. Zespół zaprojektował więc staranny system punktacji. Używają standardowej miary z eksploracji danych, zwanej lift, aby oszacować, jak silnie gen i choroba są powiązane ponad przypadkowość, a następnie przekształcają te wartości, by zmniejszyć skośność i uczynić je porównywalnymi. Nowy wynik Athar Semantic-Enriched Association (ASEA) łączy trzy składniki: bezpośrednie powiązanie gen–choroba, powiązania między genem a szerszymi rodzinami chorób oraz powiązania między szerszymi funkcjami genów a rodzinami chorób. Zastosowano też normalizację opartą na rangach, dzięki czemu wyniki zachowują porównywalne zachowanie na różnych głębokościach ontologii, co umożliwia uczciwe porównania i rankowanie.
Testowanie metody względem zaufanych baz danych
Aby ocenić, czy ASEA generuje biologicznie istotne wyniki, autorzy porównali swoje wysoko oceniane asocjacje z wpisami w zasobach kuratorowanych przez ekspertów, takich jak Comparative Toxicogenomics Database i DisGeNET. Stwierdzili, że ASEA odzyskuje więcej wysokiej jakości znanych powiązań niż którykolwiek z klasycznych algorytmów stosowanych samodzielnie, jednocześnie generując bogaty zestaw dodatkowych kandydatów. Łącznie ASEA identyfikuje 185 godnych uwagi par gen–choroba. Zostały one następnie pogrupowane w cztery kategorie: dobrze ugruntowane powiązania już obecne w głównych bazach; powiązania silnie poparte przez niedawne badania, lecz jeszcze nie zkuratowane; związki z jedynie słabym lub rozproszonym wsparciem w bazach danych; oraz czysto spekulatywne asocjacje bez obecnego poparcia, proponowane jako hipotezy do przyszłych badań laboratoryjnych lub klinicznych.
Co to oznacza dla przyszłej medycyny
Dla osób nie będących specjalistami kluczowy przekaz jest taki, że ta metoda oferuje mądrzejszy sposób przeglądania literatury biomedycznej na dużą skalę. Zamiast zliczać wyłącznie oczywiste wzmianki genu i choroby obok siebie, wykorzystuje wiedzę ekspercką o tym, jak geny i choroby są zorganizowane w rodziny, aby wzmocnić obiecujące, lecz rzadkie sygnały. Otrzymany wynik ASEA nie dowodzi, że gen powoduje chorobę, ale dostarcza przejrzystej, statystycznie ugruntowanej krótkiej listy kandydatów do dalszych badań przez naukowców i klinicystów. W dłuższej perspektywie takie wydobywanie uwzględniające ontologie może przyspieszyć odkrywanie biomarkerów, wspierać medycynę precyzyjną i pomóc przekształcić narastający potok tekstów biomedycznych w użyteczne wnioski medyczne.
Cytowanie: Naqash, M.A., Amin, M., Uddin, J. et al. Ontology-driven association rule mining for biomedical entity relationships: integrating hierarchical knowledge to improve gene-disease discovery. Sci Rep 16, 13072 (2026). https://doi.org/10.1038/s41598-026-42584-y
Słowa kluczowe: powiązania gen–choroba, wydobywanie tekstów biomedycznych, ontologie, medycyna precyzyjna, biologia obliczeniowa