Clear Sky Science · sv
Populationsskillnader i kromosom 22q11.2-duplicationsstruktur predisponerar olika för mikroutdelning och inversion
Varför denna kromosomhotspot spelar roll
Vissa personer föds utan en liten bit av kromosom 22, en förändring som kan leda till hjärtfel, inlärningssvårigheter, ansiktsavvikelser och en högre risk för schizofreni. Detta tillstånd, kallat 22q11.2 deletionssyndrom, är ett av de vanligaste kända genetiska syndromen. Det är dock märkligt mindre vanligt bland personer med afrikanskt ursprung. Denna studie undersöker den detaljerade strukturen i DNA i detta kromosomområde och visar hur subtila skillnader mellan populationer kan ändra sannolikheten för farliga brott, omkastningar och förluster av genetiskt material.
Ett skört stycke upprepat DNA
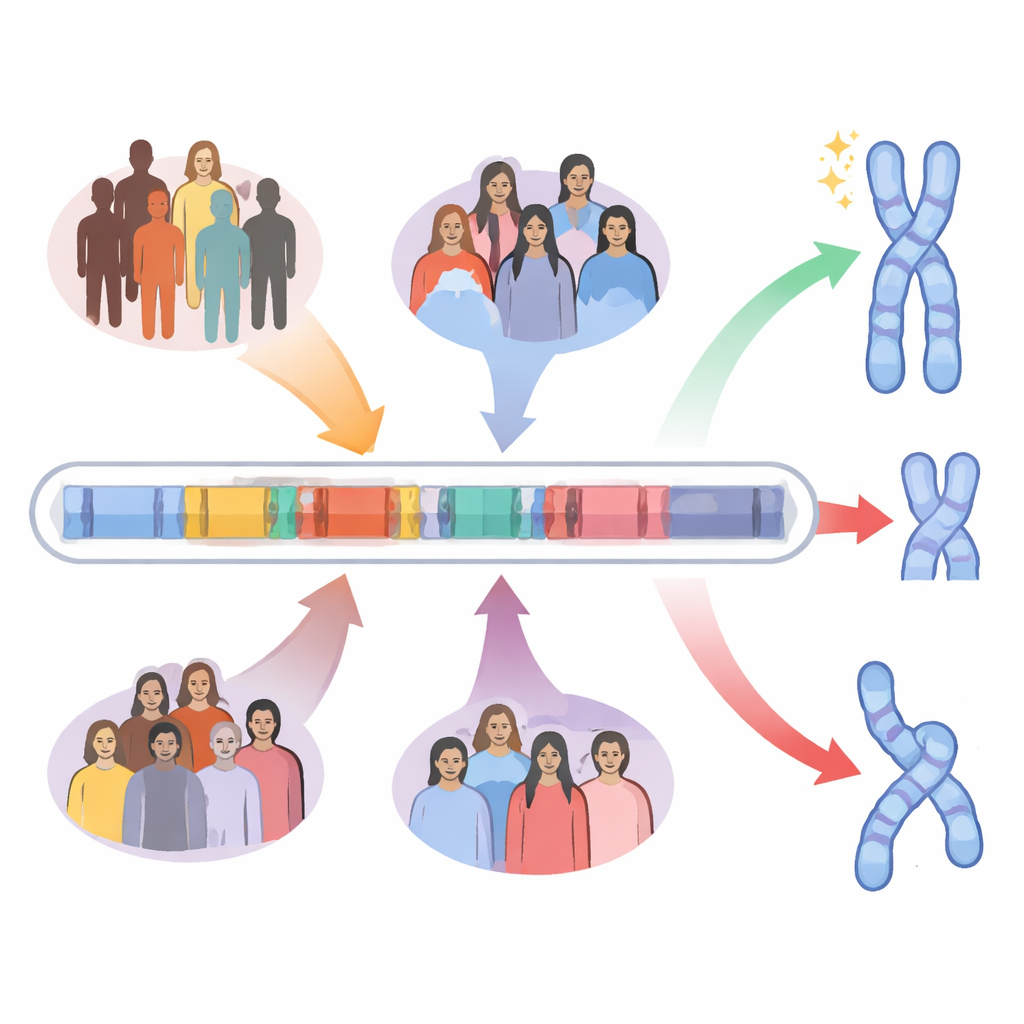
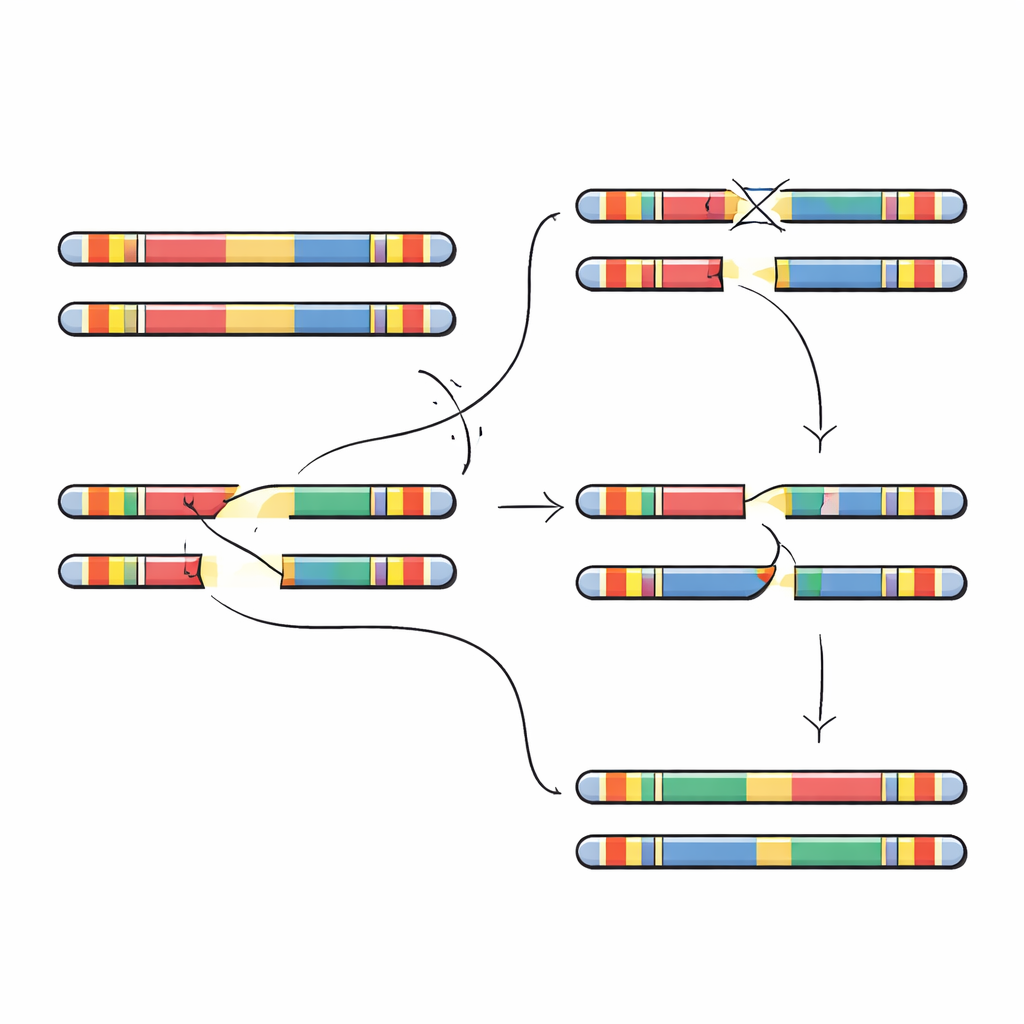
Författarna fokuserar på ett 5 miljoner bokstäver långt avsnitt av DNA på kromosom 22 som kallas 22q11.2. Detta område är fullt av stora, nästan identiska upprepade segment av DNA, så kallade low-copy repeats. Dessa repetitioner fungerar som liknande stycken i en bok: när cellerna bildar ägg eller spermier kan kopieringsmaskineriet av misstag rada upp fel upprepningar och byta bitar mellan dem. Den processen, kallad icke-allel homolog rekombination, kan ta bort sektioner, duplicera dem eller vända dem. De flesta fall av 22q11.2 deletionssyndrom uppstår när två särskilda repetitionsblock, benämnda A och D, felparar och tar bort ett ungefär 3 miljoner bokstäver långt segment som innehåller dussintals gener viktiga för utveckling och hjärnfunktion.
Läser området från ena änden till den andra
Till nyligen var denna del av kromosom 22 för repetitiv och komplex för att läsas tydligt med standard-DNA-sekvensering. Forskarna använde nya långläsningstekniker som kan följa DNA-sträckor tiotusentals bokstäver långa, i kombination med förbättrad sammanställningsprogramvara, för att återskapa 135 kompletta versioner av detta kromosomsegment från människor runt om i världen, plus flera aparter. De upptäckte 63 distinkta strukturella ”haplotyper” — olika sätt som repetitionsblocken i region A är ordnade och storleksvarierade — med mer än elva gånger skillnad i längd. Mycket av denna mångfald kommer från en kärnupprepad enhet på cirka 105 000 bokstäver, inramad av kortare upprepade delar. Denna kärnenhet har multiplicerat och blandats specifikt hos människor under det senaste miljonen åren, vilket gör vår version av 22q11.2 mycket mer invecklad än hos schimpanser, gorillor eller orangutanger.
Populationsskillnader i ett genetiskt minerfält
När teamet jämförde mänskliga grupper fann de att individer med afrikanskt ursprung tenderade att ha längre, mer repetitionsrika versioner av block A än icke‑afrikaner. Kontrarintuitivt placerar dessa längre strukturer ofta nyckelupprepningar i motsatta orienteringar i förhållande till deras partners i block D. I den konfigurationen tenderar felparning att ge upphov till ofarliga omkastningar, eller inversioner, av DNA-segment snarare än stora deletioner som tar bort gener. Genom att använda både inom-kromosom- och mellan-kromosom-jämförelser av de kärn‑105 000‑bokstavs upprepningarna byggde författarna en rangordning av haplotyper som är mer benägna att ge deletioner respektive inversioner. Afrikanska haplotyper var signifikant berikade för arkitekturer som förutspås skydda mot den klassiska deletionen, medan östasiatiska haplotyper var berikade för strukturer som förutspås gynna deletioner.
Spåra verkliga omkastningar och förluster
För att testa dessa förutsägelser sökte forskarna efter stora inversioner — segment på flera miljoner bokstäver vända från ena änden till den andra — i hundratals genom. De identifierade flera distinkta inversionstyper som spänner över 22q11.2-regionen. Var och en var ovanlig i stort, men de flesta hittades hos personer med afrikanskt eller admixed amerikanskt ursprung, vilket stöder idén att deras lokala DNA‑layout gynnar inversioner framför deletioner. Teamet zoomade sedan in på fyra familjer där ett barn hade en ny 22q11.2-deletion som inte fanns hos någon av föräldrarna. Genom att fullt sammanställa föräldrarnas och barnens kromosom 22-segment kunde de precisera var brottet och den felaktiga reparationen inträffade. I samtliga fall hamnade deletionsbrytningarna inom den 105 000‑bokstavs upprepningsenheten, men de exakta positionerna varierade och föll i små områden av nästan perfekt matchad sekvens som är särskilt benägna att felpara.
Vad detta betyder för risk och diagnostik
Tillsammans visar fynden att inte alla versioner av detta kromosomområde är lika sköra på samma sätt. Vissa arkitekturer förskjuter systemet mot omkastningar av DNA, vilket ofta lämnar det övergripande geninnehållet intakt, medan andra lättare ger upphov till genförlorande deletioner. Eftersom de skyddande arkitekturerna är vanligare hos personer med afrikanskt ursprung hjälper detta till att förklara varför 22q11.2 deletionssyndrom observerats mindre ofta i dessa populationer. Samtidigt är arkitekturer som förutspås vara mer benägna för deletioner vanligare i östasiatiska genom, vilket antyder att noggrann screening i dessa grupper kan vara särskilt viktig. Mer övergripande visar arbetet hur helhetsläsning av komplexa regioner i genomet kan avslöja dolda strukturella skillnader som formar vem som i större eller mindre utsträckning löper risk att drabbas av allvarliga genetiska sjukdomar.
Citering: Porubsky, D., Yoo, D., Koundinya, N. et al. Population differences of chromosome 22q11.2 duplication structure predispose differentially to microdeletion and inversion. Nat Commun 17, 3701 (2026). https://doi.org/10.1038/s41467-026-71905-y
Nyckelord: 22q11.2 deletionssyndrom, kromosom strukturell variation, segmentdupliceringar, populationsgenomik, genominstabilitet