Clear Sky Science · es
Diferencias poblacionales en la estructura de la duplicación del cromosoma 22q11.2 predisponen de forma diferente a microdeleciones e inversiones
Por qué importa este punto caliente cromosómico
Algunas personas nacen sin un pequeño fragmento del cromosoma 22, un cambio que puede provocar defectos cardíacos, dificultades de aprendizaje, rasgos faciales diferentes y un mayor riesgo de esquizofrenia. Esta afección, denominada síndrome de deleción 22q11.2, es uno de los trastornos genéticos conocidos más comunes. Sin embargo, resulta curiosamente menos frecuente en personas de ascendencia africana. Este estudio investiga la estructura fina del ADN en esta región cromosómica, mostrando cómo las diferencias sutiles entre poblaciones pueden alterar las probabilidades de roturas peligrosas, inversiones y pérdidas de material genético.
Un tramo frágil de ADN repetido
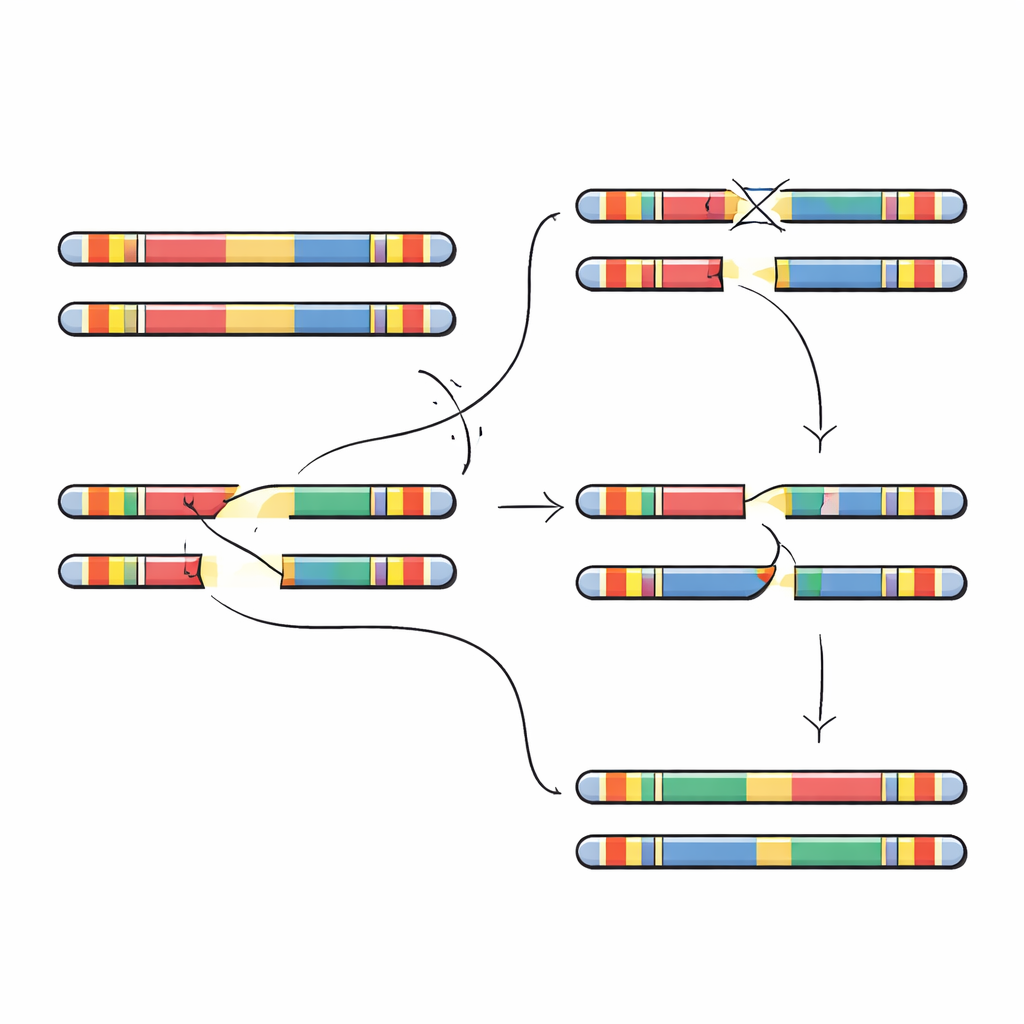
Los autores se centran en un tramo de 5 millones de letras de ADN en el cromosoma 22 llamado 22q11.2. Esta región está repleta de grandes segmentos repetidos casi idénticos, conocidos como repeticiones de baja copia. Estas repeticiones actúan como párrafos de aspecto similar en un libro: cuando las células forman óvulos o espermatozoides, la maquinaria de copia puede alinear por error repeticiones equivocadas y canjear fragmentos entre ellas. Ese proceso, llamado recombinación homóloga no alélica, puede eliminar secciones, duplicarlas o invertirlas. La mayoría de los casos del síndrome de deleción 22q11.2 se originan cuando dos bloques de repeticiones concretos, denominados A y D, se emparejan mal y eliminan un segmento de aproximadamente 3 millones de letras que contiene docenas de genes importantes para el desarrollo y la función cerebral.
Leer la región de un extremo al otro
Hasta hace poco, esta parte del cromosoma 22 era demasiado repetitiva y compleja para leerse con claridad con la secuenciación estándar. Los investigadores utilizaron nuevas tecnologías de lecturas largas que pueden seguir tramos de ADN de decenas de miles de letras, combinadas con software de ensamblaje mejorado, para reconstruir 135 versiones completas de este segmento cromosómico procedentes de personas de todo el mundo, además de varias especies de simios. Descubrieron 63 «haplotipos» estructurales distintos—diferentes maneras en que los bloques repetidos en la región A están organizados y dimensionados—con variaciones de más de once veces en longitud. Gran parte de esta diversidad proviene de una unidad repetida central de unas 105 000 letras, flanqueada por piezas repetidas más cortas. Esta unidad central se ha multiplicado y reorganizado específicamente en humanos durante el último millón de años, haciendo que nuestra versión de 22q11.2 sea mucho más compleja que la de chimpancés, gorilas u orangutanes.
Diferencias poblacionales en un campo minado genético
Al comparar grupos humanos, el equipo observó que las personas de ascendencia africana tendían a tener versiones más largas y ricas en repeticiones del bloque A que los no africanos. Contraintuitivamente, estas estructuras más largas a menudo colocan repeticiones clave en orientaciones opuestas respecto a sus homólogas en el bloque D. En esa disposición, el emparejamiento erróneo tiende a producir inversiones inocuas —o volteos— de segmentos de ADN en lugar de grandes deleciones que eliminan genes. Usando comparaciones tanto dentro del mismo cromosoma como entre cromosomas de las repeticiones centrales de 105 000 letras, los autores construyeron una clasificación de haplotipos más propensos a producir deleciones frente a aquellos más propensos a originar inversiones. Los haplotipos africanos estaban significativamente enriquecidos en arquitecturas predichas como protectoras frente a la deleción clásica, mientras que los haplotipos del este asiático estaban enriquecidos en estructuras predichas como favorables a las deleciones.
Rastreando inversiones y pérdidas en el mundo real
Para poner a prueba estas predicciones, los investigadores buscaron grandes inversiones—segmentos de varios millones de letras volteados de extremo a extremo—en cientos de genomas. Identificaron varios tipos de inversión distintos que abarcan la región 22q11.2. Cada una era rara en términos absolutos, pero la mayoría se encontró en personas de ascendencia africana o en individuos americanos mestizos, lo que concuerda con la idea de que la disposición local del ADN favorece inversiones en lugar de deleciones. El equipo examinó luego cuatro familias en las que un niño presentaba una nueva deleción 22q11.2 no presente en ninguno de los progenitores. Al ensamblar por completo los segmentos del cromosoma 22 de padres e hijos, pudieron localizar con precisión dónde ocurrió la rotura y la reparación defectuosa. En todos los casos, los puntos de ruptura de la deleción cayeron dentro de la unidad repetida de 105 000 letras, aunque las posiciones exactas variaron, localizándose en tramos pequeños de secuencia casi perfectamente coincidente que son especialmente propensos al emparejamiento erróneo.
Qué significa esto para el riesgo y el diagnóstico
En conjunto, los hallazgos muestran que no todas las versiones de esta región cromosómica son igual de frágiles de la misma manera. Algunas arquitecturas sesgan el sistema hacia inversiones del ADN, que a menudo mantienen intacto el contenido genético global, mientras que otras producen con más facilidad deleciones que eliminan genes. Dado que las arquitecturas protectoras son más comunes en personas de ascendencia africana, esto ayuda a explicar por qué el síndrome de deleción 22q11.2 se ha observado con menor frecuencia en estas poblaciones. Al mismo tiempo, las arquitecturas predichas como más propensas a deleciones son más frecuentes en genomas del este asiático, lo que sugiere que un cribado cuidadoso en estos grupos podría ser especialmente importante. En términos más generales, el trabajo demuestra cómo leer regiones complejas del genoma de extremo a extremo puede revelar diferencias estructurales ocultas que determinan quién tiene más o menos probabilidades de sufrir trastornos genéticos graves.
Cita: Porubsky, D., Yoo, D., Koundinya, N. et al. Population differences of chromosome 22q11.2 duplication structure predispose differentially to microdeletion and inversion. Nat Commun 17, 3701 (2026). https://doi.org/10.1038/s41467-026-71905-y
Palabras clave: Síndrome de deleción 22q11.2, variación estructural cromosómica, duplicaciones segmentarias, genómica poblacional, inestabilidad genómica