Clear Sky Science · pl
Różnice populacyjne w strukturze duplikacji chromosomu 22q11.2 sprzyjają w różnym stopniu mikrodelecjom i inwersjom
Dlaczego to miejsce na chromosomie ma znaczenie
Niektórzy ludzie rodzą się bez niewielkiego fragmentu chromosomu 22 — zmiana ta może powodować wady serca, trudności w nauce, różnice w rysach twarzy oraz zwiększone ryzyko schizofrenii. Stan ten, zwany zespołem delecji 22q11.2, jest jednym z najczęściej rozpoznawanych zaburzeń genetycznych. Zaskakujące jest jednak, że występuje rzadziej u osób pochodzenia afrykańskiego. Badanie to analizuje drobne różnice w strukturze DNA w tym rejonie chromosomu i pokazuje, jak subtelne różnice między populacjami mogą zmieniać prawdopodobieństwo powstawania niebezpiecznych pęknięć, odwróceń i utrat materiału genetycznego.
Wrażliwy odcinek powtarzalnego DNA
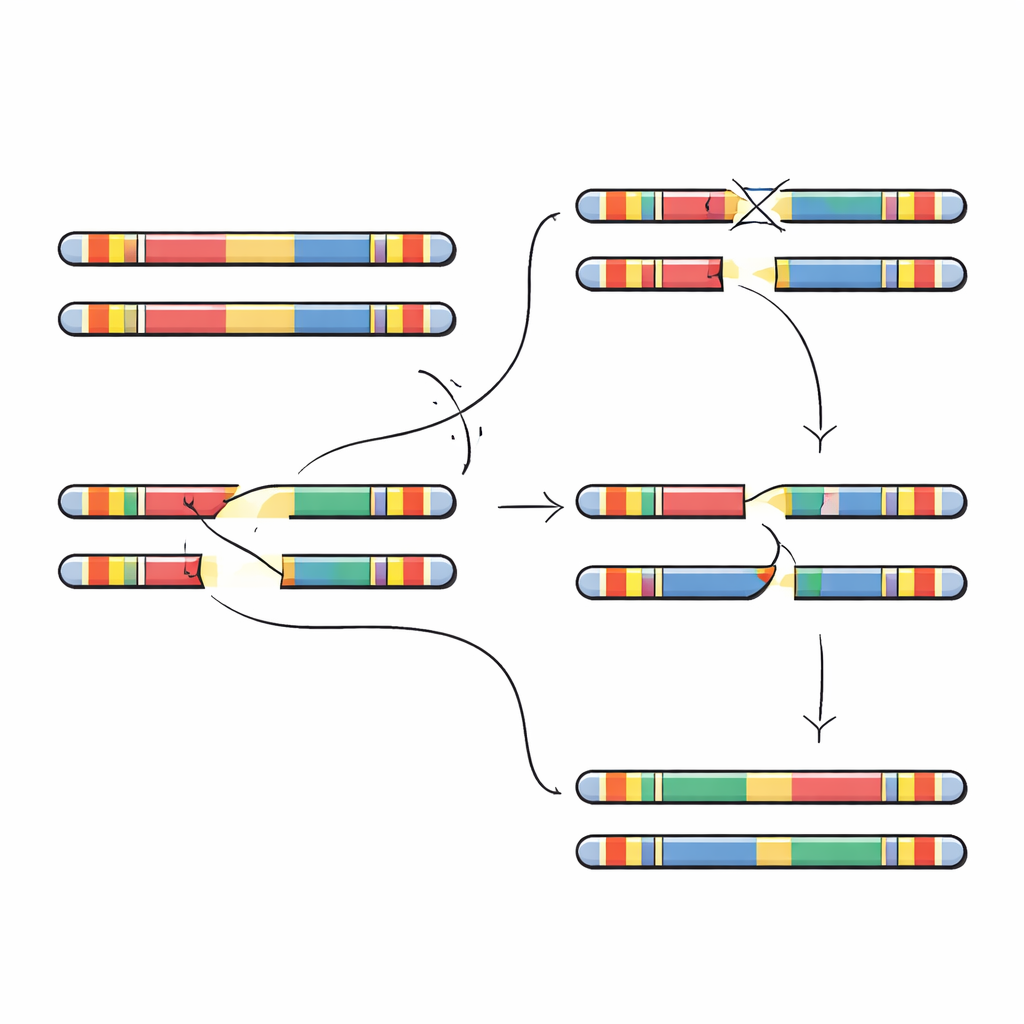
Autorzy koncentrują się na 5‑milionowym fragmencie DNA na chromosomie 22, oznaczonym jako 22q11.2. Region ten jest wypełniony dużymi, niemal identycznymi powtórzeniami DNA, zwanymi powtórzeniami o niskim kopiowaniu (low-copy repeats). Te powtórzenia działają jak podobnie wyglądające akapity w książce: gdy komórki tworzą komórki jajowe lub plemniki, mechanizmy kopiujące mogą przypadkowo wyrównać niewłaściwe powtórzenia i wymienić między nimi fragmenty. Proces ten, zwany rekombinacją homologiczną niealleliczną, może usuwać fragmenty, je powielać lub odwracać. Większość przypadków zespołu delecji 22q11.2 powstaje, gdy dwa konkretne bloki powtórzeń, oznaczone jako A i D, źle sie parują i usuwają około 3‑milionowy fragment zawierający dziesiątki genów ważnych dla rozwoju i funkcjonowania mózgu.
Czytanie regionu od początku do końca
Jeszcze niedawno ta część chromosomu 22 była zbyt powtarzalna i zbyt złożona, by odczytać ją czysto za pomocą standardowego sekwencjonowania DNA. Naukowcy zastosowali nowe technologie długiego odczytu, które potrafią śledzić odcinki DNA o długości dziesiątek tysięcy nukleotydów, w połączeniu z ulepszonym oprogramowaniem do montażu, aby odbudować 135 pełnych wersji tego segmentu chromosomu z próbek ludzi z całego świata oraz kilku gatunków małp. Odkryli 63 odrębne strukturalne „haplotypy” — różne sposoby, w jakie bloki powtórzeń w regionie A są ułożone i mają rozmaitą wielkość — różniące się ponad jedenaście razy pod względem długości. Znaczna część tej różnorodności pochodzi z rdzennej jednostki powtarzalnej o długości około 105 000 nukleotydów, otoczonej krótszymi powtórzonymi fragmentami. Ta jednostka rdzenna rozmnożyła się i przemieszała specyficznie u ludzi w ciągu ostatniego miliona lat, co sprawiło, że nasza wersja 22q11.2 jest znacznie bardziej złożona niż u szympansów, goryli czy orangutanów.
Różnice populacyjne na genetycznej minie
W porównaniu grup ludzkich badacze stwierdzili, że osoby pochodzenia afrykańskiego mają zwykle dłuższe, bardziej bogate w powtórzenia wersje bloku A niż osoby spoza Afryki. Paradoksalnie, te dłuższe struktury często ustawiają kluczowe powtórzenia w przeciwnych orientacjach względem ich partnerów w bloku D. W takim układzie błędne parowanie sprzyja powstawaniu niegroźnych odwróceń (inwersji) segmentów DNA zamiast dużych delecji usuwających geny. Wykorzystując porównania w obrębie chromosomu i między chromosomami rdzennej jednostki 105 000 nukleotydów, autorzy opracowali ranking haplotypów bardziej skłonnych do wywoływania delecji versus tych, które częściej prowadzą do inwersji. Haplotypy występujące w Afryce były istotnie wzbogacone w architektury przewidywane jako chroniące przed klasyczną delecją, natomiast haplotypy w Azji Wschodniej były wzbogacone w struktury predysponujące do delecji.
Śledzenie rzeczywistych odwróceń i utrat
Aby sprawdzić te przewidywania, badacze przeszukali setki genomów w poszukiwaniu dużych inwersji — segmentów o długości milionów nukleotydów odwróconych końcem do końca. Zidentyfikowali kilka różnych typów inwersji obejmujących region 22q11.2. Każda z nich była ogólnie rzadka, ale większość występowała u osób pochodzenia afrykańskiego lub z admiksji amerykańskiej, co zgadza się z hipotezą, że lokalna organizacja DNA sprzyja inwersjom zamiast delecji. Zespół przyjrzał się następnie czterem rodzinom, w których u dziecka wystąpiła nowa delecja 22q11.2 nieobecna u żadnego z rodziców. Dzięki pełnemu zmontowaniu segmentów chromosomu 22 u rodziców i dzieci mogli precyzyjnie ustalić miejsce pęknięcia i nieprawidłowej naprawy. W każdym przypadku punkty przerwania delecji przypadały w obrębie jednostki powtarzalnej o długości 105 000 nukleotydów, ale dokładne pozycje różniły się i występowały w małych odcinkach niemal idealnie dopasowanej sekwencji, które są szczególnie podatne na błędne parowanie.
Co to oznacza dla ryzyka i diagnozy
W sumie wyniki pokazują, że nie wszystkie wersje tego regionu chromosomu są równie kruche w ten sam sposób. Niektóre architektury skłaniają system do odwróceń DNA, które często pozostawiają ogólną zawartość genów nienaruszoną, podczas gdy inne łatwiej prowadzą do delecji pozbawiających genów. Ponieważ ochronne architektury występują częściej u osób pochodzenia afrykańskiego, pomaga to wyjaśnić, dlaczego zespół delecji 22q11.2 obserwuje się rzadziej w tych populacjach. Jednocześnie architektury przewidywane jako bardziej podatne na delecje są częstsze w genomach Azji Wschodniej, co sugeruje, że w tych grupach szczególnie istotne może być staranne badanie przesiewowe. Szerzej rzecz biorąc, praca ta pokazuje, że odczytywanie złożonych regionów genomu „od końca do końca” może ujawnić ukryte różnice strukturalne, które kształtują, kto jest bardziej lub mniej narażony na poważne zaburzenia genetyczne.
Cytowanie: Porubsky, D., Yoo, D., Koundinya, N. et al. Population differences of chromosome 22q11.2 duplication structure predispose differentially to microdeletion and inversion. Nat Commun 17, 3701 (2026). https://doi.org/10.1038/s41467-026-71905-y
Słowa kluczowe: zespół delecji 22q11.2, strukturalna zmienność chromosomowa, duplikacje segmentalne, genomika populacyjna, niestabilność genomu