Clear Sky Science · it
Differenze di popolazione nella struttura di duplicazione del cromosoma 22q11.2 predispongono in modo differenziale a microdelezioni e inversioni
Perché questo hotspot cromosomico è importante
Alcune persone nascono mancanti di un piccolo tratto del cromosoma 22, una modifica che può causare difetti cardiaci, difficoltà di apprendimento, differenze facciali e un rischio maggiore di schizofrenia. Questa condizione, chiamata sindrome da delezione 22q11.2, è uno dei disturbi genetici noti più comuni. Tuttavia è sorprendentemente meno frequente nelle persone di ascendenza africana. Questo studio approfondisce la struttura fine del DNA in questa regione cromosomica, mostrando come sottili differenze tra le popolazioni possano modificare la probabilità di rotture pericolose, inversioni e perdite di materiale genetico.
Un tratto fragile di DNA ripetuto
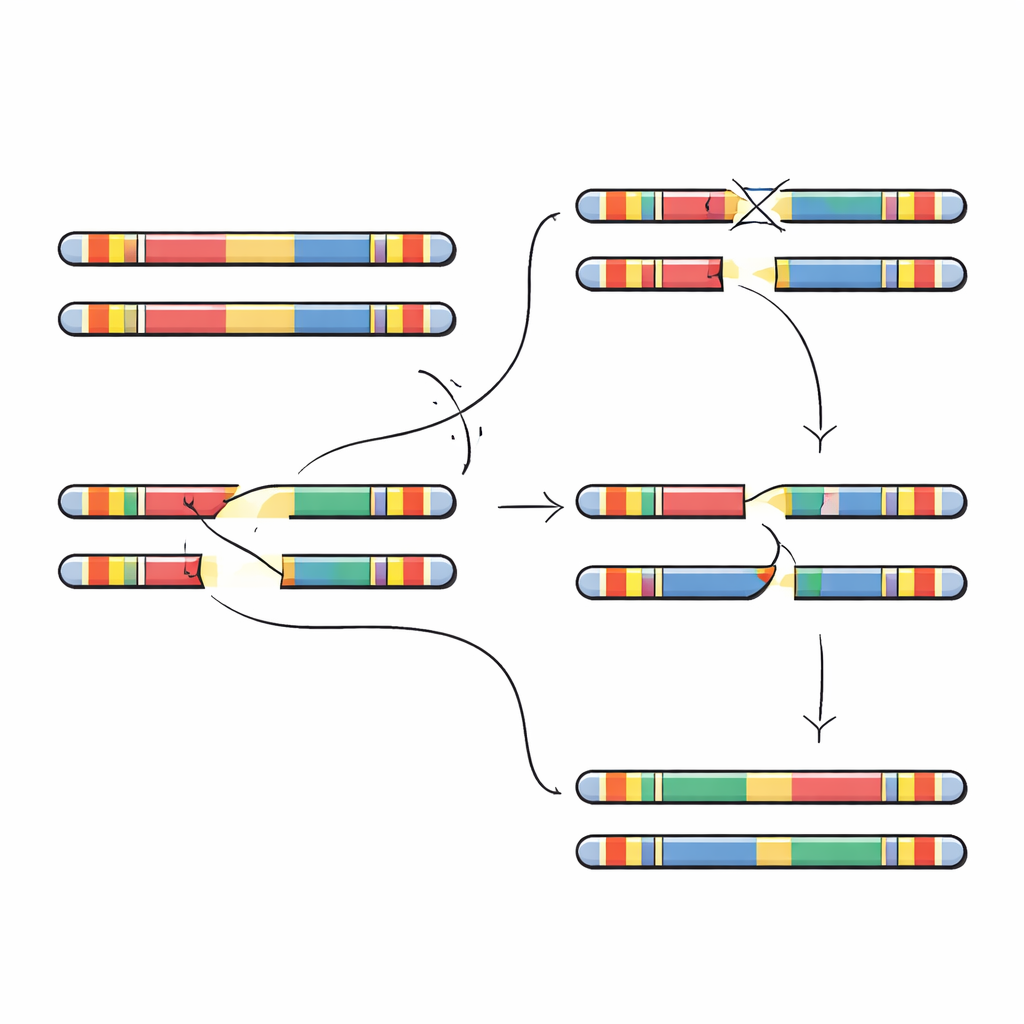
Gli autori si concentrano su un tratto di DNA lungo 5 milioni di lettere sul cromosoma 22 chiamato 22q11.2. Questa regione è piena di grandi segmenti ripetuti quasi identici, noti come low-copy repeats. Queste ripetizioni funzionano come paragrafi simili in un libro: quando le cellule producono ovuli o spermatozoi, la macchina di copiatura può allineare per errore ripetizioni sbagliate e scambiare pezzi tra di esse. Quel processo, chiamato ricombinazione omologa non allelica, può eliminare sezioni, duplicarle o capovolgerle. La maggior parte dei casi di sindrome da delezione 22q11.2 deriva da due blocchi di ripetizioni particolari, chiamati A e D, che si disallineano e rimuovono circa 3 milioni di lettere contenenti dozzine di geni importanti per lo sviluppo e la funzione cerebrale.
Leggere la regione da un capo all’altro
Fino a tempi recenti, questa parte del cromosoma 22 era troppo ripetitiva e complessa per essere letta con chiarezza con il sequenziamento standard. I ricercatori hanno usato nuove tecnologie di lettura lunga, in grado di seguire tratti di DNA lunghi decine di migliaia di lettere, combinate con software di assemblaggio migliorati, per ricostruire 135 versioni complete di questo segmento cromosomico provenienti da persone in tutto il mondo, oltre a diversi primati. Hanno scoperto 63 “aplotipi” strutturali distinti—diversi modi in cui i blocchi di ripetizione nella regione A sono organizzati e dimensionati—variando più di undici volte in lunghezza. Gran parte di questa diversità deriva da un’unità ripetuta centrale di circa 105.000 lettere, racchiusa tra pezzi ripetuti più corti. Questa unità centrale si è moltiplicata e rimescolata specificamente negli esseri umani nell’ultimo milione di anni, rendendo la nostra versione di 22q11.2 molto più elaborata rispetto a quella di scimpanzé, gorilla o oranghi.
Differenze di popolazione in un campo minato genetico
Confrontando i gruppi umani, il team ha osservato che gli individui di ascendenza africana tendevano ad avere versioni più lunghe e ricche di ripetizioni del blocco A rispetto ai non africani. Controintuitivamente, queste strutture più lunghe spesso collocano ripetizioni chiave in orientamenti opposti rispetto ai loro partner nel blocco D. In tale disposizione, il disallineamento tende a produrre capovolgimenti innocui, o inversioni, di segmenti di DNA anziché grandi delezioni che rimuovono geni. Usando confronti sia all’interno dello stesso cromosoma sia tra cromosomi delle ripetizioni centrali da 105.000 lettere, gli autori hanno costruito una graduatoria di aplotipi più propensi a dare delezioni rispetto a quelli più propensi a dare inversioni. Gli aplotipi africani risultavano significativamente arricchiti per architetture previste come protettive contro la delezione classica, mentre gli aplotipi dell’Asia orientale erano arricchiti per strutture previste favorire le delezioni.
Tracciare capovolgimenti e perdite nel mondo reale
Per verificare queste previsioni, i ricercatori hanno cercato grandi inversioni—segmenti di milioni di lettere capovolti da un capo all’altro—in centinaia di genomi. Hanno identificato diversi tipi di inversione distinti che attraversano la regione 22q11.2. Ciascuna era rara complessivamente, ma la maggior parte è stata trovata in persone di ascendenza africana o nelle popolazioni americane adatte, coerente con l’idea che la loro disposizione locale del DNA favorisca inversioni piuttosto che delezioni. Il team ha quindi esaminato quattro famiglie in cui un bambino presentava una nuova delezione 22q11.2 non presente in nessuno dei genitori. Assemblando completamente i segmenti cromosomici 22 di genitori e figli, hanno potuto individuare con precisione dove è avvenuta la rottura e la riparazione difettosa. In ogni caso, i punti di rottura delle delezioni ricadevano all’interno dell’unità ripetuta da 105.000 lettere, ma le posizioni esatte variavano, collocandosi in tratti di sequenza quasi perfettamente corrispondenti particolarmente soggetti al disallineamento.
Cosa significa per rischio e diagnosi
Nel complesso, i risultati mostrano che non tutte le versioni di questa regione cromosomica sono ugualmente fragili nello stesso modo. Alcune architetture spostano il sistema verso capovolgimenti del DNA, che spesso lasciano intatto il contenuto genico complessivo, mentre altre producono più facilmente delezioni che comportano perdita di geni. Poiché le architetture protettive sono più comuni nelle persone di ascendenza africana, ciò aiuta a spiegare perché la sindrome da delezione 22q11.2 è stata osservata meno frequentemente in queste popolazioni. Allo stesso tempo, le architetture previste come più inclini alle delezioni sono più frequenti nei genomi dell’Asia orientale, suggerendo che uno screening attento in questi gruppi potrebbe essere particolarmente importante. Più in generale, il lavoro dimostra come leggere regioni complesse del genoma da un estremo all’altro possa rivelare differenze strutturali nascoste che influenzano chi è più o meno probabile che sviluppi gravi disturbi genetici.
Citazione: Porubsky, D., Yoo, D., Koundinya, N. et al. Population differences of chromosome 22q11.2 duplication structure predispose differentially to microdeletion and inversion. Nat Commun 17, 3701 (2026). https://doi.org/10.1038/s41467-026-71905-y
Parole chiave: sindrome da delezione 22q11.2, variazione strutturale dei cromosomi, duplicazioni segmentali, genomica di popolazione, instabilità del genoma