Clear Sky Science · de
Bevölkerungsunterschiede in der Duplikationsstruktur auf Chromosom 22q11.2 prädisponieren unterschiedlich für Mikrodeletion und Inversion
Warum dieser Chromosomen-Hotspot wichtig ist
Manche Menschen werden mit einem kleinen fehlenden Abschnitt auf Chromosom 22 geboren, eine Veränderung, die zu Herzfehlern, Lernschwierigkeiten, Gesichtsauffälligkeiten und einem erhöhten Schizophrenierisiko führen kann. Diese Erkrankung, das 22q11.2-Delitionssyndrom, gehört zu den häufigsten bekannten genetischen Störungen. Rätselhafterweise tritt sie bei Menschen afrikanischer Abstammung seltener auf. Diese Studie untersucht die feine Struktur der DNA in diesem Chromosomenbereich und zeigt, wie subtile Unterschiede zwischen Populationen die Wahrscheinlichkeit für gefährliche Brüche, Umschläge und Verluste von Erbmaterial verändern können.
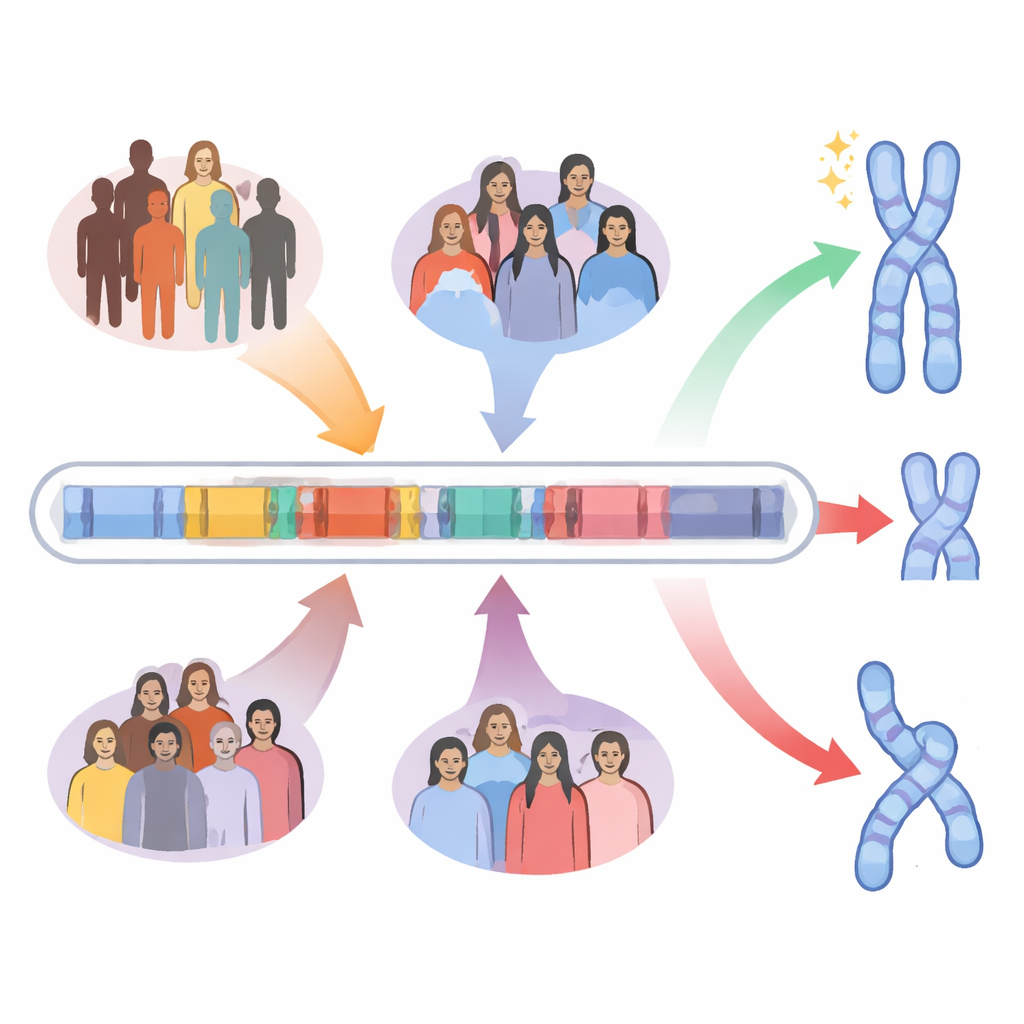
Eine fragile Strecke aus wiederholter DNA
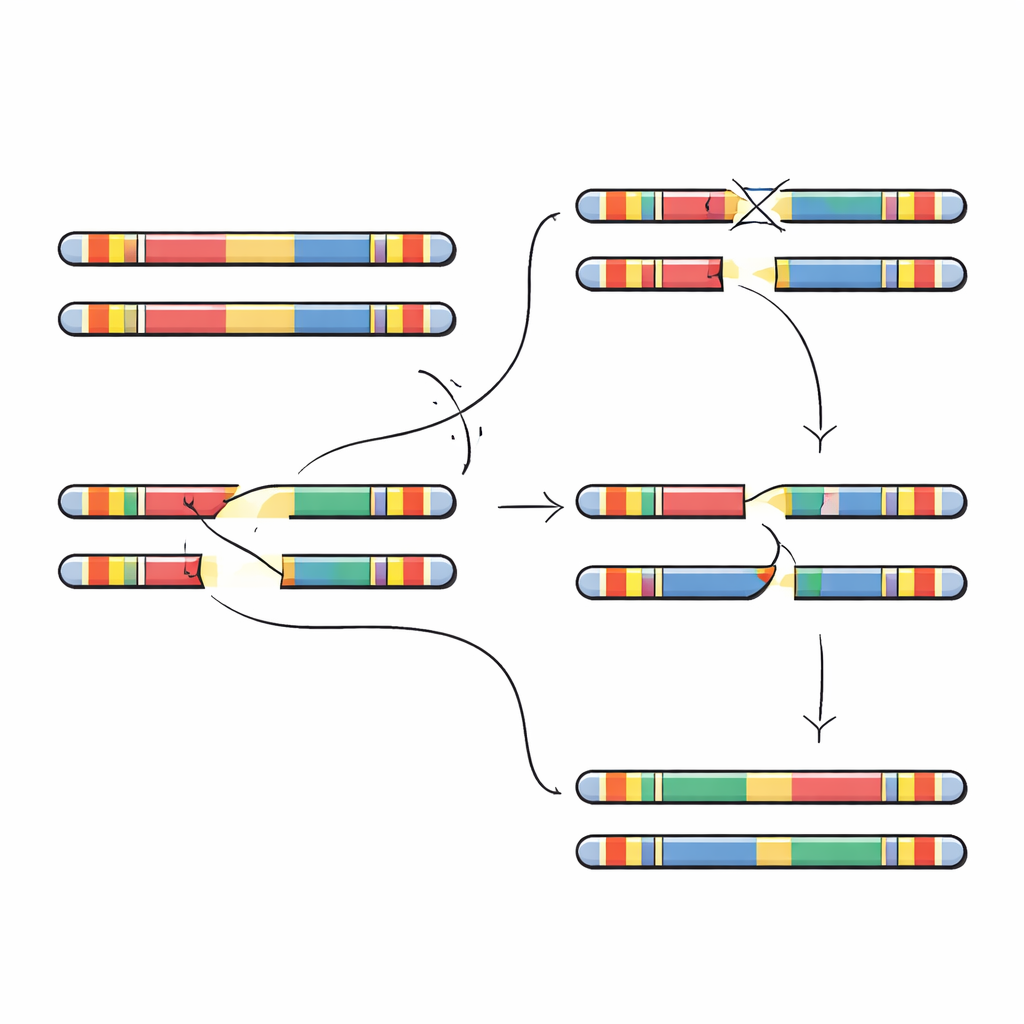
Die Autor:innen konzentrieren sich auf einen fünf Millionen Basenpaare langen Abschnitt auf Chromosom 22, genannt 22q11.2. Dieser Bereich ist voll mit großen, nahezu identischen Wiederholungssegmenten der DNA, den sogenannten Low-Copy-Repeats. Diese Wiederholungen wirken wie ähnlich aussehende Abschnitte in einem Buch: Wenn Zellen Eizellen oder Spermien bilden, kann die Kopiermaschine versehentlich die falschen Wiederholungen aneinander ausrichten und Stücke zwischen ihnen austauschen. Dieser Prozess, nicht-allelische homologe Rekombination genannt, kann Abschnitte löschen, duplizieren oder umdrehen. Die meisten Fälle des 22q11.2-Delitionssyndroms entstehen, wenn zwei bestimmte Wiederholungsblöcke, A und D genannt, falsch paaren und einen etwa drei Millionen Basenpaare langen Abschnitt entfernen, der Dutzende Gene enthält, die für Entwicklung und Gehirnfunktion wichtig sind.
Die Region komplett lesen
Bis vor kurzem war dieser Teil von Chromosom 22 zu repetitiv und komplex, um ihn mit Standard-DNA-Sequenzierung sauber zu lesen. Die Forschenden nutzten neue Langlese-Technologien, die Tausende bis Zehntausende Basenpaare lange DNA-Stücke verfolgen können, kombiniert mit verbesserter Assemblierungssoftware, um 135 vollständige Versionen dieses Chromosomenabschnitts von Menschen weltweit sowie von mehreren Menschenaffen zu rekonstruieren. Sie entdeckten 63 unterschiedliche strukturelle „Haplotypen“—verschiedene Weisen, wie die Wiederholungsblöcke in Region A angeordnet und dimensioniert sind—mit einer Variation der Länge um mehr als den Faktor elf. Ein Großteil dieser Vielfalt stammt von einer Kernwiederholungseinheit von etwa 105.000 Basenpaaren, eingefasst von kürzeren Wiederholungsstücken. Diese Kerneinheit hat sich spezifisch beim Menschen über die letzten eine Million Jahre vervielfacht und umgeordnet, wodurch unsere Version von 22q11.2 deutlich komplexer ist als die von Schimpansen, Gorillas oder Orang-Utans.
Bevölkerungsunterschiede in einem genetischen Minenfeld
Beim Vergleich menschlicher Gruppen fanden die Forschenden, dass Individuen afrikanischer Abstammung tendenziell längere, stärker wiederholungsreiche Versionen des Blocks A haben als Nicht-Afrikaner. Entgegen der Intuition bringen diese längeren Strukturen Schlüsselwiederholungen oft in entgegengesetzte Orientierungen im Vergleich zu ihren Gegenstücken in Block D. In dieser Anordnung führt falsches Paaren eher zu harmlosen Umkehrungen (Inversionen) von DNA-Segmenten als zu großen Deletionen, die Gene entfernen. Mit intra- und interchromosomalen Vergleichen der Kern-105.000-Basen-Paar-Wiederholungen bauten die Autor:innen ein Ranking von Haplotypen auf, die eher Deletionen erzeugen versus solchen, die eher Inversionen begünstigen. Afrikanische Haplotypen waren signifikant angereichert für Architekturen, die vor der klassischen Deletion schützen sollen, während ostasiatische Haplotypen für Strukturen angereichert waren, die Deletionen begünstigen sollen.
Verfolgen von realen Umschlägen und Verlusten
Um diese Vorhersagen zu testen, suchten die Forschenden in Hunderten von Genomen nach großen Inversionen—mehrere Millionen Basenpaare umfassende Segmente, die umgedreht wurden. Sie identifizierten mehrere unterschiedliche Inversionstypen, die die Region 22q11.2 überspannen. Jeder war insgesamt selten, doch die meisten wurden bei Menschen afrikanischer oder gemischter amerikanischer Abstammung gefunden, was zur Hypothese passt, dass ihre lokale DNA-Anordnung Inversionen gegenüber Deletionen begünstigt. Das Team zoomte dann auf vier Familien, in denen ein Kind eine neue 22q11.2-Deletion hatte, die bei keinem Elternteil vorhanden war. Durch vollständige Assemblierung der Chromosom-22-Segmente der Eltern und Kinder konnten sie genau feststellen, wo der Bruch und die fehlerhafte Reparatur stattfanden. In jedem Fall lagen die Deletionsbruchstellen innerhalb der 105.000-Basen-Paar-Wiederholungseinheit, die genauen Positionen variierten jedoch und fielen in kleine Strecken nahezu perfekt übereinstimmender Sequenz, die besonders anfällig für falsches Paaren sind.
Was das für Risiko und Diagnose bedeutet
In der Summe zeigen die Befunde, dass nicht alle Versionen dieses Chromosomenbereichs gleichermaßen fragil sind. Einige Architekturen verschieben die Tendenz des Systems hin zu DNA-Umkehrungen, die meist den Gesamtgenbestand intakt lassen, während andere leichter genverlierende Deletionen produzieren. Da die schützenden Architekturen bei Menschen afrikanischer Abstammung häufiger vorkommen, hilft das zu erklären, warum das 22q11.2-Delitionssyndrom in diesen Populationen seltener beobachtet wurde. Gleichzeitig sind Architekturen, die als deletionsanfälliger vorhergesagt werden, in ostasiatischen Genomen häufiger, was darauf hindeutet, dass gezielte Screenings in diesen Gruppen besonders wichtig sein könnten. Allgemeiner demonstriert die Arbeit, wie das lückenlose Lesen komplexer Regionen des Genoms verborgene strukturelle Unterschiede aufdecken kann, die beeinflussen, wer mit größerer oder geringerer Wahrscheinlichkeit schwere genetische Störungen erfährt.
Zitation: Porubsky, D., Yoo, D., Koundinya, N. et al. Population differences of chromosome 22q11.2 duplication structure predispose differentially to microdeletion and inversion. Nat Commun 17, 3701 (2026). https://doi.org/10.1038/s41467-026-71905-y
Schlüsselwörter: 22q11.2-Delitionssyndrom, strukturelle Variation des Chromosoms, segmentale Duplikationen, Populationsgenomik, Genominstabilität