Clear Sky Science · sv
H3K4me1 styr depositionen av H3K36me2 och H3K36me3 i landväxter
Hur växter minns och svarar
Växter kan inte fly från torka, värme eller årstidernas växlingar. Istället förlitar de sig på ett dolt lager av kemiska märkningar på sina DNA‑paketerande proteiner för att finjustera vilka gener som slås på eller av. Denna studie avslöjar hur ett sådant märke hos landväxter fungerar som en molekylär vägvisare och hjälper till att sätta ett annat märke som formar tillväxt, blomningstid och respons mot miljön.

En kod skriven på DNA‑paketeringen
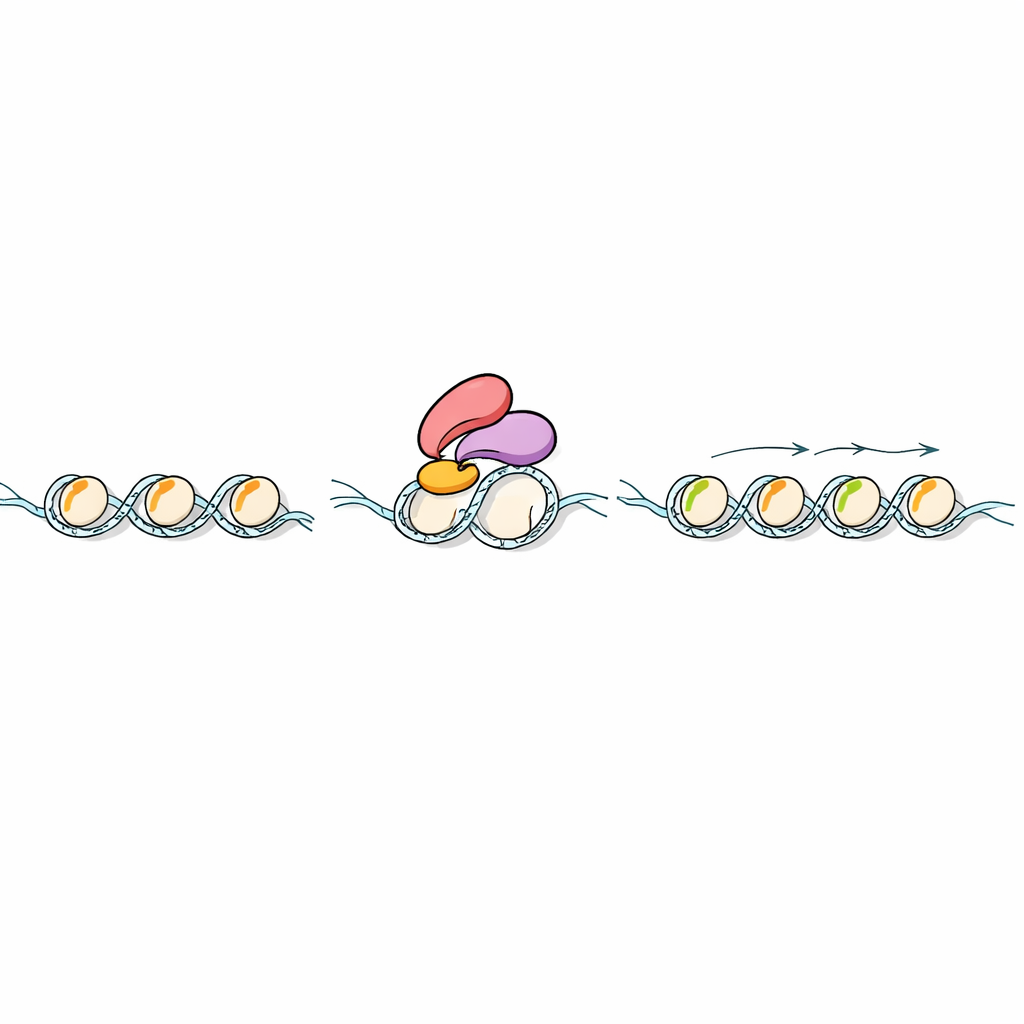
Inuti varje växtcell lindas DNA runt proteiner som kallas histoner och bildar pärlliknande strukturer längs den genetiska tråden. Dessa histoner bär små kemiska märken som tillsammans fungerar som en kod för genaktivitet. Forskarna fokuserade på två av dessa märkningar på histon H3, kända som H3K4me1 och H3K36me2/3. I djur är H3K4me1 berömt för att markera DNA‑avsnitt som stärker genaktivitet, så kallade enhancer‑regioner. Men i växter har dess roll varit gåtfull. Genom att jämföra alger, mossor, blommande växter, jäst, flugor, möss och människor visade forskarna att landväxter har ett särskilt mönster: H3K4me1 sprider sig över växtgenernas kroppar och uppvisar ett unikt samband med geners uttrycksstyrka.
Ett läsarprotein som känner igen det första märket
Kemiska märken på histoner betyder bara något om andra proteiner kan ”läsa” dem. Forskarna sökte i växtgenom efter proteiner med en särskild typ av läsarenhet kallad PHD‑finger, som är känd för att känna igen H3K4‑modifieringar. De fokuserade på ett risprotein kallat Early heading date 3 (Ehd3), redan känt för att påverka blomningstid. Biokemiska tester med artificiella histonfragment visade att Ehd3 starkt föredrar H3K4me1 framför andra närliggande märken. Högupplöst strukturarbete visade varför: Ehd3 använder ett par tätt sammankopplade PHD‑finger för att bilda en smal ficka som rymmer en enda metyleringsgrupp på lysin 4, men skulle kollidera med större varianter. Denna ovanliga tvillingficksdesign gör Ehd3 mycket selektivt för H3K4me1.
Från läsning till omskrivning av koden
Nästa fråga var vad som händer efter att Ehd3 binder H3K4me1 på kromatin. Med hjälp av proteinfångstexperiment i ris fann teamet att Ehd3 fysiskt associerar med SDG724, ett enzym som tillsätter metylgrupper på en annan position på histon H3 och skapar H3K36me2 och H3K36me3. Växter som saknade antingen Ehd3 eller SDG724 blommade sent och visade liknande skift i genaktivitet över genomet. Kartläggning av histonmärken avslöjade att förlust av Ehd3 eller SDG724 lämnar H3K4me1 i stort sett intakt men kraftigt minskar H3K36me2/3 över de påverkade generna. I rör‑tester visade SDG724 liten aktivitet på egen hand, men fungerade betydligt bättre på H3K4me1‑märkta nukleosomer när Ehd3 var närvarande, vilket indikerar att Ehd3 inte bara för SDG724 till rätt plats utan även ökar dess katalytiska kapacitet.
En evolutionär tråd genom landväxter
Forskarlaget utvidgade sin analys bortom ris. De visade att nära släktingar till Ehd3 i andra landväxter delar liknande PHD‑fingerstrukturer och i många fall samma preferens för H3K4me1. Genomgångar av genomomfattande data från mossa, Arabidopsis, ris och ytterligare arter avslöjade ett återkommande mönster: där H3K4me1 finns längs generna tenderar H3K36me2 och H3K36me3 att finnas i samma regioner. Denna täta koppling är mycket svagare eller frånvarande i alger och djur, vilket tyder på att när växter koloniserade land utvecklade de en dedikerad H3K4me1‑läsare för att hjälpa till att etablera H3K36‑metylering. Resultatet är ett integrerat märkningssystem som sannolikt hjälper växter att finjustera transkription under utveckling och vid stress.
Varför detta dolda system är viktigt
För icke‑specialister är huvudbudskapet att växter använder en flerskiktad kemisk kod på sina DNA‑paketerande proteiner för att samordna när gener är aktiva. Detta arbete visar att ett märke, H3K4me1, fungerar som en startsignal som rekryterar ett läsarprotein, Ehd3, som i sin tur aktiverar ett enzym att installera ett andra märke, H3K36me2/3, längs gener. Tillsammans formar dessa länkade märken växttillväxt, blomningstid och stressresponser. Att förstå denna händelsekedja öppnar dörrar för att avla eller ingenjörsoptimera grödor som bättre kan anpassa sig till förändrade miljöer genom att justera hur de läser och omskriver sitt eget kromatinkod.
Citering: Wu, J., Wang, J., Du, K. et al. H3K4me1 directs H3K36me2 and H3K36me3 deposition in land plants. Nat Commun 17, 2831 (2026). https://doi.org/10.1038/s41467-026-69632-5
Nyckelord: växtepigenetik, histonmetylering, kromatinreglering, blomningstid, stressresponsiva gener