Clear Sky Science · nl
H3K4me1 stuurt H3K36me2- en H3K36me3-afzetting in landplanten
Hoe planten onthouden en reageren
Planten kunnen niet wegvluchten voor droogte, hitte of wisselende seizoenen. In plaats daarvan vertrouwen ze op een verborgen laag chemische markeringen op de eiwitten die hun DNA verpakken om fijnmazig te regelen welke genen aan- of uitgezet worden. Deze studie onthult hoe één zo’n markering bij landplanten fungeert als een moleculair wegwijzer, die helpt een andere markering te plaatsen die groei, bloeitijd en reacties op de omgeving beïnvloedt.

Een code geschreven op DNA-verpakking
In elke plantencel is DNA omwikkeld rond eiwitten die histonen heten, en vormt het kralenachtige structuren langs de genetische draad. Deze histonen dragen kleine chemische labels die samen als een code voor genactiviteit fungeren. Het team concentreerde zich op twee van deze labels op histon H3, bekend onder de afkortingen H3K4me1 en H3K36me2/3. Bij dieren is H3K4me1 beroemd omdat het stukken DNA markeert die genactiviteit versterken, zogeheten enhancers. Bij planten bleef de rol ervan echter raadselachtig. Door algen, mossen, bloeiende planten, gist, vliegen, muizen en mensen te vergelijken, toonden de onderzoekers aan dat landplanten een kenmerkend patroon hebben: H3K4me1 verspreidt zich over genlichamen van planten en vertoont een unieke relatie met de sterkte van genexpressie.
Een lees-eiwit dat de eerste markering herkent
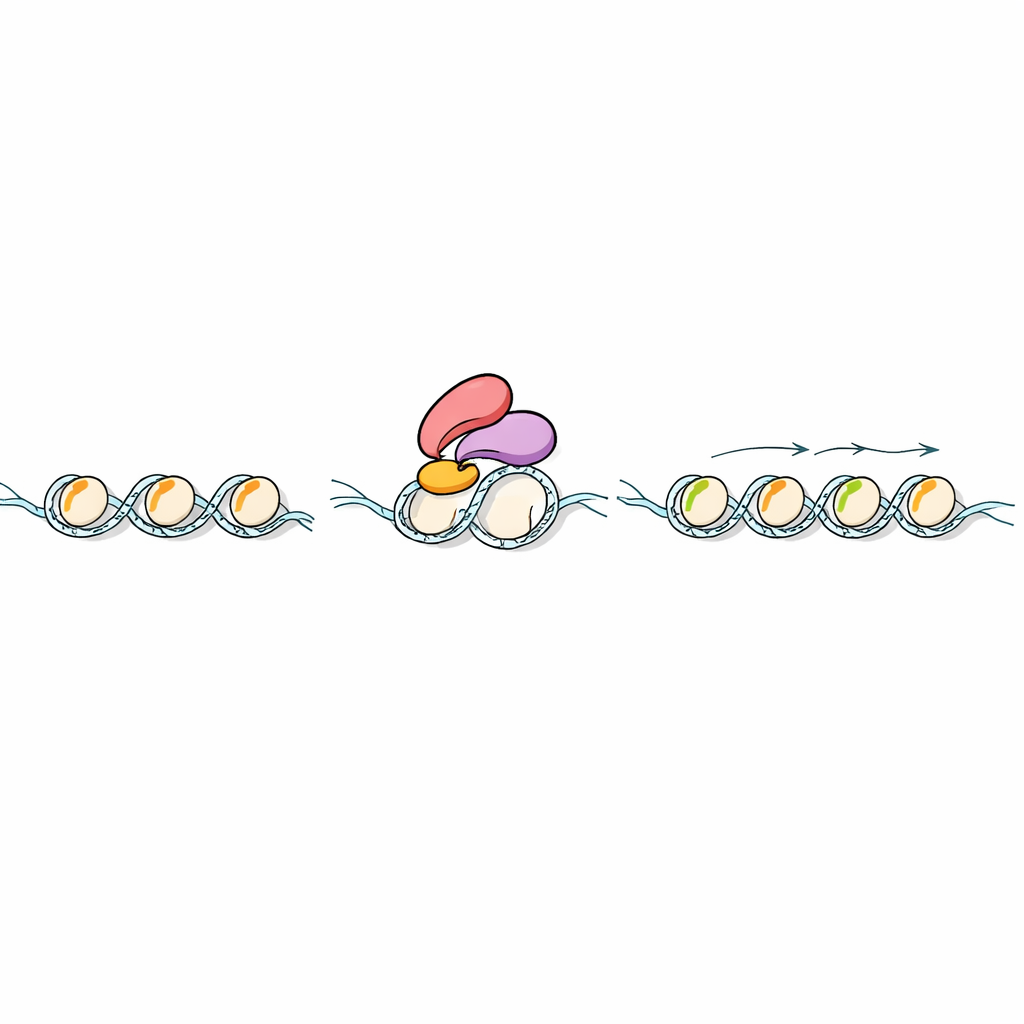
Chemische labels op histonen zijn alleen van belang als andere eiwitten ze kunnen "lezen". De wetenschappers doorzochten plantengenomen op eiwitten met een bepaald type lees-eenheid, de zogenaamde PHD-finger, die bekendstaat om H3K4-modificaties te herkennen. Ze richtten zich op een rijst-eiwit genaamd Early heading date 3 (Ehd3), dat al bekend was als beïnvloeder van bloeitijd. Biochemische tests met kunstmatige histonfragmenten toonden dat Ehd3 een sterke voorkeur heeft voor H3K4me1 boven verwante markeringen. Hoge-resolutie structureel werk onthulde vervolgens waarom: Ehd3 gebruikt een paar strak gekoppelde PHD-fingers om een smalle pocket te vormen die precies één methylgroep op lysine 4 herbergt, maar zou botsen met grotere versies. Dit ongewone dubbelpocket-ontwerp maakt Ehd3 zeer selectief voor H3K4me1.
Van lezen naar herschrijven van de code
De volgende vraag was wat er gebeurt nadat Ehd3 aan H3K4me1 op chromatine bindt. Met proteïne-‘hengel’-experimenten in rijst vond het team dat Ehd3 fysiek geassocieerd is met SDG724, een enzym dat methylgroepen toevoegt op een andere positie van histon H3 en zo H3K36me2 en H3K36me3 creëert. Planten zonder Ehd3 of SDG724 bloeiden later en vertoonden vergelijkbare veranderingen in genactiviteit over het hele genoom. Mapping van histonmarkeringen liet zien dat het ontbreken van Ehd3 of SDG724 H3K4me1 grotendeels intact laat, maar H3K36me2/3 sterk vermindert over de getroffen genen. In proefbuisassays toonde SDG724 weinig activiteit op zichzelf, maar werkte veel beter op H3K4me1-g gemarkeerde nucleosomen wanneer Ehd3 aanwezig was, wat aangeeft dat Ehd3 niet alleen SDG724 naar de juiste plek brengt maar ook zijn katalytische vermogen versterkt.
Een evolutionaire draad door landplanten
De onderzoekers breidden hun analyse buiten rijst uit. Ze toonden aan dat nauwe verwanten van Ehd3 in andere landplanten vergelijkbare PHD-finger-structuren delen en in veel gevallen dezelfde voorkeur voor H3K4me1 hebben. Genoomwijde gegevens van mos, Arabidopsis, rijst en aanvullende soorten onthulden een terugkerend patroon: waar H3K4me1 langs genen voorkomt, zitten H3K36me2 en H3K36me3 vaak in dezelfde regio’s. Deze nauwe koppeling is veel zwakker of afwezig in algen en dieren, wat suggereert dat planten tijdens de kolonisatie van land een toegewijde H3K4me1-lezers zijn gaan ontwikkelen om H3K36-methylatie te helpen vestigen. Het resultaat is een geïntegreerd markeersysteem dat waarschijnlijk helpt transcriptie fijn af te stemmen tijdens ontwikkeling en bij stress.
Waarom dit verborgen systeem er toe doet
Voor niet-specialisten is de kernboodschap dat planten een gelaagde chemische code op hun DNA-verpakkings-eiwitten gebruiken om te coördineren wanneer genen actief zijn. Dit werk laat zien dat één markering, H3K4me1, fungeert als startsein dat een leeseiwit, Ehd3, aantrekt, dat op zijn beurt een enzym activeert om een tweede markering, H3K36me2/3, over genen aan te brengen. Samen vormen deze gekoppelde markeringen het patroon dat plantengroei, bloeitijd en stressreacties vormt. Inzicht in deze keten van gebeurtenissen opent mogelijkheden om gewassen te veredelen of te ontwerpen die beter kunnen aanpassen aan veranderende omgevingen door te wijzigen hoe ze hun eigen chromatinecode lezen en herschrijven.
Bronvermelding: Wu, J., Wang, J., Du, K. et al. H3K4me1 directs H3K36me2 and H3K36me3 deposition in land plants. Nat Commun 17, 2831 (2026). https://doi.org/10.1038/s41467-026-69632-5
Trefwoorden: planten-epigenetica, histonmethylatie, chromatinregulatie, bloeitijd, stress-responsieve genen