Clear Sky Science · it
H3K4me1 dirige la deposizione di H3K36me2 e H3K36me3 nelle piante terrestri
Come le piante ricordano e rispondono
Le piante non possono fuggire dalla siccità, dal caldo o dal cambiamento delle stagioni. Invece, si affidano a uno strato nascosto di marchi chimici sulle proteine che impacchettano il DNA per modulare quali geni si accendono o si spengono. Questo studio svela come uno di questi marchi nelle piante terrestri agisca come un segnale molecolare, aiutando a posizionare un altro marchio che influenza crescita, tempo di fioritura e risposte ambientali.

Un codice scritto sull’impacchettamento del DNA
All’interno di ogni cellula vegetale, il DNA è avvolto attorno a proteine chiamate istoni, formando strutture a perline lungo il filamento genetico. Questi istoni portano piccole etichette chimiche che insieme fungono da codice per l’attività genica. Il gruppo si è concentrato su due di questi segni sull’istone H3, noti con le abbreviazioni H3K4me1 e H3K36me2/3. Negli animali, H3K4me1 è famoso per segnare porzioni di DNA che potenziano l’attività genica, chiamate enhancer. Ma nelle piante il suo ruolo è stato enigmatico. Confrontando alghe, muschi, piante da fiore, lieviti, mosche, topi e umani, i ricercatori hanno mostrato che le piante terrestri presentano uno schema distintivo: H3K4me1 si estende lungo i corpi genici delle piante e mostra una relazione unica con l’intensità di espressione genica.
Una proteina lettore che individua il primo marchio
I marchi chimici sugli istoni contano solo se altre proteine possono “leggerli”. Gli scienziati hanno cercato nei genomi vegetali proteine con un particolare tipo di unità lettore chiamata dito PHD, nota per riconoscere le modifiche di H3K4. Si sono concentrati su una proteina del riso chiamata Early heading date 3 (Ehd3), già nota per influenzare il tempo di fioritura. Test biochimici con frammenti di istoni artificiali hanno mostrato che Ehd3 preferisce fortemente H3K4me1 rispetto ad altri marchi correlati. Lavori strutturali ad alta risoluzione hanno poi rivelato il perché: Ehd3 usa una coppia di dita PHD strettamente collegate per formare una tasca stretta che accoglie un singolo gruppo metile sulla lisina 4, ma sarebbe in conflitto con versioni più ingombranti. Questo insolito design a doppia tasca rende Ehd3 altamente selettivo per H3K4me1.
Dal leggere allo riscrivere il codice
La domanda successiva era cosa accade dopo che Ehd3 si lega a H3K4me1 sulla cromatina. Usando esperimenti di “pesca” proteica nel riso, il gruppo ha scoperto che Ehd3 si associa fisicamente a SDG724, un enzima che aggiunge gruppi metile in un’altra posizione sull’istone H3, generando H3K36me2 e H3K36me3. Le piante prive di Ehd3 o di SDG724 fiorivano in ritardo e mostravano cambiamenti simili nell’attività genica su tutto il genoma. La mappatura dei marchi istonici ha rivelato che la perdita di Ehd3 o SDG724 lascia H3K4me1 in gran parte intatto ma riduce fortemente H3K36me2/3 nei geni interessati. In saggi in vitro, SDG724 mostrava poca attività da solo, ma funzionava molto meglio su nucleosomi marcati con H3K4me1 quando Ehd3 era presente, indicando che Ehd3 non solo porta SDG724 nel posto giusto ma ne potenzia anche l’attività catalitica.
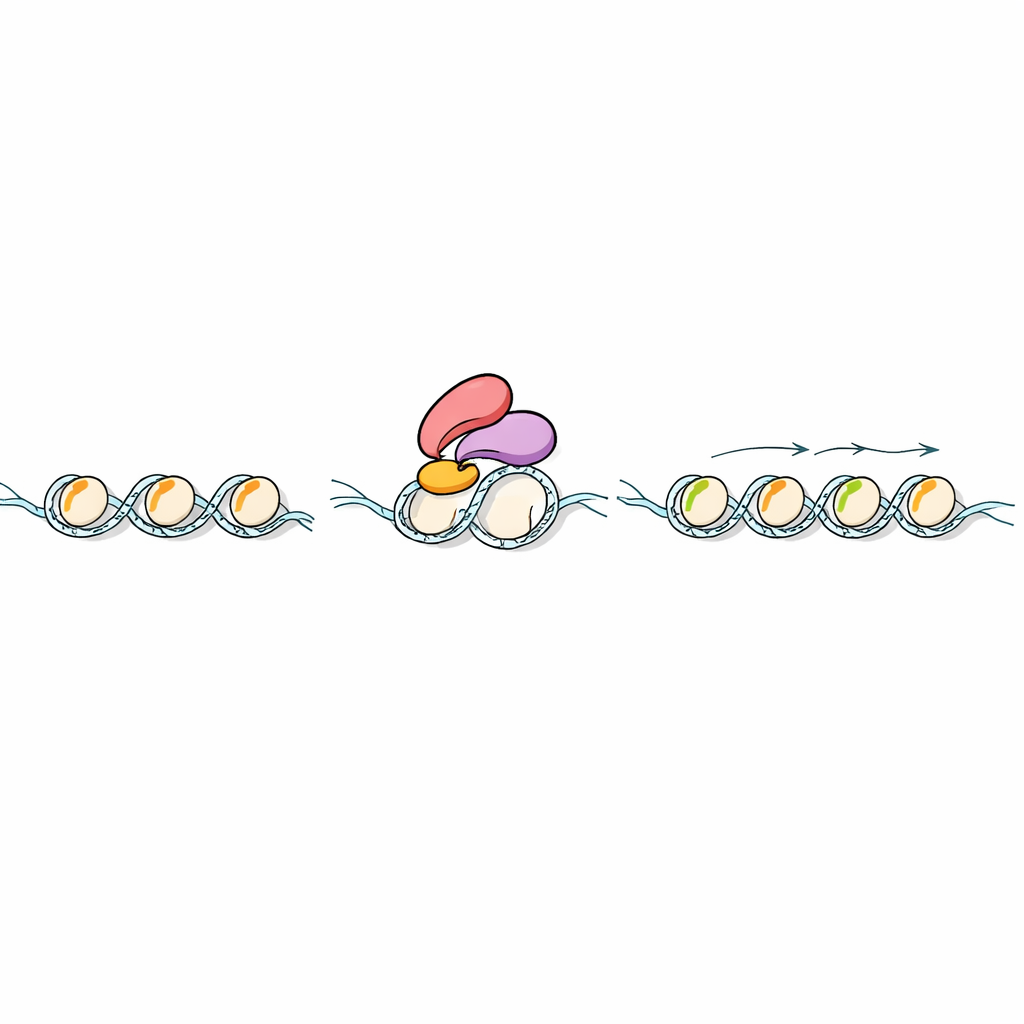
Un filo evolutivo nelle piante terrestri
I ricercatori hanno esteso la loro analisi oltre il riso. Hanno mostrato che stretti parenti di Ehd3 in altre piante terrestri condividono strutture simili delle dita PHD e, in molti casi, la stessa preferenza per H3K4me1. Dati genomici a livello di genoma da muschio, Arabidopsis, riso e altre specie hanno rivelato un modello ricorrente: dove si trova H3K4me1 lungo i geni, H3K36me2 e H3K36me3 tendono a collocarsi nelle stesse regioni. Questo accoppiamento stretto è molto più debole o assente in alghe e animali, suggerendo che, con la colonizzazione della terra da parte delle piante, si sia evoluto un lettore dedicato a H3K4me1 per aiutare a stabilire la metilazione di H3K36. Il risultato è un sistema di marcatura integrato che probabilmente aiuta le piante a modulare la trascrizione durante lo sviluppo e sotto stress.
Perché questo sistema nascosto è importante
Per chi non è specialista, il messaggio chiave è che le piante usano un codice chimico stratificato sulle proteine che impacchettano il DNA per coordinare quando i geni sono attivi. Questo lavoro mostra che un marchio, H3K4me1, funge da segnale iniziale che recluta una proteina lettore, Ehd3, che a sua volta attiva un enzima per installare un secondo marchio, H3K36me2/3, lungo i geni. Insieme, questi marchi correlati modellano crescita, tempo di fioritura e risposte allo stress delle piante. Capire questa catena di eventi apre la strada a strategie di miglioramento o ingegneria delle colture per farle adattare meglio a ambienti in cambiamento, modificando il modo in cui leggono e riscrivono il proprio codice cromatinico.
Citazione: Wu, J., Wang, J., Du, K. et al. H3K4me1 directs H3K36me2 and H3K36me3 deposition in land plants. Nat Commun 17, 2831 (2026). https://doi.org/10.1038/s41467-026-69632-5
Parole chiave: epigenetica delle piante, metilazione degli istoni, regolazione della cromatina, tempo di fioritura, geni responsivi allo stress