Clear Sky Science · pl
H3K4me1 kieruje nanoszeniem H3K36me2 i H3K36me3 u roślin lądowych
Jak rośliny pamiętają i reagują
Rośliny nie mogą uciec przed suszą, upałem czy zmieniającymi się porami roku. Zamiast tego polegają na ukrytej warstwie chemicznych znaków na białkach pakujących DNA, aby precyzyjnie sterować tym, które geny są włączane lub wyłączane. To badanie ujawnia, jak jeden z takich znaków u roślin lądowych działa jak molekularny drogowskaz, pomagając umieszczać inny znak, który kształtuje wzrost, czas kwitnienia i reakcje na środowisko.

Kod zapisany na białkach pakujących DNA
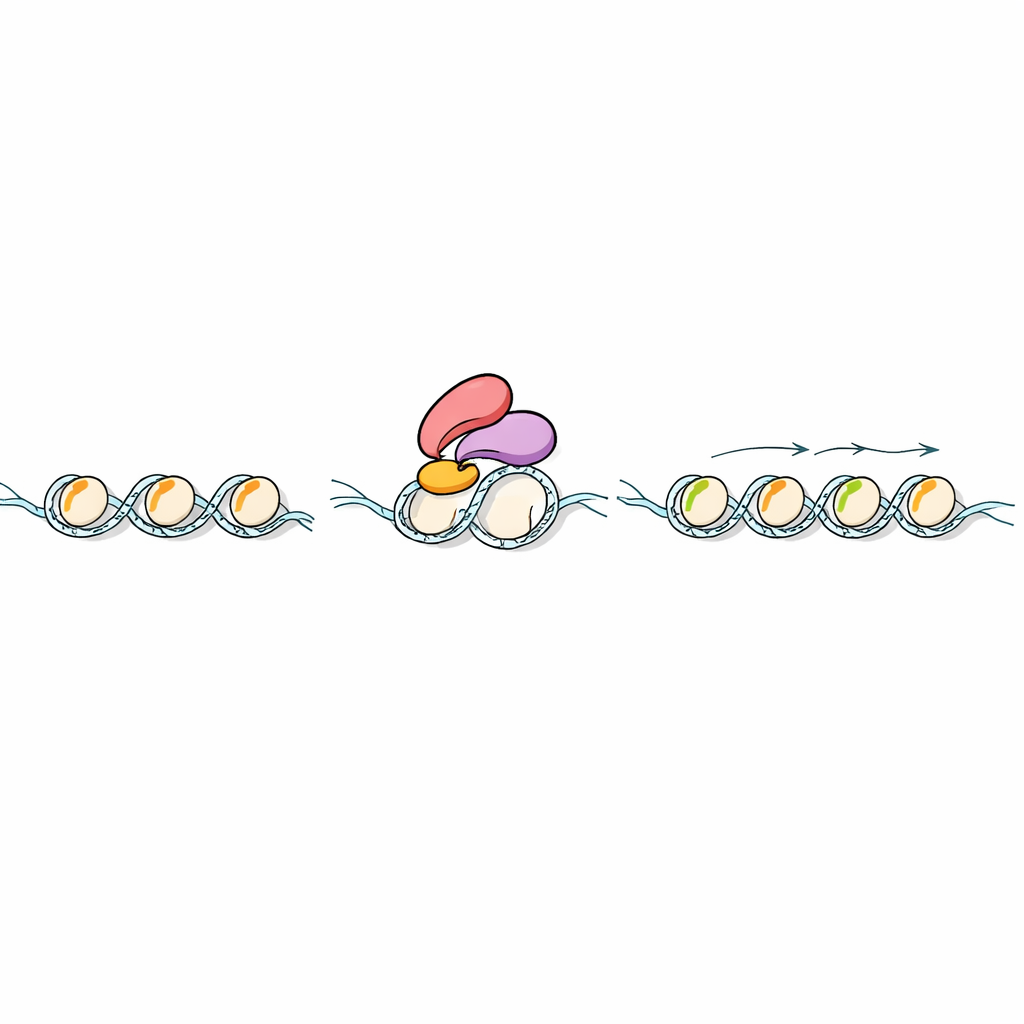
W każdej komórce roślinnej DNA jest owinięte wokół białek zwanych histonami, tworząc struktury przypominające koraliki wzdłuż nici genetycznej. Histony niosą drobne chemiczne znaczniki, które razem tworzą kod określający aktywność genów. Zespół skupił się na dwóch z tych znaków na histonie H3, znanych skrótowo jako H3K4me1 oraz H3K36me2/3. U zwierząt H3K4me1 jest sławny jako znacznik odcinków DNA wzmacniających aktywność genów, zwanych enhancerami. W roślin jednak jego rola była zagadką. Porównując glony, mchy, rośliny kwitnące, drożdże, muszki, myszy i ludzi, badacze wykazali, że rośliny lądowe mają charakterystyczny wzorzec: H3K4me1 rozciąga się w obrębie korpusów genów roślinnych i wykazuje unikalny związek z siłą ekspresji genów.
Białko-czytelnik, które rozpoznaje pierwszy znak
Chemiczne znaczniki na histonach mają znaczenie tylko wtedy, gdy inne białka potrafią je „odczytać”. Naukowcy przeszukali genomy roślin pod kątem białek zawierających określony typ modułu rozpoznawczego zwanego palcem PHD, znanego z rozpoznawania modyfikacji H3K4. Skoncentrowali się na białku ryżu o nazwie Early heading date 3 (Ehd3), już znanym z wpływu na czas kwitnienia. Testy biochemiczne z użyciem sztucznych fragmentów histonów wykazały, że Ehd3 wyraźnie preferuje H3K4me1 nad innymi pokrewnymi znacznikami. Badania strukturalne o wysokiej rozdzielczości ujawniły przyczynę: Ehd3 wykorzystuje parę ściśle związanych palców PHD, tworząc wąską kieszeń mieszczącą pojedynczą grupę metylową na lizynie 4, która kolidowałaby z większymi wersjami. Ten nietypowy, podwójny układ kieszeni sprawia, że Ehd3 jest wysoce selektywny wobec H3K4me1.
Od odczytu do przepisania kodu
Następne pytanie brzmiało: co się dzieje po związaniu Ehd3 z H3K4me1 na chromatynie. W eksperymentach „wyłapywania” białek w ryżu zespół odkrył, że Ehd3 fizycznie kojarzy się z SDG724, enzymem dodającym grupy metylowe w innej pozycji na histonie H3, tworzącym H3K36me2 i H3K36me3. Rośliny pozbawione Ehd3 lub SDG724 kwitły późno i wykazywały podobne zmiany w aktywności genów w całym genomie. Mapowanie znaków histonowych ujawniło, że utrata Ehd3 lub SDG724 pozostawia H3K4me1 w dużej mierze nienaruszone, lecz silnie redukuje H3K36me2/3 nad dotkniętymi genami. W testach in vitro SDG724 wykazywał niewielką aktywność samodzielnie, ale działał znacznie lepiej na nukleosomach oznaczonych H3K4me1, gdy obecny był Ehd3, co wskazuje, że Ehd3 nie tylko przyciąga SDG724 we właściwe miejsce, lecz także zwiększa jego aktywność katalityczną.
Ewolucyjna nić wśród roślin lądowych
Naukowcy rozszerzyli swoją analizę poza ryż. Pokażali, że bliscy krewni Ehd3 w innych roślinach lądowych mają podobne struktury palców PHD i w wielu przypadkach tę samą preferencję dla H3K4me1. Dane genomowe z mchu, Arabidopsis, ryżu i innych gatunków ujawniły powtarzający się wzorzec: tam, gdzie H3K4me1 występuje w obrębie genów, H3K36me2 i H3K36me3 mają tendencję do występowania w tych samych regionach. To ścisłe sprzężenie jest dużo słabsze lub nieobecne w glonach i u zwierząt, co sugeruje, że w miarę jak rośliny kolonizowały ląd, wyewoluowały dedykowanego czytnika H3K4me1, pomagającego ustanowić metylację H3K36. Efektem jest zintegrowany system znakowania, który prawdopodobnie pomaga roślinom precyzować transkrypcję podczas rozwoju i w warunkach stresu.
Dlaczego ten ukryty system ma znaczenie
Dla czytelników niebędących specjalistami kluczowa wiadomość jest taka, że rośliny używają wielowarstwowego chemicznego kodu na swoich białkach pakujących DNA, aby koordynować, kiedy geny są aktywne. Praca ta pokazuje, że jeden znak, H3K4me1, działa jako sygnał początkowy, który rekrutuje białko-czytnik Ehd3, które z kolei aktywuje enzym instalujący drugi znak, H3K36me2/3, wzdłuż genów. Razem te powiązane znaczniki kształtują wzrost roślin, czas kwitnienia i odpowiedzi na stres. Zrozumienie tego łańcucha zdarzeń otwiera możliwości hodowli lub inżynierii upraw, które lepiej dostosowują się do zmieniającego się środowiska przez modulowanie sposobu odczytu i przepisywania własnego kodu chromatynowego.
Cytowanie: Wu, J., Wang, J., Du, K. et al. H3K4me1 directs H3K36me2 and H3K36me3 deposition in land plants. Nat Commun 17, 2831 (2026). https://doi.org/10.1038/s41467-026-69632-5
Słowa kluczowe: epigenetyka roślin, metylacja histonów, regulacja chromatyny, czas kwitnienia, geny reagujące na stres