Clear Sky Science · pt
H3K4me1 direciona a deposição de H3K36me2 e H3K36me3 em plantas terrestres
Como as plantas memoriam e respondem
Plantas não podem fugir da seca, do calor ou das mudanças das estações. Em vez disso, elas dependem de uma camada oculta de marcas químicas nas proteínas que empacotam o DNA para ajustar finamente quais genes são ligados ou desligados. Este estudo revela como uma dessas marcas em plantas terrestres age como uma placa molecular, ajudando a posicionar outra marca que molda o crescimento, o tempo de floração e as respostas ao ambiente.

Um código escrito no empacotamento do DNA
No interior de cada célula vegetal, o DNA enrola-se em torno de proteínas chamadas histonas, formando estruturas semelhantes a contas ao longo do fio genético. Essas histonas carregam pequenas marcas químicas que, juntas, atuam como um código para a atividade gênica. A equipe concentrou-se em duas dessas marcas na histona H3, conhecidas pela sigla H3K4me1 e H3K36me2/3. Em animais, H3K4me1 é famosa por marcar trechos de DNA que aumentam a atividade gênica, chamados de enhancers. Mas nas plantas, seu papel tem sido um mistério. Ao comparar algas, musgos, plantas com flores, leveduras, moscas, camundongos e humanos, os pesquisadores mostraram que as plantas terrestres têm um padrão distinto: H3K4me1 se espalha pelo corpo dos genes das plantas e apresenta uma relação única com a intensidade da expressão gênica.
Uma proteína leitora que identifica a primeira marca
Marcas químicas nas histonas só importam se outras proteínas puderem “lê‑las”. Os cientistas buscaram em genomas de plantas proteínas com um tipo particular de módulo leitor chamado dedo PHD, conhecido por reconhecer modificações em H3K4. Focalizaram uma proteína de arroz chamada Early heading date 3 (Ehd3), já conhecida por influenciar o tempo de floração. Testes bioquímicos usando pedaços artificiais de histona mostraram que Ehd3 prefere fortemente H3K4me1 em relação a outras marcas relacionadas. Trabalhos estruturais de alta resolução revelaram o porquê: Ehd3 usa um par de dedos PHD fortemente ligados para formar um bolso estreito que acomoda um único grupo metil na lisina 4, mas entraria em colisão com versões mais volumosas. Esse desenho incomum de bolso duplo torna Ehd3 altamente seletiva para H3K4me1.
De ler para reescrever o código
A próxima pergunta foi o que acontece depois que Ehd3 se liga a H3K4me1 na cromatina. Usando experimentos de “pesca” de proteínas em arroz, a equipe descobriu que Ehd3 se associa fisicamente a SDG724, uma enzima que adiciona grupos metil em outra posição da histona H3, gerando H3K36me2 e H3K36me3. Plantas sem Ehd3 ou SDG724 floresceram tardiamente e mostraram alterações semelhantes na atividade gênica em todo o genoma. O mapeamento das marcas de histona revelou que a perda de Ehd3 ou SDG724 mantém H3K4me1 em grande parte intacta, mas reduz fortemente H3K36me2/3 sobre genes afetados. Em ensaios in vitro, SDG724 apresentou pouca atividade por conta própria, mas funcionou muito melhor em nucleossomos marcados com H3K4me1 quando Ehd3 estava presente, indicando que Ehd3 não só traz SDG724 ao local certo, como também aumenta seu poder catalítico.
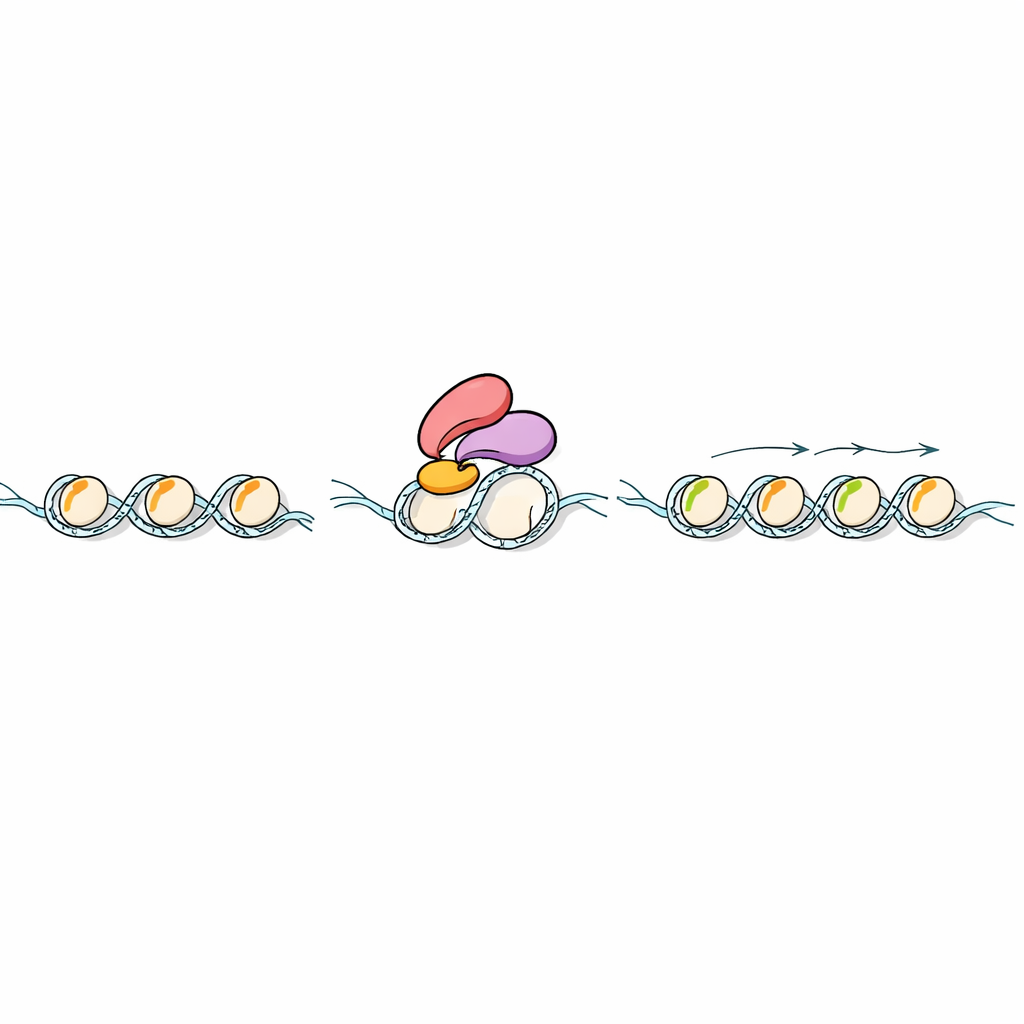
Um fio evolutivo entre plantas terrestres
Os pesquisadores estenderam sua análise além do arroz. Mostraram que parentes próximos de Ehd3 em outras plantas terrestres compartilham estruturas similares de dedos PHD e, em muitos casos, a mesma preferência por H3K4me1. Dados de genoma inteiro de musgo, Arabidopsis, arroz e espécies adicionais revelaram um padrão recorrente: onde quer que H3K4me1 esteja presente ao longo dos genes, H3K36me2 e H3K36me3 tendem a ocupar as mesmas regiões. Esse emparelhamento estreito é muito mais fraco ou ausente em algas e animais, sugerindo que, à medida que as plantas colonizaram a terra, elas evoluíram um leitor dedicado de H3K4me1 para ajudar a estabelecer a metilação em H3K36. O resultado é um sistema de marcação integrado que provavelmente ajuda as plantas a ajustar a transcrição durante o desenvolvimento e sob estresse.
Por que esse sistema oculto importa
Para não especialistas, a mensagem-chave é que as plantas usam um código químico em camadas nas proteínas que empacotam o DNA para coordenar quando os genes estão ativos. Este trabalho mostra que uma marca, H3K4me1, age como um sinal inicial que recruta uma proteína leitora, Ehd3, que por sua vez ativa uma enzima para instalar uma segunda marca, H3K36me2/3, ao longo dos genes. Juntas, essas marcas ligadas moldam o crescimento das plantas, o tempo de floração e as respostas ao estresse. Entender essa cadeia de eventos abre portas para o melhoramento ou engenharia de culturas mais adaptáveis a ambientes em mudança, ajustando como elas leem e reescrevem seu próprio código de cromatina.
Citação: Wu, J., Wang, J., Du, K. et al. H3K4me1 directs H3K36me2 and H3K36me3 deposition in land plants. Nat Commun 17, 2831 (2026). https://doi.org/10.1038/s41467-026-69632-5
Palavras-chave: epigenética vegetal, metilação de histonas, regulação da cromatina, tempo de floração, genes responsivos ao estresse