Clear Sky Science · pt
Desenho imunoinformático de uma vacina subunitária multiepitópica contra Ruminococcus torques usando proteômica subtrativa e simulações de dinâmica molecular
Por que esse microrganismo intestinal importa
Escondida nas profundezas do intestino humano vive uma bactéria chamada Ruminococcus torques que ajuda a degradar o muco que reveste o intestino. Quando sua população sai do equilíbrio, esse microrganismo está associado a distúrbios intestinais, como doença inflamatória intestinal e síndrome do intestino irritável, e até a infecções fora do trato intestinal em pacientes vulneráveis. Ainda não existe uma vacina que o almeje. Este estudo usa ferramentas computacionais para projetar um candidato a vacina destinado a direcionar o sistema imune contra R. torques, preservando ao mesmo tempo a comunidade mais ampla de bactérias intestinais benéficas. 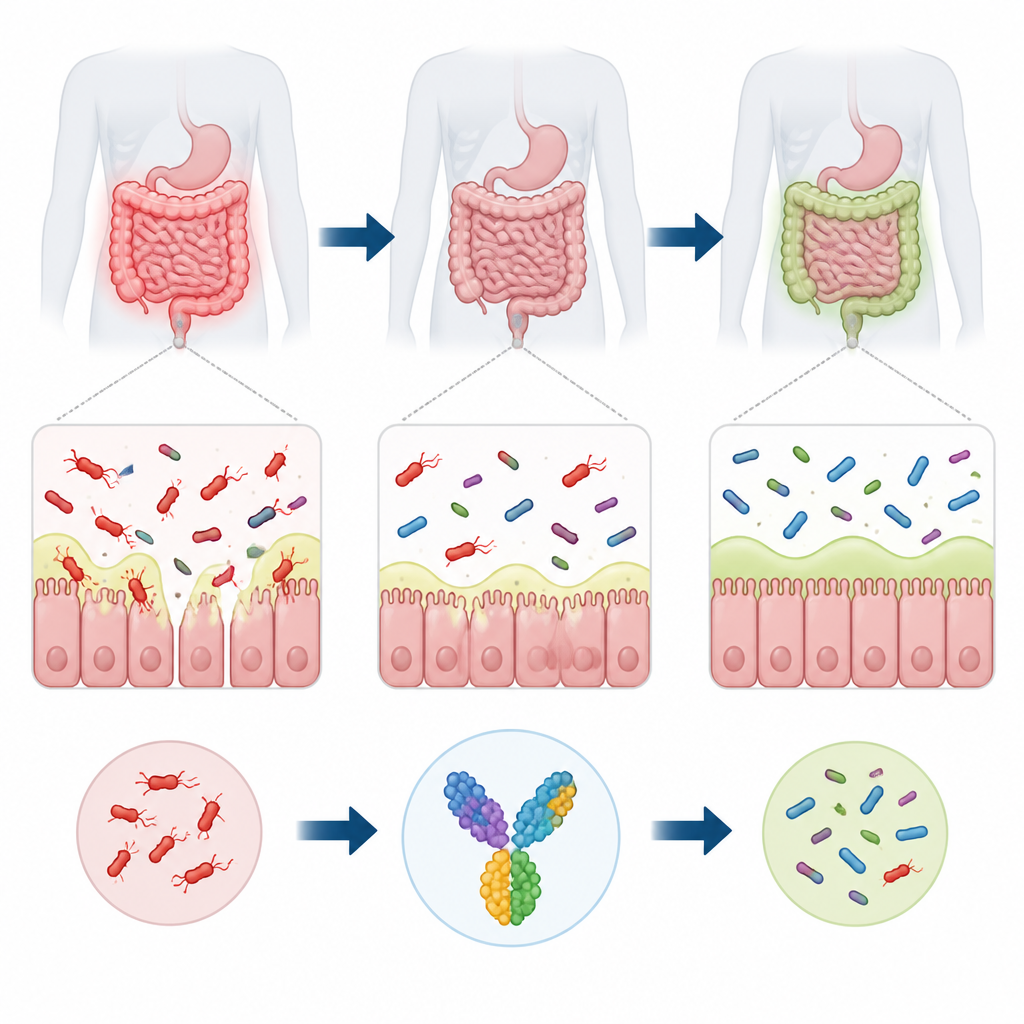
Um causador de problemas na camada de muco
A camada de muco que reveste o intestino atua como um escudo macio, porém vital, mantendo a maioria dos microrganismos à distância de segurança de nossas células. R. torques se especializa em degradar esse muco usando enzimas potentes que desmontam as cadeias açucaradas das moléculas de mucina. Em um intestino equilibrado, essa atividade pode sustentar um ecossistema saudável. Mas quando R. torques se torna excessivamente abundante, pode afinar a barreira de muco, aumentar a permeabilidade da parede intestinal e expor células imunes a um fluxo constante de fragmentos microbianos. Essa irritação persistente está associada à inflamação crônica em condições como doença de Crohn e colite ulcerativa, e também pode contribuir para obesidade e problemas metabólicos.
Usando computadores para identificar alvos vacinais
Como R. torques é difícil de estudar em laboratório, os pesquisadores recorreram ao seu catálogo completo de proteínas, ou proteoma, disponível em bases de dados públicas online. Eles utilizaram uma estratégia "subtrativa" em etapas para reduzir quase 2.800 proteínas a apenas alguns alvos promissores para vacina. Primeiro, identificaram proteínas essenciais para a sobrevivência da bactéria. Em seguida, removeram qualquer proteína que se assemelhasse fortemente a proteínas humanas ou de bactérias benéficas, para reduzir o risco de reações cruzadas indesejadas. Os candidatos remanescentes foram avaliados quanto à probabilidade de desencadear uma resposta imune sem serem tóxicos ou alergênicos. Esse processo destacou três proteínas-chave envolvidas na proteção do DNA e na construção da parede celular como alvos atraentes.
Construindo uma vacina composta por múltiplos trechos
Em vez de usar proteínas inteiras, a equipe concentrou-se em trechos curtos dessas proteínas, chamados epítopos, que são reconhecidos pelas células imunes. Eles previram epítopos para células T citotóxicas, células T auxiliares e células B, e então os filtraram usando vários critérios: forte potencial previsto de estimulação imune, ausência de sinais de toxicidade ou alergia e nenhuma semelhança próxima com proteínas humanas. Os epítopos selecionados foram encadeados como contas coloridas em uma única cadeia vacinal "multiepitópica", conectados por pequenos ligadores para que cada peça possa ser adequadamente apresentada ao sistema imune. Um componente que potencializa a resposta imune, derivado de uma subunidade da toxina da cólera, foi ligado à extremidade da construção para aumentar seu impacto. Modelos computacionais sugeriram que a proteína resultante é estável, solúvel e fortemente antigênica. 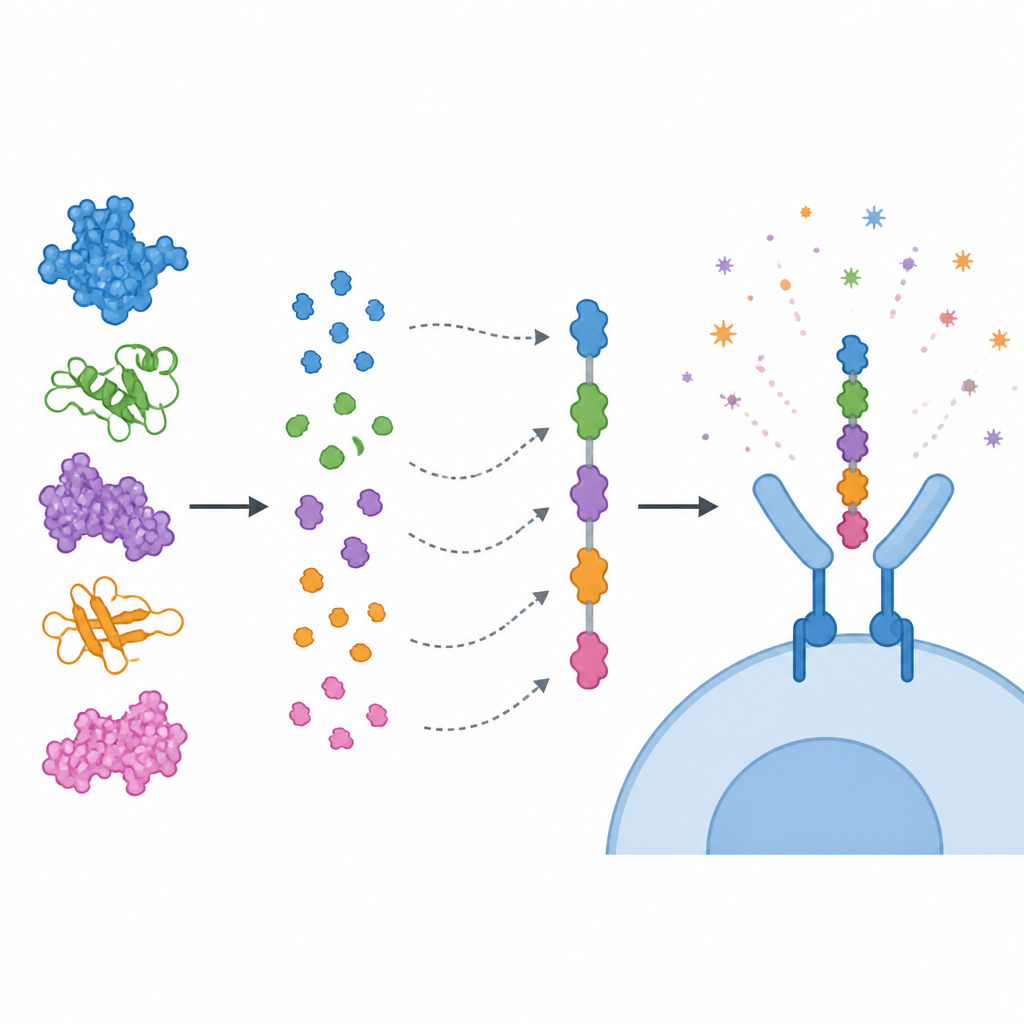
Testando encaixe e estabilidade em tela
Para verificar se essa molécula projetada poderia interagir com o sistema imune humano, os autores simularam como ela poderia se ligar ao receptor Toll-like 4, uma proteína sentinela em células imunes que detecta ameaças microbianas. Estudos de docking indicaram uma interação ajustada com muitos contatos estabilizadores, e simulações de movimento detalhadas ao longo de 100 bilionésimos de segundo sugeriram que o complexo permanece compacto e estável em um ambiente aquoso. Simulações adicionais da resposta imune previram que a vacina poderia estimular tanto a produção de anticorpos quanto respostas duradouras de células T. A sequência gênica da vacina também foi ajustada digitalmente para ser facilmente produzida em bactérias laboratoriais padrão, um primeiro passo rumo a testes no mundo real.
O que isso pode significar para tratamentos futuros
Este trabalho não entrega uma vacina pronta para uso, mas apresenta um plano cuidadosamente fundamentado. Usando apenas dados e algoritmos, os pesquisadores projetaram uma proteína multipartida que parece segura, estável e capaz de despertar o sistema imune contra R. torques. Se estudos laboratoriais e em animais confirmarem essas previsões, tal vacina poderia integrar um conjunto de ferramentas para prevenir ou atenuar distúrbios intestinais associados a esse microrganismo que consome muco, idealmente sem perturbar o equilíbrio geral do microbioma intestinal.
Citação: Kousar, S., Manzoor, I., Muhammad, S. et al. Immunoinformatic-based design of a multi-epitope subunit vaccine against Ruminococcus torques using subtractive proteomics and molecular dynamics simulations. Sci Rep 16, 15072 (2026). https://doi.org/10.1038/s41598-026-45572-4
Palavras-chave: Ruminococcus torques, microbioma intestinal, vacina multiepitópica, vacinologia reversa, imunoinformática