Clear Sky Science · pt
Uma UNet paralela integrando KAN e mamba para segmentação de imagens médicas
Por que isso importa para pacientes e médicos
Por trás de toda tomografia de rastreamento do câncer ou imagem por ultrassom, há uma etapa crucial de ensinar computadores a delinear onde uma lesão ou órgão realmente está. Esse processo, chamado segmentação, ajuda médicos a medir tumores, acompanhar a evolução da doença e planejar tratamentos. O artigo apresenta o KMP-UNet, um novo tipo de rede compacta de análise de imagens que promete traçar essas fronteiras com mais precisão e eficiência, potencialmente tornando a leitura automatizada de imagens médicas mais confiável e mais fácil de ser implementada em clínicas reais.
Enxergando o quadro inteiro em um exame médico
Imagens médicas modernas são grandes e complexas: pistas importantes podem estar distribuídas por uma ampla área, enquanto a própria lesão pode ter bordas difusas ou irregulares. Redes neurais convolucionais tradicionais, incluindo a popular família UNet, são boas em detectar padrões locais, mas têm dificuldade em conectar regiões distantes em um exame. Modelos baseados em Transformer conseguem ver a imagem inteira de uma vez, mas costumam ser pesados e lentos, o que é problemático para dados clínicos de alta resolução e hardware hospitalar limitado. Os autores constroem sobre uma família mais nova de modelos de sequência, chamados modelos de espaço de estado, e sobre um estilo recente de rede neural conhecido como Redes de Kolmogorov–Arnold, para capturar tanto o contexto amplo quanto detalhes sutis sem explodir o custo computacional.
Dois especialistas espertos trabalhando lado a lado
O KMP-UNet mantém o formato em U familiar do codificador–decodificador da UNet, mas modifica o que acontece internamente. Em vez de depender de um único tipo de processamento, ele executa duas ramificações paralelas pela rede. Uma ramificação baseia‑se em um modelo chamado Mamba, que se destaca em lidar com sequências longas e é adaptado aqui para varrer a imagem. Essa ramificação coleta de forma eficiente contexto de longo alcance, ajudando a rede a entender como regiões distantes se relacionam. A segunda ramificação usa Redes de Kolmogorov–Arnold, que substituem funções de ativação fixas por curvas flexíveis e aprendíveis. Isso dá ao modelo poder extra para representar padrões não lineares difíceis, como mudanças sutis de intensidade ao longo da borda de uma lesão de pele ou de um pólipo.
Fusão mais inteligente de características e contornos mais claros
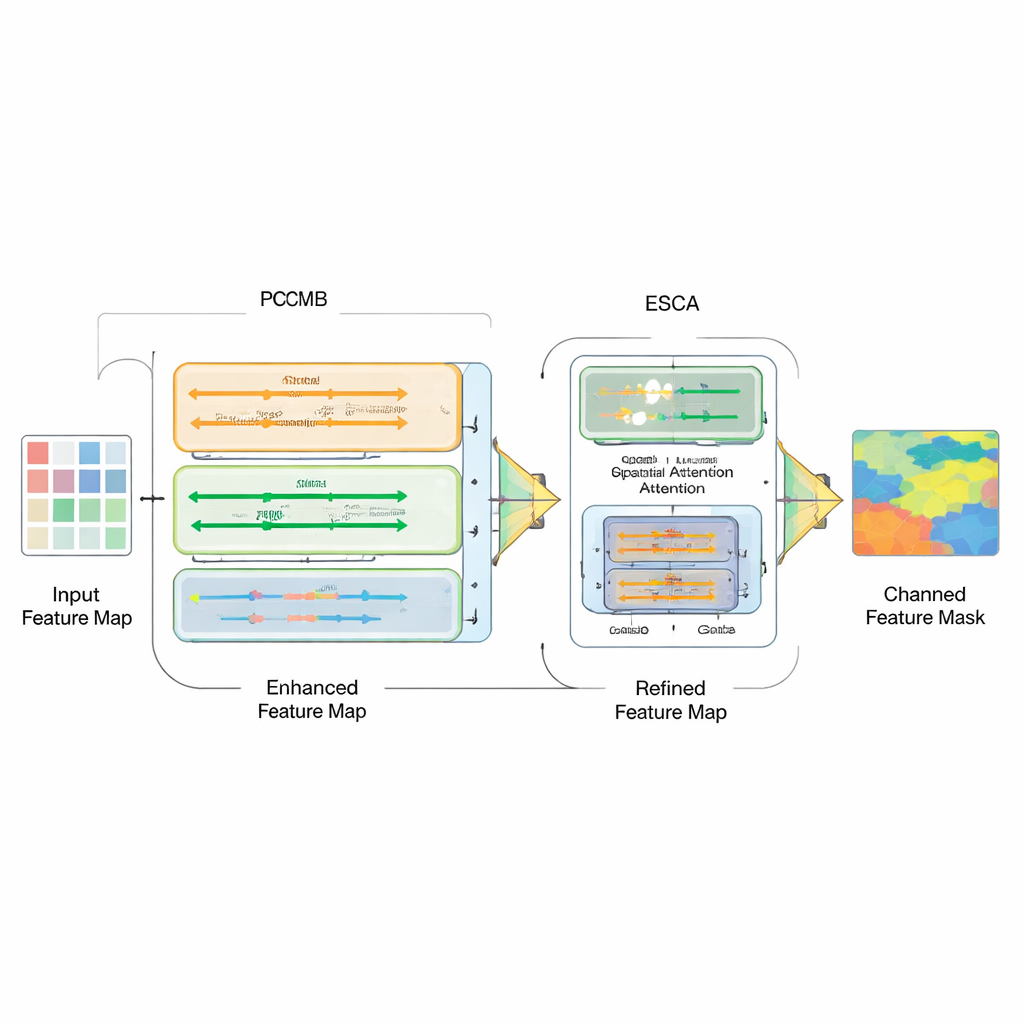
Simplesmente unir diferentes tipos de modelos não é suficiente; o verdadeiro desafio é como combinar suas forças. Para isso, os autores introduzem um Bloco Paralelo de Convolução Mamba (PCMB), que divide as características em grupos e as processa por vários caminhos leves baseados em Mamba e convolução antes de fundi-las novamente. Esse desenho equilibra contexto global e detalhes finos mantendo o custo computacional baixo. Eles também revisitam as conexões de salto que ligam o codificador e o decodificador. Um novo módulo de Atenção Espaço-Canal Aprimorada (ESCA) enfatiza seletivamente locais e canais de característica importantes, preservando informação útil por meio de conexões residuais. Isso torna a rede menos suscetível a confusões causadas por distrações como cabelo, reflexo ou texturas ruidosas ao redor de uma lesão.
Quão bem a nova abordagem funciona?
A equipe avalia o KMP-UNet em quatro conjuntos de dados públicos cobrindo lesões de pele, pólipos do cólon e imagens de ultrassom de mama, e também testa a transferência para outro conjunto de pele. Nesses benchmarks, o modelo consistentemente alcança desempenho igual ou superior a uma gama de fortes linhas de base, incluindo variantes clássicas de UNet, projetos baseados em Transformer e outras redes recentes aprimoradas por Mamba e KAN. Por exemplo, em um conjunto de dados amplamente usado de lesões de pele (ISIC2018), o KMP-UNet alcança um alto escore Dice e boa acurácia enquanto usa aproximadamente um milhão de parâmetros—muito menos do que muitos concorrentes. Experimentos detalhados mostram que cada componente—modelagem de contexto baseada em Mamba, refinamento não linear baseado em KAN e refinamento de salto baseado em ESCA—contribui com ganhos mensuráveis, particularmente na qualidade dos contornos e na redução de regiões de falso positivo.
O que isso significa para futuras ferramentas de IA médica
Para não especialistas, a principal conclusão é que o KMP-UNet oferece uma forma mais compacta e ainda capaz de ensinar computadores a delinear lesões e órgãos em imagens, permitindo que dois “especialistas” complementares trabalhem em paralelo e depois fundam suas percepções cuidadosamente. Embora o método ainda encontre dificuldades nos casos mais desafiadores—formas muito irregulares, bordas extremamente borradas ou artefatos intensos—ele fornece uma base sólida para segmentação precisa e eficiente. Com trabalho adicional no tratamento de fundos ruidosos e na adaptação entre centros de imagem, abordagens como o KMP-UNet podem ajudar a aproximar uma análise de imagens rápida e confiável da prática clínica cotidiana.
Citação: Liu, J., Wu, J., Xu, L. et al. A parallel UNet integrating KAN and mamba for medical image segmentation. Sci Rep 16, 13579 (2026). https://doi.org/10.1038/s41598-026-43127-1
Palavras-chave: segmentação de imagens médicas, aprendizado profundo, UNet, modelos de espaço de estado, redes de Kolmogorov–Arnold