Clear Sky Science · es
Una UNet paralela que integra KAN y mamba para la segmentación de imágenes médicas
Por qué esto importa para pacientes y médicos
Detrás de cada exploración de cribado oncológico o imagen por ultrasonido hay un paso crucial: enseñar a los ordenadores a delinear dónde está realmente una lesión u órgano. Este proceso, llamado segmentación, ayuda a los médicos a medir tumores, seguir la evolución de la enfermedad y planificar tratamientos. El artículo presenta KMP-UNet, un nuevo tipo de red compacta para el análisis de imágenes que promete trazar estos límites con mayor precisión y eficiencia, lo que podría hacer que la lectura automatizada de imágenes médicas sea más fiable y más fácil de desplegar en clínicas reales.
Ver la imagen completa en una exploración médica
Las imágenes médicas modernas son grandes y complejas: las pistas importantes pueden distribuirse por una amplia área, mientras que la propia lesión puede tener bordes difusos o irregulares. Las redes convolucionales tradicionales, incluida la popular familia UNet, son buenas detectando patrones locales pero tienen dificultades para conectar regiones distantes en una imagen. Los modelos basados en transformers pueden ver la imagen completa de una vez, pero tienden a ser pesados y lentos, lo que es problemático para datos clínicos de alta resolución y hardware limitado en hospitales. Los autores se apoyan en una familia más reciente de modelos de secuencia, llamados modelos de espacio de estados, y en un estilo novedoso de red neuronal conocido como Kolmogorov–Arnold Networks, para capturar tanto el contexto amplio como los detalles sutiles sin disparar el coste computacional.
Dos especialistas inteligentes que trabajan lado a lado
KMP-UNet mantiene la familiar disposición en U de codificador–decodificador de la UNet pero cambia lo que ocurre en su interior. En lugar de depender de un único tipo de procesamiento, ejecuta dos ramas paralelas a lo largo de la red. Una rama se basa en un modelo llamado Mamba, que sobresale en el manejo de secuencias largas y aquí se adapta para recorrer la imagen. Esta rama reúne de forma eficiente contexto a larga distancia, ayudando a la red a entender cómo se relacionan regiones separadas. La segunda rama utiliza Kolmogorov–Arnold Networks, que sustituyen funciones de activación fijas por curvas flexibles y aprendibles. Esto le da al modelo mayor capacidad para representar patrones no lineales complejos, como cambios sutiles de intensidad en el borde de una lesión cutánea o un pólipo.
Fusión más inteligente de características y límites más nítidos
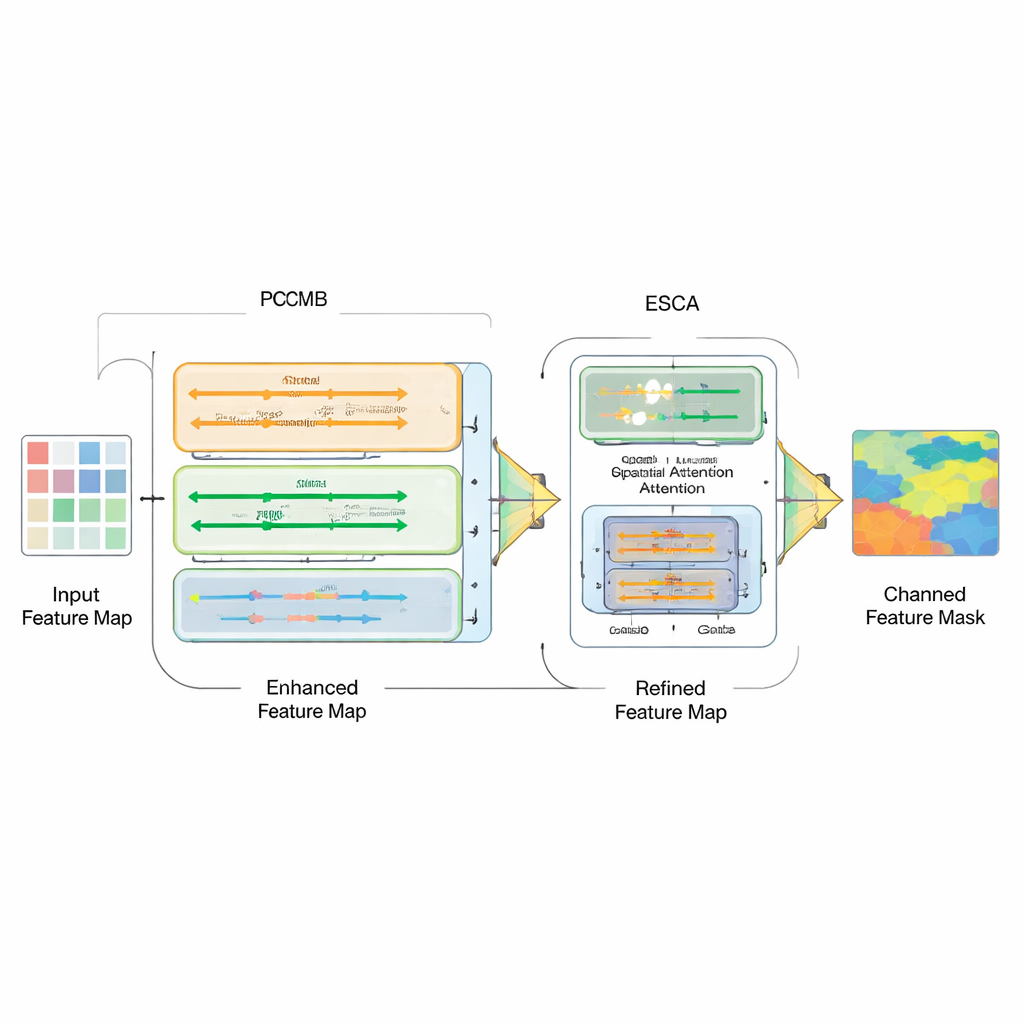
Simplemente ensamblar distintos tipos de modelos no basta; el reto real es cómo combinar sus fortalezas. Con ese fin, los autores introducen un Bloque Paralelo de Convolución Mamba (PCMB), que divide las características en grupos y las procesa a través de varias rutas ligeras basadas en Mamba y en convoluciones antes de fusionarlas de nuevo. Este diseño equilibra el contexto global y el detalle fino manteniendo bajo el coste computacional. También revisan las conexiones de salto que enlazan el codificador y el decodificador. Un nuevo módulo de Atención Espacial‑Canal Mejorada (ESCA) enfatiza de forma selectiva ubicaciones y canales de características importantes, al tiempo que preserva información útil mediante conexiones residuales. Esto hace que la red sea menos proclive a confundirse por distracciones como pelo, reflejos o texturas ruidosas alrededor de una lesión.
¿Qué tan bien funciona el nuevo enfoque?
El equipo evalúa KMP-UNet en cuatro conjuntos de datos públicos que abarcan lesiones cutáneas, pólipos de colon e imágenes de ecografía mamaria, y también prueba la transferencia a otro conjunto de piel. En estos benchmarks, el modelo iguala o supera de forma consistente a una gama de fuertes baselines, incluidas variantes clásicas de UNet, diseños basados en transformers y otras redes recientes mejoradas con Mamba y KAN. Por ejemplo, en un conjunto de lesiones cutáneas muy usado (ISIC2018), KMP-UNet alcanza una alta puntuación Dice y precisión utilizando aproximadamente un millón de parámetros—mucho menos que muchos competidores. Experimentos detallados muestran que cada componente—modelado de contexto basado en Mamba, refinamiento no lineal basado en KAN y refinamiento de saltos basado en ESCA—aporta mejoras medibles, especialmente en la calidad de los límites y la reducción de regiones de falsos positivos.
Qué significa esto para las futuras herramientas de IA médica
Para los no especialistas, la conclusión clave es que KMP-UNet ofrece una forma más compacta pero capaz de enseñar a los ordenadores a delinear lesiones y órganos en imágenes, permitiendo que dos “expertos” complementarios trabajen en paralelo y luego fusionando cuidadosamente sus conocimientos. Aunque el método todavía tiene dificultades con los casos más desafiantes—formas muy irregulares, bordes extremadamente difuminados o artefactos intensos—proporciona una base sólida para una segmentación precisa y eficiente. Con trabajo adicional en el manejo de fondos ruidosos y en la adaptación entre centros de imagen, enfoques como KMP-UNet podrían ayudar a acercar el análisis de imágenes fiable y rápido a la práctica clínica diaria.
Cita: Liu, J., Wu, J., Xu, L. et al. A parallel UNet integrating KAN and mamba for medical image segmentation. Sci Rep 16, 13579 (2026). https://doi.org/10.1038/s41598-026-43127-1
Palabras clave: segmentación de imágenes médicas, aprendizaje profundo, UNet, modelos de espacio de estados, redes de Kolmogorov–Arnold