Clear Sky Science · it
Una UNet parallela che integra KAN e mamba per la segmentazione di immagini mediche
Perché è importante per pazienti e medici
Dietro ogni esame di screening oncologico o ecografia c’è una tappa cruciale: insegnare ai computer a delimitare dove si trova davvero una lesione o un organo. Questo processo, chiamato segmentazione, aiuta i medici a misurare i tumori, monitorare l’evoluzione della malattia e pianificare le terapie. L’articolo presenta KMP-UNet, un nuovo tipo di rete compatta per l’analisi d’immagine che promette di tracciare questi confini in modo più accurato ed efficiente, rendendo la lettura automatizzata delle immagini mediche più affidabile e più semplice da impiegare nelle cliniche reali.
Cogliere il quadro complessivo in una scansione medica
Le immagini mediche moderne sono grandi e complesse: indizi importanti possono essere distribuiti su ampie aree, mentre la lesione stessa può avere margini sfumati o irregolari. Le reti neurali convoluzionali tradizionali, inclusa la popolare famiglia UNet, sono abili a riconoscere pattern locali ma faticano a collegare regioni distanti di una scansione. I modelli basati su Transformer possono considerare l’immagine nella sua interezza ma tendono a essere pesanti e lenti, un problema per dati clinici ad alta risoluzione e per hardware ospedaliero limitato. Gli autori si basano su una famiglia più recente di modelli di sequenza, chiamati modelli di spazio di stato, e su uno stile nuovo di rete neurale noto come Kolmogorov–Arnold Network, per catturare sia il contesto ampio sia i dettagli sottili senza far esplodere il costo computazionale.
Due specialisti “cervelloni” che lavorano fianco a fianco
KMP-UNet mantiene la nota struttura a U encoder–decoder della UNet, ma modifica ciò che avviene al suo interno. Invece di affidarsi a un unico tipo di elaborazione, esegue due rami paralleli attraverso la rete. Un ramo è basato su un modello chiamato Mamba, che eccelle nella gestione di lunghe sequenze ed è qui adattato per scansionare l’immagine. Questo ramo raccoglie in modo efficiente il contesto a lungo raggio, aiutando la rete a comprendere come regioni distanti siano correlate. Il secondo ramo utilizza le Kolmogorov–Arnold Networks, che sostituiscono funzioni di attivazione fisse con curve flessibili e apprendibili. Ciò conferisce al modello maggiore capacità di rappresentare pattern non lineari complessi, come sottili variazioni di intensità lungo il bordo di una lesione cutanea o di un polipo.
Fusione più intelligente delle caratteristiche e confini più netti
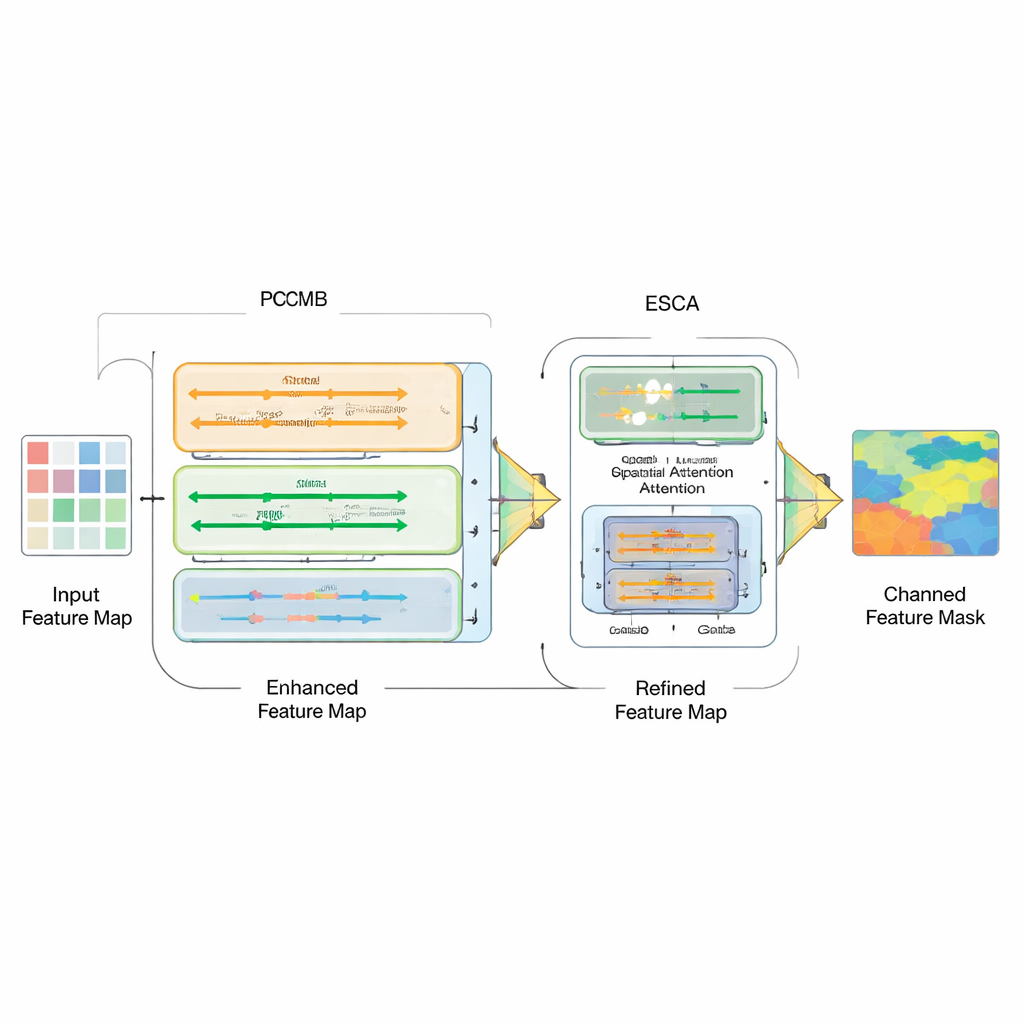
Mettere insieme tipi diversi di modello non basta; la vera sfida è combinare i loro punti di forza. A questo scopo, gli autori introducono un Parallel Convolution Mamba Block (PCMB), che suddivide le feature in gruppi e le elabora attraverso diversi percorsi leggeri basati su Mamba e convoluzioni prima di riunirle. Questo design bilancia contesto globale e dettagli fini mantenendo basso il costo computazionale. Vengono inoltre rivisti i collegamenti skip che legano encoder e decoder. Un nuovo modulo Enhanced Spatial-Channel Attention (ESCA) enfatizza selettivamente posizioni e canali di feature importanti, preservando informazioni utili tramite connessioni residuali. Questo rende la rete meno incline a essere confusa da distrazioni come capelli, riflessi o texture rumorose attorno a una lesione.
Quanto funziona bene il nuovo approccio?
Il team valuta KMP-UNet su quattro dataset pubblici che coprono lesioni cutanee, polipi del colon e immagini ecografiche della mammella, e testa anche il trasferimento su un altro dataset cutaneo. Su questi benchmark, il modello eguaglia o supera costantemente una serie di forti baseline, incluse varianti classiche di UNet, progetti basati su Transformer e altre reti recenti potenziate con Mamba e KAN. Per esempio, su un noto dataset per lesioni cutanee (ISIC2018), KMP-UNet raggiunge un alto valore di Dice e accuratezza utilizzando circa un milione di parametri—molto meno di molti concorrenti. Esperimenti dettagliati mostrano che ciascun componente—modellazione del contesto basata su Mamba, raffinamento non lineare basato su KAN e perfezionamento degli skip basato su ESCA—contribuisce con guadagni misurabili, particolarmente nella qualità dei confini e nella riduzione delle aree con falsi positivi.
Cosa significa per i futuri strumenti di IA medica
Per i non specialisti, la conclusione principale è che KMP-UNet offre un modo più compatto ma capace per insegnare ai computer a delimitare lesioni e organi nelle immagini, permettendo a due “esperti” complementari di lavorare in parallelo e poi fondere con cura i loro contributi. Pur mantenendo difficoltà nei casi più ostici—forme molto irregolari, bordi estremamente sfocati o forti artefatti—il metodo fornisce una solida base per una segmentazione accurata ed efficiente. Con ulteriori lavori per gestire sfondi rumorosi e adattarsi tra centri di imaging diversi, approcci come KMP-UNet potrebbero avvicinare un’analisi delle immagini affidabile e veloce alla pratica clinica quotidiana.
Citazione: Liu, J., Wu, J., Xu, L. et al. A parallel UNet integrating KAN and mamba for medical image segmentation. Sci Rep 16, 13579 (2026). https://doi.org/10.1038/s41598-026-43127-1
Parole chiave: segmentazione di immagini mediche, deep learning, UNet, modelli di spazio di stato, reti di Kolmogorov–Arnold