Clear Sky Science · pt
Uma expansão de repetição em GOLGA8A é um grande fator de risco para degeneração lobar frontotemporal atípica com inclusões ubiquitina-positivas
Por que essa descoberta sobre demência precoce é importante
Uma forma pequena, porém devastadora, de demência de início precoce atinge pessoas no auge da vida, frequentemente na casa dos 30, 40 ou 50 anos, alterando personalidade e comportamento muito antes de surgirem problemas de memória. Até agora, os médicos não sabiam por que a maioria desses casos parecia surgir do nada, sem histórico familiar claro ou gene responsável. Este estudo revela um importante fator de risco genético para uma dessas condições — chamada degeneração lobar frontotemporal atípica com inclusões ubiquitina-positivas (aFTLD-U) — ao identificar um trecho estranho de DNA que está anormalmente repetido em muitos pacientes. O trabalho abre uma nova janela sobre como instabilidades ocultas em nosso genoma podem, silenciosamente, preparar o terreno para doenças cerebrais graves.
Uma demência rara que atinge o córtex frontal
A demência frontotemporal (DFT) é uma das causas mais comuns de demência antes dos 65 anos. Ao contrário da doença de Alzheimer, que afeta principalmente a memória, a DFT frequentemente começa com mudanças dramáticas na personalidade, no julgamento e no comportamento social. A aFTLD-U é um subtipo patológico raro dentro desse grupo. Pessoas com aFTLD-U geralmente desenvolvem sintomas comportamentais graves, com linguagem e movimento relativamente preservados. Exames cerebrais mostram encolhimento marcante dos lobos frontais e de estruturas profundas que ajudam a controlar motivação e hábitos. Ao microscópio, células cerebrais afetadas acumulam aglomerados anormais de certas proteínas ligadoras de RNA, conhecidas coletivamente como proteínas FET. Ainda assim, em contraste com outros subtipos de DFT, nenhum gene causador claro havia sido identificado para esses pacientes, que na maioria pareciam ser casos “esporádicos”.
Caçando uma região de risco oculta no genoma
Para rastrear contribuintes genéticos, pesquisadores formaram um consórcio internacional e reuniram DNA e amostras cerebrais de pessoas diagnosticadas com certeza com aFTLD-U em autópsia. Eles compararam 59 desses casos com mais de 3.000 indivíduos controles usando um estudo de associação em nível genômico, uma varredura que busca milhões de marcadores de DNA por diferenças entre pacientes e controles. Uma região no cromossomo 15 (chamada 15q14) destacou-se com um sinal excepcionalmente forte, apontando para dois padrões relacionados de variação genética, ou haplótipos, que eram muito mais comuns em pacientes do que em pessoas saudáveis. Esses haplótipos de risco ficam próximos a um par de genes quase idênticos, GOLGA8A e GOLGA8B, em uma parte do genoma notoriamente difícil de analisar porque contém muitos segmentos duplicados e rearranjados.
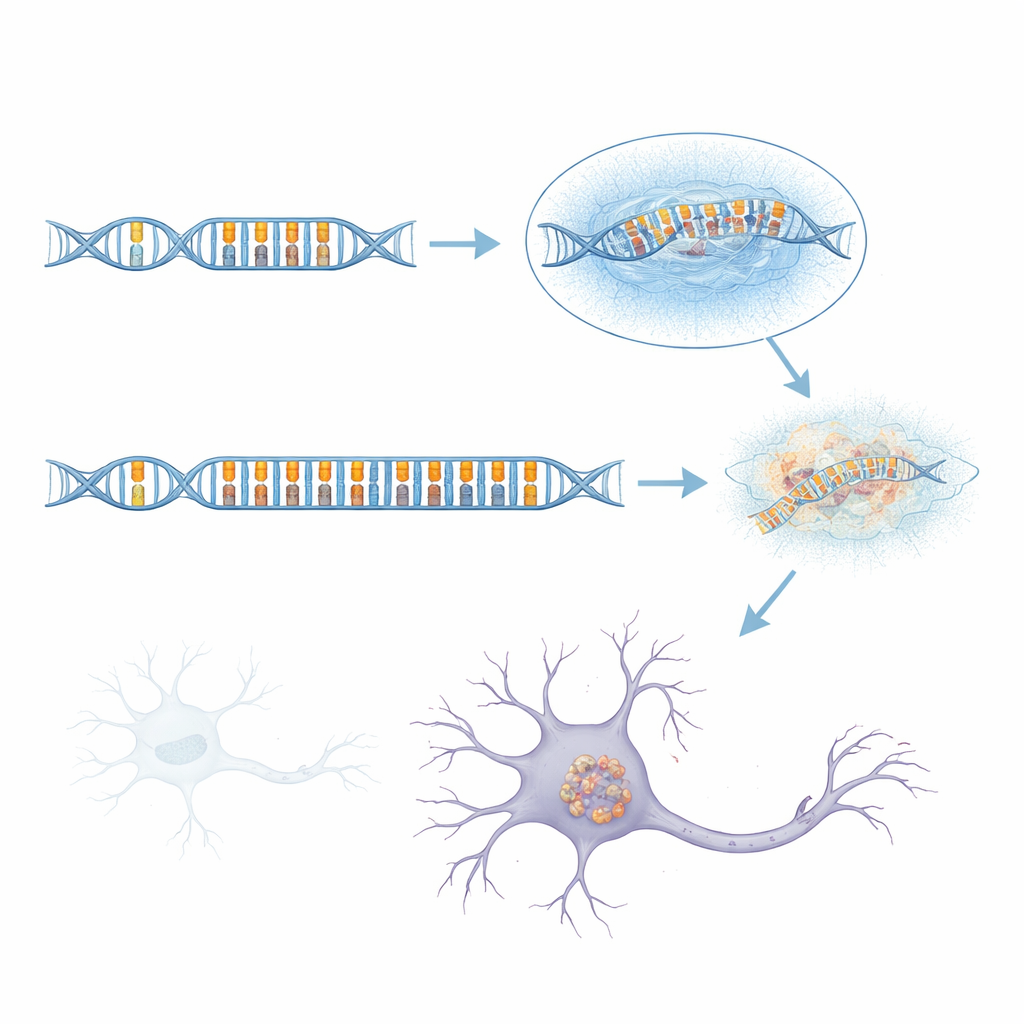
Uma repetição de DNA longa e instável surge como peça chave
Como o sequenciamento por curtíssima leitura padrão tem dificuldades nessa região complexa, a equipe recorreu ao sequenciamento de leitura longa, que consegue ler trechos muito maiores de DNA em uma única passagem. Examinando mais de 1.700 genomas, incluindo muitos casos de aFTLD-U e grupos de comparação com outras doenças cerebrais, descobriram que os haplótipos de risco quase sempre carregavam uma “repetição em tandem” excepcionalmente longa dentro de um íntron do gene GOLGA8A. Repetições em tandem são como gaguejos na sequência de DNA, em que pequenas unidades de letras são copiadas repetidas vezes. Em pessoas saudáveis, essa repetição é curta; em muitos pacientes com aFTLD-U, ela estava massivamente expandida, às vezes estendendo-se por mais de 2.000 letras de DNA. Essas versões expandidas não eram todas idênticas, mas as mais fortemente associadas à doença eram dominadas por um padrão simples de duas letras baseado nas bases C e T repetidas em pares. Quando os pesquisadores classificaram os portadores por comprimento de repetição e porcentagem de conteúdo CT, expansões longas e ricas em CT previram aFTLD-U muito melhor do que os marcadores variantes originais.
Variação, herança e risco sutil
A história não é tão simples quanto uma única mutação que sempre causa a doença. Algumas pessoas na população geral, incluindo parentes de pacientes com aFTLD-U, carregavam grandes expansões ricas em CT em GOLGA8A, porém não haviam desenvolvido demência — pelo menos até o momento em que foram estudadas. A repetição expandida também mostrou sinais de instabilidade: seu comprimento variava de célula para célula e de um tecido para outro, sugerindo que ela pode continuar crescendo ou encolhendo ao longo da vida de uma pessoa. Intrigantemente, cerca de 70% dos pacientes com aFTLD-U na coorte eram do sexo masculino, indicando que fatores biológicos relacionados ao sexo ou exposições ambientais podem influenciar se um portador realmente adoece. Além disso, aproximadamente 40% dos casos confirmados de aFTLD-U não apresentaram essa expansão em particular, o que implica que outros gatilhos genéticos ou ambientais ainda não descobertos podem produzir a mesma patologia cerebral.
O que isso significa para entender e diagnosticar a doença
Embora os cientistas ainda não saibam como essa repetição intrônica de GOLGA8A prejudica as células cerebrais, sua localização e composição sugerem várias possibilidades. O DNA expandido pode alterar como genes próximos são ligados e desligados, produzir moléculas de RNA incomuns que aprisionam proteínas vitais, ou formar estruturas tóxicas dentro dos neurônios. Seja qual for o mecanismo preciso, a presença de uma repetição muito longa e rica em CT em quase 60% dos casos de aFTLD-U a identifica como um grande fator de risco, comparável a influências genéticas fortes em doenças neurodegenerativas mais familiares. Em termos práticos, testar os haplótipos do cromossomo 15 e a repetição de GOLGA8A pode ajudar a identificar pessoas com sintomas comportamentais iniciais que provavelmente têm esse subtipo específico de DFT, auxiliando no diagnóstico e na pesquisa. Mais amplamente, este trabalho destaca como expansões de repetições crípticas — longos trechos de DNA repetido escondidos em terrenos genômicos difíceis — podem estar na base de distúrbios cerebrais aparentemente esporádicos, e abre caminho para estudos futuros que desvendem sua biologia e, possivelmente, os ataquem terapeuticamente.
Citação: De Coster, W., Van den Broeck, M., Baker, M. et al. A repeat expansion in GOLGA8A is a major risk factor for atypical frontotemporal lobar degeneration with ubiquitin-positive inclusions. Nat Genet 58, 726–736 (2026). https://doi.org/10.1038/s41588-026-02537-7
Palavras-chave: demência frontotemporal, expansão de repetição, GOLGA8A, neurodegeneração, risco genético