Clear Sky Science · es
Una expansión de repeticiones en GOLGA8A es un importante factor de riesgo para la degeneración lobar frontotemporal atípica con inclusiones ubiquitina-positivas
Por qué importa este descubrimiento sobre demencias precoces
Una forma pequeña pero devastadora de demencia de inicio temprano afecta a personas en la mejor etapa de la vida, a menudo en sus 30, 40 o 50 años, alterando la personalidad y el comportamiento mucho antes de que aparezcan problemas de memoria. Hasta ahora, los médicos no sabían por qué la mayoría de estos casos parecían surgir de forma inesperada, sin historia familiar clara ni un gen culpable identificado. Este estudio descubre un importante factor de riesgo genético para una de esas condiciones —denominada degeneración lobar frontotemporal atípica con inclusiones ubiquitina-positivas (aFTLD-U)— al localizar un tramo inusual de ADN que está repetido de forma anómala en muchos pacientes. El trabajo abre una nueva ventana sobre cómo las inestabilidades ocultas en nuestro genoma pueden preparar silenciosamente el terreno para enfermedades cerebrales graves.
Una demencia rara que afecta la región frontal del cerebro
La demencia frontotemporal (DFT) es una de las causas más comunes de demencia antes de los 65 años. A diferencia de la enfermedad de Alzheimer, que afecta principalmente la memoria, la DFT suele comenzar con cambios dramáticos en la personalidad, el juicio y el comportamiento social. La aFTLD-U es un subtipo patológico raro dentro de este grupo. Las personas con aFTLD-U suelen desarrollar síntomas conductuales severos pero mantienen relativamente el lenguaje y el movimiento. Las imágenes cerebrales muestran una atrofia marcada de los lóbulos frontales y de estructuras profundas que ayudan a controlar la motivación y los hábitos. Al microscopio, las neuronas afectadas acumulan agregados anormales de ciertas proteínas que se unen a ARN, conocidas colectivamente como proteínas FET. Sin embargo, a diferencia de otros subtipos de DFT, no se había identificado un gen causante claro para estos pacientes, que en su mayoría parecían ser casos “esporádicos”.
Buscando una región de riesgo oculta en el genoma
Para localizar contribuyentes genéticos, los investigadores formaron un consorcio internacional y recopilaron ADN y muestras cerebrales de personas diagnosticadas de forma concluyente con aFTLD-U en la autopsia. Compararon 59 de estos casos con más de 3.000 individuos control mediante un estudio de asociación a nivel del genoma, un análisis que busca millones de marcadores de ADN para detectar diferencias entre pacientes y controles. Una región en el cromosoma 15 (llamada 15q14) mostró una señal excepcionalmente fuerte, señalando dos patrones relacionados de variación genética, o haplotipos, que eran mucho más comunes en los pacientes que en las personas sanas. Estos haplotipos de riesgo se sitúan cerca de un par de genes casi idénticos, GOLGA8A y GOLGA8B, en una parte del genoma que es notoriamente difícil de analizar porque contiene muchos segmentos duplicados y reorganizados.
Una larga repetición de ADN inestable emerge como actor clave
Dado que la secuenciación de lectura corta estándar tiene dificultades en esta región compleja, el equipo recurrió a la secuenciación de lecturas largas, que puede leer fragmentos mucho mayores de ADN en una sola pasada. Al examinar más de 1.700 genomas, incluidos muchos casos de aFTLD-U y grupos de comparación con otras enfermedades cerebrales, descubrieron que los haplotipos de riesgo casi siempre portaban una «repetición en tándem» inusualmente larga dentro de un intrón del gen GOLGA8A. Las repeticiones en tándem son como tartamudeos en la secuencia de ADN, donde unidades pequeñas de letras se copian una y otra vez. En personas sanas, esta repetición es corta; en muchos pacientes con aFTLD-U, estaba masivamente expandida, a veces abarcando más de 2.000 bases de ADN. Estas versiones expandidas no eran todas iguales, pero las que se asociaron con mayor fuerza a la enfermedad estaban dominadas por un patrón simple de dos letras basado en los nucleótidos C y T repetidos en pares. Cuando los investigadores clasificaron a los portadores según la longitud de la repetición y el porcentaje de contenido CT, las expansiones largas y ricas en CT predijeron la aFTLD-U mucho mejor que las variantes marcadoras originales.
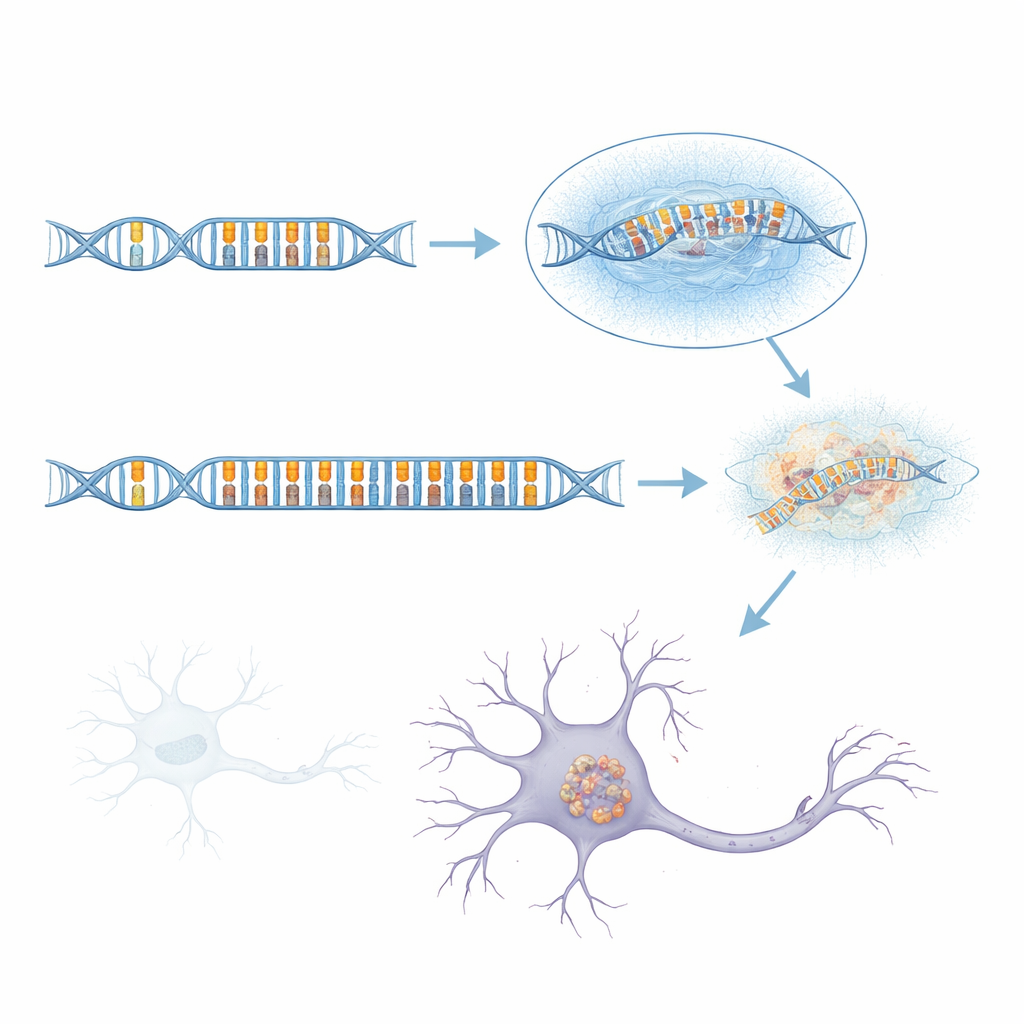
Variación, herencia y un riesgo sutil
La historia no es tan simple como una única mutación que siempre causa la enfermedad. Algunas personas en la población general, incluidos parientes de pacientes con aFTLD-U, portaban grandes expansiones ricas en CT en GOLGA8A pero no habían desarrollado demencia, al menos en el momento en que fueron estudiadas. La repetición expandida también mostró signos de inestabilidad: su longitud variaba de célula a célula y de un tejido a otro, lo que sugiere que puede seguir creciendo o encogiéndose a lo largo de la vida de una persona. De manera intrigante, alrededor del 70% de los pacientes con aFTLD-U en la cohorte eran hombres, lo que sugiere que factores biológicos relacionados con el sexo o exposiciones ambientales pueden influir en si un portador finalmente enferma. Además, aproximadamente el 40% de los casos confirmados de aFTLD-U no presentaron esta expansión en particular, lo que implica que otros desencadenantes genéticos o ambientales aún por descubrir pueden producir la misma patología cerebral.
Qué significa esto para entender y diagnosticar la enfermedad
Aunque los científicos aún no saben cómo esta repetición intrónica de GOLGA8A daña las células cerebrales, su ubicación y composición sugieren varias posibilidades. El ADN expandido podría alterar cómo se activan y desactivan genes cercanos, producir moléculas de ARN inusuales que atrapan proteínas vitales o formar estructuras tóxicas dentro de las neuronas. Sea cual sea el mecanismo preciso, la presencia de una repetición muy larga y rica en CT en casi el 60% de los casos de aFTLD-U la señala como un factor de riesgo importante, comparable con influencias genéticas fuertes en enfermedades neurodegenerativas más familiares. En términos prácticos, analizar los haplotipos del cromosoma 15 y la repetición de GOLGA8A podría ayudar a identificar a personas con síntomas conductuales tempranos que probablemente tengan este subtipo específico de DFT, facilitando el diagnóstico y la investigación. Más ampliamente, este trabajo destaca cómo las expansiones de repeticiones crípticas —largos tramos de ADN repetido ocultos en terreno genómico difícil— pueden estar detrás de trastornos cerebrales aparentemente esporádicos, y prepara el camino para futuros estudios que desentrañen su biología y, potencialmente, los apunten terapéuticamente.
Cita: De Coster, W., Van den Broeck, M., Baker, M. et al. A repeat expansion in GOLGA8A is a major risk factor for atypical frontotemporal lobar degeneration with ubiquitin-positive inclusions. Nat Genet 58, 726–736 (2026). https://doi.org/10.1038/s41588-026-02537-7
Palabras clave: demencia frontotemporal, expansión de repeticiones, GOLGA8A, neurodegeneración, riesgo genético