Clear Sky Science · de
Eine Wiederholungsexpansion in GOLGA8A ist ein wichtiger Risikofaktor für atypische frontotemporale Lappenentzündung mit ubiquitin-positiven Einschlüssen
Warum diese Entdeckung zur frühen Demenz wichtig ist
Eine kleine, aber verheerende Form der früh einsetzenden Demenz trifft Menschen in der Blüte ihres Lebens, oft in ihren 30ern, 40ern oder 50ern, und verändert Persönlichkeit und Verhalten lange bevor sich Gedächtnisprobleme zeigen. Bislang wussten Ärztinnen und Ärzte nicht, warum die meisten dieser Fälle scheinbar aus heiterem Himmel auftraten, ohne klare Familiengeschichte oder offensichtliches krankheitsverursachendes Gen. Diese Studie deckt einen wichtigen genetischen Risikofaktor für eine solche Erkrankung auf — genannt atypische frontotemporale Lappenentzündung mit ubiquitin-positiven Einschlüssen (aFTLD-U) — indem sie eine ungewöhnliche DNA-Strecke identifiziert, die bei vielen Patientinnen und Patienten abnormal vervielfacht ist. Die Arbeit eröffnet ein neues Fenster darauf, wie verborgene Instabilitäten in unserem Genom still und heimlich die Grundlage für schwere Hirnerkrankungen legen können.
Eine seltene Demenz, die den Stirnhirnbereich trifft
Die frontotemporale Demenz (FTD) ist eine der häufigsten Ursachen für Demenz vor dem 65. Lebensjahr. Anders als die Alzheimer-Krankheit, die vor allem das Gedächtnis betrifft, beginnt FTD oft mit drastischen Veränderungen von Persönlichkeit, Urteilsvermögen und sozialem Verhalten. aFTLD-U ist ein seltener pathologischer Subtyp innerhalb dieser Gruppe. Betroffene entwickeln meist schwere Verhaltensstörungen bei relativ erhaltenen Sprach- und Bewegungsfunktionen. Hirnbildgebung zeigt auffälligen Schwund der Stirnlappen und tiefer liegender Hirnstrukturen, die Motivation und Gewohnheiten steuern. Unter dem Mikroskop sammeln sich in betroffenen Nervenzellen abnorme Aggregate bestimmter RNA-bindender Proteine, zusammengefasst als FET-Proteine. Im Gegensatz zu anderen FTD-Subtypen war jedoch für diese Patienten, die größtenteils als „sporadisch“ erschienen, kein eindeutiges krankheitsverursachendes Gen identifiziert worden.
Auf der Suche nach einer verborgenen Risikoregion im Genom
Um genetische Beiträge aufzuspüren, bildeten Forschende ein internationales Konsortium und sammelten DNA- und Hirnproben von Menschen, bei denen aFTLD-U post mortem eindeutig diagnostiziert worden war. Sie verglichen 59 solcher Fälle mit mehr als 3.000 Kontrollpersonen in einer genomweiten Assoziationsstudie, einem Scan, der Millionen von DNA-Markern nach Unterschieden zwischen Patientinnen/Patienten und Kontrollen durchsucht. Eine Region auf Chromosom 15 (genannt 15q14) zeigte ein außergewöhnlich starkes Signal und wies auf zwei verwandte Muster genetischer Variation, sogenannte Haplotypen, die bei den Patientinnen und Patienten deutlich häufiger vorkamen als bei Gesunden. Diese Risikohaplotypen liegen in der Nähe eines Paars nahezu identischer Gene, GOLGA8A und GOLGA8B, in einem Bereich des Genoms, der notorisch schwer zu analysieren ist, weil er viele duplizierte und umstrukturierte Segmente enthält.
Eine lange, instabile DNA-Wiederholung tritt als Schlüsselakteur hervor
Da Standardverfahren mit kurzen Reads in dieser komplexen Region an ihre Grenzen stoßen, wandte sich das Team der Langread-Sequenzierung zu, die sehr viel größere DNA-Abschnitte in einem Durchgang lesen kann. Bei der Untersuchung von mehr als 1.700 Genomen, darunter viele aFTLD-U-Fälle und Vergleichsgruppen mit anderen Hirnerkrankungen, entdeckten sie, dass die Risikohaplotypen fast immer eine ungewöhnlich lange „Tandemrepeat“-Sequenz in einem Intron des GOLGA8A-Gens trugen. Tandemwiederholungen sind wie Stottern in der DNA-Sequenz, bei dem kurze Einheiten immer wieder kopiert werden. Bei gesunden Personen ist diese Wiederholung kurz; bei vielen aFTLD-U-Patienten war sie massiv expandiert und reichte manchmal über 2.000 DNA-Basen. Diese expandierten Versionen waren nicht identisch, aber diejenigen, die am stärksten mit der Krankheit assoziiert waren, bestanden überwiegend aus einem einfachen Zwei-Basen-Muster aus C und T, paarweise wiederholt. Als die Forschenden Trägerinnen und Träger nach Wiederholungslänge und CT-Anteil klassifizierten, sagten lange, CT-reiche Expansionen aFTLD-U deutlich besser vorher als die ursprünglichen Markervarianten.
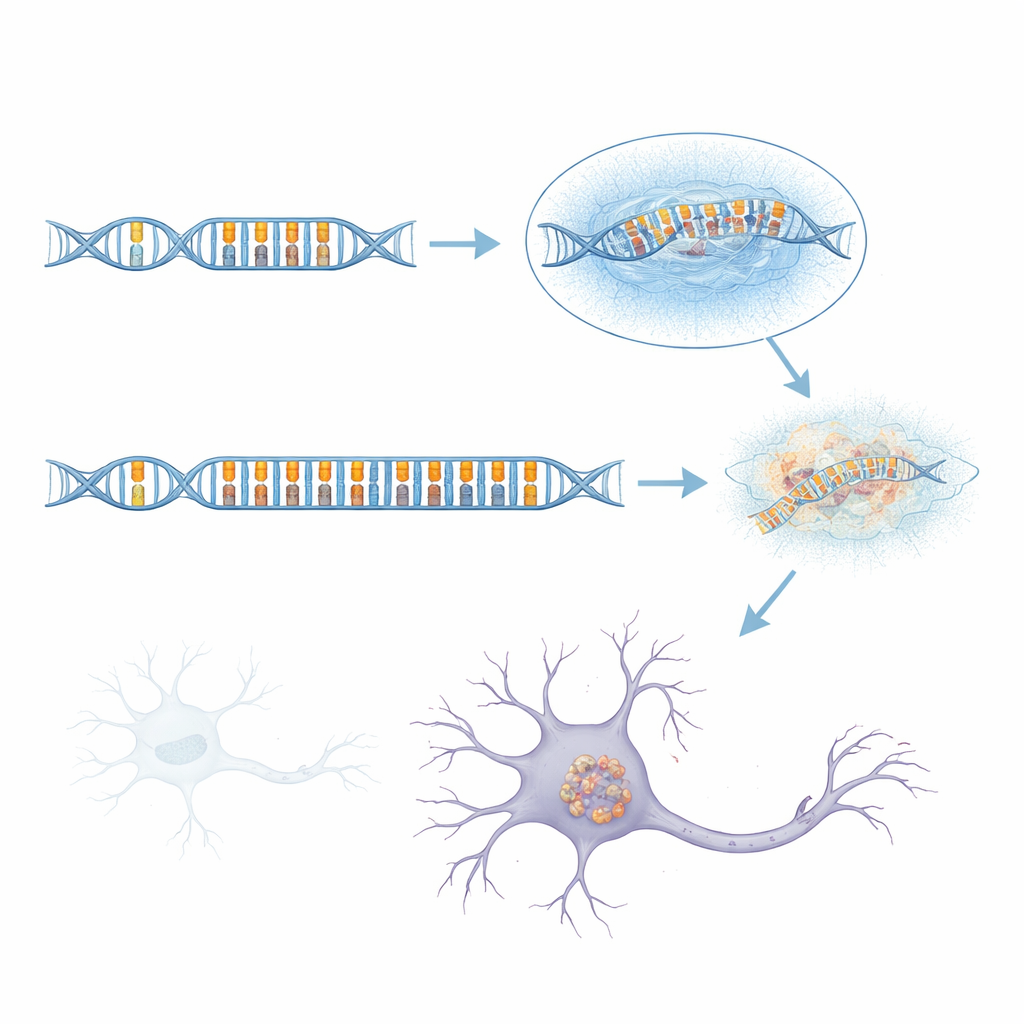
Variation, Vererbung und subtiler Risikocharakter
Die Geschichte ist nicht so eindeutig wie eine einzelne Mutation, die immer Krankheit verursacht. Einige Menschen in der Allgemeinbevölkerung, einschließlich Verwandter von aFTLD-U-Patienten, trugen große, CT-reiche Expansionen in GOLGA8A, hatten aber bis zum Zeitpunkt der Studie noch keine Demenz entwickelt. Die expandierte Wiederholung zeigte auch Anzeichen von Instabilität: Ihre Länge variierte von Zelle zu Zelle und zwischen Geweben, was darauf hindeutet, dass sie im Lebensverlauf weiter wachsen oder schrumpfen kann. Auffällig war, dass etwa 70 % der aFTLD-U-Patienten in der Kohorte männlich waren, was nahelegt, dass geschlechtsbezogene biologische Faktoren oder Umweltfaktoren beeinflussen könnten, ob ein Träger tatsächlich erkrankt. Außerdem zeigten etwa 40 % der bestätigten aFTLD-U-Fälle diese spezielle Expansion überhaupt nicht, was darauf hindeutet, dass andere, bisher unentdeckte genetische oder umweltbedingte Auslöser dieselbe Hirnpathologie hervorrufen können.
Was das für das Verständnis und die Diagnose der Krankheit bedeutet
Obwohl noch nicht bekannt ist, wie genau diese intronische GOLGA8A-Wiederholung Nervenzellen schädigt, deuten Lage und Zusammensetzung auf mehrere Möglichkeiten hin. Die expandierte DNA könnte die Regulation benachbarter Gene verändern, ungewöhnliche RNA-Moleküle produzieren, die wichtige Proteine binden, oder toxische Strukturen in Neuronen bilden. Unabhängig vom genauen Mechanismus kennzeichnet das Vorhandensein einer sehr langen, CT-reichen Wiederholung in fast 60 % der aFTLD-U-Fälle sie als einen bedeutenden Risikofaktor, vergleichbar mit starken genetischen Einflüssen bei bekannteren neurodegenerativen Erkrankungen. Praktisch gesehen könnten Tests auf die Chromosom-15-Haplotypen und die GOLGA8A-Wiederholung helfen, Personen mit frühen Verhaltenssymptomen zu identifizieren, die wahrscheinlich diesen spezifischen Subtyp der FTD haben, und so Diagnose und Forschung unterstützen. In einem weiteren Sinne unterstreicht diese Arbeit, wie kryptische Wiederholungsexpansionen — lange, wiederholte DNA-Strecken, die in schwer zugänglichem genomischem Terrain versteckt sind — scheinbar sporadische Hirnerkrankungen zugrunde liegen können, und sie ebnet den Weg für zukünftige Studien, ihre Biologie aufzuklären und möglicherweise therapeutisch anzugehen.
Zitation: De Coster, W., Van den Broeck, M., Baker, M. et al. A repeat expansion in GOLGA8A is a major risk factor for atypical frontotemporal lobar degeneration with ubiquitin-positive inclusions. Nat Genet 58, 726–736 (2026). https://doi.org/10.1038/s41588-026-02537-7
Schlüsselwörter: frontotemporale Demenz, Wiederholungsexpansion, GOLGA8A, Neurodegeneration, genetisches Risiko