Clear Sky Science · fr
Une expansion de répétition dans GOLGA8A est un facteur de risque majeur pour une dégénérescence lobaire frontotemporale atypique avec inclusions ubiquitine-positives
Pourquoi cette découverte sur la démence précoce compte
Une forme rare mais dévastatrice de démence d’apparition précoce frappe des personnes en pleine vie active, souvent dans la trentaine, la quarantaine ou la cinquantaine, modifiant la personnalité et le comportement bien avant l’apparition de troubles de la mémoire. Jusqu’à présent, les cliniciens n’expliquaient pas la plupart de ces cas qui semblaient surgir sans antécédents familiaux clairs ni gène responsable évident. Cette étude met au jour un facteur de risque génétique majeur pour l’une de ces affections — appelée dégénérescence lobaire frontotemporale atypique avec inclusions ubiquitine‑positives (aFTLD‑U) — en identifiant une séquence d’ADN inhabituelle anormalement répétée chez de nombreux patients. Ce travail ouvre une nouvelle fenêtre sur la façon dont des instabilités cachées dans notre génome peuvent silencieusement préparer le terrain à des maladies cérébrales graves.
Une démence rare qui touche le cortex frontal
La démence frontotemporale (DFT) est l’une des causes les plus fréquentes de démence avant 65 ans. Contrairement à la maladie d’Alzheimer, qui affecte principalement la mémoire, la DFT débute souvent par des changements marqués de la personnalité, du jugement et du comportement social. L’aFTLD‑U est une sous‑forme pathologique rare au sein de ce groupe. Les personnes atteintes d’aFTLD‑U développent généralement des symptômes comportementaux sévères mais conservent relativement le langage et la motricité. Les imageries cérébrales montrent une atrophie marquée des lobes frontaux et de structures profondes impliquées dans la motivation et les habitudes. Au microscope, les cellules cérébrales affectées accumulent des amas anormaux de certains protéines liant l’ARN connues collectivement sous le nom de protéines FET. Pourtant, contrairement à d’autres sous‑types de DFT, aucun gène causal clair n’avait été identifié pour ces patients, qui semblaient majoritairement des cas « sporadiques ».
À la recherche d’une région de risque cachée dans le génome
Pour identifier des contributeurs génétiques, les chercheurs ont constitué un consortium international et réuni de l’ADN et des échantillons cérébraux de personnes diagnostiquées de façon définitive avec une aFTLD‑U à l’autopsie. Ils ont comparé 59 cas à plus de 3 000 témoins par une étude d’association à l’échelle du génome, un balayage qui cherche des différences à des millions de marqueurs d’ADN entre patients et témoins. Une région du chromosome 15 (appelée 15q14) a affiché un signal exceptionnellement fort, pointant vers deux haplotypes apparentés de variation génétique beaucoup plus fréquents chez les patients que chez les personnes en bonne santé. Ces haplotypes de risque se situent près d’une paire de gènes presque identiques, GOLGA8A et GOLGA8B, dans une partie du génome notoirement difficile à analyser car elle contient de nombreux segments dupliqués et réarrangés.
Une longue répétition d’ADN instable émerge comme acteur clé
Comme le séquençage à courtes lectures standard peine dans cette région complexe, l’équipe a eu recours au séquençage à longues lectures, qui peut lire des fragments d’ADN beaucoup plus grands en une seule passe. En examinant plus de 1 700 génomes, incluant de nombreux cas d’aFTLD‑U et des groupes de comparaison atteints d’autres maladies cérébrales, ils ont découvert que les haplotypes de risque portaient presque toujours une « répétition en tandem » anormalement longue à l’intérieur d’un intron du gène GOLGA8A. Les répétitions en tandem ressemblent à des bégaiements dans la séquence d’ADN, où de petites unités de lettres sont copiées encore et encore. Chez les personnes saines, cette répétition est courte ; chez de nombreux patients atteints d’aFTLD‑U, elle était massivement étendue, atteignant parfois plus de 2 000 nucléotides. Ces variantes étendues n’étaient pas toutes identiques, mais celles le plus fortement associées à la maladie étaient dominées par un motif simple de deux lettres basé sur les nucléotides C et T répétés par paires. Lorsque les chercheurs ont classé les porteurs selon la longueur de la répétition et le pourcentage de contenu CT, les expansions longues et riches en CT prédisaient l’aFTLD‑U bien mieux que les variants marqueurs initiaux.
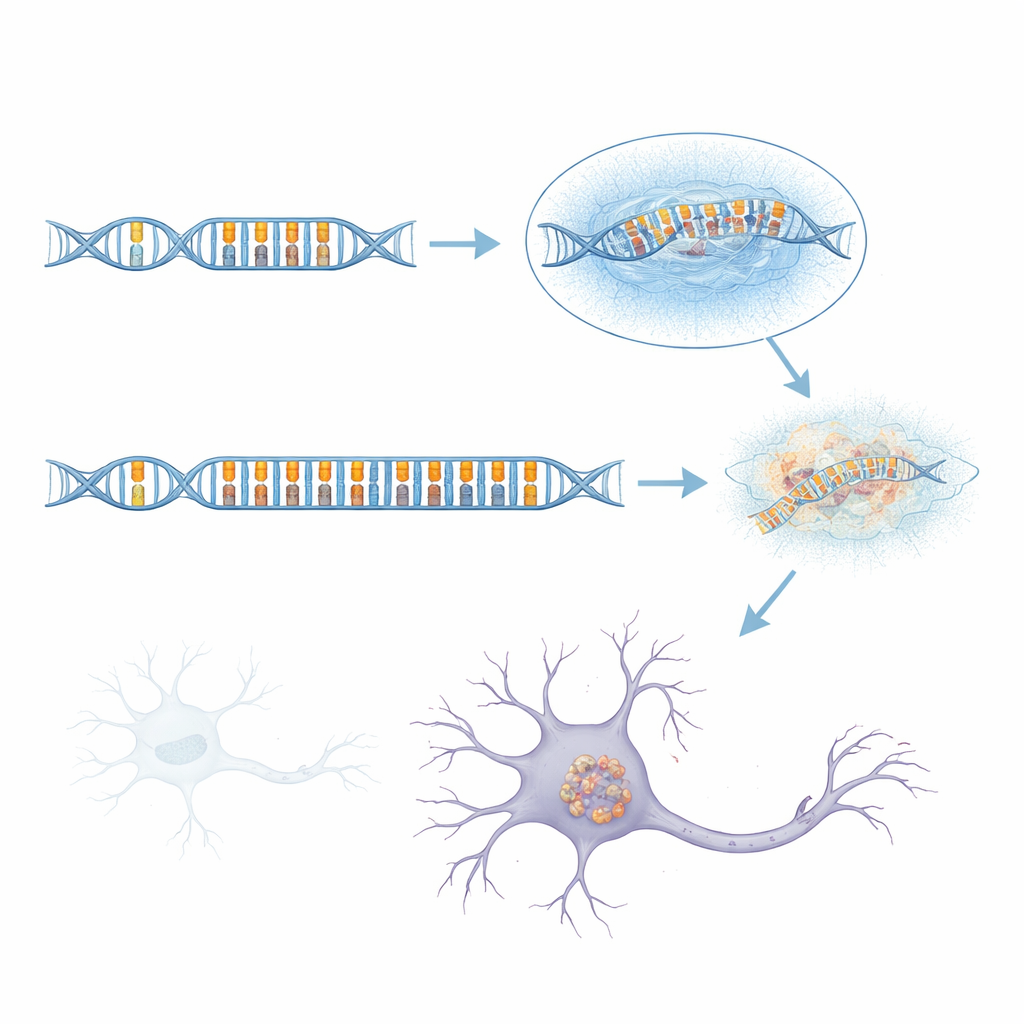
Variation, héritage et risque subtil
L’histoire n’est pas aussi simple qu’une mutation unique qui cause toujours la maladie. Certaines personnes de la population générale, y compris des apparentés de patients aFTLD‑U, portaient de larges expansions riches en CT dans GOLGA8A mais n’avaient pas développé de démence — du moins pas au moment de l’étude. La répétition étendue montrait aussi des signes d’instabilité : sa longueur variait d’une cellule à l’autre et d’un tissu à l’autre, suggérant qu’elle peut continuer à croître ou à rétrécir au cours de la vie d’une personne. Fait intéressant, environ 70 % des patients aFTLD‑U de la cohorte étaient des hommes, ce qui suggère que des facteurs biologiques liés au sexe ou des expositions environnementales peuvent influencer si un porteur devient malade. En outre, environ 40 % des cas confirmés d’aFTLD‑U n’affichaient pas du tout cette expansion particulière, ce qui implique que d’autres facteurs génétiques ou environnementaux, encore inconnus, peuvent produire la même pathologie cérébrale.
Ce que cela signifie pour la compréhension et le diagnostic de la maladie
Bien que les scientifiques ne sachent pas encore comment cette répétition intronique de GOLGA8A nuit aux cellules cérébrales, sa localisation et sa composition suggèrent plusieurs pistes. L’ADN étendu pourrait modifier la régulation des gènes voisins, produire des molécules d’ARN inhabituelles qui piègent des protéines essentielles, ou former des structures toxiques à l’intérieur des neurones. Quel que soit le mécanisme précis, la présence d’une répétition très longue et riche en CT dans près de 60 % des cas d’aFTLD‑U en fait un facteur de risque majeur, comparable aux influences génétiques fortes observées dans des maladies neurodégénératives plus connues. Sur le plan pratique, le dépistage des haplotypes du chromosome 15 et de la répétition GOLGA8A pourrait aider à identifier les personnes présentant des symptômes comportementaux précoces susceptibles d’appartenir à ce sous‑type spécifique de DFT, facilitant le diagnostic et la recherche. Plus largement, ce travail souligne comment des expansions de répétitions cryptiques — de longues séquences d’ADN répétées cachées dans des régions génomiques difficiles — peuvent sous‑tendre des troubles cérébraux apparemment sporadiques, et il prépare le terrain pour des études futures visant à élucider leur biologie et, potentiellement, à les cibler thérapeutiquement.
Citation: De Coster, W., Van den Broeck, M., Baker, M. et al. A repeat expansion in GOLGA8A is a major risk factor for atypical frontotemporal lobar degeneration with ubiquitin-positive inclusions. Nat Genet 58, 726–736 (2026). https://doi.org/10.1038/s41588-026-02537-7
Mots-clés: démence frontotemporale, expansion de répétition, GOLGA8A, neurodégénérescence, risque génétique