Clear Sky Science · nl
tRNA-deacylase-gestuurde ontdekking van biosynthetische routes
Verborgen chemie binnen levende cellen
Veel van de medicijnen van vandaag, van pijnstillers tot antibiotica en kankertherapieën, begonnen als kleine moleculen die microben of planten voor zichzelf maken. Toch vermoeden onderzoekers, ondanks decennia van onderzoek, dat het merendeel van de chemische vindingen uit de natuur nog onontdekt is. Deze studie onthult een nieuwe manier om moeilijk vindbare routes in microbieel DNA op te sporen die ongebruikelijke aminozuren en korte peptiden bouwen—moleculen die de medicijnen of onderzoekstools van morgen kunnen worden.
Waarom speciale bouwstenen ertoe doen
Aminozuren zijn vooral bekend als bouwstenen van eiwitten, maar cellen zetten ze ook om in een enorme verscheidenheid aan andere moleculen. Sommige zijn niet‑standaard aminozuren die zeldzame elementen bevatten zoals fluor of arseen, of ongebruikelijke bindingen tussen stikstofatomen. Andere worden ingebouwd in complexe antibiotica, neuromodulatoren zoals psilocybine, of peptidehormonen zoals insuline. Omdat deze structuren zo divers zijn, lijken de genen die ze maken vaak niet op de klassieke enzymfamilies waar huidige genoom‑zoekhulpmiddelen op letten. Daardoor blijven veel van de onderliggende routes onzichtbaar in de enorme hoeveelheden microbieel DNA die nu worden gesequenced.
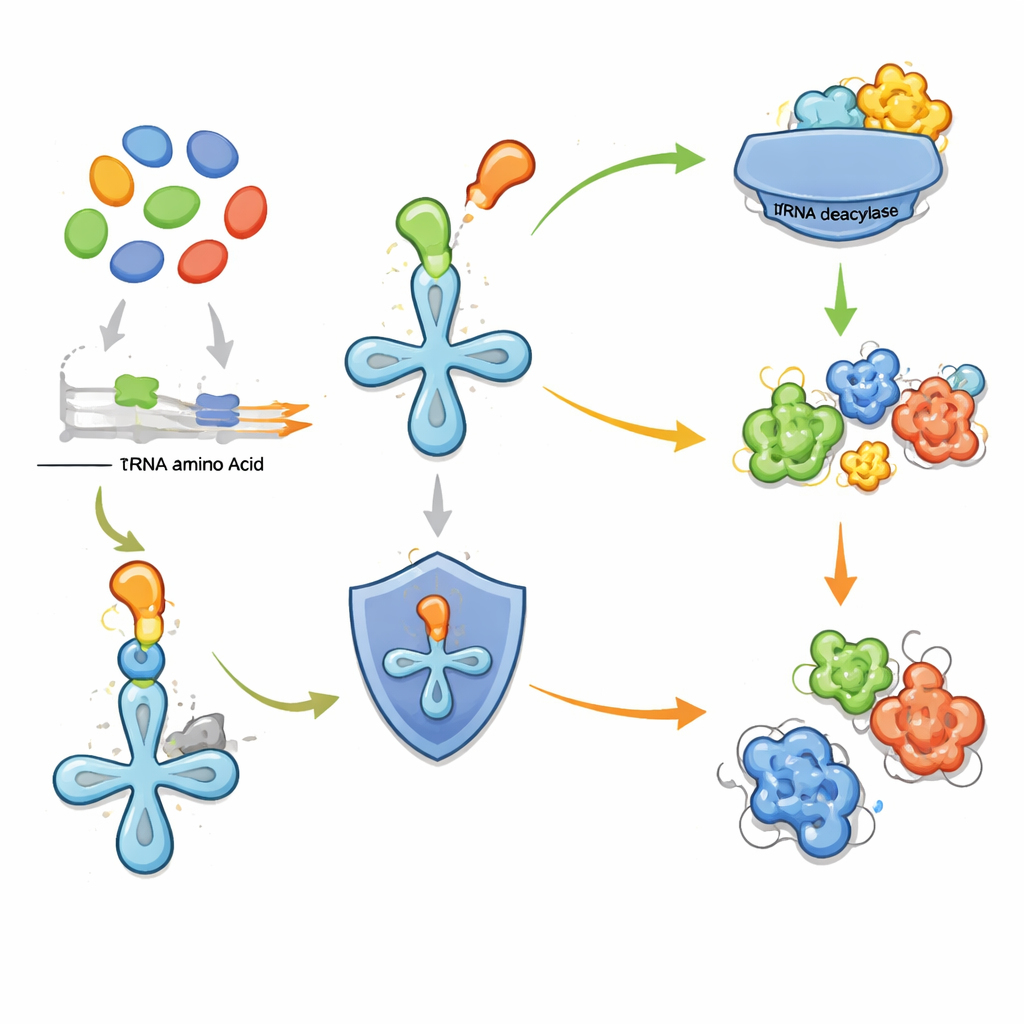
Kwaliteitscontrole‑enzymen als wegwijzers
Het belangrijkste inzicht van het nieuwe werk is dat bepaalde cellulaire "proeflees"‑enzymen kunnen fungeren als bakens voor nabije routes die vreemde aminozuren maken. Wanneer een cel een niet‑standaard aminozuur produceert, bestaat het risico dat het per ongeluk in eiwitten wordt ingebouwd en hun functie schaadt. Om dit te voorkomen dragen sommige microben zelfstandige tRNA‑deacylases—enzymen die onjuist aangehechte aminozuren van transfer‑RNA verwijderen, de adaptoren die bouwstenen aan de eiwitfabriek leveren. De auteurs hadden eerder aangetoond dat een dergelijke deacylase bacteriën beschermt tegen het misbruiken van gefluoreerd threonine. Hier breiden ze dat idee uit: als een deacylase‑gen naast een cluster van andere metabole genen staat, kan het er zitten om te waarschuwen tegen een lokaal gemaakt, mogelijk schadelijk aminozuur. Dat maakt de deacylase tot een handig marker voor een anders cryptisch biosynthetisch gencluster.
Genomen doorzoeken met een nieuwe blik
Met de focus op één deacylase‑familie genaamd AlaX doorzocht het team meer dan 23.000 gerelateerde sequenties. Ze bouwden een visualisatietool, tR3D, die in kaart brengt hoe elk deacylase‑gen wordt omringd door zijn buren in het genoom. De meeste AlaX‑enzymen verschenen naast huishoudgenen die betrokken zijn bij routinematige aminozuur‑ en eiwitmetabolisme. Maar ongeveer 11 procent bevond zich in een meer exotisch gezelschap, nabij transporteiwitten, regulatoren en ongewone enzymen die typisch zijn voor secundaire metabolisme—de gespecialiseerde chemie die microben gebruiken voor verdediging of signaalgeving. Deze korte lijst van veelbelovende clusters bevatte slechts een bescheiden fractie die tot bekende klassen natuurlijke producten behoorde, wat suggereert dat veel anderen eerder over het hoofd geziene chemie vertegenwoordigen.
Nieuwe moleculen uit gemarkeerde clusters
Om de strategie te testen, onderzochten de onderzoekers experimenteel twee heel verschillende genclusters die door nabije deacylases waren gemarkeerd. Het eerste, een compact viergenen‑unit die in meer dan honderd soorten voorkomt, codeert voor een eenvoudig enzym dat een hydroxylgroep aan methionine toevoegt, een veelvoorkomend aminozuur, waarmee een niet‑standaard variant ontstaat. De partner‑deacylase verwijdert selectief dit gewijzigde methionine van transfer‑RNA en beschermt de cel tegen het verkeerd herkennen ervan als het normale bouwblok. Het tweede cluster, afkomstig van een bodemmicrobe, is uitgebreider. Het combineert enzymen die een reactieve stikstof–stikstofeenheid genereren met anderen die drie aminozuurderivaten aan elkaar koppelen. Door de route opnieuw op te bouwen in laboratoriumbacteriën en gelabelde uitgangsstoffen te volgen, ontdekte het team een nieuw hydrazide‑verbonden tripeptide dat ze fuscazine noemen. De ruggengraat ervan is gebouwd uit arginine, alanine en een ringvormig derivaat van lysine, verbonden op een ongebruikelijke manier die eerder alleen in complexere systemen was gezien.
Deuren openen naar toekomstige ontdekkingen
Deze casestudies tonen aan dat tRNA‑deacylases meer zijn dan eenvoudige kwaliteitscontrolemiddelen—ze wijzen ook DNA‑buurten aan waar de evolutie de aminozuurchemie in nieuw terrein heeft geduwd. Door deze wegwijzers te volgen identificeerden de auteurs duizenden kandidaat‑clusters, waarvan veel buiten de standaardcategorieën van huidig genoom‑mining vallen. Hun tR3D‑platform kan ook op andere enzymfamilies worden toegepast, waardoor onderzoekers kunnen inzoomen op genen die waarschijnlijk ongebruikelijke bindingsvormende reacties coderen. Voor niet‑experts is de conclusie dat levende cellen een enorme bibliotheek aan chemische oplossingen verbergen, en dat slimme manieren om genomen te lezen—geleid door ingebouwde veiligheidskleppen zoals deacylases—die beginnen te onthullen. Elke nieuw in kaart gebrachte route vergroot niet alleen het fundamentele begrip van hoe het leven moleculen bouwt, maar biedt ook frisse uitgangspunten voor het ontwerpen van geneesmiddelen en biokatalysatoren.
Bronvermelding: Millar, D.C., Zhou, Y., Marchand, J.A. et al. tRNA-deacylase-directed discovery of biosynthetic pathways. Nat. Chem. 18, 863–871 (2026). https://doi.org/10.1038/s41557-026-02126-5
Trefwoorden: natuurlijke producten, niet‑standaard aminozuren, genoom‑mining, tRNA‑kwaliteitscontrole, biosynthetische genclusters