Clear Sky Science · de
tRNA-Deacylase-gesteuerte Entdeckung biosynthetischer Wege
Verborgene Chemie in lebenden Zellen
Viele der heutigen Medikamente, von Schmerzmitteln über Antibiotika bis hin zu Krebsmedikamenten, begannen als kleine Moleküle, die Mikroben oder Pflanzen für ihre eigenen Zwecke herstellen. Doch selbst nach Jahrzehnten der Suche vermuten Wissenschaftler, dass die meisten chemischen Raffinessen der Natur noch unentdeckt sind. Diese Studie zeigt einen neuen Weg auf, schwer auffindbare Pfade in mikrobieller DNA zu erkennen, die ungewöhnliche Aminosäuren und kurze Peptide bauen—Moleküle, die zukünftig zu Arzneistoffen oder Forschungswerkzeugen werden könnten.
Warum besondere Bausteine wichtig sind
Aminosäuren sind vor allem als Bausteine von Proteinen bekannt, doch Zellen formen sie auch zu einer enormen Vielfalt anderer Moleküle um. Einige sind nicht‑standardisierte Aminosäuren, die seltene Elemente wie Fluor oder Arsen enthalten oder ungewöhnliche Bindungen zwischen Stickstoffatomen aufweisen. Andere werden in komplexe Antibiotika, Neuromodulatoren wie Psilocybin oder Peptidhormone wie Insulin eingebaut. Weil diese Strukturen so vielfältig sind, ähneln die Gene, die sie produzieren, oft nicht den klassischen Enzymfamilien, nach denen heutige Genomsuchwerkzeuge suchen. Infolgedessen bleiben viele der zugrunde liegenden Wege in den riesigen Mengen mikrobieller DNA, die derzeit sequenziert werden, unsichtbar.
Qualitätskontroll‑Enzyme als Wegweiser
Die zentrale Einsicht der neuen Arbeit ist, dass bestimmte zelluläre „Korrekturlese“‑Enzyme als Leuchttürme für benachbarte Wege dienen können, die seltsame Aminosäuren herstellen. Wenn eine Zelle eine nicht‑standardmäßige Aminosäure produziert, besteht das Risiko, dass sie fälschlich in Proteine eingebaut wird und deren Funktion schädigt. Um das zu vermeiden, tragen einige Mikroben eigenständige tRNA‑Deacylasen—Enzyme, die fälschlich angehängte Aminosäuren von der Transfer‑RNA entfernen, den Adaptoren, die Bausteine in die Proteinfabrik einspeisen. Die Autoren hatten zuvor gezeigt, dass eine solche Deacylase Bakterien davor schützt, eine fluorierte Threoninvariante zu missbrauchen. Hier erweitern sie diese Idee: Wenn ein Deacylase‑Gen neben einem Cluster anderer Stoffwechselgene liegt, könnte es dazu dienen, gegen eine lokal gebildete, potenziell schädliche Aminosäure zu schützen. Das macht die Deacylase zu einem hilfreichen Marker für ein sonst kryptisches biosynthetisches Gencluster.
Genome mit neuer Perspektive durchsuchen
Mit Fokus auf eine Deacylase‑Familie namens AlaX durchforstete das Team mehr als 23.000 verwandte Sequenzen. Sie entwickelten ein Visualisierungswerkzeug, tR3D, das abbildet, wie jedes Deacylase‑Gen von seinen Nachbarn im Genom umgeben ist. Die meisten AlaX‑Enzyme traten neben sogenannten Haushaltsgenen auf, die an der routinemäßigen Aminosäure‑ und Proteinmetabolismus beteiligt sind. Etwa 11 Prozent jedoch standen in exotischerer Gesellschaft, in der Nähe von Transportern, Regulatoren und ungewöhnlichen Enzymen, wie sie typisch sind für die Sekundärmetabolismus‑Chemie—die spezialisierte Chemie, die Mikroben für Abwehr oder Signalgebung verwenden. Diese kurze Liste vielversprechender Cluster enthielt nur einen bescheidenen Anteil, der zu bekannten Naturstoffklassen gehörte, was darauf hindeutet, dass viele andere zuvor übersehene Chemie darstellen.
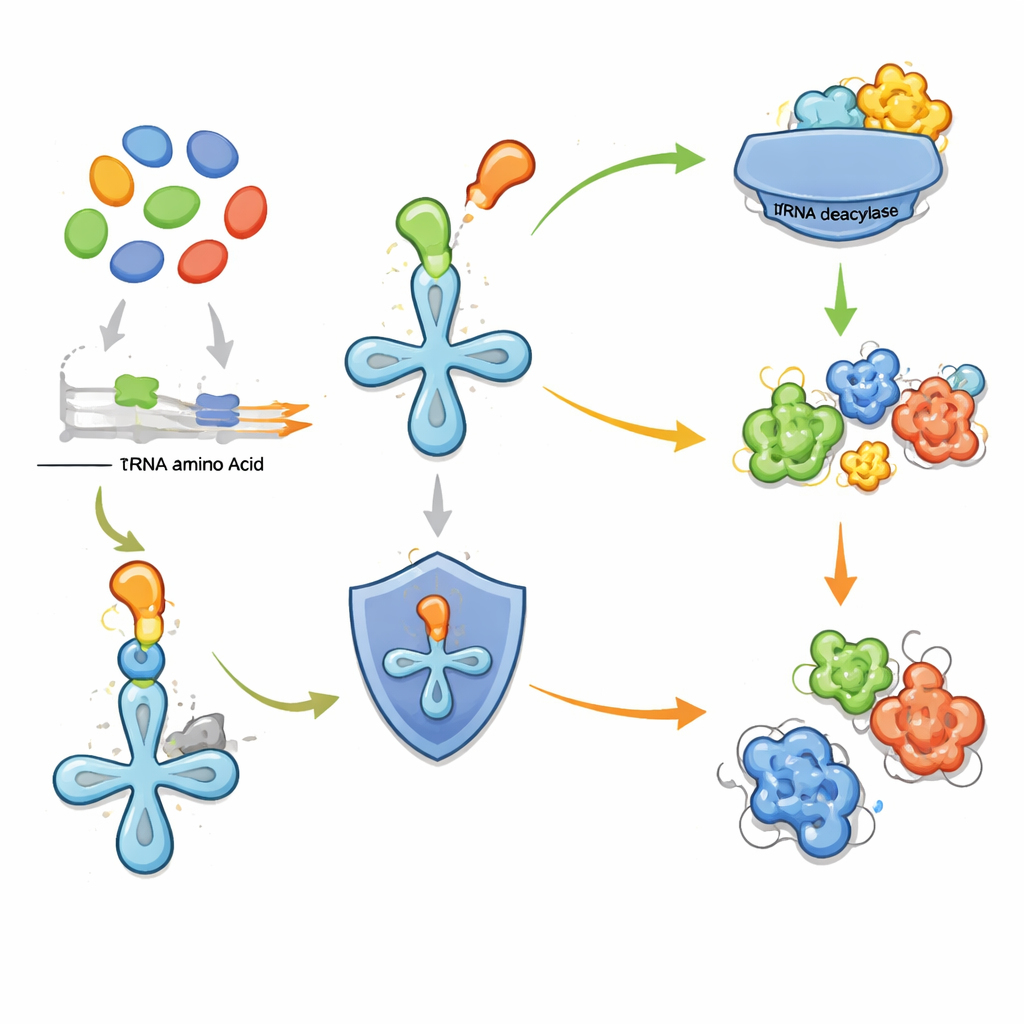
Neue Moleküle aus markierten Clustern
Um die Strategie zu testen, untersuchten die Forschenden experimentell zwei sehr unterschiedliche Gencluster, die durch benachbarte Deacylasen markiert worden waren. Das erste, eine kompakte Vier‑Gen‑Einheit, die in über hundert Arten vorkommt, kodiert ein einfaches Enzym, das eine Hydroxylgruppe an Methionin anfügt und so eine nicht‑standardmäßige Variante erzeugt. Die dazugehörige Deacylase entfernt selektiv dieses modifizierte Methionin von der Transfer‑RNA und schützt die Zelle davor, es fälschlich als normalen Baustein zu verwenden. Das zweite Cluster aus einem Bodenmikroben ist komplexer. Es kombiniert Enzyme, die eine reaktive Stickstoff‑Stickstoff‑Einheit erzeugen, mit anderen, die drei aus Aminosäuren abgeleitete Bausteine zusammenfügen. Durch Rekonstituieren des Weges in Laborbakterien und Verfolgen markierter Ausgangsmaterialien entdeckte das Team ein neues, hydrazidverknüpftes Tripeptid, das sie fuscazine nennen. Dessen Rückgrat besteht aus Arginin, Alanin und einer ringförmigen Lysin‑Derivat‑Einheit, verbunden auf eine ungewöhnliche Weise, die zuvor nur in komplexeren Systemen beobachtet worden war.
Tore für zukünftige Entdeckungen öffnen
Diese Fallstudien zeigen, dass tRNA‑Deacylasen mehr sind als einfache Qualitätskontroll‑Werkzeuge—sie machen auch DNA‑Nachbarschaften sichtbar, in denen die Evolution die Aminosäurechemie in neues Gelände vorangetrieben hat. Indem man diesen Wegweisern folgt, identifizierten die Autoren Tausende Kandidatencluster, von denen viele außerhalb der Standardkategorien liegen, die beim heutigen Genom‑Mining verwendet werden. Ihre tR3D‑Plattform lässt sich auch auf andere Enzymfamilien anwenden und hilft Forschern, Gene zu fokussieren, die wahrscheinlich ungewöhnliche Bindungsbildende Reaktionen kodieren. Für Nicht‑Experten lautet die Botschaft: Lebende Zellen verbergen eine riesige Bibliothek chemischer Lösungen, und intelligente Methoden, Genome zu lesen—geführ t von eingebauten Sicherheitsventilen wie Deacylasen—beginnen, sie zu offenbaren. Jeder neu kartierte Weg erweitert nicht nur das grundlegende Verständnis dafür, wie Leben Moleküle baut, sondern bietet auch frische Ausgangspunkte für die Entwicklung von Medikamenten und Biokatalysatoren.
Zitation: Millar, D.C., Zhou, Y., Marchand, J.A. et al. tRNA-deacylase-directed discovery of biosynthetic pathways. Nat. Chem. 18, 863–871 (2026). https://doi.org/10.1038/s41557-026-02126-5
Schlüsselwörter: Naturstoffe, nichtkanonische Aminosäuren, Genom‑Mining, tRNA‑Qualitätskontrolle, biosynthetische Gencluster