Clear Sky Science · fr
découverte de voies biosynthétiques guidée par les déacylases de l’ARNt
Chimie cachée à l’intérieur des cellules vivantes
Beaucoup des médicaments d’aujourd’hui, des analgésiques aux antibiotiques en passant par les traitements anticancéreux, ont d’abord été de petites molécules fabriquées par des microbes ou des plantes pour leurs propres besoins. Pourtant, malgré des décennies de recherche, les scientifiques soupçonnent que la plupart des astuces chimiques de la nature restent à découvrir. Cette étude révèle une nouvelle façon de repérer dans l’ADN microbien des voies difficiles à trouver qui synthétisent des acides aminés inhabituels et de courts peptides — des molécules qui pourraient devenir les médicaments ou outils de recherche de demain.
Pourquoi les blocs de construction spéciaux comptent
Les acides aminés sont surtout connus comme les blocs de construction des protéines, mais les cellules les remodèlent aussi en une immense variété d’autres molécules. Certaines sont des acides aminés non standard contenant des éléments rares comme le fluor ou l’arsenic, ou présentant des liaisons inhabituelles entre atomes d’azote. D’autres sont assemblés en antibiotiques complexes, en neuromodulateurs tels que la psilocybine, ou en peptides hormonaux comme l’insuline. Parce que ces structures sont si diverses, les gènes qui les produisent ne ressemblent souvent pas aux familles d’enzymes classiques que recherchent les outils d’exploration de génomes actuels. En conséquence, de nombreuses voies sous‑jacentes restent invisibles dans les vastes ensembles d’ADN microbien séquencés aujourd’hui.
Des enzymes de contrôle qualité comme panneaux indicateurs
L’idée clé du nouveau travail est que certaines enzymes cellulaires de « relecture » peuvent servir de balises pour repérer des voies voisines qui fabriquent des acides aminés étranges. Lorsqu’une cellule produit un acide aminé non standard, il y a un risque qu’il soit inséré par erreur dans des protéines, nuisant à leur fonction. Pour éviter cela, certains microbes portent des déacylases d’ARNt autonomes — des enzymes qui retirent les acides aminés mal attachés de l’ARN de transfert, les adaptateurs qui alimentent la machinerie de fabrication des protéines. Les auteurs avaient montré précédemment qu’une telle déacylase protège les bactéries contre l’utilisation inappropriée d’une thréonine fluorée. Ici ils étendent cette idée : si un gène de déacylase est situé à côté d’un groupe d’autres gènes métaboliques, il peut être là pour protéger contre un acide aminé produit localement et potentiellement nocif. Cela fait de la déacylase un marqueur pratique pour un cluster de gènes biosynthétiques autrement cryptique.
Explorer les génomes avec une nouvelle perspective
En se concentrant sur une famille de déacylases appelée AlaX, l’équipe a passé au crible plus de 23 000 séquences apparentées. Ils ont construit un outil de visualisation, tR3D, qui cartographie l’entourage génomique de chaque gène de déacylase. La plupart des enzymes AlaX apparaissaient à côté de gènes de maintenance impliqués dans le métabolisme courant des acides aminés et des protéines. Mais environ 11 % se trouvaient en compagnie plus exotique, à proximité de transporteurs, de régulateurs et d’enzymes inhabituelles typiques du métabolisme secondaire — la chimie spécialisée que les microbes utilisent pour la défense ou la signalisation. Cette courte liste de clusters prometteurs comprenait seulement une fraction modeste appartenant à des classes de produits naturels bien connues, suggérant que beaucoup d’autres représentent une chimie jusque‑là négligée.
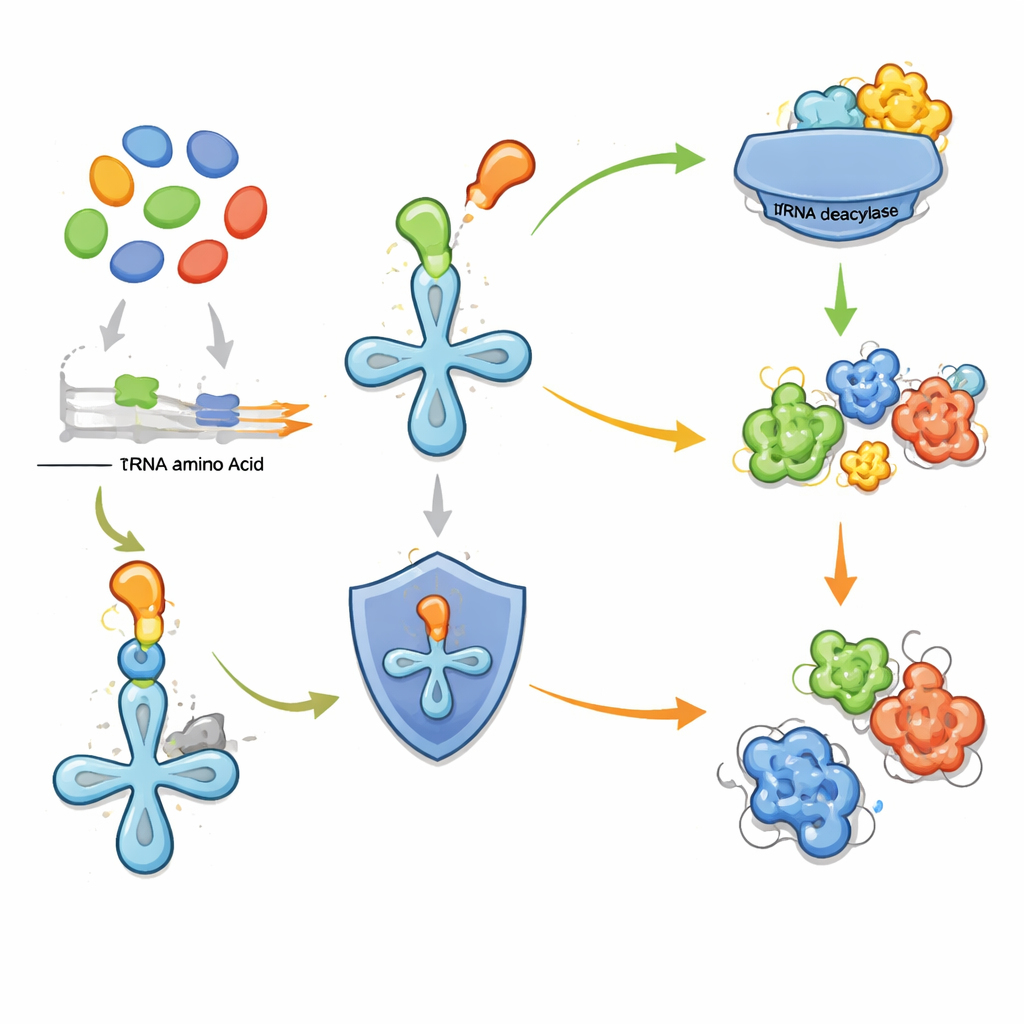
Nouvelles molécules issues de clusters marqués
Pour tester la stratégie, les chercheurs ont étudié expérimentalement deux clusters de gènes très différents repérés par des déacylases voisines. Le premier, une unité compacte de quatre gènes trouvée dans plus d’une centaine d’espèces, code pour une enzyme simple qui ajoute un groupe hydroxyle sur la méthionine, un acide aminé courant, créant une variante non standard. La déacylase partenaire enlève sélectivement cette méthionine modifiée de l’ARN de transfert, protégeant la cellule contre son interprétation comme bloc de construction normal. Le second cluster, issu d’un microbe du sol, est plus élaboré. Il combine des enzymes qui génèrent une unité réactive azote‑azote avec d’autres qui assemblent trois fragments dérivés d’acides aminés. En reconstituant la voie dans des bactéries de laboratoire et en suivant des précurseurs marqués, l’équipe a mis au jour un nouveau tripeptide lié par une hydrazide qu’ils nomment fuscazine. Son ossature est construite à partir d’arginine, d’alanine et d’un dérivé cyclique de lysine, connectés d’une manière inhabituelle jusqu’alors observée seulement dans des systèmes plus complexes.
Ouvrir la voie à de futures découvertes
Ces études de cas montrent que les déacylases d’ARNt sont plus que de simples outils de contrôle qualité — elles mettent aussi en évidence des quartiers d’ADN où l’évolution a poussé la chimie des acides aminés vers de nouveaux territoires. En suivant ces panneaux indicateurs, les auteurs ont identifié des milliers de clusters candidats, dont beaucoup échappent aux catégories standard employées dans l’exploration génomique actuelle. Leur plateforme tR3D peut être appliquée à d’autres familles d’enzymes, aidant les chercheurs à cibler des gènes susceptibles de coder des réactions de formation de liaisons inhabituelles. Pour le grand public, la conclusion est que les cellules vivantes cachent une vaste bibliothèque de solutions chimiques, et que des méthodes intelligentes de lecture des génomes — guidées par des soupapes de sécurité intégrées comme les déacylases — commencent à la révéler. Chaque voie nouvellement cartographiée élargit non seulement la compréhension fondamentale de la façon dont la vie construit des molécules, mais offre aussi de nouveaux points de départ pour concevoir des médicaments et des biocatalyseurs.
Citation: Millar, D.C., Zhou, Y., Marchand, J.A. et al. tRNA-deacylase-directed discovery of biosynthetic pathways. Nat. Chem. 18, 863–871 (2026). https://doi.org/10.1038/s41557-026-02126-5
Mots-clés: produits naturels, acides aminés non canoniques, exploration de génomes, contrôle de qualité de l’ARNt, clusters de gènes biosynthétiques