Clear Sky Science · nl
Wereldwijde nucleïnezuurarchieven mogelijk maken via veelzijdige, schaalbare biochemische selectie uit kamertemperatuurarchieven
Waarom het bewaren van genetisch materiaal ertoe doet
Stel je voor dat je nieuwe virussen kunt volgen, zeldzame ziekten kunt bestuderen en het genetische spoor van volledige ecosystemen kunt bewaren zonder rijen energieverslindende vriezers. Vandaag moet de meeste DNA en zeker kwetsbaar RNA extreem koud bewaard worden, wat kostbaar en onpraktisch is voor veel klinieken en laboratoria wereldwijd. Dit artikel presenteert een nieuwe manier om omvangrijke verzamelingen genetische monsters bij kamertemperatuur op te slaan en doorzoekbaar te maken, terwijl men toch snel precies die monsters kan vinden die wetenschappers voor testen nodig hebben.
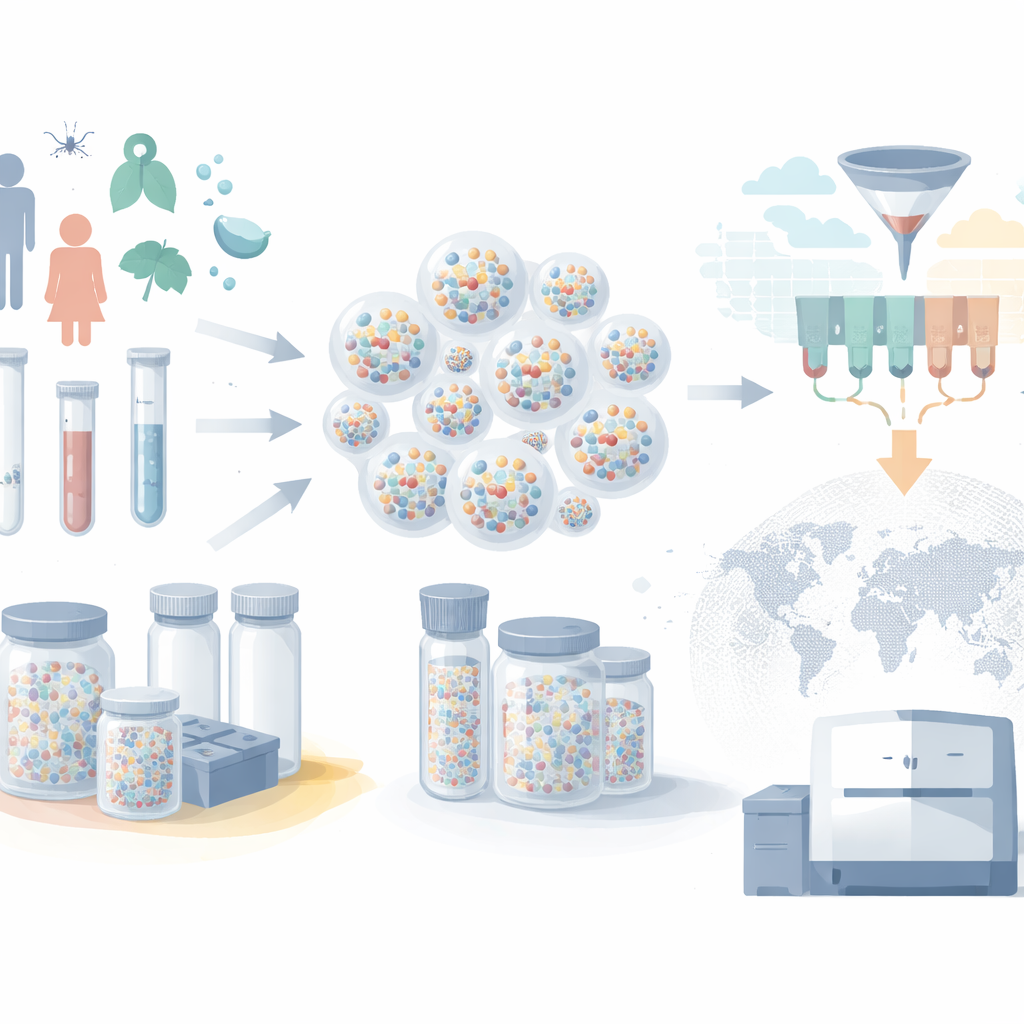
Van vrieshuisen naar kleine capsules
Moderne biobanken bewaren miljoenen bloed-, speeksel- en weefselmonsters, maar elk monster zit doorgaans in een eigen gelabelde buis in een grote vriezer. Naarmate collecties groeien, wordt deze "één buis per monster"-aanpak duur en traag. Vriezers vragen voortdurend elektriciteit, robots verplaatsen monsters één voor één, en RNA kan degraderen als er iets misgaat. De auteurs gebruiken in plaats daarvan microscopische silica-schelpen — microcapsules — om genetisch materiaal te beschermen. DNA en RNA worden gevangen in deze duurzame deeltjes die stabiel blijven bij kamertemperatuur. Veel verschillende nucleïnezuren kunnen samen in dezelfde capsule worden opgeslagen, en enorme aantallen capsules kunnen worden gebundeld in één klein buisje, wat opslagruimte en energieverbruik drastisch verlaagt.
Buisjes veranderen in een doorzoekbare database
Opslag van monsters is slechts de helft van het probleem; onderzoekers moeten ook het juiste deel kunnen selecteren wanneer nieuwe vragen ontstaan. De sleutelinnovatie in dit werk is een slim barcode‑schema dat elke capsule als een klein databankrecord behandelt. Korte DNA-stukjes die aan de buitenkant van elke capsule zijn bevestigd fungeren als "tags" die het monster beschrijven: bijvoorbeeld leeftijd van de patiënt, stad van herkomst, maand en jaar van monstername, vaccinatiestatus en of de persoon symptomen had. In plaats van voor elke mogelijke waarde een unieke tag toe te kennen, hergebruikt het systeem een compacte set tags en combineert die op verschillende manieren, vergelijkbaar met hoe cijfers getallen vormen of hoe categorieën met combinaties worden gecodeerd. Dit "type-bewuste" ontwerp maakt het mogelijk om eenvoudige fysieke bewerkingen op tags uit te voeren die het krachtige bereik- en filtergedrag van digitale databases nabootsen.
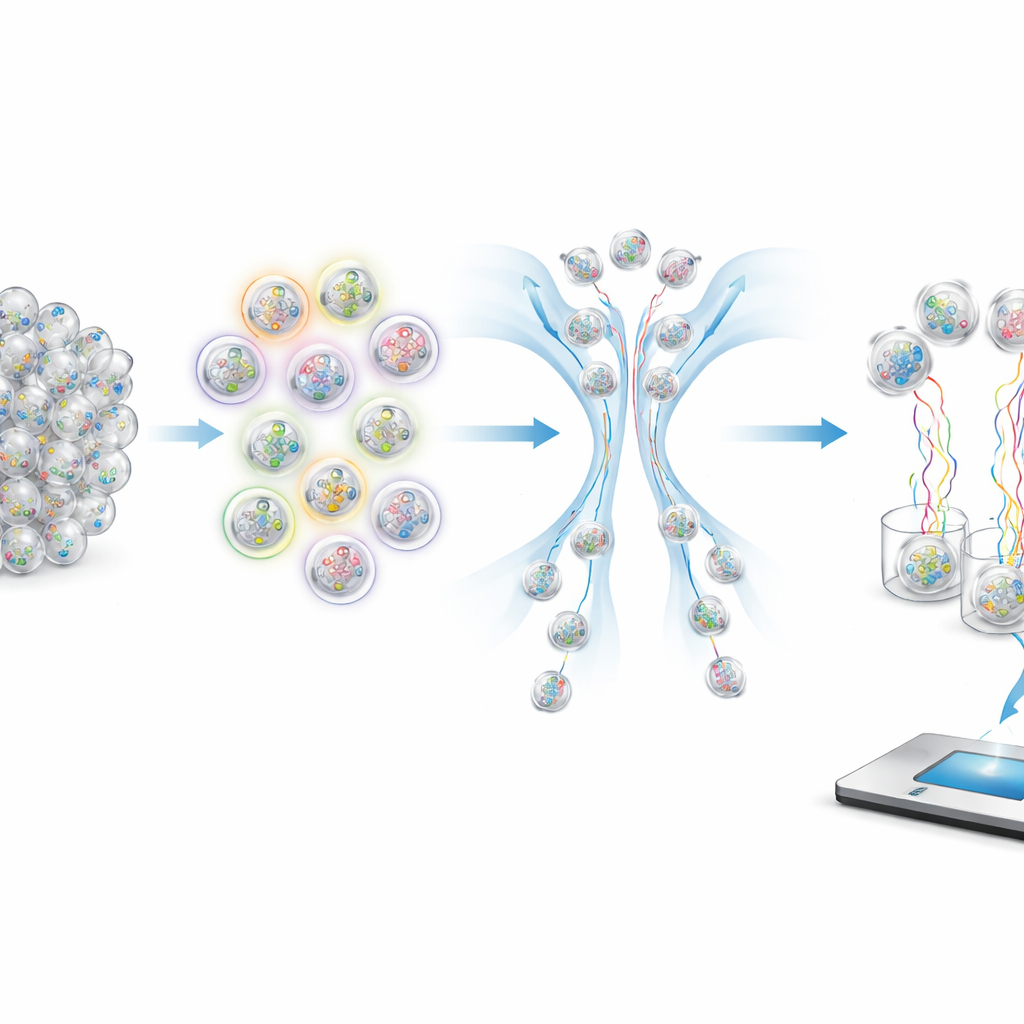
Hoe je moleculen vragen stelt
Om specifieke monsters uit een volle buis te halen gebruiken de auteurs fluorescente probes die alleen hechten aan capsules met overeenkomende tags. Deze probes dragen gekleurde kleurstoffen die door een flow‑sorter gelezen kunnen worden; fel oplichtende capsules worden naar één pad gestuurd en zwak lichtende naar een ander. Door te kiezen welke tags op te lichten en hoe de kleuren te combineren, kan het systeem logische bewerkingen zoals EN, OF en NIET uitvoeren. Bijvoorbeeld, het selecteren van "niet symptomatisch" houdt in dat elke capsule die oplicht bij de symptoom‑tag wordt verworpen. Numerieke bereiken zoals leeftijdscategorieën of datumbereiken worden afgehandeld door sommige minder belangrijke "cijfers" in de gecodeerde leeftijd of datum te negeren, zodat één enkele query alle capsules kan ophalen waarvan de tags binnen een gekozen venster vallen.
Het systeem testen met een nepuitbraak
Om te laten zien dat hun aanpak in de praktijk werkt, bouwden de onderzoekers een kleine maar realistische testdatabase van 96 synthetische SARS-CoV-2‑monsters, gemodelleerd alsof ze waren verzameld van vliegtuigpassagiers die in Boston aankwamen. Elke capsule droeg fragmenten van viraal RNA plus een unieke interne identificator en externe tags met verzonnen patiënt- en vluchtgegevens. Vervolgens voerden ze een reeks queries uit die echte epidemiologie weerspiegelen: alle asymptomatische passagiers vinden, specifieke leeftijdsgroepen selecteren om naar variantpatronen te zoeken, en een complexe gecombineerde query uitvoeren die passagiers uit een bepaalde stad in bepaalde maanden van 2020 naar voren haalt die ofwel symptomatisch waren of niet gevaccineerd. Het sequencen van de opgehaalde capsules bevestigde dat de juiste monsters met zeer hoge nauwkeurigheid waren verrijkt, zelfs wanneer de gewenste groep slechts een fractie van de totale pool was.
Bewijs dat echte patiëntmonsters bewaard kunnen blijven
Buiten synthetische tests om encapsuleerde het team echte patiëntafgeleide SARS-CoV-2‑monsters met verschillende Omicron-sublineages. Na opslag en herstel sequentieerden ze de virale genomen en vergeleken die met dezelfde monsters die nooit waren geëncapsuleerd. Ondanks het werken met zeer lage hoeveelheden viraal RNA herstelde de methode nog steeds de correcte varianten, wat aantoont dat de silica-bescherming subtiele genetische verschillen niet uitwist. Omdat niet‑doelcapsules na elke zoekopdracht bewaard kunnen worden, kan de pool herhaaldelijk worden hergebruikt, en eenvoudige interne DNA-identificatoren maken doorlopende integriteitscontroles van het archief mogelijk, vergelijkbaar met controlemechanismen in digitale opslag.
Wat dit betekent voor de toekomst
Kort gezegd laat deze studie zien dat genetische monsters in kleine, duurzame capsules kunnen worden verpakt, compact bij kamertemperatuur kunnen worden opgeslagen en later uit elkaar gehaald kunnen worden met flexibele, databaseachtige zoekopdrachten. De methode vermindert de afhankelijkheid van vriezers drastisch en maakt rijke queries mogelijk die leeftijdsgroepen, locaties, data en gezondheidsstatussen in één enkele bewerking kunnen combineren. Met verdere opschaling zouden dergelijke archieven bij kamertemperatuur wereldwijde pathogeenbewaking, precisiegeneeskunde en zelfs langdurige ecologische monitoring kunnen ondersteunen op plekken waar koudeketeninfrastructuur schaars is. Het werk wijst op een toekomst waarin ’s werelds biologische informatie compact kan worden opgeslagen en even gemakkelijk toegankelijk is als bestanden in de cloud.
Bronvermelding: Berleant, J.D., Banal, J.L., Rao, D.K. et al. Enabling global-scale nucleic acid repositories through versatile, scalable biochemical selection from room-temperature archives. Nat Commun 17, 2807 (2026). https://doi.org/10.1038/s41467-026-69402-3
Trefwoorden: opslag van nucleïnezuur, moleculaire database, DNA-barcode, pathogeenbewaking, biobanking bij kamertemperatuur