Clear Sky Science · de
Ermöglichung globaler Nukleinsäure-Archive durch vielseitige, skalierbare biochemische Selektion aus Raumtemperatur-Archiven
Warum die Aufbewahrung genetischen Materials wichtig ist
Stellen Sie sich vor, man könnte neue Viren überwachen, seltene Krankheiten erforschen und die genetischen Spuren ganzer Ökosysteme bewahren, ohne Reihen stromfressender Gefrierschränke zu benötigen. Heute müssen die meisten DNA- und insbesondere die empfindlichen RNA-Proben extrem kalt gehalten werden, was teuer und für viele Kliniken und Labore weltweit unpraktisch ist. Diese Arbeit stellt einen neuen Weg vor, riesige Sammlungen genetischer Proben bei Raumtemperatur zu lagern und dennoch schnell genau die Proben zu finden, die Wissenschaftler für Tests benötigen.
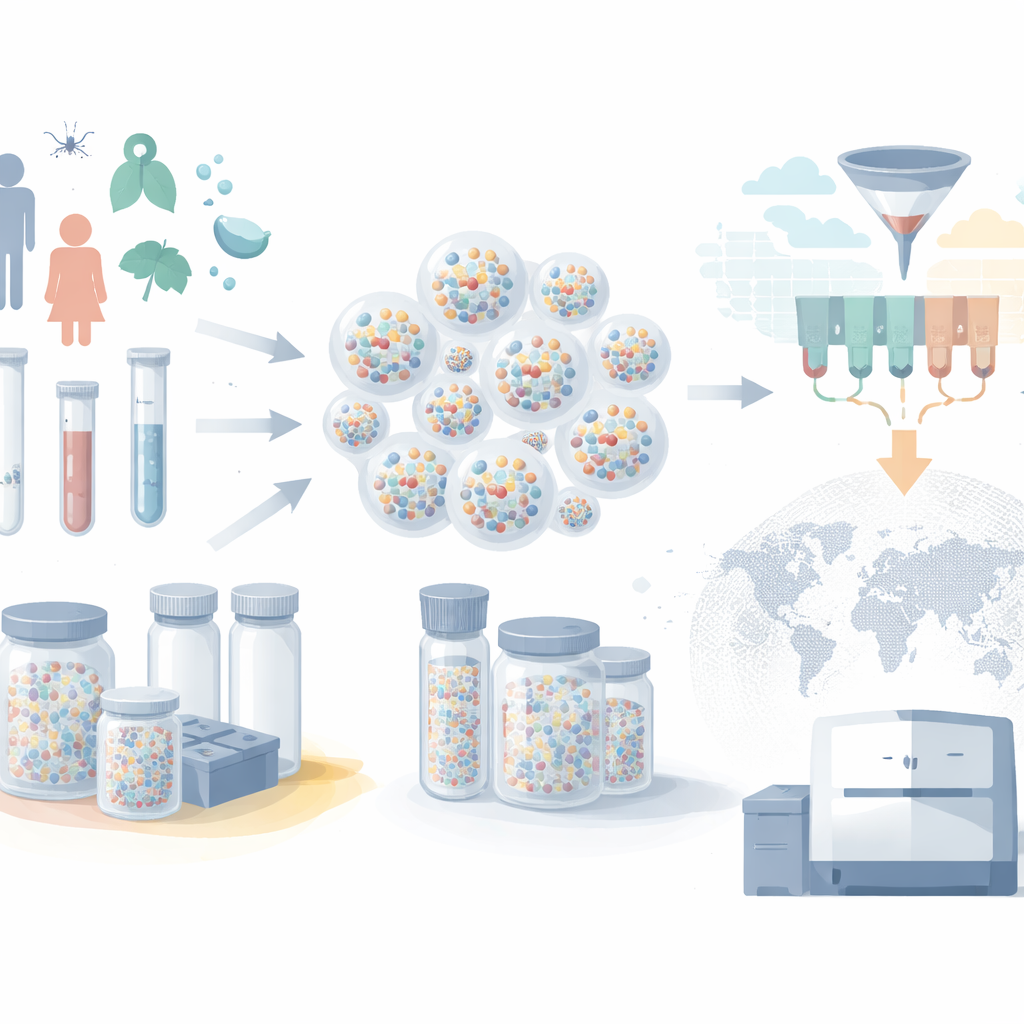
Von Gefrierschranksammlungen zu winzigen Kapseln
Moderne Biobanken verwahren Millionen von Blut-, Speichel- und Gewebeproben, doch typischerweise steckt jede Probe in einem beschrifteten Röhrchen in einem großen Gefrierschrank. Wenn Sammlungen wachsen, wird dieses „ein Röhrchen pro Probe“-Prinzip teuer und langsam. Gefrierschränke benötigen dauerhafte Stromversorgung, robotische Systeme bewegen Proben einzeln, und RNA kann degradiert werden, wenn etwas schiefläuft. Die Autoren verwenden stattdessen mikroskopisch kleine Silikat-Schalen—Mikrokapseln—zum Schutz des genetischen Materials. DNA und RNA werden in diesen robusten Partikeln eingeschlossen, die bei Raumtemperatur stabil bleiben. Viele verschiedene Nukleinsäuren können gemeinsam in derselben Kapsel gelagert werden, und riesige Mengen von Kapseln lassen sich zu einer einzigen kleinen Probe zusammenfassen, wodurch Lagerraum und Energiebedarf stark reduziert werden.
Röhrchen in durchsuchbare Datenbanken verwandeln
Proben zu lagern ist nur die halbe Aufgabe; Forscher müssen auch in der Lage sein, die richtige Teilmenge auszuwählen, wenn neue Fragen auftreten. Die Schlüsselinnovation dieser Arbeit ist ein cleveres Barcodeschema, das jede Kapsel wie einen kleinen Datenbankeintrag behandelt. Kurze DNA-Stücke, die außen an jeder Kapsel befestigt sind, fungieren als „Tags“, die die Probe beschreiben: zum Beispiel Alter des Patienten, Herkunftsstadt, Monat und Jahr der Entnahme, Impfstatus und ob die Person Symptome zeigte. Anstatt für jeden möglichen Wert ein einzigartiges Tag zu vergeben, verwendet das System eine kompakte Menge von Tags, die in unterschiedlicher Kombination wiederverwendet werden—ähnlich wie Ziffern zur Darstellung von Zahlen oder wie Kategorien durch Kombinationen kodiert werden können. Dieses „typenbewusste“ Design erlaubt einfache physische Operationen an den Tags, die die mächtigen Bereichs- und Filterabfragen digitaler Datenbanken nachahmen.
Wie man Molekülen Fragen stellt
Um spezifische Proben aus einem vollen Röhrchen zu gewinnen, verwenden die Autoren fluoreszierende Sonden, die nur an Kapseln binden, die passende Tags tragen. Diese Sonden tragen farbige Farbstoffe, die von einem strömungsbasierten Sortierer ausgelesen werden; hell leuchtende Kapseln werden auf einen Pfad und schwach leuchtende auf einen anderen geleitet. Durch die Wahl, welche Tags beleuchtet werden und wie die Farben kombiniert werden, kann das System logische Operationen wie UND, ODER und NICHT ausführen. Beispielsweise bedeutet die Auswahl „nicht symptomatisch“, alle Kapseln auszuschließen, die beim Test auf das Symptom-Tag aufleuchten. Numerische Bereiche wie Altersklassen oder Datumsintervalle werden behandelt, indem einige der weniger wichtigen „Ziffern“ in der kodierten Alters- oder Datumsangabe ignoriert werden, sodass eine einzige Anfrage alle Kapseln herausziehen kann, deren Tags in ein gewähltes Fenster fallen.
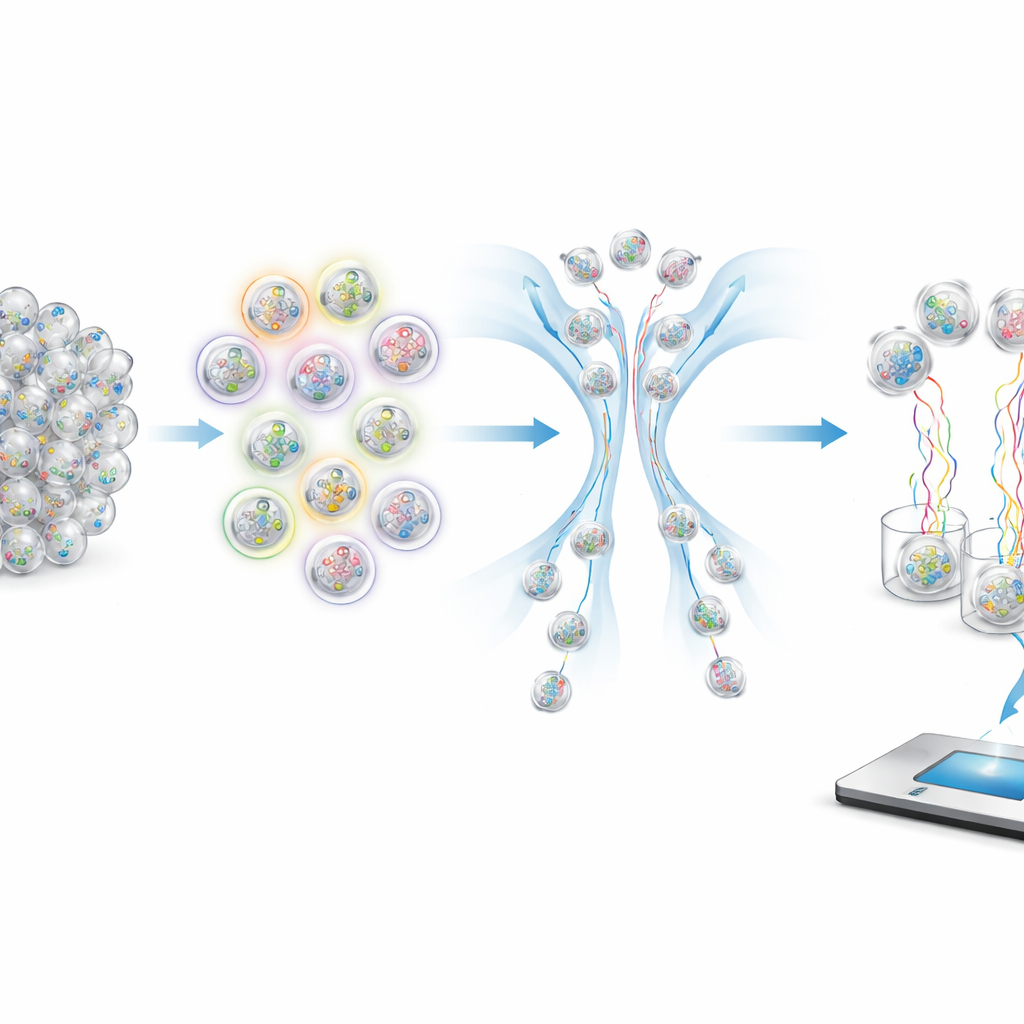
Systemtests mit einem simulierten Ausbruch
Um zu zeigen, dass ihr Ansatz praktisch funktioniert, bauten die Forscher eine kleine, aber realistische Testdatenbank mit 96 synthetischen SARS-CoV-2-Proben, modelliert als wären sie von Flugpassagieren gesammelt worden, die in Boston angekommen sind. Jede Kapsel enthielt Fragmente viraler RNA sowie eine eindeutige interne Kennung und externe Tags, die erfundene Patienten- und Fluginformationen kodierten. Anschließend führten sie eine Reihe von Abfragen durch, die reale epidemiologische Fragestellungen widerspiegeln: das Auffinden aller asymptomatischen Passagiere, die Auswahl bestimmter Altersgruppen zur Suche nach Variantenmustern und eine komplexe kombinierte Abfrage, die Passagiere aus einer bestimmten Stadt in bestimmten Monaten 2020 auswählte, die entweder symptomatisch oder ungeimpft waren. Die Sequenzierung der abgerufenen Kapseln bestätigte, dass die richtigen Proben mit sehr hoher Genauigkeit angereichert wurden, selbst wenn die gewünschte Gruppe nur einen Bruchteil des gesamten Pools ausmachte.
Beleg, dass echte Patientenproben erhalten bleiben können
Über synthetische Testfälle hinaus kapselte das Team echte, von Patienten stammende SARS-CoV-2-Proben mit verschiedenen Omikron-Sublineages ein. Nach Lagerung und Rückgewinnung sequenzierten sie die viralen Genome und verglichen sie mit denselben Proben, die niemals kapsuliert worden waren. Trotz sehr geringer Mengen viraler RNA konnte die Methode die korrekten Varianten wiedergewinnen, was zeigt, dass der Silikatschutz subtile genetische Unterschiede nicht verwischt. Da nicht zielgerichtete Kapseln nach jeder Suche aufbewahrt werden können, lässt sich der Pool wiederholt wiederverwenden, und einfache interne DNA-Kennungen erlauben fortlaufende Gesundheitsprüfungen des Archivs—ähnlich den Integritätsprüfungen in der digitalen Speicherung.
Was das für die Zukunft bedeutet
Kurz gesagt zeigt diese Studie, dass genetische Proben in winzige, langlebige Kapseln verpackt, bei Raumtemperatur dicht zusammen gelagert und später mittels flexibler, datenbankähnlicher Suchvorgänge wieder getrennt werden können. Die Methode reduziert die Abhängigkeit von Gefrierschränken drastisch und erlaubt gleichzeitig reichhaltige Abfragen, die Altersbereiche, Herkunftsorte, Daten und Gesundheitszustände in einem einzigen Vorgang kombinieren. Mit weiterer Skalierung könnten solche Archive bei Raumtemperatur die globale Pathogenüberwachung, Präzisionsmedizin und sogar langfristiges ökologisches Monitoring an Orten unterstützen, an denen Kaltketteninfrastruktur knapp ist. Die Arbeit weist auf eine Zukunft hin, in der die biologischen Informationen der Welt kompakt gespeichert und ebenso leicht zugänglich sind wie Dateien in der Cloud.
Zitation: Berleant, J.D., Banal, J.L., Rao, D.K. et al. Enabling global-scale nucleic acid repositories through versatile, scalable biochemical selection from room-temperature archives. Nat Commun 17, 2807 (2026). https://doi.org/10.1038/s41467-026-69402-3
Schlüsselwörter: Speicherung von Nukleinsäuren, molekulare Datenbank, DNA-Barcoding, Pathogenüberwachung, Biobanking bei Raumtemperatur