Clear Sky Science · it
Analisi trascrittomiche a singola cellula e bulk rivelano sottotipi immunitari associati a caratteristiche della morte cellulare programmata nel colangiocarcinoma intraepatico
Perché questo studio sul cancro del fegato è importante
Il colangiocarcinoma intraepatico è un tumore in rapida crescita che origina dai piccoli dotti biliari all'interno del fegato ed è spesso diagnosticato troppo tardi per l'intervento chirurgico. I clinici sanno che alcuni pazienti vivono molto più a lungo o rispondono meglio alle nuove immunoterapie rispetto ad altri, ma predire chi trarrà beneficio è stato difficile. Questo studio utilizza profilazioni genetiche avanzate e analisi a singola cellula per mostrare come diverse forme di morte cellulare "programmata" e il sistema immunitario interagiscano in questi tumori, e costruisce un punteggio pratico che potrebbe aiutare a personalizzare i trattamenti e guidare le decisioni cliniche.
Esplorare i tumori epatici cellula per cellula
I ricercatori hanno raccolto ampi set di dati di attività genica da centinaia di campioni tumorali, includendo sia tessuto bulk sia cellule singole, da risorse pubbliche e da una grande coorte clinica. Si sono concentrati su 2.701 geni legati a 21 tipi di morte cellulare programmata — i meccanismi intrinseci con cui le cellule possono autodistruggersi quando sono danneggiate o anomale. Confrontando il tessuto tumorale con il fegato non canceroso circostante, hanno ridotto l'elenco a 87 geni che risultavano sia deregolarizzati nel cancro sia potenzialmente importanti per la sopravvivenza dei pazienti. Questi geni erano coinvolti in note vie oncogeniche e forme di morte cellulare come l'apoptosi e la necroptosi, e mostravano anche schemi caratteristici di mutazioni e alterazioni cromosomiche nei tumori dei dotti biliari epatici. 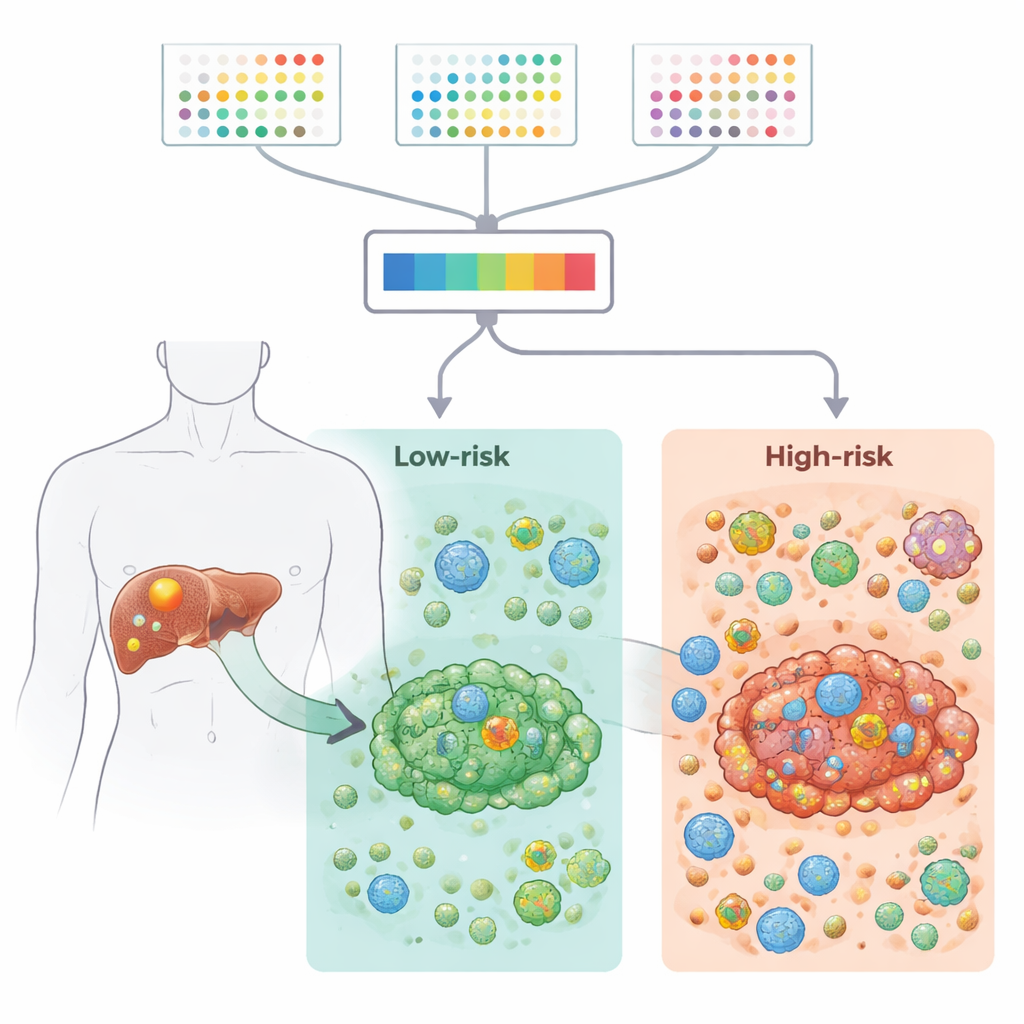
Costruire un punteggio di rischio a partire da nove geni chiave
Per convertire queste informazioni complesse in qualcosa di clinicamente utile, il gruppo ha testato 117 combinazioni di metodi di machine learning e modelli di sopravvivenza. L'approccio con le migliori prestazioni, che combinava regressione di Cox stepwise con random survival forests, ha distillato l'informazione in nove geni. A ogni paziente è stato assegnato un punteggio di rischio basato su quanto questi geni fossero attivati o repressi nel loro tumore. In più cohort indipendenti di pazienti, questa firma a nove geni ha separato in modo affidabile individui a rischio alto e basso con tempi di sopravvivenza nettamente diversi. I tumori ad alto rischio erano arricchiti per vie legate a stress e infiammazione, mentre i tumori a basso rischio mostravano vie metaboliche e di detossificazione più attive, suggerendo differenze biologiche fondamentali tra i due gruppi.
Quartieri immunitari all'interno del tumore
Lo studio si è quindi concentrato sul microambiente tumorale — l'insieme di cellule immunitarie, cellule di supporto e tessuto connettivo che circondano e infiltrano il cancro. Utilizzando più strumenti computazionali, gli autori hanno mostrato che i tumori ad alto rischio avevano punteggi immunitari e stromali più elevati, segnali infiammatori più forti e caratteristiche più immunosoppressive, inclusa un'aumentata presenza di cellule T regolatorie che possono attenuare le risposte antitumorali. Il sequenziamento RNA a singola cellula ha confermato che queste cellule T regolatorie e i fibroblasti erano più abbondanti nei tumori ad alto rischio e partecipavano a reti dense di comunicazione cellula–cellula. Al contrario, i tumori a basso rischio presentavano segnali più forti legati al collagene e un ambiente più equilibrato e meno suppressivo. Nel complesso, questi risultati suggeriscono che il pattern a nove geni è strettamente legato a quanto il "quartiere" immunitario locale sia favorevole o ostile al tumore. 
Orientare immunoterapia e scelte farmacologiche
Riconoscendo che l'immunoterapia sta diventando centrale nella cura del cancro, i ricercatori hanno creato un "PCD score" separato basato sugli stessi nove geni per prevedere la risposta al blocco dei checkpoint immunitari. In tre coorti indipendenti di pazienti trattati con questi farmaci (provenienti da altri tipi di cancro con dati disponibili), punteggi PCD più alti sono stati costantemente associati a risposte migliori, implicando che il punteggio cattura caratteristiche dell'ambiente tumorale che rendono l'immunoterapia più efficace. Il gruppo ha inoltre utilizzato database di sensibilità farmacologica e simulazioni di docking computazionale per prevedere quali farmaci potrebbero essere più efficaci nei diversi gruppi di rischio. I pazienti ad alto rischio sembravano più sensibili a certi agenti mirati, inclusi quelli che interferiscono con le vie TGF-beta e mTOR, offrendo possibili strategie di combinazione per superare l'immunosoppressione.
Dalla biologia complessa a strumenti pratici
Per facilitare la traduzione clinica di questi risultati, gli autori hanno costruito un nomogramma — un calcolatore visivo del rischio — che combina il punteggio di rischio basato sui geni con informazioni cliniche di routine come lo stadio e l'invasione vascolare. Questo strumento ha predetto con precisione la sopravvivenza a uno, tre e quattro anni nella loro coorte principale di pazienti. Sebbene il lavoro richieda ancora test prospettici in gruppi più ampi e definiti per trattamento di pazienti con colangiocarcinoma intraepatico, fornisce una roadmap su come i pattern di geni legati alla morte cellulare possano essere usati per classificare i tumori, comprendere i loro ecosistemi immunitari e orientare la terapia. Per i pazienti, la promessa a lungo termine è una prognosi più precisa e trattamenti meglio calibrati sulla base dell'impronta genetica e immunitaria unica del loro tumore.
Citazione: Zhang, T., Dou, D., Liu, Q. et al. Single-cell and bulk transcriptomic analyses uncover immune subtypes associated with programmed cell death features in intrahepatic cholangiocarcinoma. Sci Rep 16, 13678 (2026). https://doi.org/10.1038/s41598-026-44332-8
Parole chiave: colangiocarcinoma intraepatico, morte cellulare programmata, microambiente immunitario tumorale, sequenziamento RNA a singola cellula, risposta all'immunoterapia